+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Mycobacterium smegmatis inosine monophosphate dehydrogenase (IMPDH) ATP+GTP-bound form, compressed | |||||||||
 マップデータ マップデータ | RELION post-processed map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Octamer / ATP+GTP complex / Purine metabolism / IMPDH / OXIDOREDUCTASE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報IMP dehydrogenase activity / IMP dehydrogenase / GMP biosynthetic process / GTP biosynthetic process / nucleotide binding / metal ion binding / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) | |||||||||
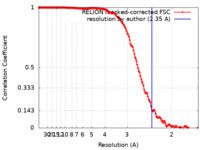
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.35 Å | |||||||||
 データ登録者 データ登録者 | Bulvas O / Kouba T / Pichova I | |||||||||
| 資金援助 | European Union, 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Mycobacterium smegmatis inosine monophosphate dehydrogenase (IMPDH) apo form 著者: Bulvas O / Kouba T / Pichova I | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_18600.map.gz emd_18600.map.gz | 262.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-18600-v30.xml emd-18600-v30.xml emd-18600.xml emd-18600.xml | 20.7 KB 20.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_18600_fsc.xml emd_18600_fsc.xml | 14.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_18600.png emd_18600.png | 94 KB | ||
| マスクデータ |  emd_18600_msk_1.map emd_18600_msk_1.map | 282.6 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-18600.cif.gz emd-18600.cif.gz | 6.8 KB | ||
| その他 |  emd_18600_additional_1.map.gz emd_18600_additional_1.map.gz emd_18600_half_map_1.map.gz emd_18600_half_map_1.map.gz emd_18600_half_map_2.map.gz emd_18600_half_map_2.map.gz | 139.1 MB 225.3 MB 225.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-18600 http://ftp.pdbj.org/pub/emdb/structures/EMD-18600 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18600 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18600 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8qqpMC  17988  18184  18601  18602  18604  18606  18607  18608  8pw3C  8q65C  8qqqC  8qqrC  8qqtC  8qqvC  8qqwC  8qqxC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_18600.map.gz / 形式: CCP4 / 大きさ: 282.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_18600.map.gz / 形式: CCP4 / 大きさ: 282.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION post-processed map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8336 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_18600_msk_1.map emd_18600_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Octameric assembly of inosine monophosphate dehydrogenase in comp...
| 全体 | 名称: Octameric assembly of inosine monophosphate dehydrogenase in complex with ATP+GTP |
|---|---|
| 要素 |
|
-超分子 #1: Octameric assembly of inosine monophosphate dehydrogenase in comp...
| 超分子 | 名称: Octameric assembly of inosine monophosphate dehydrogenase in complex with ATP+GTP タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) |
| 分子量 | 理論値: 426.658 KDa |
-分子 #1: Inosine-5'-monophosphate dehydrogenase
| 分子 | 名称: Inosine-5'-monophosphate dehydrogenase / タイプ: protein_or_peptide / ID: 1 / コピー数: 8 / 光学異性体: LEVO / EC番号: IMP dehydrogenase |
|---|---|
| 由来(天然) | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア)株: MC2 155 |
| 分子量 | 理論値: 53.388988 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSIAESSVPI AVPVPTGGDD PTKVAMLGLT FDDVLLLPAA SDVVPATADT SSQLTKRIRL RVPLVSSAMD TVTESRMAIA MARAGGMGV LHRNLPVAEQ AGQVETVKRS EAGMVTDPVT CSPDNTLAEV DAMCARFRIS GLPVVDDTGE LVGIITNRDM R FEVDQSKP ...文字列: MSIAESSVPI AVPVPTGGDD PTKVAMLGLT FDDVLLLPAA SDVVPATADT SSQLTKRIRL RVPLVSSAMD TVTESRMAIA MARAGGMGV LHRNLPVAEQ AGQVETVKRS EAGMVTDPVT CSPDNTLAEV DAMCARFRIS GLPVVDDTGE LVGIITNRDM R FEVDQSKP VSEVMTKAPL ITAKEGVSAE AALGLLRRHK IEKLPIVDGH GKLTGLITVK DFVKTEQFPL STKDSDGRLL VG AAVGVGD DAWTRAMTLV DAGVDVLIVD TAHAHNRGVL DMVSRLKQAV GERVDVVGGN VATRAAAAAL VEAGADAVKV GVG PGSICT TRVVAGVGAP QITAILEAVA ACKPYGVPVI ADGGLQYSGD IAKALAAGAS TAMLGSLLAG TAESPGELIF VNGK QFKSY RGMGSLGAMQ GRGAAKSYSK DRYFQDDVLS EDKLVPEGIE GRVPFRGPLG TVIHQLTGGL RAAMGYTGSA TIEQL QQAQ FVQITAAGLK ESHPHDITMT VEAPNYYTR UniProtKB: Inosine-5'-monophosphate dehydrogenase |
-分子 #2: ADENOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 2 / コピー数: 8 / 式: ATP |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information |  ChemComp-ATP: |
-分子 #3: GUANOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: GUANOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 3 / コピー数: 8 / 式: GTP |
|---|---|
| 分子量 | 理論値: 523.18 Da |
| Chemical component information |  ChemComp-GTP: |
-分子 #4: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 4 / コピー数: 16 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #5: water
| 分子 | 名称: water / タイプ: ligand / ID: 5 / コピー数: 110 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
詳細: 50 mM HEPES (pH 7.5), 200 mM KCl, 5 mM DTT,4 mM MgCl2 Ligand: 0.5 mM ATP + 2 mM GTP + 1 mM IMP | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 実像数: 40440 / 平均露光時間: 2.0 sec. / 平均電子線量: 44.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 0.4 µm / 倍率(公称値): 165000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: AlphaFold / Chain - Initial model type: in silico model |
|---|---|
| 詳細 | Initial fitting was done in UCSF ChimeraX. Model refinement was done by iterative cycles of manual fitting with Coot and ISOLDE and automated fitting with phenix.real_space_refine. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 温度因子: 47.35 / 当てはまり具合の基準: CC coefficient |
| 得られたモデル |  PDB-8qqp: |
 ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X