+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Engineered glycolyl-CoA carboxylase (G20R variant) with bound CoA | ||||||||||||
 マップデータ マップデータ | main map | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | glycolyl-CoA carboxylase / LIGASE | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報propionyl-CoA carboxylase / urea carboxylase activity / propionyl-CoA carboxylase activity / methylcrotonoyl-CoA carboxylase activity / lipid catabolic process / ATP binding / metal ion binding 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Methylorubrum extorquens AM1 (バクテリア) Methylorubrum extorquens AM1 (バクテリア) | ||||||||||||
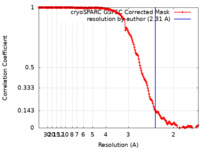
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.31 Å | ||||||||||||
 データ登録者 データ登録者 | Zarzycki J / Marchal DG / Schulz L / Prinz S / Erb TJ | ||||||||||||
| 資金援助 | European Union,  ドイツ, 3件 ドイツ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: ACS Synth Biol / 年: 2023 ジャーナル: ACS Synth Biol / 年: 2023タイトル: Machine Learning-Supported Enzyme Engineering toward Improved CO-Fixation of Glycolyl-CoA Carboxylase. 著者: Daniel G Marchal / Luca Schulz / Ingmar Schuster / Jelena Ivanovska / Nicole Paczia / Simone Prinz / Jan Zarzycki / Tobias J Erb /  要旨: Glycolyl-CoA carboxylase (GCC) is a new-to-nature enzyme that catalyzes the key reaction in the tartronyl-CoA (TaCo) pathway, a synthetic photorespiration bypass that was recently designed to improve ...Glycolyl-CoA carboxylase (GCC) is a new-to-nature enzyme that catalyzes the key reaction in the tartronyl-CoA (TaCo) pathway, a synthetic photorespiration bypass that was recently designed to improve photosynthetic CO fixation. GCC was created from propionyl-CoA carboxylase (PCC) through five mutations. However, despite reaching activities of naturally evolved biotin-dependent carboxylases, the quintuple substitution variant GCC M5 still lags behind 4-fold in catalytic efficiency compared to its template PCC and suffers from futile ATP hydrolysis during CO fixation. To further improve upon GCC M5, we developed a machine learning-supported workflow that reduces screening efforts for identifying improved enzymes. Using this workflow, we present two novel GCC variants with 2-fold increased carboxylation rate and 60% reduced energy demand, respectively, which are able to address kinetic and thermodynamic limitations of the TaCo pathway. Our work highlights the potential of combining machine learning and directed evolution strategies to reduce screening efforts in enzyme engineering. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_17778.map.gz emd_17778.map.gz | 246.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-17778-v30.xml emd-17778-v30.xml emd-17778.xml emd-17778.xml | 17.4 KB 17.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_17778_fsc.xml emd_17778_fsc.xml | 16.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_17778.png emd_17778.png | 178.5 KB | ||
| Filedesc metadata |  emd-17778.cif.gz emd-17778.cif.gz | 6.4 KB | ||
| その他 |  emd_17778_half_map_1.map.gz emd_17778_half_map_1.map.gz emd_17778_half_map_2.map.gz emd_17778_half_map_2.map.gz | 441.8 MB 441.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-17778 http://ftp.pdbj.org/pub/emdb/structures/EMD-17778 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17778 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17778 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_17778_validation.pdf.gz emd_17778_validation.pdf.gz | 1.1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_17778_full_validation.pdf.gz emd_17778_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  emd_17778_validation.xml.gz emd_17778_validation.xml.gz | 26.2 KB | 表示 | |
| CIF形式データ |  emd_17778_validation.cif.gz emd_17778_validation.cif.gz | 34.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-17778 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-17778 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-17778 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-17778 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8pn8MC  8pn7C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_17778.map.gz / 形式: CCP4 / 大きさ: 476.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_17778.map.gz / 形式: CCP4 / 大きさ: 476.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | main map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.837 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: half map A
| ファイル | emd_17778_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
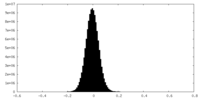
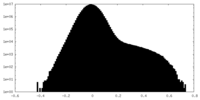
| 注釈 | half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map B
| ファイル | emd_17778_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
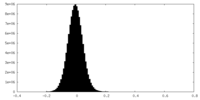
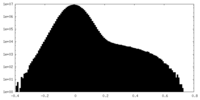
| 注釈 | half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : glycolyl-CoA carboxylase with bound CoA
| 全体 | 名称: glycolyl-CoA carboxylase with bound CoA |
|---|---|
| 要素 |
|
-超分子 #1: glycolyl-CoA carboxylase with bound CoA
| 超分子 | 名称: glycolyl-CoA carboxylase with bound CoA / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Methylorubrum extorquens AM1 (バクテリア) Methylorubrum extorquens AM1 (バクテリア) |
-分子 #1: Propionyl-CoA carboxylase beta chain
| 分子 | 名称: Propionyl-CoA carboxylase beta chain / タイプ: protein_or_peptide / ID: 1 / コピー数: 6 / 光学異性体: LEVO / EC番号: propionyl-CoA carboxylase |
|---|---|
| 由来(天然) | 生物種:  Methylorubrum extorquens AM1 (バクテリア) Methylorubrum extorquens AM1 (バクテリア) |
| 分子量 | 理論値: 55.990953 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MKDILEKLEE RRAQARLGGG EKRLEAQHKR GKLTARERIE LLLDHGSFEE FDMFVQHRST DFGMEKQKIP GDGVVTGWGT VNGRTVFLF SKDFTVFGGS NSEAHAAKIV KVQDMALKMR APIIGIFDAG GARIQEGVAA LGGHGEVFRR NVAASGVIPQ I SVIMGPCA ...文字列: MKDILEKLEE RRAQARLGGG EKRLEAQHKR GKLTARERIE LLLDHGSFEE FDMFVQHRST DFGMEKQKIP GDGVVTGWGT VNGRTVFLF SKDFTVFGGS NSEAHAAKIV KVQDMALKMR APIIGIFDAG GARIQEGVAA LGGHGEVFRR NVAASGVIPQ I SVIMGPCA GGDVYSPAMT DFIFMVRDTS YMFVTGPDVV KTVTNEVVTA EELGGAKVHT SKSSIADGSF ENDVEAILQI RR LLDFLPA NNIEGVPEIE SFDDVNRLDK SLDTLIPDNP NKPYDMGELI RRVVDEGDFF EIQAAYARNI ITGFGRVEGR TVG FVANQP LVLAGVLDSD ASRKAARFVR FCNAFSIPIV TFVDVPGFLP GTAQEYGGLI KHGAKLLFAY SQATVPLVTI ITRK AFGGA YIVMASKHVG ADLNYAWPTA QIAVMGAKGA VEIIFRAEIG DADKVAERTK EYEDRFLSPF VAAERGYIDE VIMPH STRK RIARALGMLR TKEMEQPRKK HDNIPL UniProtKB: Propionyl-CoA carboxylase beta chain |
-分子 #2: Propionyl-CoA carboxylase alpha subunit
| 分子 | 名称: Propionyl-CoA carboxylase alpha subunit / タイプ: protein_or_peptide / ID: 2 / コピー数: 6 / 光学異性体: LEVO / EC番号: propionyl-CoA carboxylase |
|---|---|
| 由来(天然) | 生物種:  Methylorubrum extorquens AM1 (バクテリア) Methylorubrum extorquens AM1 (バクテリア) |
| 分子量 | 理論値: 71.986961 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MFDKILIANR GEIACRIIKT AQKMGIKTVA VYSDADRDAV HVAMADEAVH IGPAPAAQSY LLIEKIIDAC KQTGAQAVHP GYGFLSERE SFPKALAEAG IVFIGPNPGA IAAMGDKIES KKAAAAAEVS TVPGFLGVIE SPEHAVTIAD EIGYPVMIKA S AGGGGKGM ...文字列: MFDKILIANR GEIACRIIKT AQKMGIKTVA VYSDADRDAV HVAMADEAVH IGPAPAAQSY LLIEKIIDAC KQTGAQAVHP GYGFLSERE SFPKALAEAG IVFIGPNPGA IAAMGDKIES KKAAAAAEVS TVPGFLGVIE SPEHAVTIAD EIGYPVMIKA S AGGGGKGM RIAESADEVA EGFARAKSEA SSSFGDDRVF VEKFITDPRH IEIQVIGDKH GNVIYLGERE CSIQRRNQKV IE EAPSPLL DEETRRKMGE QAVALAKAVN YDSAGTVEFV AGQDKSFYFL EMNTRLQVEH PVTEMITGLD LVELMIRVAA GEK LPLSQD QVKLDGWAVE SRVYAEDPTR NFLPSIGRLT TYQPPEEGPL GGAIVRNDTG VEEGGEIAIH YDPMIAKLVT WAPT RLEAI EAQATALDAF AIEGIRHNIP FLATLMAHPR WRDGRLSTGF IKEEFPEGFI APEPEGPVAH RLAAVAAAID HKLNI RKRG ISGQMRDPSL LTFQRERVVV LSGQRFNVTV DPDGDDLLVT FDDGTTAPVR SAWRPGAPVW SGTVGDQSVA IQVRPL LNG VFLQHAGAAA EARVFTRREA ELADLMPVKE NAGSGKQLLC PMPGLVKQIM VSEGQEVKNG EPLAIVEAMK MENVLRA ER DGTISKIAAK EGDSLAVDAV ILEFA UniProtKB: propionyl-CoA carboxylase |
-分子 #3: COENZYME A
| 分子 | 名称: COENZYME A / タイプ: ligand / ID: 3 / コピー数: 6 / 式: COA |
|---|---|
| 分子量 | 理論値: 767.534 Da |
| Chemical component information | 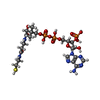 ChemComp-COA: |
-分子 #4: 5-(HEXAHYDRO-2-OXO-1H-THIENO[3,4-D]IMIDAZOL-6-YL)PENTANAL
| 分子 | 名称: 5-(HEXAHYDRO-2-OXO-1H-THIENO[3,4-D]IMIDAZOL-6-YL)PENTANAL タイプ: ligand / ID: 4 / コピー数: 6 / 式: BTI |
|---|---|
| 分子量 | 理論値: 228.311 Da |
| Chemical component information |  ChemComp-BTI: |
-分子 #5: water
| 分子 | 名称: water / タイプ: ligand / ID: 5 / コピー数: 866 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | 2D array |
- 試料調製
試料調製
| 緩衝液 | pH: 7.8 |
|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 55.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー










 Z
Z Y
Y X
X