+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of IgE bound to the ectodomain of FceRIa | ||||||||||||
 マップデータ マップデータ | consensus map | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | adaptive immune system / IgE / Fc receptor / allergy / IMMUNE SYSTEM | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報high-affinity IgE receptor activity / adaptive immune memory response / primary adaptive immune response / IgE B cell receptor complex / B cell antigen processing and presentation / type I hypersensitivity / Fc receptor-mediated immune complex endocytosis / IgD immunoglobulin complex / eosinophil degranulation / IgA immunoglobulin complex ...high-affinity IgE receptor activity / adaptive immune memory response / primary adaptive immune response / IgE B cell receptor complex / B cell antigen processing and presentation / type I hypersensitivity / Fc receptor-mediated immune complex endocytosis / IgD immunoglobulin complex / eosinophil degranulation / IgA immunoglobulin complex / IgM immunoglobulin complex / IgE immunoglobulin complex / macrophage activation / IgE binding / type 2 immune response / CD22 mediated BCR regulation / IgG immunoglobulin complex / Fc epsilon receptor (FCERI) signaling / antibody-dependent cellular cytotoxicity / Classical antibody-mediated complement activation / Initial triggering of complement / mast cell degranulation / immunoglobulin complex, circulating / immunoglobulin receptor binding / B cell proliferation / macrophage differentiation / FCGR activation / Role of phospholipids in phagocytosis / Role of LAT2/NTAL/LAB on calcium mobilization / immunoglobulin mediated immune response / Scavenging of heme from plasma / complement activation, classical pathway / antigen binding / FCERI mediated Ca+2 mobilization / FCGR3A-mediated IL10 synthesis / Antigen activates B Cell Receptor (BCR) leading to generation of second messengers / Regulation of Complement cascade / Cell surface interactions at the vascular wall / FCERI mediated MAPK activation / FCGR3A-mediated phagocytosis / B cell receptor signaling pathway / Regulation of actin dynamics for phagocytic cup formation / FCERI mediated NF-kB activation / Immunoregulatory interactions between a Lymphoid and a non-Lymphoid cell / antibacterial humoral response / Interleukin-4 and Interleukin-13 signaling / blood microparticle / adaptive immune response / Potential therapeutics for SARS / cell surface receptor signaling pathway / inflammatory response / immune response / external side of plasma membrane / cell surface / extracellular space / extracellular exosome / extracellular region / plasma membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.1 Å | ||||||||||||
 データ登録者 データ登録者 | Andersen GR / Jensen RK | ||||||||||||
| 資金援助 |  デンマーク, 3件 デンマーク, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Structure of IgE bound to the ectodomain of FceRIa 著者: Andersen GR / Jensen RK | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_16378.map.gz emd_16378.map.gz | 120.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-16378-v30.xml emd-16378-v30.xml emd-16378.xml emd-16378.xml | 17.2 KB 17.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_16378.png emd_16378.png | 84.2 KB | ||
| Filedesc metadata |  emd-16378.cif.gz emd-16378.cif.gz | 6 KB | ||
| その他 |  emd_16378_half_map_1.map.gz emd_16378_half_map_1.map.gz emd_16378_half_map_2.map.gz emd_16378_half_map_2.map.gz | 222.6 MB 226.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-16378 http://ftp.pdbj.org/pub/emdb/structures/EMD-16378 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16378 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16378 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_16378_validation.pdf.gz emd_16378_validation.pdf.gz | 668.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_16378_full_validation.pdf.gz emd_16378_full_validation.pdf.gz | 668 KB | 表示 | |
| XML形式データ |  emd_16378_validation.xml.gz emd_16378_validation.xml.gz | 16 KB | 表示 | |
| CIF形式データ |  emd_16378_validation.cif.gz emd_16378_validation.cif.gz | 19 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16378 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16378 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16378 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16378 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8c1cMC  8c1bC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_16378.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_16378.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | consensus map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.03625 Å | ||||||||||||||||||||||||||||||||||||
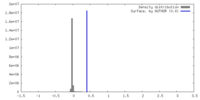
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: half map B for consensus map
| ファイル | emd_16378_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map B for consensus map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map A for consensus map
| ファイル | emd_16378_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map A for consensus map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : IgE-FceRIa complex
| 全体 | 名称: IgE-FceRIa complex |
|---|---|
| 要素 |
|
-超分子 #1: IgE-FceRIa complex
| 超分子 | 名称: IgE-FceRIa complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 詳細: complex of IgE bound to the ectodomain of the FceRIa subunit |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 220 KDa |
-分子 #1: Immunoglobulin heavy constant epsilon
| 分子 | 名称: Immunoglobulin heavy constant epsilon / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 46.831613 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ASTQSPSVFP LTRCCKNIPS NATSVTLGCL ATGYFPEPVM VTWDTGSLNG TTMTLPATTL TLSGHYATIS LLTVSGAWAK QMFTCRVAH TPSSTDWVDN KTFSVCSRDF TPPTVKILQS SCDGGGHFPP TIQLLCLVSG YTPGTINITW LEDGQVMDVD L STASTTQE ...文字列: ASTQSPSVFP LTRCCKNIPS NATSVTLGCL ATGYFPEPVM VTWDTGSLNG TTMTLPATTL TLSGHYATIS LLTVSGAWAK QMFTCRVAH TPSSTDWVDN KTFSVCSRDF TPPTVKILQS SCDGGGHFPP TIQLLCLVSG YTPGTINITW LEDGQVMDVD L STASTTQE GELASTQSEL TLSQKHWLSD RTYTCQVTYQ GHTFEDSTKK CADSNPRGVS AYLSRPSPFD LFIRKSPTIT CL VVDLAPS KGTVNLTWSR ASGKPVNHST RKEEKQRNGT LTVTSTLPVG TRDWIEGETY QCRVTHPHLP RALMRSTTKT SGP RAAPEV YAFATPEWPG SRDKRTLACL IQNFMPEDIS VQWLHNEVQL PDARHSTTQP RKTKGSGFFV FSRLEVTRAE WEQK DEFIC RAVHEAASPS QTVQRAVSSV A UniProtKB: Immunoglobulin heavy constant epsilon |
-分子 #2: Immunoglobulin kappa constant
| 分子 | 名称: Immunoglobulin kappa constant / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 11.763983 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: RTVGAPSVFI FPPSDEQLKS GTASVVCLLN NFYPREAKVQ WKVDNALQSG NSQESVTEQD SKDSTYSLSS TLTLSKADYE KHKVYACEV THQGLSSPVT KSFNRGEC UniProtKB: Immunoglobulin kappa constant |
-分子 #3: High affinity immunoglobulin epsilon receptor subunit alpha
| 分子 | 名称: High affinity immunoglobulin epsilon receptor subunit alpha タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 19.88007 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: KPKVSLNPPW NRIFKGENVT LTCNGNNFFE VSSTKWFHNG SLSEETNSSL NIVNAKFEDS GEYKCQHQQV NESEPVYLEV FSDWLLLQA SAEVVMEGQP LFLRCHGWRN WDVYKVIYYK DGEALKYWYE NHNISITNAT VEDSGTYYCT GKVWQLDYES E PLNITVIK APR UniProtKB: High affinity immunoglobulin epsilon receptor subunit alpha |
-分子 #7: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 7 / コピー数: 2 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.1 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 59.16 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL In silico モデル: Stochastic gradient descent based model |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 4.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC / 使用した粒子像数: 573328 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー


























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)