+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-11563 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Mouse Hoxa9 IRES-like element bound to the human 40S ribosomal subunit head - IRES binding site | ||||||||||||
 マップデータ マップデータ | mouse Hoxa9 IRES-like element bound to the human 40S ribosomal subunit | ||||||||||||
 試料 試料 |
| ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
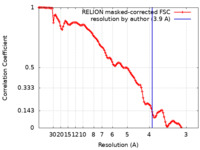
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | ||||||||||||
 データ登録者 データ登録者 | Boehringer D / Lenarcic T / Quade N / Leppek K / Fujii K / Susanto TT / Xue S / Genuth NR / Barna M / Ban N | ||||||||||||
| 資金援助 |  米国, 米国,  スイス, 3件 スイス, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2020 ジャーナル: Mol Cell / 年: 2020タイトル: Gene- and Species-Specific Hox mRNA Translation by Ribosome Expansion Segments. 著者: Kathrin Leppek / Kotaro Fujii / Nick Quade / Teodorus Theo Susanto / Daniel Boehringer / Tea Lenarčič / Shifeng Xue / Naomi R Genuth / Nenad Ban / Maria Barna /   要旨: Ribosomes have been suggested to directly control gene regulation, but regulatory roles for ribosomal RNA (rRNA) remain largely unexplored. Expansion segments (ESs) consist of multitudes of tentacle- ...Ribosomes have been suggested to directly control gene regulation, but regulatory roles for ribosomal RNA (rRNA) remain largely unexplored. Expansion segments (ESs) consist of multitudes of tentacle-like rRNA structures extending from the core ribosome in eukaryotes. ESs are remarkably variable in sequence and size across eukaryotic evolution with largely unknown functions. In characterizing ribosome binding to a regulatory element within a Homeobox (Hox) 5' UTR, we identify a modular stem-loop within this element that binds to a single ES, ES9S. Engineering chimeric, "humanized" yeast ribosomes for ES9S reveals that an evolutionary change in the sequence of ES9S endows species-specific binding of Hoxa9 mRNA to the ribosome. Genome editing to site-specifically disrupt the Hoxa9-ES9S interaction demonstrates the functional importance for such selective mRNA-rRNA binding in translation control. Together, these studies unravel unexpected gene regulation directly mediated by rRNA and how ribosome evolution drives translation of critical developmental regulators. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_11563.map.gz emd_11563.map.gz | 6.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-11563-v30.xml emd-11563-v30.xml emd-11563.xml emd-11563.xml | 15.6 KB 15.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_11563_fsc.xml emd_11563_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_11563.png emd_11563.png | 129.9 KB | ||
| マスクデータ |  emd_11563_msk_1.map emd_11563_msk_1.map | 125 MB |  マスクマップ マスクマップ | |
| その他 |  emd_11563_half_map_1.map.gz emd_11563_half_map_1.map.gz emd_11563_half_map_2.map.gz emd_11563_half_map_2.map.gz | 98.3 MB 98.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-11563 http://ftp.pdbj.org/pub/emdb/structures/EMD-11563 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11563 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11563 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_11563_validation.pdf.gz emd_11563_validation.pdf.gz | 433.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_11563_full_validation.pdf.gz emd_11563_full_validation.pdf.gz | 432.7 KB | 表示 | |
| XML形式データ |  emd_11563_validation.xml.gz emd_11563_validation.xml.gz | 17.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-11563 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-11563 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-11563 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-11563 | HTTPS FTP |
-関連構造データ
| 関連構造データ | C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_11563.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_11563.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | mouse Hoxa9 IRES-like element bound to the human 40S ribosomal subunit | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.39 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
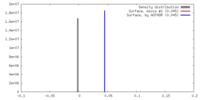
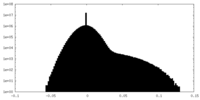
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_11563_msk_1.map emd_11563_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
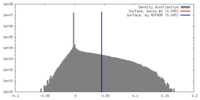
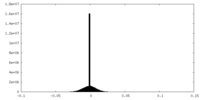
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_11563_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
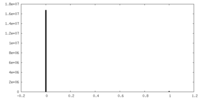
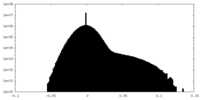
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_11563_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
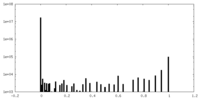
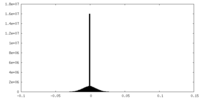
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : human 40S ribosomal subunit - mouse Hoxa9 IRES like element complex
| 全体 | 名称: human 40S ribosomal subunit - mouse Hoxa9 IRES like element complex |
|---|---|
| 要素 |
|
-超分子 #1: human 40S ribosomal subunit - mouse Hoxa9 IRES like element complex
| 超分子 | 名称: human 40S ribosomal subunit - mouse Hoxa9 IRES like element complex タイプ: complex / ID: 1 / 親要素: 0 詳細: The map includes the binding site of the mouse Hoxa9 IRES-like element bound to the human 40S ribosomal subunit head. (Mouse Hoxa9 IRES was produced by in vitro transcription) |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 株: HEK293-6E cells Homo sapiens (ヒト) / 株: HEK293-6E cells |
-超分子 #2: 40S ribosomal subunit
| 超分子 | 名称: 40S ribosomal subunit / タイプ: organelle_or_cellular_component / ID: 2 / 親要素: 1 |
|---|
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 |
|---|---|
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS |
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 検出モード: INTEGRATING / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)