+Search query
-Structure paper
| Title | An SI3-σ arch stabilizes cyanobacteria transcription initiation complex. |
|---|---|
| Journal, issue, pages | Proc Natl Acad Sci U S A, Vol. 120, Issue 16, Page e2219290120, Year 2023 |
| Publish date | Apr 18, 2023 |
 Authors Authors | Liqiang Shen / Giorgio Lai / Linlin You / Jing Shi / Xiaoxian Wu / Maria Puiu / Zhanxi Gu / Yu Feng / Yulia Yuzenkova / Yu Zhang /   |
| PubMed Abstract | Multisubunit RNA polymerases (RNAPs) associate with initiation factors (σ in bacteria) to start transcription. The σ factors are responsible for recognizing and unwinding promoter DNA in all ...Multisubunit RNA polymerases (RNAPs) associate with initiation factors (σ in bacteria) to start transcription. The σ factors are responsible for recognizing and unwinding promoter DNA in all bacterial RNAPs. Here, we report two cryo-EM structures of cyanobacterial transcription initiation complexes at near-atomic resolutions. The structures show that cyanobacterial RNAP forms an "SI3-σ" arch interaction between domain 2 of σ (σ) and sequence insertion 3 (SI3) in the mobile catalytic domain Trigger Loop (TL). The "SI3-σ" arch facilitates transcription initiation from promoters of different classes through sealing the main cleft and thereby stabilizing the RNAP-promoter DNA open complex. Disruption of the "SI3-σ" arch disturbs cyanobacteria growth and stress response. Our study reports the structure of cyanobacterial RNAP and a unique mechanism for its transcription initiation. Our data suggest functional plasticity of SI3 and provide the foundation for further research into cyanobacterial and chloroplast transcription. |
 External links External links |  Proc Natl Acad Sci U S A / Proc Natl Acad Sci U S A /  PubMed:37036976 / PubMed:37036976 /  PubMed Central PubMed Central |
| Methods | EM (single particle) / X-ray diffraction |
| Resolution | 1.552 - 3.13 Å |
| Structure data | EMDB-34397, PDB-8gzg: EMDB-34398, PDB-8gzh:  PDB-8h02: |
| Chemicals |  ChemComp-MG:  ChemComp-ZN: 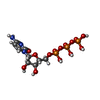 ChemComp-CTP:  ChemComp-HOH: |
| Source |
|
 Keywords Keywords | TRANSCRIPTION/DNA/RNA / Cryo-EM / Synechocystis sp. PCC 6803 / Syn6803 / Transcription initiation / RPitc / Transcription / Cyanobacteria / TRANSCRIPTION-DNA-RNA complex / CTP-bound RPitc / RNA polymerase / SI3 |
 Movie
Movie Controller
Controller Structure viewers
Structure viewers About Yorodumi Papers
About Yorodumi Papers








