+検索条件
-Structure paper
| タイトル | Structural basis for inhibition and regulation of a chitin synthase from Candida albicans. |
|---|---|
| ジャーナル・号・ページ | Nat Struct Mol Biol, Vol. 29, Issue 7, Page 653-664, Year 2022 |
| 掲載日 | 2022年7月4日 |
 著者 著者 | Zhenning Ren / Abhishek Chhetri / Ziqiang Guan / Yang Suo / Kenichi Yokoyama / Seok-Yong Lee /  |
| PubMed 要旨 | Chitin is an essential component of the fungal cell wall. Chitin synthases (Chss) catalyze chitin formation and translocation across the membrane and are targets of antifungal agents, including ...Chitin is an essential component of the fungal cell wall. Chitin synthases (Chss) catalyze chitin formation and translocation across the membrane and are targets of antifungal agents, including nikkomycin Z and polyoxin D. Lack of structural insights into the action of these inhibitors on Chs has hampered their further development to the clinic. We present the cryo-EM structures of Chs2 from Candida albicans (CaChs2) in the apo, substrate-bound, nikkomycin Z-bound, and polyoxin D-bound states. CaChs2 adopts a unique domain-swapped dimer configuration where a conserved motif in the domain-swapped region controls enzyme activity. CaChs2 has a dual regulation mechanism where the chitin translocation tunnel is closed by the extracellular gate and plugged by a lipid molecule in the apo state to prevent non-specific leak. Analyses of substrate and inhibitor binding provide insights into the chemical logic of Chs inhibition, which can guide Chs-targeted antifungal development. |
 リンク リンク |  Nat Struct Mol Biol / Nat Struct Mol Biol /  PubMed:35788183 / PubMed:35788183 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) |
| 解像度 | 2.95 - 3.19 Å |
| 構造データ | EMDB-25432, PDB-7stl: EMDB-25433, PDB-7stm: EMDB-25434, PDB-7stn: EMDB-25435, PDB-7sto: |
| 化合物 |  ChemComp-3PE:  ChemComp-MG:  ChemComp-UD1: 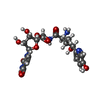 ChemComp-BGI:  ChemComp-BJ9: |
| 由来 |
|
 キーワード キーワード | MEMBRANE PROTEIN / chitin synthesis / glycosyltransferase / TRANSFERASE / Nikkomycin Z / polyoxin D |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について









 candida albicans (酵母)
candida albicans (酵母)