+検索条件
-Structure paper
| タイトル | TMPRSS2 and glycan receptors synergistically facilitate coronavirus entry. |
|---|---|
| ジャーナル・号・ページ | Cell, Year 2024 |
| 掲載日 | 2024年6月21日 |
 著者 著者 | Haofeng Wang / Xiaoce Liu / Xiang Zhang / Zhuoqian Zhao / Yuchi Lu / Dingzhe Pu / Zeyang Zhang / Jie Chen / Yajie Wang / Mengfei Li / Xuxue Dong / Yinkai Duan / Yujia He / Qiyu Mao / Hangtian Guo / Haoran Sun / Yihan Zhou / Qi Yang / Yan Gao / Xiuna Yang / Hongzhi Cao / Luke Guddat / Lei Sun / Zihe Rao / Haitao Yang /   |
| PubMed 要旨 | The entry of coronaviruses is initiated by spike recognition of host cellular receptors, involving proteinaceous and/or glycan receptors. Recently, TMPRSS2 was identified as the proteinaceous ...The entry of coronaviruses is initiated by spike recognition of host cellular receptors, involving proteinaceous and/or glycan receptors. Recently, TMPRSS2 was identified as the proteinaceous receptor for HCoV-HKU1 alongside sialoglycan as a glycan receptor. However, the underlying mechanisms for viral entry remain unknown. Here, we investigated the HCoV-HKU1C spike in the inactive, glycan-activated, and functionally anchored states, revealing that sialoglycan binding induces a conformational change of the NTD and promotes the neighboring RBD of the spike to open for TMPRSS2 recognition, exhibiting a synergistic mechanism for the entry of HCoV-HKU1. The RBD of HCoV-HKU1 features an insertion subdomain that recognizes TMPRSS2 through three previously undiscovered interfaces. Furthermore, structural investigation of HCoV-HKU1A in combination with mutagenesis and binding assays confirms a conserved receptor recognition pattern adopted by HCoV-HKU1. These studies advance our understanding of the complex viral-host interactions during entry, laying the groundwork for developing new therapeutics against coronavirus-associated diseases. |
 リンク リンク |  Cell / Cell /  PubMed:38964329 PubMed:38964329 |
| 手法 | EM (単粒子) |
| 解像度 | 2.95 - 3.65 Å |
| 構造データ | EMDB-39025, PDB-8y7x: EMDB-39026, PDB-8y7y: EMDB-39036, PDB-8y87: EMDB-39037, PDB-8y88: EMDB-39038, PDB-8y89: EMDB-39039, PDB-8y8a: EMDB-39040, PDB-8y8b: EMDB-39041, PDB-8y8c: EMDB-39042, PDB-8y8d: EMDB-39043, PDB-8y8e: EMDB-39044, PDB-8y8f: EMDB-39045, PDB-8y8g: EMDB-39046, PDB-8y8h: EMDB-39047, PDB-8y8i: EMDB-39048, PDB-8y8j: |
| 化合物 |  ChemComp-NAG: 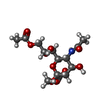 ChemComp-MJJ: |
| 由来 |
|
 キーワード キーワード | VIRAL PROTEIN / HKU1A / spike / TMPRSS2 / HKU1C |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について

































 human coronavirus hku1 (ウイルス)
human coronavirus hku1 (ウイルス) homo sapiens (ヒト)
homo sapiens (ヒト)