+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1rgr | ||||||
|---|---|---|---|---|---|---|---|
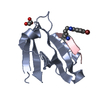
| タイトル | Cyclic Peptides Targeting PDZ Domains of PSD-95: Structural Basis for Enhanced Affinity and Enzymatic Stability | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード |  STRUCTURAL PROTEIN/DE NOVO PROTEIN (構造) / PDZ1 domain / STRUCTURAL PROTEIN/DE NOVO PROTEIN (構造) / PDZ1 domain /  STRUCTURAL PROTEIN-DE NOVO PROTEIN COMPLEX (構造) STRUCTURAL PROTEIN-DE NOVO PROTEIN COMPLEX (構造) | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RHO GTPases activate CIT / positive regulation of AMPA glutamate receptor clustering / neuronal ion channel clustering / P2Y1 nucleotide receptor binding / Neurexins and neuroligins /  beta-1 adrenergic receptor binding / neuroligin family protein binding / structural constituent of postsynaptic density / proximal dendrite / receptor localization to synapse ...RHO GTPases activate CIT / positive regulation of AMPA glutamate receptor clustering / neuronal ion channel clustering / P2Y1 nucleotide receptor binding / Neurexins and neuroligins / beta-1 adrenergic receptor binding / neuroligin family protein binding / structural constituent of postsynaptic density / proximal dendrite / receptor localization to synapse ...RHO GTPases activate CIT / positive regulation of AMPA glutamate receptor clustering / neuronal ion channel clustering / P2Y1 nucleotide receptor binding / Neurexins and neuroligins /  beta-1 adrenergic receptor binding / neuroligin family protein binding / structural constituent of postsynaptic density / proximal dendrite / receptor localization to synapse / positive regulation of neuron projection arborization / regulation of grooming behavior / synaptic vesicle maturation / cerebellar mossy fiber / cellular response to potassium ion / protein localization to synapse / vocalization behavior / LGI-ADAM interactions / Trafficking of AMPA receptors / neuron spine / beta-1 adrenergic receptor binding / neuroligin family protein binding / structural constituent of postsynaptic density / proximal dendrite / receptor localization to synapse / positive regulation of neuron projection arborization / regulation of grooming behavior / synaptic vesicle maturation / cerebellar mossy fiber / cellular response to potassium ion / protein localization to synapse / vocalization behavior / LGI-ADAM interactions / Trafficking of AMPA receptors / neuron spine /  樹状突起 / Activation of Ca-permeable Kainate Receptor / AMPA glutamate receptor clustering / juxtaparanode region of axon / establishment or maintenance of epithelial cell apical/basal polarity / dendritic spine morphogenesis / 樹状突起 / Activation of Ca-permeable Kainate Receptor / AMPA glutamate receptor clustering / juxtaparanode region of axon / establishment or maintenance of epithelial cell apical/basal polarity / dendritic spine morphogenesis /  frizzled binding / negative regulation of receptor internalization / postsynaptic neurotransmitter receptor diffusion trapping / neuron projection terminus / dendritic spine organization / frizzled binding / negative regulation of receptor internalization / postsynaptic neurotransmitter receptor diffusion trapping / neuron projection terminus / dendritic spine organization /  acetylcholine receptor binding / positive regulation of synapse assembly / RAF/MAP kinase cascade / Synaptic adhesion-like molecules / neurotransmitter receptor localization to postsynaptic specialization membrane / positive regulation of dendrite morphogenesis / acetylcholine receptor binding / positive regulation of synapse assembly / RAF/MAP kinase cascade / Synaptic adhesion-like molecules / neurotransmitter receptor localization to postsynaptic specialization membrane / positive regulation of dendrite morphogenesis /  beta-2 adrenergic receptor binding / cortical cytoskeleton / regulation of neuronal synaptic plasticity / locomotory exploration behavior / beta-2 adrenergic receptor binding / cortical cytoskeleton / regulation of neuronal synaptic plasticity / locomotory exploration behavior /  regulation of NMDA receptor activity / regulation of NMDA receptor activity /  social behavior / positive regulation of excitatory postsynaptic potential / social behavior / positive regulation of excitatory postsynaptic potential /  kinesin binding / AMPA glutamate receptor complex / neuromuscular process controlling balance / kinesin binding / AMPA glutamate receptor complex / neuromuscular process controlling balance /  excitatory synapse / excitatory synapse /  D1 dopamine receptor binding / Unblocking of NMDA receptors, glutamate binding and activation / D1 dopamine receptor binding / Unblocking of NMDA receptors, glutamate binding and activation /  glutamate receptor binding / positive regulation of protein tyrosine kinase activity / positive regulation of synaptic transmission / glutamate receptor binding / positive regulation of protein tyrosine kinase activity / positive regulation of synaptic transmission /  ionotropic glutamate receptor binding / ionotropic glutamate receptor binding /  extrinsic component of cytoplasmic side of plasma membrane / dendrite cytoplasm / extrinsic component of cytoplasmic side of plasma membrane / dendrite cytoplasm /  synaptic membrane / synaptic membrane /  PDZ domain binding / cell periphery / postsynaptic density membrane / regulation of long-term neuronal synaptic plasticity / PDZ domain binding / cell periphery / postsynaptic density membrane / regulation of long-term neuronal synaptic plasticity /  neuromuscular junction / establishment of protein localization / neuromuscular junction / establishment of protein localization /  細胞接着 / cerebral cortex development / 細胞接着 / cerebral cortex development /  kinase binding / cell-cell junction / kinase binding / cell-cell junction /  シナプス小胞 / シナプス小胞 /  細胞結合 / positive regulation of cytosolic calcium ion concentration / chemical synaptic transmission / postsynapse / 細胞結合 / positive regulation of cytosolic calcium ion concentration / chemical synaptic transmission / postsynapse /  scaffold protein binding / scaffold protein binding /  postsynaptic membrane / basolateral plasma membrane / postsynaptic membrane / basolateral plasma membrane /  protein phosphatase binding / protein-containing complex assembly / protein phosphatase binding / protein-containing complex assembly /  樹状突起スパイン / 樹状突起スパイン /  postsynaptic density / neuron projection / postsynaptic density / neuron projection /  signaling receptor binding / signaling receptor binding /  樹状突起 / 樹状突起 /  シナプス / glutamatergic synapse / protein-containing complex binding / シナプス / glutamatergic synapse / protein-containing complex binding /  protein kinase binding / protein kinase binding /  小胞体 / 小胞体 /  生体膜 / 生体膜 /  細胞膜 / 細胞膜 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | ||||||
| 生物種 |   Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) | ||||||
| 手法 |  溶液NMR / torsion angle dynamics, cartesian MD in water 溶液NMR / torsion angle dynamics, cartesian MD in water | ||||||
 データ登録者 データ登録者 | Piserchio, A. / Salinas, G.D. / Li, T. / Marshall, J. / Spaller, M.R. / Mierke, D.F. | ||||||
 引用 引用 |  ジャーナル: Chem.Biol. / 年: 2004 ジャーナル: Chem.Biol. / 年: 2004タイトル: Targeting Specific PDZ Domains of PSD-95; Structural Basis for Enhanced Affinity and Enzymatic Stability of a Cyclic Peptide. 著者: Piserchio, A. / Salinas, G.D. / Li, T. / Marshall, J. / Spaller, M.R. / Mierke, D.F. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1rgr.cif.gz 1rgr.cif.gz | 654.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1rgr.ent.gz pdb1rgr.ent.gz | 566.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1rgr.json.gz 1rgr.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rg/1rgr https://data.pdbj.org/pub/pdb/validation_reports/rg/1rgr ftp://data.pdbj.org/pub/pdb/validation_reports/rg/1rgr ftp://data.pdbj.org/pub/pdb/validation_reports/rg/1rgr | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質 | 分子量: 10860.138 Da / 分子数: 1 / 断片: PDZ1 domain of PSD-95 / 由来タイプ: 組換発現 / 由来: (組換発現)   Rattus norvegicus (ドブネズミ) / 遺伝子: DLG4, PSD95 / 発現宿主: Rattus norvegicus (ドブネズミ) / 遺伝子: DLG4, PSD95 / 発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P31016 Escherichia coli (大腸菌) / 参照: UniProt: P31016 |
|---|---|
| #2: タンパク質・ペプチド | 分子量: 768.897 Da / 分子数: 1 / 断片: C-terminus / Mutation: Q98K, S100E / 由来タイプ: 合成 / 詳細: The peptide was chemically synthesized. / 参照: GenBank: 3098551 |
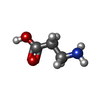
| #3: 化合物 | ChemComp-BAL /  Β-アラニン Β-アラニン |
-実験情報
-実験
| 実験 | 手法:  溶液NMR 溶液NMR |
|---|
- 試料調製
試料調製
| 詳細 | 内容: 1mM PZ1 U-15N,13C, 3mM peptide, 10 mM phospate buffer 150 mM NaCl, pH 6.8 溶媒系: 90% H2O/10% D2O |
|---|
-NMR測定
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
|---|---|
| 放射波長 | 相対比: 1 |
| NMRスペクトロメーター | タイプ: Bruker AVANCE / 製造業者: Bruker / モデル : AVANCE / 磁場強度: 600 MHz : AVANCE / 磁場強度: 600 MHz |
- 解析
解析
| NMR software |
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: torsion angle dynamics, cartesian MD in water / ソフトェア番号: 1 | ||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with acceptable covalent geometry,structures with the least restraint violations 計算したコンフォーマーの数: 100 / 登録したコンフォーマーの数: 22 |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj