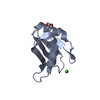
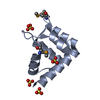
登録情報 データベース : PDB / ID : 1eoqタイトル ROUS SARCOMA VIRUS CAPSID PROTEIN: C-TERMINAL DOMAIN GAG POLYPROTEIN CAPSID PROTEIN P27 キーワード / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 手法 / データ登録者 Kingston, R.L. / Fitzon-Ostendorp, T. / Eisenmesser, E.Z. / Schatz, G.W. / Vogt, V.M. / Post, C.B. / Rossmann, M.G. ジャーナル : Structure Fold.Des. / 年 : 2000タイトル : Structure and self-association of the Rous sarcoma virus capsid protein.著者 : Kingston, R.L. / Fitzon-Ostendorp, T. / Eisenmesser, E.Z. / Schatz, G.W. / Vogt, V.M. / Post, C.B. / Rossmann, M.G. 履歴 登録 2000年3月23日 登録サイト / 処理サイト 改定 1.0 2000年8月2日 Provider / タイプ 改定 1.1 2008年4月27日 Group 改定 1.2 2011年7月13日 Group 改定 1.3 2019年6月5日 Group / Derived calculations / Structure summaryカテゴリ / pdbx_struct_assembly / pdbx_struct_oper_listItem 改定 1.4 2022年12月21日 Group / カテゴリ / struct_ref_seq_difItem / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード VIRAL PROTEIN (ウイルスタンパク質) / VIRUS/VIRAL PROTEIN
VIRAL PROTEIN (ウイルスタンパク質) / VIRUS/VIRAL PROTEIN 機能・相同性情報
機能・相同性情報 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ /
加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ /  カプシド / structural constituent of virion /
カプシド / structural constituent of virion /  nucleic acid binding / aspartic-type endopeptidase activity / host cell plasma membrane /
nucleic acid binding / aspartic-type endopeptidase activity / host cell plasma membrane /  タンパク質分解 ...host cell nucleoplasm / viral procapsid maturation / host cell nucleolus /
タンパク質分解 ...host cell nucleoplasm / viral procapsid maturation / host cell nucleolus /  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ /
加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ /  カプシド / structural constituent of virion /
カプシド / structural constituent of virion /  nucleic acid binding / aspartic-type endopeptidase activity / host cell plasma membrane /
nucleic acid binding / aspartic-type endopeptidase activity / host cell plasma membrane /  タンパク質分解 / zinc ion binding /
タンパク質分解 / zinc ion binding /  生体膜
生体膜
 Rous sarcoma virus - Prague C (ラウス肉腫ウイルス)
Rous sarcoma virus - Prague C (ラウス肉腫ウイルス) 溶液NMR / torsion angle dynamics,
溶液NMR / torsion angle dynamics,  simulated annealing
simulated annealing  データ登録者
データ登録者 引用
引用 ジャーナル: Structure Fold.Des. / 年: 2000
ジャーナル: Structure Fold.Des. / 年: 2000 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1eoq.cif.gz
1eoq.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1eoq.ent.gz
pdb1eoq.ent.gz PDB形式
PDB形式 1eoq.json.gz
1eoq.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/eo/1eoq
https://data.pdbj.org/pub/pdb/validation_reports/eo/1eoq ftp://data.pdbj.org/pub/pdb/validation_reports/eo/1eoq
ftp://data.pdbj.org/pub/pdb/validation_reports/eo/1eoq リンク
リンク 集合体
集合体
 要素
要素
 Rous sarcoma virus - Prague C (ラウス肉腫ウイルス)
Rous sarcoma virus - Prague C (ラウス肉腫ウイルス) アルファレトロウイルス属 / 生物種: Rous sarcoma virus
アルファレトロウイルス属 / 生物種: Rous sarcoma virus ラウス肉腫ウイルス / 株: PRAGUE C / プラスミド: PET-3XC (NOVAGEN) / 発現宿主:
ラウス肉腫ウイルス / 株: PRAGUE C / プラスミド: PET-3XC (NOVAGEN) / 発現宿主: 
 Escherichia coli (大腸菌) / 参照: UniProt: P03322
Escherichia coli (大腸菌) / 参照: UniProt: P03322 溶液NMR
溶液NMR 試料調製
試料調製
 : UNITYPLUS / 磁場強度: 600 MHz
: UNITYPLUS / 磁場強度: 600 MHz 解析
解析 simulated annealing / ソフトェア番号: 1
simulated annealing / ソフトェア番号: 1  ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj