+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23017 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | GluK2/K5 apo | |||||||||
 マップデータ マップデータ | GluK2/K5 apo | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of synaptic vesicle fusion to presynaptic active zone membrane / protein retention in ER lumen /  mossy fiber rosette / detection of cold stimulus involved in thermoception / Activation of Na-permeable kainate receptors / kainate selective glutamate receptor complex / Activation of Ca-permeable Kainate Receptor / negative regulation of synaptic transmission, glutamatergic / regulation of short-term neuronal synaptic plasticity / mossy fiber rosette / detection of cold stimulus involved in thermoception / Activation of Na-permeable kainate receptors / kainate selective glutamate receptor complex / Activation of Ca-permeable Kainate Receptor / negative regulation of synaptic transmission, glutamatergic / regulation of short-term neuronal synaptic plasticity /  inhibitory postsynaptic potential ...regulation of synaptic vesicle fusion to presynaptic active zone membrane / protein retention in ER lumen / inhibitory postsynaptic potential ...regulation of synaptic vesicle fusion to presynaptic active zone membrane / protein retention in ER lumen /  mossy fiber rosette / detection of cold stimulus involved in thermoception / Activation of Na-permeable kainate receptors / kainate selective glutamate receptor complex / Activation of Ca-permeable Kainate Receptor / negative regulation of synaptic transmission, glutamatergic / regulation of short-term neuronal synaptic plasticity / mossy fiber rosette / detection of cold stimulus involved in thermoception / Activation of Na-permeable kainate receptors / kainate selective glutamate receptor complex / Activation of Ca-permeable Kainate Receptor / negative regulation of synaptic transmission, glutamatergic / regulation of short-term neuronal synaptic plasticity /  inhibitory postsynaptic potential / inhibitory postsynaptic potential /  glutamate receptor activity / ubiquitin conjugating enzyme binding / modulation of excitatory postsynaptic potential / receptor clustering / neuronal action potential / regulation of JNK cascade / kainate selective glutamate receptor activity / glutamate receptor activity / ubiquitin conjugating enzyme binding / modulation of excitatory postsynaptic potential / receptor clustering / neuronal action potential / regulation of JNK cascade / kainate selective glutamate receptor activity /  ionotropic glutamate receptor complex / extracellularly glutamate-gated ion channel activity / behavioral fear response / positive regulation of synaptic transmission / glutamate-gated receptor activity / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / ionotropic glutamate receptor complex / extracellularly glutamate-gated ion channel activity / behavioral fear response / positive regulation of synaptic transmission / glutamate-gated receptor activity / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential /  excitatory postsynaptic potential / hippocampal mossy fiber to CA3 synapse / presynaptic modulation of chemical synaptic transmission / excitatory postsynaptic potential / hippocampal mossy fiber to CA3 synapse / presynaptic modulation of chemical synaptic transmission /  regulation of membrane potential / dendrite cytoplasm / regulation of membrane potential / dendrite cytoplasm /  生物発光 / 生物発光 /  SNARE binding / transmitter-gated monoatomic ion channel activity involved in regulation of postsynaptic membrane potential / SNARE binding / transmitter-gated monoatomic ion channel activity involved in regulation of postsynaptic membrane potential /  synaptic transmission, glutamatergic / generation of precursor metabolites and energy / synaptic transmission, glutamatergic / generation of precursor metabolites and energy /  PDZ domain binding / establishment of localization in cell / cellular response to glucose stimulus / postsynaptic density membrane / regulation of long-term neuronal synaptic plasticity / modulation of chemical synaptic transmission / PDZ domain binding / establishment of localization in cell / cellular response to glucose stimulus / postsynaptic density membrane / regulation of long-term neuronal synaptic plasticity / modulation of chemical synaptic transmission /  terminal bouton / intracellular calcium ion homeostasis / terminal bouton / intracellular calcium ion homeostasis /  SH3 domain binding / positive regulation of neuron apoptotic process / SH3 domain binding / positive regulation of neuron apoptotic process /  presynaptic membrane / presynaptic membrane /  perikaryon / chemical synaptic transmission / perikaryon / chemical synaptic transmission /  scaffold protein binding / scaffold protein binding /  postsynaptic membrane / neuron apoptotic process / negative regulation of neuron apoptotic process / postsynaptic membrane / neuron apoptotic process / negative regulation of neuron apoptotic process /  postsynaptic density / postsynaptic density /  神経繊維 / neuronal cell body / 神経繊維 / neuronal cell body /  樹状突起 / 樹状突起 /  シナプス / glutamatergic synapse / シナプス / glutamatergic synapse /  ubiquitin protein ligase binding / ubiquitin protein ligase binding /  小胞体 / 小胞体 /  生体膜 / identical protein binding / 生体膜 / identical protein binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) | |||||||||
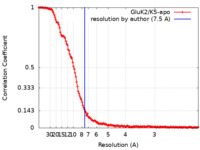
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 7.5 Å クライオ電子顕微鏡法 / 解像度: 7.5 Å | |||||||||
 データ登録者 データ登録者 | Khanra N / Brown PMGE / Perozzo AM / Bowie D / Meyerson JM | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2021 ジャーナル: Elife / 年: 2021タイトル: Architecture and structural dynamics of the heteromeric GluK2/K5 kainate receptor. 著者: Nandish Khanra / Patricia Mge Brown / Amanda M Perozzo / Derek Bowie / Joel R Meyerson /   要旨: Kainate receptors (KARs) are L-glutamate-gated ion channels that regulate synaptic transmission and modulate neuronal circuits. KARs have strict assembly rules and primarily function as heteromeric ...Kainate receptors (KARs) are L-glutamate-gated ion channels that regulate synaptic transmission and modulate neuronal circuits. KARs have strict assembly rules and primarily function as heteromeric receptors in the brain. A longstanding question is how KAR heteromer subunits organize and coordinate together to fulfill their signature physiological roles. Here we report structures of the GluK2/GluK5 heteromer in apo, antagonist-bound, and desensitized states. The receptor assembles with two copies of each subunit, ligand binding domains arranged as two heterodimers and GluK5 subunits proximal to the channel. Strikingly, during desensitization, GluK2, but not GluK5, subunits undergo major structural rearrangements to facilitate channel closure. We show how the large conformational differences between antagonist-bound and desensitized states are mediated by the linkers connecting the pore helices to the ligand binding domains. This work presents the first KAR heteromer structure, reveals how its subunits are organized, and resolves how the heteromer can accommodate functionally distinct closed channel structures. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23017.map.gz emd_23017.map.gz | 259 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23017-v30.xml emd-23017-v30.xml emd-23017.xml emd-23017.xml | 11.9 KB 11.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_23017_fsc.xml emd_23017_fsc.xml | 15 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_23017.png emd_23017.png | 50.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23017 http://ftp.pdbj.org/pub/emdb/structures/EMD-23017 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23017 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23017 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7ks0C  7ks3C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10658 (タイトル: GluK2/K5 apo / Data size: 230.4 / Data #1: GluK2/K5-apo [micrographs - multiframe]) EMPIAR-10658 (タイトル: GluK2/K5 apo / Data size: 230.4 / Data #1: GluK2/K5-apo [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23017.map.gz / 形式: CCP4 / 大きさ: 274.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23017.map.gz / 形式: CCP4 / 大きさ: 274.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | GluK2/K5 apo | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.083 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : GluK2/K5 apo
| 全体 | 名称: GluK2/K5 apo |
|---|---|
| 要素 |
|
-超分子 #1: GluK2/K5 apo
| 超分子 | 名称: GluK2/K5 apo / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) / 組換細胞: HEK293S GnTI- Homo sapiens (ヒト) / 組換細胞: HEK293S GnTI- |
-分子 #1: Glutamate receptor ionotropic, kainate 5,Green fluorescent protei...
| 分子 | 名称: Glutamate receptor ionotropic, kainate 5,Green fluorescent protein chimera タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MPAELLLLLI VAFANPSCQV LSSLRMAAIL DDQTVCGRGE RLALALAREQ INGIIEVPAK ARVEVDIFE LQRDSQYETT DTMCQILPKG VVSVLGPSSS PASASTVSHI CGEKEIPHIK V GPEETPRL QYLRFASVSL YPSNEDVSLA VSRILKSFNY PSASLICAKA ...文字列: MPAELLLLLI VAFANPSCQV LSSLRMAAIL DDQTVCGRGE RLALALAREQ INGIIEVPAK ARVEVDIFE LQRDSQYETT DTMCQILPKG VVSVLGPSSS PASASTVSHI CGEKEIPHIK V GPEETPRL QYLRFASVSL YPSNEDVSLA VSRILKSFNY PSASLICAKA ECLLRLEELV RG FLISKET LSVRMLDDSR DPTPLLKEIR DDKVSTIIID ANASISHLVL RKASELGMTS AFY KYILTT MDFPILHLDG IVEDSSNILG FSMFNTSHPF YPEFVRSLNM SWRENCEAST YPGP ALSAA LMFDAVHVVV SAVRELNRSQ EIGVKPLACT SANIWPHGTS LMNYLRMVEY DGLTG RVEF NSKGQRTNYT LRILEKSRQG HREIGVWYSN RTLAMNATTL DINLSQTLAN KTLVVT TIL ENPYVMRRPN FQALSGNERF EGFCVDMLRE LAELLRFRYR LRLVEDGLYG APEPNGS WT GMVGELINRK ADLAVAAFTI TAEREKVIDF SKPFMTLGIS ILYRVHMGRK PGYFSFLD P FSPAVWLFML LAYLAVSVVL FLAARLSPYE WYNPHPSLRA RPHILENQYT LGNSLWFPV GGFMQQGSEI MPRALSTRIV SGVWWAFTLI IISSYTANLA AFLTVQRMEV PVESADDLAD QTNIEYGTI HAGSTMTFFQ NSRYQTYQRM WNYMQSKQPS VFVKSTEEGI ARVLNSRYAF L LESTMNEY HRRLNCNLTQ IGGLLDTKGY GIGMPLGSPF RDEITLAILQ LQENNRLEIL KR KWWEGGR CPKEEDHRAK GLGMENIGGI FVVLIAGLII AVFVAVMEFI YKSRAEAKRM KGL VPRGSA AAAMVSKGEE LFTGVVPILV ELDGDVNGHK FSVSGEGEGD ATYGKLTLKF ICTT GKLPV PWPTLVTTLT YGVQCFSRYP DHMKQHDFFK SAMPEGYVQE RTIFFKDDGN YKTRA EVKF EGDTLVNRIE LKGIDFKEDG NILGHKLEYN YNSHNVYIMA DKQKNGIKVN FKIRHN IED GSVQLADHYQ QNTPIGDGPV LLPDNHYLST QSKLSKDPNE KRDHMVLLEF VTAAGIT LG MDELYKSGLR TETSQVAPA |
-分子 #2: Glutamate receptor ionotropic, kainate 2
| 分子 | 名称: Glutamate receptor ionotropic, kainate 2 / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MKIISPVLSN LVFSRSIKVL LCLLWIGYSQ GTTHVLRFGG IFEYVESGPM GAEELAFRFA VNTINRNRTL LPNTTLTYDT QKINLYDSFE ASKKACDQLS LGVAAIFGPS HSSSANAVQS ICNALGVPHI QTRWKHQVSD NKDSFYVSLY PDFSSLSRAI LDLVQFFKWK ...文字列: MKIISPVLSN LVFSRSIKVL LCLLWIGYSQ GTTHVLRFGG IFEYVESGPM GAEELAFRFA VNTINRNRTL LPNTTLTYDT QKINLYDSFE ASKKACDQLS LGVAAIFGPS HSSSANAVQS ICNALGVPHI QTRWKHQVSD NKDSFYVSLY PDFSSLSRAI LDLVQFFKWK TVTVVYDDST GLIRLQELIK APSRYNLRLK IRQLPADTKD AKPLLKEMKR GKEFHVIFDC SHEMAAGILK QALAMGMMTE YYHYIFTTLD LFALDVEPYR YSGVNMTGFR ILNTENTQVS SIIEKWSMER LQAPPKPDSG LLDGFMTTDA ALMYDAVHVV SVAVQQFPQM TVSSLQCNRH KPWRFGTRFM SLIKEAHWEG LTGRITFNKT NGLRTDFDLD VISLKEEGLE KIGTWDPASG LNMTESQKGK PANITDSLSN RSLIVTTILE EPYVLFKKSD KPLYGNDRFE GYCIDLLREL STILGFTYEI RLVEDGKYGA QDDVNGQWNG MVRELIDHKA DLAVAPLAIT YVREKVIDFS KPFMTLGISI LYRKPNGTNP GVFSFLNPLS PDIWMYVLLA YLGVSVVLFV IARFSPYEWY NPHPSNPDSD VVENNFTLLN SFWFGVGALM QQGSELMPKA LSTRIVGGIW WFFTLIIISS YTANLAAFLT VERMESPIDS ADDLAKQTKI EYGAVEDGAT MTFFKKSKIS TYDKMWAFMS SRRQSVLVKS NEEGIQRVLT SDYAFLMEST TIEFVTQRNC NLTQIGGLID SKGYGVGTPM GSPYRDKITI AILQLQEEGK LHMMKEKWWR GNGCPEEESK EASALGVQNI GGIFIVLAAG LVLSVFVAVG EFLYKSKKNA QLEKRSFCSA MVEELRMSLK CQRRLKHKPQ APVIVKTEEV INMHTFNDRR LPGKETMASG LRSAWSHPQF EKGGGSGGGS GGGSWSHPQF EK |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.7 mg/mL | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 295 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 51.23 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー