+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of K27A mutant E.coli DPS | |||||||||
 マップデータ マップデータ | Structure of K27A mutant E.coli DPS determined by movement-free cryoEM. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  ferritin (フェリチン) / ferritin (フェリチン) /  DNA (デオキシリボ核酸) / METAL BINDING PROTEIN DNA (デオキシリボ核酸) / METAL BINDING PROTEIN | |||||||||
| 機能・相同性 | :  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | |||||||||
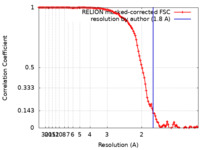
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 1.8 Å クライオ電子顕微鏡法 / 解像度: 1.8 Å | |||||||||
 データ登録者 データ登録者 | Dickerson JL / Russo CJ | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Ultramicroscopy / 年: 2024 ジャーナル: Ultramicroscopy / 年: 2024タイトル: Accurate magnification determination for cryoEM using gold. 著者: Joshua L Dickerson / Erin Leahy / Mathew J Peet / Katerina Naydenova / Christopher J Russo /  要旨: Determining the correct magnified pixel size of single-particle cryoEM micrographs is necessary to maximize resolution and enable accurate model building. Here we describe a simple and rapid ...Determining the correct magnified pixel size of single-particle cryoEM micrographs is necessary to maximize resolution and enable accurate model building. Here we describe a simple and rapid procedure for determining the absolute magnification in an electron cryomicroscope to a precision of <0.5%. We show how to use the atomic lattice spacings of crystals of thin and readily available test specimens, such as gold, as an absolute reference to determine magnification for both room temperature and cryogenic imaging. We compare this method to other commonly used methods, and show that it provides comparable accuracy in spite of its simplicity. This magnification calibration method provides a definitive reference quantity for data analysis and processing, simplifies the combination of multiple datasets from different microscopes and detectors, and improves the accuracy with which the contrast transfer function of the microscope can be determined. We also provide an open source program, magCalEM, which can be used to accurately estimate the magnified pixel size of a cryoEM dataset ex post facto. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_17992.map.gz emd_17992.map.gz | 15.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-17992-v30.xml emd-17992-v30.xml emd-17992.xml emd-17992.xml | 14.2 KB 14.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_17992_fsc.xml emd_17992_fsc.xml | 11.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_17992.png emd_17992.png | 271.8 KB | ||
| マスクデータ |  emd_17992_msk_1.map emd_17992_msk_1.map | 125 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-17992.cif.gz emd-17992.cif.gz | 4.7 KB | ||
| その他 |  emd_17992_half_map_1.map.gz emd_17992_half_map_1.map.gz emd_17992_half_map_2.map.gz emd_17992_half_map_2.map.gz | 97.8 MB 97.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-17992 http://ftp.pdbj.org/pub/emdb/structures/EMD-17992 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17992 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17992 | HTTPS FTP |
-関連構造データ
| 関連構造データ | C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_17992.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_17992.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Structure of K27A mutant E.coli DPS determined by movement-free cryoEM. | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.646 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_17992_msk_1.map emd_17992_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Unfiltered half map 1
| ファイル | emd_17992_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Unfiltered half map 2
| ファイル | emd_17992_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : DNA protection during starvation protein (DPS)
| 全体 | 名称: DNA protection during starvation protein (DPS) |
|---|---|
| 要素 |
|
-超分子 #1: DNA protection during starvation protein (DPS)
| 超分子 | 名称: DNA protection during starvation protein (DPS) / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 分子量 | 理論値: 224 KDa |
-分子 #1: DNA protection during starvation protein (DPS)
| 分子 | 名称: DNA protection during starvation protein (DPS) / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli BL21(DE3) (大腸菌) Escherichia coli BL21(DE3) (大腸菌) |
| 配列 | 文字列: MSTAKLVKSK ATNLLYTRND VSDSEKAATV ELLNRQVIQF IDLSLITKQA HWNMRGANFI AVHEMLDGFR TALIDHLDTM AERAVQLGG VALGTTQVIN SKTPLKSYPL DIHNVQDHLK ELADRYAIVA NDVRKAIGEA KDDDTADILT AASRDLDKFL W FIESNIE UniProtKB:  UNIPROTKB: POABT2 UNIPROTKB: POABT2 |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.7 |
|---|---|
| グリッド | 材質: GOLD / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY ARRAY / 支持フィルム - Film thickness: 30 / 前処理 - タイプ: PLASMA CLEANING |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 1.6 µm / 最小 デフォーカス(公称値): 0.6 µm Bright-field microscopy / 最大 デフォーカス(公称値): 1.6 µm / 最小 デフォーカス(公称値): 0.6 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 60.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)