+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the human nuclear cap-binding complex bound to ARS2[147-871] and m7GTP | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Nuclear cap-binding complex / ARS2 / Pol II transcript metabolism /  RNA BINDING PROTEIN (RNA結合タンパク質) RNA BINDING PROTEIN (RNA結合タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報mRNA cap binding complex binding / snRNA export from nucleus / nuclear cap binding complex / mRNA metabolic process / RNA cap binding complex / histone mRNA metabolic process / positive regulation of mRNA 3'-end processing / positive regulation of RNA export from nucleus / cap-dependent translational initiation / Processing of Intronless Pre-mRNAs ...mRNA cap binding complex binding / snRNA export from nucleus / nuclear cap binding complex / mRNA metabolic process / RNA cap binding complex / histone mRNA metabolic process / positive regulation of mRNA 3'-end processing / positive regulation of RNA export from nucleus / cap-dependent translational initiation / Processing of Intronless Pre-mRNAs /  snRNA binding / positive regulation of RNA binding / snRNA binding / positive regulation of RNA binding /  RNA cap binding / alternative mRNA splicing, via spliceosome / SLBP independent Processing of Histone Pre-mRNAs / SLBP Dependent Processing of Replication-Dependent Histone Pre-mRNAs / neuronal stem cell population maintenance / RNA cap binding / alternative mRNA splicing, via spliceosome / SLBP independent Processing of Histone Pre-mRNAs / SLBP Dependent Processing of Replication-Dependent Histone Pre-mRNAs / neuronal stem cell population maintenance /  regulation of mRNA processing / miRNA-mediated post-transcriptional gene silencing / primary miRNA processing / regulatory ncRNA-mediated post-transcriptional gene silencing / : / RNA 7-methylguanosine cap binding / mRNA 3'-end processing / Transport of the SLBP independent Mature mRNA / Transport of the SLBP Dependant Mature mRNA / mRNA 3'-end processing / response to arsenic-containing substance / Transport of Mature mRNA Derived from an Intronless Transcript / mRNA cis splicing, via spliceosome / positive regulation of mRNA splicing, via spliceosome / RNA catabolic process / Transport of Mature mRNA derived from an Intron-Containing Transcript / Abortive elongation of HIV-1 transcript in the absence of Tat / regulation of translational initiation / RNA Polymerase II Transcription Termination / FGFR2 alternative splicing / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay / positive regulation of neurogenesis / Signaling by FGFR2 IIIa TM / spliceosomal complex assembly / Formation of the Early Elongation Complex / Formation of the HIV-1 Early Elongation Complex / mRNA Capping / mRNA Splicing - Minor Pathway / 7-methylguanosine mRNA capping / RNA polymerase II transcribes snRNA genes / Processing of Capped Intron-Containing Pre-mRNA / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Formation of HIV-1 elongation complex containing HIV-1 Tat / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / Formation of HIV elongation complex in the absence of HIV Tat / mRNA export from nucleus / Formation of RNA Pol II elongation complex / RNA Polymerase II Pre-transcription Events / mRNA Splicing - Major Pathway / regulation of mRNA processing / miRNA-mediated post-transcriptional gene silencing / primary miRNA processing / regulatory ncRNA-mediated post-transcriptional gene silencing / : / RNA 7-methylguanosine cap binding / mRNA 3'-end processing / Transport of the SLBP independent Mature mRNA / Transport of the SLBP Dependant Mature mRNA / mRNA 3'-end processing / response to arsenic-containing substance / Transport of Mature mRNA Derived from an Intronless Transcript / mRNA cis splicing, via spliceosome / positive regulation of mRNA splicing, via spliceosome / RNA catabolic process / Transport of Mature mRNA derived from an Intron-Containing Transcript / Abortive elongation of HIV-1 transcript in the absence of Tat / regulation of translational initiation / RNA Polymerase II Transcription Termination / FGFR2 alternative splicing / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay / positive regulation of neurogenesis / Signaling by FGFR2 IIIa TM / spliceosomal complex assembly / Formation of the Early Elongation Complex / Formation of the HIV-1 Early Elongation Complex / mRNA Capping / mRNA Splicing - Minor Pathway / 7-methylguanosine mRNA capping / RNA polymerase II transcribes snRNA genes / Processing of Capped Intron-Containing Pre-mRNA / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Formation of HIV-1 elongation complex containing HIV-1 Tat / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / Formation of HIV elongation complex in the absence of HIV Tat / mRNA export from nucleus / Formation of RNA Pol II elongation complex / RNA Polymerase II Pre-transcription Events / mRNA Splicing - Major Pathway /  RNA splicing / positive regulation of transcription elongation by RNA polymerase II / mRNA transcription by RNA polymerase II / RNA splicing / positive regulation of transcription elongation by RNA polymerase II / mRNA transcription by RNA polymerase II /  転写後修飾 / 転写後修飾 /  mRNA splicing, via spliceosome / Regulation of expression of SLITs and ROBOs / protein-macromolecule adaptor activity / mRNA splicing, via spliceosome / Regulation of expression of SLITs and ROBOs / protein-macromolecule adaptor activity /  snRNP Assembly / positive regulation of cell growth / defense response to virus / molecular adaptor activity / snRNP Assembly / positive regulation of cell growth / defense response to virus / molecular adaptor activity /  nuclear body / nuclear body /  ribonucleoprotein complex / ribonucleoprotein complex /  mRNA binding / regulation of DNA-templated transcription / protein-containing complex / mRNA binding / regulation of DNA-templated transcription / protein-containing complex /  ミトコンドリア / ミトコンドリア /  DNA binding / DNA binding /  RNA binding / RNA binding /  核質 / 核質 /  細胞核 / 細胞核 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.43 Å クライオ電子顕微鏡法 / 解像度: 3.43 Å | |||||||||
 データ登録者 データ登録者 | Dubiez E / Pellegrini E / Foucher AE / Cusack S / Kadlec J | |||||||||
| 資金援助 |  フランス, 1件 フランス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2024 ジャーナル: Cell Rep / 年: 2024タイトル: Structural basis for competitive binding of productive and degradative co-transcriptional effectors to the nuclear cap-binding complex. 著者: Etienne Dubiez / Erika Pellegrini / Maja Finderup Brask / William Garland / Anne-Emmanuelle Foucher / Karine Huard / Torben Heick Jensen / Stephen Cusack / Jan Kadlec /   要旨: The nuclear cap-binding complex (CBC) coordinates co-transcriptional maturation, transport, or degradation of nascent RNA polymerase II (Pol II) transcripts. CBC with its partner ARS2 forms mutually ...The nuclear cap-binding complex (CBC) coordinates co-transcriptional maturation, transport, or degradation of nascent RNA polymerase II (Pol II) transcripts. CBC with its partner ARS2 forms mutually exclusive complexes with diverse "effectors" that promote either productive or destructive outcomes. Combining AlphaFold predictions with structural and biochemical validation, we show how effectors NCBP3, NELF-E, ARS2, PHAX, and ZC3H18 form competing binary complexes with CBC and how PHAX, NCBP3, ZC3H18, and other effectors compete for binding to ARS2. In ternary CBC-ARS2 complexes with PHAX, NCBP3, or ZC3H18, ARS2 is responsible for the initial effector recruitment but inhibits their direct binding to the CBC. We show that in vivo ZC3H18 binding to both CBC and ARS2 is required for nuclear RNA degradation. We propose that recruitment of PHAX to CBC-ARS2 can lead, with appropriate cues, to competitive displacement of ARS2 and ZC3H18 from the CBC, thus promoting a productive rather than a degradative RNA fate. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_17763.map.gz emd_17763.map.gz | 89.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-17763-v30.xml emd-17763-v30.xml emd-17763.xml emd-17763.xml | 17.8 KB 17.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_17763_fsc.xml emd_17763_fsc.xml | 11.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_17763.png emd_17763.png | 34 KB | ||
| マスクデータ |  emd_17763_msk_1.map emd_17763_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-17763.cif.gz emd-17763.cif.gz | 6.6 KB | ||
| その他 |  emd_17763_half_map_1.map.gz emd_17763_half_map_1.map.gz emd_17763_half_map_2.map.gz emd_17763_half_map_2.map.gz | 165.4 MB 165.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-17763 http://ftp.pdbj.org/pub/emdb/structures/EMD-17763 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17763 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17763 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_17763.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_17763.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.839 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_17763_msk_1.map emd_17763_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_17763_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_17763_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Structure of the human nuclear cap-binding complex bound to ARS2[...
| 全体 | 名称: Structure of the human nuclear cap-binding complex bound to ARS2[147-871] and m7GTP |
|---|---|
| 要素 |
|
-超分子 #1: Structure of the human nuclear cap-binding complex bound to ARS2[...
| 超分子 | 名称: Structure of the human nuclear cap-binding complex bound to ARS2[147-871] and m7GTP タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Nuclear cap-binding protein subunit 1
| 分子 | 名称: Nuclear cap-binding protein subunit 1 / タイプ: protein_or_peptide / ID: 1 詳細: CBP80 construct has the N-terminal 20 residues (containing the NLS) deleted and replaced by a methionine コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 89.781938 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MKTSDANETE DHLESLICKV GEKSACSLES NLEGLAGVLE ADLPNYKSKI LRLLCTVARL LPEKLTIYTT LVGLLNARNY NFGGEFVEA MIRQLKESLK ANNYNEAVYL VRFLSDLVNC HVIAAPSMVA MFENFVSVTQ EEDVPQVRRD WYVYAFLSSL P WVGKELYE ...文字列: MKTSDANETE DHLESLICKV GEKSACSLES NLEGLAGVLE ADLPNYKSKI LRLLCTVARL LPEKLTIYTT LVGLLNARNY NFGGEFVEA MIRQLKESLK ANNYNEAVYL VRFLSDLVNC HVIAAPSMVA MFENFVSVTQ EEDVPQVRRD WYVYAFLSSL P WVGKELYE KKDAEMDRIF ANTESYLKRR QKTHVPMLQV WTADKPHPQE EYLDCLWAQI QKLKKDRWQE RHILRPYLAF DS ILCEALQ HNLPPFTPPP HTEDSVYPMP RVIFRMFDYT DDPEGPVMPG SHSVERFVIE ENLHCIIKSH WKERKTCAAQ LVS YPGKNK IPLNYHIVEV IFAELFQLPA PPHIDVMYTT LLIELCKLQP GSLPQVLAQA TEMLYMRLDT MNTTCVDRFI NWFS HHLSN FQFRWSWEDW SDCLSQDPES PKPKFVREVL EKCMRLSYHQ RILDIVPPTF SALCPANPTC IYKYGDESSN SLPGH SVAL CLAVAFKSKA TNDEIFSILK DVPNPNQDDD DDEGFSFNPL KIEVFVQTLL HLAAKSFSHS FSALAKFHEV FKTLAE SDE GKLHVLRVMF EVWRNHPQMI AVLVDKMIRT QIVDCAAVAN WIFSSELSRD FTRLFVWEIL HSTIRKMNKH VLKIQKE LE EAKEKLARQH KRRSDDDDRS SDRKDGVLEE QIERLQEKVE SAQSEQKNLF LVIFQRFIMI LTEHLVRCET DGTSVLTP W YKNCIERLQQ IFLQHHQIIQ QYMVTLENLL FTAELDPHIL AVFQQFCALQ A UniProtKB: Nuclear cap-binding protein subunit 1 |
-分子 #2: Nuclear cap-binding protein subunit 2
| 分子 | 名称: Nuclear cap-binding protein subunit 2 / タイプ: protein_or_peptide / ID: 2 / 詳細: Additional GA at the N-terminus / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 18.028131 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSGGLLKALR SDSYVELSQY RDQHFRGDNE EQEKLLKKSC TLYVGNLSFY TTEEQIYELF SKSGDIKKII MGLDKMKKTA CGFCFVEYY SRADAENAMR YINGTRLDDR IIRTDWDAGF KEGRQYGRGR SGGQVRDEYR QDYDAGRGGY GKLAQNQ UniProtKB: Nuclear cap-binding protein subunit 2 |
-分子 #3: Serrate RNA effector molecule homolog
| 分子 | 名称: Serrate RNA effector molecule homolog / タイプ: protein_or_peptide / ID: 3 詳細: ARS2 has N-terminal 147 residues deleted and replaced by a methionine コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 83.061391 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: VMKTFKEFLL SLDDSVDETE AVKRYNDYKL DFRRQQMQDF FLAHKDEEWF RSKYHPDEVG KRRQEARGAL QNRLRVFLSL METGWFDNL LLDIDKADAI VKMLDAAVIK MEGGTENDLR ILEQEEEEEQ AGKPGEPSKK EEGRAGAGLG DGERKTNDKD E KKEDGKQA ...文字列: VMKTFKEFLL SLDDSVDETE AVKRYNDYKL DFRRQQMQDF FLAHKDEEWF RSKYHPDEVG KRRQEARGAL QNRLRVFLSL METGWFDNL LLDIDKADAI VKMLDAAVIK MEGGTENDLR ILEQEEEEEQ AGKPGEPSKK EEGRAGAGLG DGERKTNDKD E KKEDGKQA ENDSSNDDKT KKSEGDGDKE EKKEDSEKEA KKSSKKRNRK HSGDDSFDEG SVSESESESE SGQAEEEKEE AE EALKEKE KPKEEEWEKP KDAAGLECKP RPLHKTCSLF MRNIAPNISR AEIISLCKRY PGFMRVALSE PQPERRFFRR GWV TFDRSV NIKEICWNLQ NIRLRECELS PGVNRDLTRR VRNINGITQH KQIVRNDIKL AAKLIHTLDD RTQLWASEPG TPPL PTSLP SQNPILKNIT DYLIEEVSAE EEELLGSSGG APPEEPPKEG NPAEINVERD EKLIKVLDKL LLYLRIVHSL DYYNT CEYP NEDEMPNRCG IIHVRGPMPP NRISHGEVLE WQKTFEEKLT PLLSVRESLS EEEAQKMGRK DPEQEVEKFV TSNTQE LGK DKWLCPLSGK KFKGPEFVRK HIFNKHAEKI EEVKKEVAFF NNFLTDAKRP ALPEIKPAQP PGPAQILPPG LTPGLPY PH QTPQGLMPYG QPRPPILGYG AGAVRPAVPT GGPPYPHAPY GAGRGNYDAF RGQGGYPGKP RNRMVRGDPR AIVEYRDL D APDDVDFF UniProtKB: Serrate RNA effector molecule homolog |
-分子 #4: 7N-METHYL-8-HYDROGUANOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: 7N-METHYL-8-HYDROGUANOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 1 / 式: MGT |
|---|---|
| 分子量 | 理論値: 539.223 Da |
| Chemical component information | 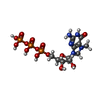 ChemComp-MGT: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.5 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.5 µm最小 デフォーカス(公称値): 0.7000000000000001 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 40.13 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)