+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | S-layer protein SlaA from Sulfolobus acidocaldarius at pH 10.0 S層 S層 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  S-layer (S層) / dimer / S-layer (S層) / dimer /  N-glycosylation (N-結合型グリコシル化) / N-glycosylation (N-結合型グリコシル化) /  STRUCTURAL PROTEIN (タンパク質) STRUCTURAL PROTEIN (タンパク質) | |||||||||
| 機能・相同性 |  S層 / extracellular region / S層 / extracellular region /  S-layer protein A S-layer protein A 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |    Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.2 Å クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Gambelli L / Isupov MN / Daum B | |||||||||
| 資金援助 | European Union, 1件
| |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2024 ジャーナル: Elife / 年: 2024タイトル: Structure of the two-component S-layer of the archaeon . 著者: Lavinia Gambelli / Mathew McLaren / Rebecca Conners / Kelly Sanders / Matthew C Gaines / Lewis Clark / Vicki A M Gold / Daniel Kattnig / Mateusz Sikora / Cyril Hanus / Michail N Isupov / Bertram Daum /     要旨: Surface layers (S-layers) are resilient two-dimensional protein lattices that encapsulate many bacteria and most archaea. In archaea, S-layers usually form the only structural component of the cell ...Surface layers (S-layers) are resilient two-dimensional protein lattices that encapsulate many bacteria and most archaea. In archaea, S-layers usually form the only structural component of the cell wall and thus act as the final frontier between the cell and its environment. Therefore, S-layers are crucial for supporting microbial life. Notwithstanding their importance, little is known about archaeal S-layers at the atomic level. Here, we combined single-particle cryo electron microscopy, cryo electron tomography, and Alphafold2 predictions to generate an atomic model of the two-component S-layer of . The outer component of this S-layer (SlaA) is a flexible, highly glycosylated, and stable protein. Together with the inner and membrane-bound component (SlaB), they assemble into a porous and interwoven lattice. We hypothesise that jackknife-like conformational changes in SlaA play important roles in S-layer assembly. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15530.map.gz emd_15530.map.gz | 56.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15530-v30.xml emd-15530-v30.xml emd-15530.xml emd-15530.xml | 15.7 KB 15.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_15530_fsc.xml emd_15530_fsc.xml | 9.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_15530.png emd_15530.png | 39.5 KB | ||
| Filedesc metadata |  emd-15530.cif.gz emd-15530.cif.gz | 6.8 KB | ||
| その他 |  emd_15530_half_map_1.map.gz emd_15530_half_map_1.map.gz emd_15530_half_map_2.map.gz emd_15530_half_map_2.map.gz | 49.7 MB 49.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15530 http://ftp.pdbj.org/pub/emdb/structures/EMD-15530 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15530 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15530 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15530.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15530.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.054 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_15530_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_15530_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Monomeric S-layer protein SlaA with N-glycosylation
| 全体 | 名称: Monomeric S-layer protein SlaA with N-glycosylation |
|---|---|
| 要素 |
|
-超分子 #1: Monomeric S-layer protein SlaA with N-glycosylation
| 超分子 | 名称: Monomeric S-layer protein SlaA with N-glycosylation / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:    Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) |
-分子 #1: S-layer protein A
| 分子 | 名称: S-layer protein A / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) Sulfolobus acidocaldarius DSM 639 (好気性・好酸性)株: ATCC 33909 / DSM 639 / JCM 8929 / NBRC 15157 / NCIMB 11770 |
| 分子量 | 理論値: 151.078406 KDa |
| 組換発現 | 生物種:    Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) Sulfolobus acidocaldarius DSM 639 (好気性・好酸性) |
| 配列 | 文字列: MNKLVGLLVS SLFLASILIG IAPAITTTAL TPPVSAGGIQ AYLLTGSGAP ASGLVLFVVN VSNIQVSSSN VTNVISTVVS NIQINAKTE NAQTGATTGS VTVRFPTSGY NAYYDSVDKV VFVVVSFLYP YTTTSVNIPL SYLSKYLPGL LTAQPYDETG A QVTSVSST ...文字列: MNKLVGLLVS SLFLASILIG IAPAITTTAL TPPVSAGGIQ AYLLTGSGAP ASGLVLFVVN VSNIQVSSSN VTNVISTVVS NIQINAKTE NAQTGATTGS VTVRFPTSGY NAYYDSVDKV VFVVVSFLYP YTTTSVNIPL SYLSKYLPGL LTAQPYDETG A QVTSVSST PFGSLIDTST GQQILGTNPV LTSYNSYTTQ ANTNMQEGVV SGTLTSFTLG GQSFSGSTVP VILYAPFIFS NS PYQAGLY NPMQVNGNLG SLSSEAYYHP VIWGRALINT TLIDTYASGS VPFTFQLNYS VPGPLTINMA QLAWIASINN LPT SFTYLS YKFSNGYESF LGIISNSTQL TAGALTINPS GNFTINGKKF YVYLLVVGST NSTTPVEYVT KLVVEYPSST NFLP QGVTV TTSSNKYTLP VYEIGGPAGT TITLTGNWYS TPYTVQITVG STPTLTNYVS QILLKAVAYE GINVSTTQSP YYSTA ILST PPSEISITGS STITAQGKLT ATSASATVNL LTNATLTYEN IPLTQYSFNG IIVTPGYAAI NGTTAMAYVI GALYNK TSD YVLSFAGSQE PMQVMNNNLT EVTTLAPFGL TLLAPSVPAT ETGTSPLQLE FFTVPSTSYI ALVDFGLWGN LTSVTVS AY DTVNNKLSVN LGYFYGIVIP PSISTAPYNY QNFICPNNYV TVTIYDPDAV LDPYPSGSFT TSSLPLKYGN MNITGAVI F PGSSVYNPSG VFGYSNFNKG AAVTTFTYTA QSGPFSPVAL TGNTNYLSQY ADNNPTDNYY FIQTVNGMPV LMGGLSIVA SPVSASLPSS TSSPGFMYLL PSAAQVPSPL PGMATPNYNL NIYITYKIDG ATVGNNMING LYVASQNTLI YVVPNGSFVG SNIKLTYTT TDYAVLHYFY STGQYKVFKT VSVPNVTANL YFPSSTTPLY QLSVPLYLSE PYYGSPLPTY IGLGTNGTSL W NSPNYVLF GVSAVQQYLG FIKSISVTLS NGTTVVIPLT TSNMQTLFPQ LVGQELQACN GTFQFGISIT GLEKLLNLNV QQ LNNSILS VTYHDYVTGE TLTATTKLVA LSTLSLVAKG AGVVEFLLTA YPYTGNITFA PPWFIAENVV KQPFMTYSDL QFA KTNPSA ILSLSTVNIT VVGLGGKASV YYNSTSGQTV ITNIYGQTVA TLSGNVLPTL TELAAGNGTF TGSLQFTIVP NNTV VQIPS SLTKTSFAVY TNGSLAIVLN GKAYSLGPAG LFLLPFVTYT GSAIGANATA IITVSDGVGT STTQVPITAE NFTPI RLAP FQVPAQVPLP NAPKLKYEYN GSIVITPQQQ VLKIYVTSIL PYPQEFQIQA FVYEASQFNV HTGSPTAAPV YFSYSA VRA YPALGIGTSV PNLLVYVQLQ GISNLPAGKY VIVLSAVPFA GGPVLSEYPA QLIFTNVTLT Q UniProtKB:  S-layer protein A S-layer protein A |
-分子 #8: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 8 / コピー数: 3 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 10 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 61.0 e/Å2 |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
- 画像解析
画像解析
| 粒子像選択 | 選択した数: 280004 |
|---|---|
| 初期モデル | モデルのタイプ: NONE |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 29819 |
FSC曲線 (解像度の算出) | 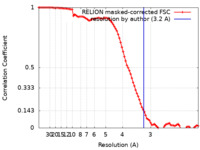 |
 ムービー
ムービー コントローラー
コントローラー












 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)