+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
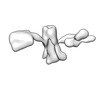
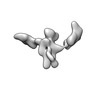
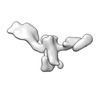
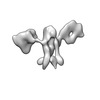
| タイトル | Cryo-EM SPA reconstruction of an extended RNA origami 5 helix tile (5HT-B-3X) | |||||||||
 マップデータ マップデータ | Unsharpened map from cryoSPARC local refinement. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  RNA (リボ核酸) / RNA (リボ核酸) /  origami (折り紙) / origami (折り紙) /  nanostructure (ナノ構造体) nanostructure (ナノ構造体) | |||||||||
| 生物種 | synthetic construct (人工物) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 6.5 Å クライオ電子顕微鏡法 / 解像度: 6.5 Å | |||||||||
 データ登録者 データ登録者 | McRae EKS / Bogglid A / Boesen T / Andersen ES | |||||||||
| 資金援助 |  デンマーク, 1件 デンマーク, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Nanotechnol / 年: 2023 ジャーナル: Nat Nanotechnol / 年: 2023タイトル: Structure, folding and flexibility of co-transcriptional RNA origami. 著者: Ewan K S McRae / Helena Østergaard Rasmussen / Jianfang Liu / Andreas Bøggild / Michael T A Nguyen / Nestor Sampedro Vallina / Thomas Boesen / Jan Skov Pedersen / Gang Ren / Cody Geary / Ebbe Sloth Andersen /   要旨: RNA origami is a method for designing RNA nanostructures that can self-assemble through co-transcriptional folding with applications in nanomedicine and synthetic biology. However, to advance the ...RNA origami is a method for designing RNA nanostructures that can self-assemble through co-transcriptional folding with applications in nanomedicine and synthetic biology. However, to advance the method further, an improved understanding of RNA structural properties and folding principles is required. Here we use cryogenic electron microscopy to study RNA origami sheets and bundles at sub-nanometre resolution revealing structural parameters of kissing-loop and crossover motifs, which are used to improve designs. In RNA bundle designs, we discover a kinetic folding trap that forms during folding and is only released after 10 h. Exploration of the conformational landscape of several RNA designs reveal the flexibility of helices and structural motifs. Finally, sheets and bundles are combined to construct a multidomain satellite shape, which is characterized by individual-particle cryo-electron tomography to reveal the domain flexibility. Together, the study provides a structural basis for future improvements to the design cycle of genetically encoded RNA nanodevices. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
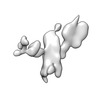
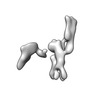
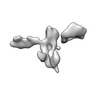
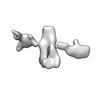
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13592.map.gz emd_13592.map.gz | 32.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13592-v30.xml emd-13592-v30.xml emd-13592.xml emd-13592.xml | 18.3 KB 18.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_13592_fsc.xml emd_13592_fsc.xml | 8.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_13592.png emd_13592.png | 47.7 KB | ||
| マスクデータ |  emd_13592_msk_1.map emd_13592_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| その他 |  emd_13592_half_map_1.map.gz emd_13592_half_map_1.map.gz emd_13592_half_map_2.map.gz emd_13592_half_map_2.map.gz | 59.5 MB 59.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13592 http://ftp.pdbj.org/pub/emdb/structures/EMD-13592 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13592 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13592 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13592.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13592.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map from cryoSPARC local refinement. | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.64 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_13592_msk_1.map emd_13592_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
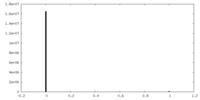
| 密度ヒストグラム |
-ハーフマップ: Half-map A from cryoSPARC local refinement.
| ファイル | emd_13592_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map A from cryoSPARC local refinement. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
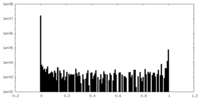
| 密度ヒストグラム |
-ハーフマップ: Half-map B from cryoSPARC local refinement.
| ファイル | emd_13592_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map B from cryoSPARC local refinement. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
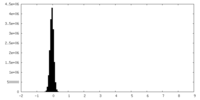
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : 5-helix tile B 3X extended version
| 全体 | 名称: 5-helix tile B 3X extended version |
|---|---|
| 要素 |
|
-超分子 #1: 5-helix tile B 3X extended version
| 超分子 | 名称: 5-helix tile B 3X extended version / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 423 KDa |
-分子 #1: 5HT-B-3X
| 分子 | 名称: 5HT-B-3X / タイプ: rna / ID: 1 / 詳細: In vitro transcribed RNA. |
|---|---|
| 配列 | 文字列: GGAACCUAAU CAUAAUUCCC UUUUCAUCCU CUUCUCAACU CUACUUUUCU UGAUCUUCCG CCUCUCAUCC UUUCAUUAUC UUCAUCCCUG CUUGCAUAUA GUGCCUUCGG GUACUAUGUG CAAGUAGGGG CGUCUGUGAU UCGUGGCUGU UCGCAGUCAC GAAUUACAGA ...文字列: GGAACCUAAU CAUAAUUCCC UUUUCAUCCU CUUCUCAACU CUACUUUUCU UGAUCUUCCG CCUCUCAUCC UUUCAUUAUC UUCAUCCCUG CUUGCAUAUA GUGCCUUCGG GUACUAUGUG CAAGUAGGGG CGUCUGUGAU UCGUGGCUGU UCGCAGUCAC GAAUUACAGA CCAGGCUGUC GGAGAUGGGU UUUCGAAUCC AUCUGGCCAG GGGUUCGCCC UUGGGAACUU UUAUUCGUAG AAGUUCAAAA GUUUAGGAAU GGACAACCUA AGCUUUUCCA UCAGUCGUGC AAGAACGGAG CACGGCUGAU CCGACGGCCU GCGCUACAAA CUGACAGUAG CGGCUGGGAU GCGCUAAACG UUGAAGCGCG UCCCAAUGAA GGUAAUGGAA GGAUGAGGGG CGGAGGAUGG UACAGGUGAA GAACAACGUA CUUCAUCUGU AGGUUGGGUG UGACGUAACA AGUCAGUAGU UGCGUGGAGG AUUAUCCGAA CCGUUCACGG AUGAUCCUAC UUCGUGGUAG GAAUGUCCAA CCUACCGCGA AGUGGACUUC AAACAAUGGC UAAGUUUGGA GUCCCCGAGU GGGGACGAAU UUCCCACGUC CUCACUCCAC ACUCAACCAC GGUCAAGGUG UAAGACCGUC CUUAGAUCGG CUAACUAGUG AAGCCGGUCU AACAAGAAGA GUAGGGUUGA GAAGGGGAUG AGAAGCCCGA AAUGUGACAA CACUAGAGUC ACGUUUCGCA UACUCACGAC UAGAACAAUA CACCAGUUUU AGGGCUCCAU GCUACAAGGG AAAAGUAGCG UGGAGGGUCC CGAUACGCAA UAGCCAAGCG UAUUGGGACC UAGCAUACCC UAACUCCACA AGGGUGUGCU ACCGAGUGUA CGGGAACGGA UAACCCGUGC ACUCUCGUGG GUAUGACAAC AAAAGGUAGA UGUUGUGGUU CCUGACGGGA AUCGUCUACC CGUUAGGAAG GAAUUGUGAU UGGGUUCCAA AUUUCACCUA AUCCUGUCCU ACUCAAAAGA CGAAUGAGUG GGACACCGGG AGCGAACGCG GGGAACUACC UACCCUGCGG CCUCAGGAAG CGAAUAUCCG ACGCUUUCUG AGCUAGUCUU UCGGAAAGUG GAGAUCCGAA GGACUAGUAU GGCAGUCAUG AUGGUGGUUC GCCACCGUCA UGAUUGCCAU AGCGAUGCGC GGGUGAGCUG CUUCGGCGGC UCGCCCGUGC AUCUUCGCUU CCGGGGAGGG UUCUUCGGAA CCUUCUGGGA CGUCGUUCGC GGCGUCGGUU UAAGGUUCGC CUUAGACCAU UGGGUGAAGU UU |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.5 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: Freshly prepared and filtered through 0.22 micron filter prior to use. | ||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.039 kPa / 詳細: 15mA current | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 99 % / チャンバー内温度: 294 K / 装置: LEICA EM GP 詳細: 3 microlitre droplet, 4 second delay before blotting, 6 second blot, 0 second delay before plunging.. | ||||||||||||
| 詳細 | Sample was purified by size exclusion chromatography and concentrated in an Amicon spin concentrator prior to grid preparation. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 倍率(公称値): 130000 Bright-field microscopy / Cs: 2.7 mm / 倍率(公称値): 130000 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 8620 / 平均露光時間: 1.5 sec. / 平均電子線量: 60.0 e/Å2 / 詳細: Images were collected as 56 frame movies. |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 温度因子: 271.2 |
|---|
 ムービー
ムービー コントローラー
コントローラー

























 Z
Z Y
Y X
X