+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-11992 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | the molecular sociology at the HeLa cell nuclear periphery | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  電子線トモグラフィー法 / 電子線トモグラフィー法 /  クライオ電子顕微鏡法 クライオ電子顕微鏡法 | |||||||||
 データ登録者 データ登録者 | Mahamid J / Pfeffer S / Schaffer M / Villa E / Danev R / Kuhn-Cuellar L / Foerster F / Hyman A / Plitzko J / Baumeister W | |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2016 ジャーナル: Science / 年: 2016タイトル: Visualizing the molecular sociology at the HeLa cell nuclear periphery. 著者: Julia Mahamid / Stefan Pfeffer / Miroslava Schaffer / Elizabeth Villa / Radostin Danev / Luis Kuhn Cuellar / Friedrich Förster / Anthony A Hyman / Jürgen M Plitzko / Wolfgang Baumeister /   要旨: The molecular organization of eukaryotic nuclear volumes remains largely unexplored. Here we combined recent developments in cryo-electron tomography (cryo-ET) to produce three-dimensional snapshots ...The molecular organization of eukaryotic nuclear volumes remains largely unexplored. Here we combined recent developments in cryo-electron tomography (cryo-ET) to produce three-dimensional snapshots of the HeLa cell nuclear periphery. Subtomogram averaging and classification of ribosomes revealed the native structure and organization of the cytoplasmic translation machinery. Analysis of a large dynamic structure-the nuclear pore complex-revealed variations detectable at the level of individual complexes. Cryo-ET was used to visualize previously elusive structures, such as nucleosome chains and the filaments of the nuclear lamina, in situ. Elucidation of the lamina structure provides insight into its contribution to metazoan nuclear stiffness. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
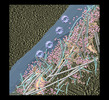
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_11992.map.gz emd_11992.map.gz | 1.3 GB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-11992-v30.xml emd-11992-v30.xml emd-11992.xml emd-11992.xml | 10.4 KB 10.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_11992.png emd_11992.png | 327.1 KB | ||
| マスクデータ |  emd_11992_msk_1.map emd_11992_msk_1.map emd_11992_msk_2.map emd_11992_msk_2.map emd_11992_msk_3.map emd_11992_msk_3.map emd_11992_msk_4.map emd_11992_msk_4.map emd_11992_msk_5.map emd_11992_msk_5.map emd_11992_msk_6.map emd_11992_msk_6.map emd_11992_msk_7.map emd_11992_msk_7.map | 1.6 GB 1.6 GB 1.6 GB 821.3 MB 1.6 GB 1.6 GB 1.6 GB |  マスクマップ マスクマップ | |
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-11992 http://ftp.pdbj.org/pub/emdb/structures/EMD-11992 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11992 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11992 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_11992.map.gz / 形式: CCP4 / 大きさ: 1.6 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_11992.map.gz / 形式: CCP4 / 大きさ: 1.6 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 16.84 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_11992_msk_1.map emd_11992_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
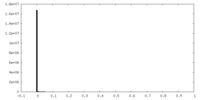
| 投影像・断面図 |
| ||||||||||||
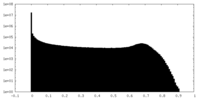
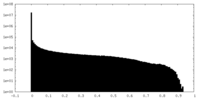
| 密度ヒストグラム |
-マスク #2
| ファイル |  emd_11992_msk_2.map emd_11992_msk_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
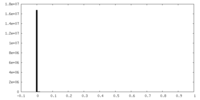
| 投影像・断面図 |
| ||||||||||||
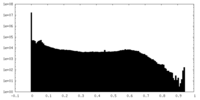
| 密度ヒストグラム |
-マスク #3
| ファイル |  emd_11992_msk_3.map emd_11992_msk_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-マスク #4
| ファイル |  emd_11992_msk_4.map emd_11992_msk_4.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-マスク #5
| ファイル |  emd_11992_msk_5.map emd_11992_msk_5.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-マスク #6
| ファイル |  emd_11992_msk_6.map emd_11992_msk_6.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-マスク #7
| ファイル |  emd_11992_msk_7.map emd_11992_msk_7.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Interphase HeLa cell
| 全体 | 名称: Interphase HeLa cell |
|---|---|
| 要素 |
|
-超分子 #1: Interphase HeLa cell
| 超分子 | 名称: Interphase HeLa cell / タイプ: cell / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  電子線トモグラフィー法 電子線トモグラフィー法 |
| 試料の集合状態 | cell |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE-PROPANE / 装置: FEI VITROBOT MARK IV |
| 切片作成 | 集束イオンビーム - 装置: OTHER / 集束イオンビーム - イオン: OTHER / 集束イオンビーム - 電圧: 30 kV / 集束イオンビーム - 電流: 0.5 nA / 集束イオンビーム - 時間: 1800 sec. / 集束イオンビーム - 温度: 94 K / 集束イオンビーム - Initial thickness: 10000 nm / 集束イオンビーム - 最終 厚さ: 190 nm 集束イオンビーム - 詳細: The value given for _emd_sectioning_focused_ion_beam.instrument is Quanta 3D FEG, FEI. This is not in a list of allowed values {'DB235', 'OTHER'} so OTHER is written into the XML file. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 特殊光学系 | 位相板: VOLTA PHASE PLATE |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 0.8 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | ソフトウェア - 名称:  IMOD / 使用した粒子像数: 50 IMOD / 使用した粒子像数: 50 |
|---|
 ムービー
ムービー コントローラー
コントローラー







 Z
Z Y
Y X
X