+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0103 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Identification of a druggable VP1-VP3 interprotomer pocket in the capsid of enteroviruses | |||||||||
 マップデータ マップデータ | Coxsackievirus B3 Nancy in complex with a small-molecule inhibitor | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Inhibitor /  complex / complex /  virus (ウイルス) virus (ウイルス) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 : / symbiont-mediated perturbation of host gene expression / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity / : / symbiont-mediated perturbation of host gene expression / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity /  ピコルナイン2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / ピコルナイン2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane /  picornain 3C / T=pseudo3 icosahedral viral capsid ... picornain 3C / T=pseudo3 icosahedral viral capsid ... : / symbiont-mediated perturbation of host gene expression / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity / : / symbiont-mediated perturbation of host gene expression / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity /  ピコルナイン2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / ピコルナイン2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane /  picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / endocytosis involved in viral entry into host cell / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / endocytosis involved in viral entry into host cell /  : / nucleoside-triphosphate phosphatase / protein complex oligomerization / monoatomic ion channel activity / : / nucleoside-triphosphate phosphatase / protein complex oligomerization / monoatomic ion channel activity /  DNA複製 / DNA複製 /  RNA helicase activity / induction by virus of host autophagy / RNA helicase activity / induction by virus of host autophagy /  RNA依存性RNAポリメラーゼ / symbiont-mediated suppression of host gene expression / viral RNA genome replication / cysteine-type endopeptidase activity / RNA依存性RNAポリメラーゼ / symbiont-mediated suppression of host gene expression / viral RNA genome replication / cysteine-type endopeptidase activity /  RNA-dependent RNA polymerase activity / DNA-templated transcription / host cell nucleus / virion attachment to host cell / structural molecule activity / RNA-dependent RNA polymerase activity / DNA-templated transcription / host cell nucleus / virion attachment to host cell / structural molecule activity /  ATP hydrolysis activity / ATP hydrolysis activity /  タンパク質分解 / タンパク質分解 /  RNA binding / RNA binding /  ATP binding / ATP binding /  生体膜 / 生体膜 /  metal ion binding metal ion binding類似検索 - 分子機能 | |||||||||
| 生物種 |   Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.0 Å クライオ電子顕微鏡法 / 解像度: 4.0 Å | |||||||||
 データ登録者 データ登録者 | Geraets JA / Flatt JW | |||||||||
| 資金援助 |  フィンランド, 1件 フィンランド, 1件
| |||||||||
 引用 引用 |  ジャーナル: PLoS Biol / 年: 2019 ジャーナル: PLoS Biol / 年: 2019タイトル: A novel druggable interprotomer pocket in the capsid of rhino- and enteroviruses. 著者: Rana Abdelnabi / James A Geraets / Yipeng Ma / Carmen Mirabelli / Justin W Flatt / Aušra Domanska / Leen Delang / Dirk Jochmans / Timiri Ajay Kumar / Venkatesan Jayaprakash / Barij Nayan ...著者: Rana Abdelnabi / James A Geraets / Yipeng Ma / Carmen Mirabelli / Justin W Flatt / Aušra Domanska / Leen Delang / Dirk Jochmans / Timiri Ajay Kumar / Venkatesan Jayaprakash / Barij Nayan Sinha / Pieter Leyssen / Sarah J Butcher / Johan Neyts /    要旨: Rhino- and enteroviruses are important human pathogens, against which no antivirals are available. The best-studied inhibitors are "capsid binders" that fit in a hydrophobic pocket of the viral ...Rhino- and enteroviruses are important human pathogens, against which no antivirals are available. The best-studied inhibitors are "capsid binders" that fit in a hydrophobic pocket of the viral capsid. Employing a new class of entero-/rhinovirus inhibitors and by means of cryo-electron microscopy (EM), followed by resistance selection and reverse genetics, we discovered a hitherto unknown druggable pocket that is formed by viral proteins VP1 and VP3 and that is conserved across entero-/rhinovirus species. We propose that these inhibitors stabilize a key region of the virion, thereby preventing the conformational expansion needed for viral RNA release. A medicinal chemistry effort resulted in the identification of analogues targeting this pocket with broad-spectrum activity against Coxsackieviruses B (CVBs) and compounds with activity against enteroviruses (EV) of groups C and D, and even rhinoviruses (RV). Our findings provide novel insights in the biology of the entry of entero-/rhinoviruses and open new avenues for the design of broad-spectrum antivirals against these pathogens. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0103.map.gz emd_0103.map.gz | 55.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0103-v30.xml emd-0103-v30.xml emd-0103.xml emd-0103.xml | 20.6 KB 20.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_0103_fsc.xml emd_0103_fsc.xml | 14.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_0103.png emd_0103.png | 291.5 KB | ||
| Filedesc metadata |  emd-0103.cif.gz emd-0103.cif.gz | 6.6 KB | ||
| その他 |  emd_0103_half_map_1.map.gz emd_0103_half_map_1.map.gz emd_0103_half_map_2.map.gz emd_0103_half_map_2.map.gz | 128.2 MB 128.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0103 http://ftp.pdbj.org/pub/emdb/structures/EMD-0103 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0103 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0103 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6gzvMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10199 (タイトル: Identification of a druggable VP1-VP3 interprotomer pocket in the capsid of enteroviruses EMPIAR-10199 (タイトル: Identification of a druggable VP1-VP3 interprotomer pocket in the capsid of enterovirusesData size: 2.2 TB Data #1: Unaligned multi-frame micrographs of CVB3 in complex with a small molecular inhibitor [micrographs - single frame]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0103.map.gz / 形式: CCP4 / 大きさ: 163.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0103.map.gz / 形式: CCP4 / 大きさ: 163.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Coxsackievirus B3 Nancy in complex with a small-molecule inhibitor | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.048 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-ハーフマップ: #2
| ファイル | emd_0103_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_0103_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Coxsackievirus B3 (strain Nancy)
| 全体 | 名称:   Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Coxsackievirus B3 (strain Nancy)
| 超分子 | 名称: Coxsackievirus B3 (strain Nancy) / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 詳細: Coxsackievirus B3 (strain Nancy) NCBI Taxonomy ID: 103903 Full, non-enveloped virion from natural source Diameter: ~314A Triangulation: 1 (pT3) Benzene sulfonamide derivative Molecular weight: ...詳細: Coxsackievirus B3 (strain Nancy) NCBI Taxonomy ID: 103903 Full, non-enveloped virion from natural source Diameter: ~314A Triangulation: 1 (pT3) Benzene sulfonamide derivative Molecular weight: 422Da Binding sites on capsid: 60 NCBI-ID: 103903 / 生物種: Coxsackievirus B3 (strain Nancy) / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| ウイルス殻 | Shell ID: 1 / 直径: 314.0 Å / T番号(三角分割数): 1 |
-分子 #1: Capsid protein VP1
| 分子 | 名称: Capsid protein VP1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号:  ピコルナイン2A ピコルナイン2A |
|---|---|
| 由来(天然) | 生物種:   Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス)株: Nancy |
| 分子量 | 理論値: 31.639438 KDa |
| 配列 | 文字列: GPVEDAITAA IGRVADTVGT GPTNSEAIPA LTAAETGHTS QVVPGDTMQT RHVKNYHSRS ESTIENFLCR SACVYFTEYK NSGAKRYAE WVLTPRQAAQ LRRKLEFFTY VRFDLELTFV ITSTQQPSTT QNQDAQILTH QIMYVPPGGP VPDKVDSYVW Q TSTNPSVF ...文字列: GPVEDAITAA IGRVADTVGT GPTNSEAIPA LTAAETGHTS QVVPGDTMQT RHVKNYHSRS ESTIENFLCR SACVYFTEYK NSGAKRYAE WVLTPRQAAQ LRRKLEFFTY VRFDLELTFV ITSTQQPSTT QNQDAQILTH QIMYVPPGGP VPDKVDSYVW Q TSTNPSVF WTEGNAPPRM SIPFLSIGNA YSNFYDGWSE FSRNGVYGIN TLNNMGTLYA RHVNAGSTGP IKSTIRIYFK PK HVKAWIP RPPRLCQYEK AKNVNFQPSG VTTTRQSITT MTNTGAF UniProtKB: Genome polyprotein |
-分子 #2: Capsid protein VP2
| 分子 | 名称: Capsid protein VP2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO / EC番号:  ピコルナイン2A ピコルナイン2A |
|---|---|
| 由来(天然) | 生物種:   Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス)株: Nancy |
| 分子量 | 理論値: 28.836502 KDa |
| 配列 | 文字列: SPTVEECGYS DRARSITLGN STITTQECAN VVVGYGVWPD YLKDSEATAE DQPTQPDVAT CRFYTLDSVQ WQKTSPGWWW KLPDALSNL GLFGQNMQYH YLGRTGYTVH VQCNASKFHQ GCLLVVCVPE AEMGCATLDN TPSSAELLGG DTAKEFADKP V ASGSNKLV ...文字列: SPTVEECGYS DRARSITLGN STITTQECAN VVVGYGVWPD YLKDSEATAE DQPTQPDVAT CRFYTLDSVQ WQKTSPGWWW KLPDALSNL GLFGQNMQYH YLGRTGYTVH VQCNASKFHQ GCLLVVCVPE AEMGCATLDN TPSSAELLGG DTAKEFADKP V ASGSNKLV QRVVYNAGMG VGVGNLTIFP HQWINLRTNN SATIVMPYTN SVPMDNMFRH NNVTLMVIPF VPLDYCPGST TY VPITVTI APMCAEYNGL RLAGHQ UniProtKB: Genome polyprotein |
-分子 #3: Capsid protein VP3
| 分子 | 名称: Capsid protein VP3 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO / EC番号:  ピコルナイン2A ピコルナイン2A |
|---|---|
| 由来(天然) | 生物種:   Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス)株: Nancy |
| 分子量 | 理論値: 26.195727 KDa |
| 配列 | 文字列: GLPTMNTPGS CQFLTSDDFQ SPSAMPQYDV TPEMRIPGEV KNLMEIAEVD SVVPVQNVGE KVNSMEAYQI PVRSNEGSGT QVFGFPLQP GYSSVFSRTL LGEILNYYTH WSGSIKLTFM FCGSAMATGK FLLAYSPPGA GAPTKRVDAM LGTHVIWDVG L QSSCVLCI ...文字列: GLPTMNTPGS CQFLTSDDFQ SPSAMPQYDV TPEMRIPGEV KNLMEIAEVD SVVPVQNVGE KVNSMEAYQI PVRSNEGSGT QVFGFPLQP GYSSVFSRTL LGEILNYYTH WSGSIKLTFM FCGSAMATGK FLLAYSPPGA GAPTKRVDAM LGTHVIWDVG L QSSCVLCI PWISQTHYRF VASDEYTAGG FITCWYQTNI VVPADAQSSC YIMCFVSACN DFSVRLLKDT PFISQQNFFQ UniProtKB: Genome polyprotein |
-分子 #4: Capsid protein VP4
| 分子 | 名称: Capsid protein VP4 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO / EC番号:  ピコルナイン2A ピコルナイン2A |
|---|---|
| 由来(天然) | 生物種:   Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス) Coxsackievirus B3 (strain Nancy) (コクサッキーウイルス)株: Nancy |
| 分子量 | 理論値: 7.580377 KDa |
| 配列 | 文字列: MGAQVSTQKT GAHETRLNAS GNSIIHYTNI NYYKDAASNS ANRQDFTQDP GKFTEPVKDI MIKSLPALN UniProtKB: Genome polyprotein |
-分子 #5: 4-[[4-[1,3-bis(oxidanylidene)isoindol-2-yl]phenyl]sulfonylamino]b...
| 分子 | 名称: 4-[[4-[1,3-bis(oxidanylidene)isoindol-2-yl]phenyl]sulfonylamino]benzoic acid タイプ: ligand / ID: 5 / コピー数: 1 / 式: FHK |
|---|---|
| 分子量 | 理論値: 422.411 Da |
| Chemical component information | 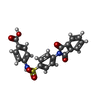 ChemComp-FHK: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 凍結 | 凍結剤: ETHANE / 装置: HOMEMADE PLUNGER | |||||||||
| 詳細 | Inhibitor was added at 2500:1 molar ratio to purified CVB3 and incubated for 1h at 37C |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm Bright-field microscopy / Cs: 2.7 mm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 47.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-6gzv: |
 ムービー
ムービー コントローラー
コントローラー












 Z
Z Y
Y X
X