[English] 日本語
 Yorodumi
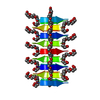
Yorodumi- PDB-7luz: GQTVTK segment from the Nucleoprotein of SARS-CoV-2, residues 243-248 -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7luz | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | GQTVTK segment from the Nucleoprotein of SARS-CoV-2, residues 243-248 | ||||||||||||
 Components Components | Nucleoprotein GQTVTK | ||||||||||||
 Keywords Keywords | PROTEIN FIBRIL /  amyloid fibril amyloid fibril | ||||||||||||
| Function / homology |  Function and homology information Function and homology informationcytoplasmic capsid assembly / viral RNA genome packaging / response to host immune response / negative regulation of interferon-beta production / Maturation of nucleoprotein / positive regulation of NLRP3 inflammasome complex assembly / intracellular non-membrane-bounded organelle / MHC class I protein binding / CD28 dependent PI3K/Akt signaling / SARS-CoV-2 targets host intracellular signalling and regulatory pathways ...cytoplasmic capsid assembly / viral RNA genome packaging / response to host immune response / negative regulation of interferon-beta production / Maturation of nucleoprotein / positive regulation of NLRP3 inflammasome complex assembly / intracellular non-membrane-bounded organelle / MHC class I protein binding / CD28 dependent PI3K/Akt signaling / SARS-CoV-2 targets host intracellular signalling and regulatory pathways / RNA stem-loop binding / protein sequestering activity / VEGFR2 mediated vascular permeability / molecular condensate scaffold activity / TAK1-dependent IKK and NF-kappa-B activation / NOD1/2 Signaling Pathway / DDX58/IFIH1-mediated induction of interferon-alpha/beta / MHC class I protein complex / Interleukin-1 signaling /  viral capsid / Interferon alpha/beta signaling / PIP3 activates AKT signaling / Transcription of SARS-CoV-2 sgRNAs / host cell endoplasmic reticulum-Golgi intermediate compartment / host cell Golgi apparatus / viral nucleocapsid / Translation of Structural Proteins / Virion Assembly and Release / host extracellular space / Induction of Cell-Cell Fusion / Attachment and Entry / host cell perinuclear region of cytoplasm / viral capsid / Interferon alpha/beta signaling / PIP3 activates AKT signaling / Transcription of SARS-CoV-2 sgRNAs / host cell endoplasmic reticulum-Golgi intermediate compartment / host cell Golgi apparatus / viral nucleocapsid / Translation of Structural Proteins / Virion Assembly and Release / host extracellular space / Induction of Cell-Cell Fusion / Attachment and Entry / host cell perinuclear region of cytoplasm /  ribonucleoprotein complex / SARS-CoV-2 activates/modulates innate and adaptive immune responses / protein homodimerization activity / ribonucleoprotein complex / SARS-CoV-2 activates/modulates innate and adaptive immune responses / protein homodimerization activity /  RNA binding / extracellular region / identical protein binding / RNA binding / extracellular region / identical protein binding /  cytoplasm cytoplasmSimilarity search - Function | ||||||||||||
| Biological species |   Severe acute respiratory syndrome coronavirus 2 Severe acute respiratory syndrome coronavirus 2 | ||||||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / AB INITIO PHASING / Resolution: 1.101 Å SYNCHROTRON / AB INITIO PHASING / Resolution: 1.101 Å | ||||||||||||
| Model details | Amyloid Fibril | ||||||||||||
 Authors Authors | Balbirnie, M. / Sawaya, M.R. / Eisenberg, D.S. / Cascio, D. | ||||||||||||
| Funding support |  United States, 3items United States, 3items
| ||||||||||||
 Citation Citation |  Journal: Biorxiv / Year: 2021 Journal: Biorxiv / Year: 2021Title: Inhibition of amyloid formation of the Nucleoprotein of SARS-CoV-2. Authors: Tayeb-Fligelman, E. / Cheng, X. / Tai, C. / Bowler, J.T. / Griner, S. / Sawaya, M.R. / Seidler, P.M. / Jiang, Y.X. / Lu, J. / Rosenberg, G.M. / Salwinski, L. / Abskharon, R. / Zee, C.T. / ...Authors: Tayeb-Fligelman, E. / Cheng, X. / Tai, C. / Bowler, J.T. / Griner, S. / Sawaya, M.R. / Seidler, P.M. / Jiang, Y.X. / Lu, J. / Rosenberg, G.M. / Salwinski, L. / Abskharon, R. / Zee, C.T. / Hou, K. / Li, Y. / Boyer, D.R. / Murray, K.A. / Falcon, G. / Anderson, D.H. / Cascio, D. / Saelices, L. / Damoiseaux, R. / Guo, F. / Eisenberg, D.S. | ||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7luz.cif.gz 7luz.cif.gz | 14.8 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7luz.ent.gz pdb7luz.ent.gz | 7.9 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7luz.json.gz 7luz.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/lu/7luz https://data.pdbj.org/pub/pdb/validation_reports/lu/7luz ftp://data.pdbj.org/pub/pdb/validation_reports/lu/7luz ftp://data.pdbj.org/pub/pdb/validation_reports/lu/7luz | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein/peptide | Mass: 633.714 Da / Num. of mol.: 1 / Source method: obtained synthetically Source: (synth.)   Severe acute respiratory syndrome coronavirus 2 Severe acute respiratory syndrome coronavirus 2References: UniProt: P0DTC9 |
|---|---|
| #2: Water | ChemComp-HOH /  Water Water |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 1.69 Å3/Da / Density % sol: 27.14 % |
|---|---|
Crystal grow | Temperature: 298 K / Method: vapor diffusion, hanging drop / pH: 7.5 / Details: 2M Ammonium Sulfate, HEPES, pH 7.5, PEG 400 |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 24-ID-E / Wavelength: 0.9792 Å / Beamline: 24-ID-E / Wavelength: 0.9792 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: DECTRIS EIGER X 16M / Detector: PIXEL / Date: Jun 20, 2020 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Monochromator: Si (111) / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength : 0.9792 Å / Relative weight: 1 : 0.9792 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.1→22.874 Å / Num. obs: 1726 / % possible obs: 87.1 % / Redundancy: 2.71 % / Biso Wilson estimate: 11.978 Å2 / CC1/2: 0.995 / Rmerge(I) obs: 0.085 / Rrim(I) all: 0.105 / Χ2: 0.884 / Net I/σ(I): 6.02 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : AB INITIO PHASING / Resolution: 1.101→22.874 Å / Cor.coef. Fo:Fc: 0.987 / Cor.coef. Fo:Fc free: 0.984 / SU B: 1.392 / SU ML: 0.026 / Cross valid method: THROUGHOUT / ESU R: 0.034 / ESU R Free: 0.034 : AB INITIO PHASING / Resolution: 1.101→22.874 Å / Cor.coef. Fo:Fc: 0.987 / Cor.coef. Fo:Fc free: 0.984 / SU B: 1.392 / SU ML: 0.026 / Cross valid method: THROUGHOUT / ESU R: 0.034 / ESU R Free: 0.034 Details: Hydrogens have been added in their riding positions
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.2 Å / Solvent model: MASK BULK SOLVENT | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 10.078 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.101→22.874 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 20
|
 Movie
Movie Controller
Controller












 PDBj
PDBj





