[English] 日本語
 Yorodumi
Yorodumi- PDB-4zxi: Crystal Structure of holo-AB3403 a four domain nonribosomal pepti... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4zxi | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Crystal Structure of holo-AB3403 a four domain nonribosomal peptide synthetase bound to AMP and Glycine | |||||||||
 Components Components | Tyrocidine synthetase 3 | |||||||||
 Keywords Keywords |  BIOSYNTHETIC PROTEIN / BIOSYNTHETIC PROTEIN /  Nonribosomal peptide synthetase / NRPS / Nonribosomal peptide synthetase / NRPS /  Condensation / Condensation /  Adenylation / PCP / Adenylation / PCP /  Thioesterase / Thioesterase /  phosphopantetheine phosphopantetheine | |||||||||
| Function / homology |  Function and homology information Function and homology informationamide biosynthetic process / organonitrogen compound biosynthetic process / secondary metabolite biosynthetic process / carboxylic acid metabolic process /  phosphopantetheine binding / phosphopantetheine binding /  catalytic activity / catalytic activity /  nucleotide binding nucleotide bindingSimilarity search - Function | |||||||||
| Biological species |   Acinetobacter baumannii (bacteria) Acinetobacter baumannii (bacteria) | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 2.9 Å SAD / Resolution: 2.9 Å | |||||||||
 Authors Authors | Drake, E.J. / Miller, B.R. / Allen, C.L. / Gulick, A.M. | |||||||||
| Funding support |  United States, 2items United States, 2items
| |||||||||
 Citation Citation |  Journal: Nature / Year: 2016 Journal: Nature / Year: 2016Title: Structures of two distinct conformations of holo-non-ribosomal peptide synthetases. Authors: Drake, E.J. / Miller, B.R. / Shi, C. / Tarrasch, J.T. / Sundlov, J.A. / Allen, C.L. / Skiniotis, G. / Aldrich, C.C. / Gulick, A.M. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4zxi.cif.gz 4zxi.cif.gz | 521.8 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4zxi.ent.gz pdb4zxi.ent.gz | 436.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4zxi.json.gz 4zxi.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/zx/4zxi https://data.pdbj.org/pub/pdb/validation_reports/zx/4zxi ftp://data.pdbj.org/pub/pdb/validation_reports/zx/4zxi ftp://data.pdbj.org/pub/pdb/validation_reports/zx/4zxi | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 147665.891 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Acinetobacter baumannii (strain AB307-0294) (bacteria) Acinetobacter baumannii (strain AB307-0294) (bacteria)Strain: AB307-0294 / Gene: ABBFA_003403 / Plasmid: pET15b / Production host:   Escherichia coli (E. coli) / Strain (production host): BL21(DE3) / References: UniProt: B7H2D0, UniProt: A0A0X1KH98*PLUS Escherichia coli (E. coli) / Strain (production host): BL21(DE3) / References: UniProt: B7H2D0, UniProt: A0A0X1KH98*PLUS |
|---|
-Non-polymers , 7 types, 22 molecules 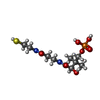











| #2: Chemical | ChemComp-PNS /  Phosphopantetheine Phosphopantetheine |
|---|---|
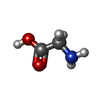
| #3: Chemical | ChemComp-GLY /  Glycine Glycine |
| #4: Chemical | ChemComp-AMP /  Adenosine monophosphate Adenosine monophosphate |
| #5: Chemical | ChemComp-XP4 / |
| #6: Chemical | ChemComp-NI /  Nickel Nickel |
| #7: Chemical | ChemComp-MG / |
| #8: Water | ChemComp-HOH /  Water Water |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.9 Å3/Da / Density % sol: 68.48 % |
|---|---|
Crystal grow | Temperature: 287.15 K / Method: vapor diffusion, hanging drop / pH: 8 Details: 0.75-0.95 M potassium citrate, 0.01-0.025 M glycine, 0.05 M BTP |
-Data collection
| Diffraction | Mean temperature: 113.15 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 23-ID-B / Wavelength: 1.0332 Å / Beamline: 23-ID-B / Wavelength: 1.0332 Å |
| Detector | Type: MARMOSAIC 300 mm CCD / Detector: CCD / Date: Mar 14, 2015 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength : 1.0332 Å / Relative weight: 1 : 1.0332 Å / Relative weight: 1 |
| Reflection | Resolution: 2.9→45.03 Å / Num. obs: 52900 / % possible obs: 99.99 % / Redundancy: 1.9 % / Rmerge(I) obs: 0.054 / Net I/σ(I): 8.82 |
| Reflection shell | Resolution: 2.9→3 Å / Redundancy: 2 % / Rmerge(I) obs: 0.336 / Mean I/σ(I) obs: 2.25 / % possible all: 100 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  SAD / Resolution: 2.9→45.03 Å / SU ML: 0.35 / Cross valid method: FREE R-VALUE / σ(F): 0.01 / Phase error: 23.01 / Stereochemistry target values: ML SAD / Resolution: 2.9→45.03 Å / SU ML: 0.35 / Cross valid method: FREE R-VALUE / σ(F): 0.01 / Phase error: 23.01 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 141.73 Å2 / Biso mean: 53.6487 Å2 / Biso min: 17.09 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 2.9→45.03 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 21 / % reflection obs: 100 %
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj
















