[English] 日本語
 Yorodumi
Yorodumi- PDB-4dx7: Transport of drugs by the multidrug transporter AcrB involves an ... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4dx7 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Transport of drugs by the multidrug transporter AcrB involves an access and a deep binding pocket that are separated by a switch-loop | ||||||
 Components Components |
| ||||||
 Keywords Keywords |  MEMBRANE PROTEIN / MEMBRANE PROTEIN /  TRANSPORT PROTEIN / TRANSPORT PROTEIN /  DARPin / DARPin /  multidrug efflux protein multidrug efflux protein | ||||||
| Function / homology |  Function and homology information Function and homology informationxenobiotic detoxification by transmembrane export across the cell outer membrane /  efflux pump complex / periplasmic side of plasma membrane / efflux transmembrane transporter activity / xenobiotic transmembrane transporter activity / outer membrane-bounded periplasmic space / efflux pump complex / periplasmic side of plasma membrane / efflux transmembrane transporter activity / xenobiotic transmembrane transporter activity / outer membrane-bounded periplasmic space /  membrane / identical protein binding / membrane / identical protein binding /  plasma membrane plasma membraneSimilarity search - Function | ||||||
| Biological species |   Escherichia coli (E. coli) Escherichia coli (E. coli)SYNTHETIC CONSTRUCT (others) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.253 Å MOLECULAR REPLACEMENT / Resolution: 2.253 Å | ||||||
 Authors Authors | Eicher, T. / Cha, H. / Seeger, M.A. / Brandstaetter, L. / El-Delik, J. / Bohnert, J.A. / Kern, W.V. / Verrey, F. / Gruetter, M.G. / Diederichs, K. / Pos, K.M. | ||||||
 Citation Citation |  Journal: Proc.Natl.Acad.Sci.USA / Year: 2012 Journal: Proc.Natl.Acad.Sci.USA / Year: 2012Title: Transport of drugs by the multidrug transporter AcrB involves an access and a deep binding pocket that are separated by a switch-loop. Authors: Eicher, T. / Cha, H.J. / Seeger, M.A. / Brandstatter, L. / El-Delik, J. / Bohnert, J.A. / Kern, W.V. / Verrey, F. / Grutter, M.G. / Diederichs, K. / Pos, K.M. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4dx7.cif.gz 4dx7.cif.gz | 1.4 MB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4dx7.ent.gz pdb4dx7.ent.gz | 1.1 MB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4dx7.json.gz 4dx7.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/dx/4dx7 https://data.pdbj.org/pub/pdb/validation_reports/dx/4dx7 ftp://data.pdbj.org/pub/pdb/validation_reports/dx/4dx7 ftp://data.pdbj.org/pub/pdb/validation_reports/dx/4dx7 | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 2 types, 5 molecules ABCDE
| #1: Protein | Mass: 114736.289 Da / Num. of mol.: 3 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Escherichia coli (E. coli) / Strain: K12 / Gene: acrB, acrE, b0462, JW0451 / Plasmid: pET24 / Production host: Escherichia coli (E. coli) / Strain: K12 / Gene: acrB, acrE, b0462, JW0451 / Plasmid: pET24 / Production host:   Escherichia coli (E. coli) / Strain (production host): C43(DE3) / References: UniProt: P31224 Escherichia coli (E. coli) / Strain (production host): C43(DE3) / References: UniProt: P31224#2: Protein |  Mass: 18317.566 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.) SYNTHETIC CONSTRUCT (others) / Plasmid: PQE30 / Production host:   Escherichia coli (E. coli) / Strain (production host): Xl1blue Escherichia coli (E. coli) / Strain (production host): Xl1blue |
|---|
-Sugars , 2 types, 8 molecules 
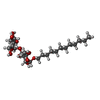

| #3: Sugar | ChemComp-LMT / #7: Sugar | ChemComp-LMU / | |
|---|
-Non-polymers , 6 types, 1716 molecules 
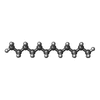
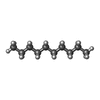

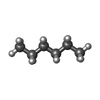






| #4: Chemical |  Doxorubicin Doxorubicin#5: Chemical | ChemComp-D12 /  Dodecane Dodecane#6: Chemical | ChemComp-D10 /  Decane Decane#8: Chemical |  Glycerol Glycerol#9: Chemical |  Hexane Hexane#10: Water | ChemComp-HOH / |  Water Water |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.84 Å3/Da / Density % sol: 68.01 % |
|---|---|
Crystal grow | Temperature: 290 K / Method: vapor diffusion, hanging drop / pH: 6.5 Details: 0.025M ADA, pH 6.5, 0.2M ammonium sulfate, 7.66% PEG 4000, 8.8% glycerol, 0.004M doxorubicin, VAPOR DIFFUSION, HANGING DROP, temperature 290K |
-Data collection
| Diffraction | Mean temperature: 100 K | ||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06SA / Wavelength: 1 Å / Beamline: X06SA / Wavelength: 1 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: MARRESEARCH / Detector: CCD / Date: Apr 20, 2007 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength : 1 Å / Relative weight: 1 : 1 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 2.25→49.153 Å / Num. all: 274592 / Num. obs: 274585 / % possible obs: 99.5 % / Observed criterion σ(I): -3 / Rmerge(I) obs: 0.095 / Net I/σ(I): 14.94 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  MOLECULAR REPLACEMENT / Resolution: 2.253→49.093 Å / Occupancy max: 1 / Occupancy min: 1 / SU ML: 0.33 / σ(F): 1.99 / Phase error: 22.28 / Stereochemistry target values: ML MOLECULAR REPLACEMENT / Resolution: 2.253→49.093 Å / Occupancy max: 1 / Occupancy min: 1 / SU ML: 0.33 / σ(F): 1.99 / Phase error: 22.28 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.73 Å / VDW probe radii: 1 Å / Solvent model: FLAT BULK SOLVENT MODEL / Bsol: 54.01 Å2 / ksol: 0.32 e/Å3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.253→49.093 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Origin x: 40.481 Å / Origin y: -31.4143 Å / Origin z: -30.5952 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group | Selection details: all |
 Movie
Movie Controller
Controller














 PDBj
PDBj







