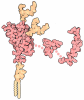
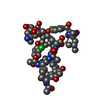
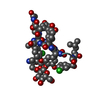
登録情報 データベース : PDB / ID : 1ze9タイトル Zinc-binding domain of Alzheimer's disease amyloid beta-peptide complexed with a zinc (II) cation 16-mer from Alzheimer's disease amyloid Protein キーワード / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 手法 / データ登録者 Zirah, S. / Kozin, S.A. / Mazur, A.K. / Blond, A. / Cheminant, M. / Segalas-Milazzo, I. / Debey, P. / Rebuffat, S. ジャーナル : J.Biol.Chem. / 年 : 2006タイトル : Structural changes of region 1-16 of the Alzheimer disease amyloid beta-peptide upon zinc binding and in vitro aging.著者 : Zirah, S. / Kozin, S.A. / Mazur, A.K. / Blond, A. / Cheminant, M. / Segalas-Milazzo, I. / Debey, P. / Rebuffat, S. 履歴 登録 2005年4月18日 登録サイト / 処理サイト 改定 1.0 2005年5月3日 Provider / タイプ 改定 1.1 2008年4月30日 Group 改定 1.2 2011年7月13日 Group 改定 1.3 2013年10月9日 Group
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 regulation of Wnt signaling pathway / mating behavior /
regulation of Wnt signaling pathway / mating behavior /  繊毛 / Lysosome Vesicle Biogenesis /
繊毛 / Lysosome Vesicle Biogenesis /  PTB domain binding / Golgi-associated vesicle / positive regulation of amyloid fibril formation / neuron remodeling / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / : / Deregulated CDK5 triggers multiple neurodegenerative pathways in Alzheimer's disease models / presynaptic active zone / nuclear envelope lumen / modulation of excitatory postsynaptic potential / suckling behavior / COPII-coated ER to Golgi transport vesicle / dendrite development /
PTB domain binding / Golgi-associated vesicle / positive regulation of amyloid fibril formation / neuron remodeling / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / : / Deregulated CDK5 triggers multiple neurodegenerative pathways in Alzheimer's disease models / presynaptic active zone / nuclear envelope lumen / modulation of excitatory postsynaptic potential / suckling behavior / COPII-coated ER to Golgi transport vesicle / dendrite development /  小胞体 /
小胞体 /  regulation of NMDA receptor activity / TRAF6 mediated NF-kB activation / Advanced glycosylation endproduct receptor signaling / neuromuscular process controlling balance / regulation of presynapse assembly / The NLRP3 inflammasome / intracellular copper ion homeostasis / transition metal ion binding / regulation of multicellular organism growth / negative regulation of long-term synaptic potentiation / negative regulation of neuron differentiation / ECM proteoglycans / spindle midzone / positive regulation of T cell migration /
regulation of NMDA receptor activity / TRAF6 mediated NF-kB activation / Advanced glycosylation endproduct receptor signaling / neuromuscular process controlling balance / regulation of presynapse assembly / The NLRP3 inflammasome / intracellular copper ion homeostasis / transition metal ion binding / regulation of multicellular organism growth / negative regulation of long-term synaptic potentiation / negative regulation of neuron differentiation / ECM proteoglycans / spindle midzone / positive regulation of T cell migration /  Purinergic signaling in leishmaniasis infection / positive regulation of calcium-mediated signaling / forebrain development / regulation of peptidyl-tyrosine phosphorylation / positive regulation of chemokine production /
Purinergic signaling in leishmaniasis infection / positive regulation of calcium-mediated signaling / forebrain development / regulation of peptidyl-tyrosine phosphorylation / positive regulation of chemokine production /  クラスリン /
クラスリン /  Notchシグナリング / positive regulation of G2/M transition of mitotic cell cycle / ionotropic glutamate receptor signaling pathway / positive regulation of protein metabolic process / neuron projection maintenance / cholesterol metabolic process / extracellular matrix organization / positive regulation of glycolytic process / positive regulation of mitotic cell cycle / response to interleukin-1 /
Notchシグナリング / positive regulation of G2/M transition of mitotic cell cycle / ionotropic glutamate receptor signaling pathway / positive regulation of protein metabolic process / neuron projection maintenance / cholesterol metabolic process / extracellular matrix organization / positive regulation of glycolytic process / positive regulation of mitotic cell cycle / response to interleukin-1 /  軸索誘導 / adult locomotory behavior / trans-Golgi network membrane / dendritic shaft / locomotory behavior / platelet alpha granule lumen / positive regulation of peptidyl-threonine phosphorylation /
軸索誘導 / adult locomotory behavior / trans-Golgi network membrane / dendritic shaft / locomotory behavior / platelet alpha granule lumen / positive regulation of peptidyl-threonine phosphorylation /  学習 /
学習 /  central nervous system development / positive regulation of interleukin-1 beta production / positive regulation of long-term synaptic potentiation / astrocyte activation / endosome lumen / synapse organization /
central nervous system development / positive regulation of interleukin-1 beta production / positive regulation of long-term synaptic potentiation / astrocyte activation / endosome lumen / synapse organization /  Post-translational protein phosphorylation / regulation of long-term neuronal synaptic plasticity / positive regulation of JNK cascade / microglial cell activation / TAK1-dependent IKK and NF-kappa-B activation /
Post-translational protein phosphorylation / regulation of long-term neuronal synaptic plasticity / positive regulation of JNK cascade / microglial cell activation / TAK1-dependent IKK and NF-kappa-B activation /  visual learning /
visual learning /  neuromuscular junction / serine-type endopeptidase inhibitor activity / recycling endosome /
neuromuscular junction / serine-type endopeptidase inhibitor activity / recycling endosome /  認識 / positive regulation of inflammatory response / Golgi lumen / neuron cellular homeostasis /
認識 / positive regulation of inflammatory response / Golgi lumen / neuron cellular homeostasis /  エンドサイトーシス / positive regulation of interleukin-6 production / positive regulation of non-canonical NF-kappaB signal transduction / cellular response to amyloid-beta / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / neuron projection development / positive regulation of DNA-binding transcription factor activity / G2/M transition of mitotic cell cycle / cell-cell junction /
エンドサイトーシス / positive regulation of interleukin-6 production / positive regulation of non-canonical NF-kappaB signal transduction / cellular response to amyloid-beta / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / neuron projection development / positive regulation of DNA-binding transcription factor activity / G2/M transition of mitotic cell cycle / cell-cell junction /  シナプス小胞 / positive regulation of tumor necrosis factor production /
シナプス小胞 / positive regulation of tumor necrosis factor production /  regulation of translation
regulation of translation 溶液NMR /
溶液NMR /  simulated annealing
simulated annealing  データ登録者
データ登録者 引用
引用 ジャーナル: J.Biol.Chem. / 年: 2006
ジャーナル: J.Biol.Chem. / 年: 2006 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1ze9.cif.gz
1ze9.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1ze9.ent.gz
pdb1ze9.ent.gz PDB形式
PDB形式 1ze9.json.gz
1ze9.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ze/1ze9
https://data.pdbj.org/pub/pdb/validation_reports/ze/1ze9 ftp://data.pdbj.org/pub/pdb/validation_reports/ze/1ze9
ftp://data.pdbj.org/pub/pdb/validation_reports/ze/1ze9 リンク
リンク 集合体
集合体
 要素
要素 溶液NMR
溶液NMR 試料調製
試料調製 : DMX / 磁場強度: 600 MHz
: DMX / 磁場強度: 600 MHz 解析
解析 simulated annealing / ソフトェア番号: 1
simulated annealing / ソフトェア番号: 1  ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj