登録情報 データベース : PDB / ID : 1k5wタイトル THREE-DIMENSIONAL STRUCTURE OF THE SYNAPTOTAGMIN 1 C2B-DOMAIN: SYNAPTOTAGMIN 1 AS A PHOSPHOLIPID BINDING MACHINE Synaptotagmin I キーワード / / / / / / / / / 機能・相同性 生物種 Rattus norvegicus (ドブネズミ)手法 / データ登録者 Fernandez, I. / Arac, D. / Ubach, J. / Gerber, S.H. / Shin, O. / Gao, Y. / Anderson, R.G.W. / Sudhof, T.C. / Rizo, J. ジャーナル : Neuron / 年 : 2001タイトル : Three-dimensional structure of the synaptotagmin 1 C2B-domain: synaptotagmin 1 as a phospholipid binding machine.著者 : Fernandez, I. / Arac, D. / Ubach, J. / Gerber, S.H. / Shin, O. / Gao, Y. / Anderson, R.G. / Sudhof, T.C. / Rizo, J. 履歴 登録 2001年10月12日 登録サイト / 処理サイト 改定 1.0 2002年1月23日 Provider / タイプ 改定 1.1 2008年4月27日 Group 改定 1.2 2011年7月13日 Group 改定 1.3 2022年2月23日 Group / Database references / Derived calculationsカテゴリ database_2 / pdbx_nmr_software ... database_2 / pdbx_nmr_software / pdbx_struct_assembly / pdbx_struct_conn_angle / pdbx_struct_oper_list / struct_conn / struct_site Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_nmr_software.name / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id 改定 1.4 2024年5月22日 Group / カテゴリ / chem_comp_bond
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
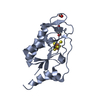
要素 Synaptotagmin
Synaptotagmin  キーワード
キーワード SYNAPTOTAGMIN I / CALCIUM-BINDING / PHOSPHOLIPID-BINDING /
SYNAPTOTAGMIN I / CALCIUM-BINDING / PHOSPHOLIPID-BINDING /  SYNAPSIS /
SYNAPSIS /  NEUROTRANSMITTER RELEASE (エキソサイトーシス) / SYNAPTIC VESICLE EXOCYTOSIS / ENDOCYTOSIS-EXOCYTOSIS COMPLEX
NEUROTRANSMITTER RELEASE (エキソサイトーシス) / SYNAPTIC VESICLE EXOCYTOSIS / ENDOCYTOSIS-EXOCYTOSIS COMPLEX 機能・相同性情報
機能・相同性情報 syntaxin-3 binding / calcium-dependent activation of synaptic vesicle fusion / regulation of regulated secretory pathway / calcium ion sensor activity / spontaneous neurotransmitter secretion / Glutamate Neurotransmitter Release Cycle / Norepinephrine Neurotransmitter Release Cycle ...synchronous neurotransmitter secretion / fast, calcium ion-dependent exocytosis of neurotransmitter / positive regulation of calcium ion-dependent exocytosis of neurotransmitter /
syntaxin-3 binding / calcium-dependent activation of synaptic vesicle fusion / regulation of regulated secretory pathway / calcium ion sensor activity / spontaneous neurotransmitter secretion / Glutamate Neurotransmitter Release Cycle / Norepinephrine Neurotransmitter Release Cycle ...synchronous neurotransmitter secretion / fast, calcium ion-dependent exocytosis of neurotransmitter / positive regulation of calcium ion-dependent exocytosis of neurotransmitter /  syntaxin-3 binding / calcium-dependent activation of synaptic vesicle fusion / regulation of regulated secretory pathway / calcium ion sensor activity / spontaneous neurotransmitter secretion / Glutamate Neurotransmitter Release Cycle / Norepinephrine Neurotransmitter Release Cycle / Acetylcholine Neurotransmitter Release Cycle / Serotonin Neurotransmitter Release Cycle / dense core granule / GABA synthesis, release, reuptake and degradation / positive regulation of vesicle fusion / chromaffin granule membrane / Dopamine Neurotransmitter Release Cycle / calcium ion-regulated exocytosis of neurotransmitter / positive regulation of calcium ion-dependent exocytosis / vesicle docking / regulation of calcium ion-dependent exocytosis / exocytic vesicle / positive regulation of dopamine secretion / protein heterooligomerization / Cargo recognition for clathrin-mediated endocytosis /
syntaxin-3 binding / calcium-dependent activation of synaptic vesicle fusion / regulation of regulated secretory pathway / calcium ion sensor activity / spontaneous neurotransmitter secretion / Glutamate Neurotransmitter Release Cycle / Norepinephrine Neurotransmitter Release Cycle / Acetylcholine Neurotransmitter Release Cycle / Serotonin Neurotransmitter Release Cycle / dense core granule / GABA synthesis, release, reuptake and degradation / positive regulation of vesicle fusion / chromaffin granule membrane / Dopamine Neurotransmitter Release Cycle / calcium ion-regulated exocytosis of neurotransmitter / positive regulation of calcium ion-dependent exocytosis / vesicle docking / regulation of calcium ion-dependent exocytosis / exocytic vesicle / positive regulation of dopamine secretion / protein heterooligomerization / Cargo recognition for clathrin-mediated endocytosis /  Clathrin-mediated endocytosis / calcium-ion regulated exocytosis / neurotransmitter secretion / positive regulation of dendrite extension / calcium-dependent phospholipid binding / neuron projection terminus /
Clathrin-mediated endocytosis / calcium-ion regulated exocytosis / neurotransmitter secretion / positive regulation of dendrite extension / calcium-dependent phospholipid binding / neuron projection terminus /  syntaxin-1 binding /
syntaxin-1 binding /  syntaxin binding / regulation of synaptic vesicle exocytosis /
syntaxin binding / regulation of synaptic vesicle exocytosis /  clathrin binding / low-density lipoprotein particle receptor binding /
clathrin binding / low-density lipoprotein particle receptor binding /  phosphatidylserine binding / regulation of dopamine secretion / synaptic vesicle exocytosis /
phosphatidylserine binding / regulation of dopamine secretion / synaptic vesicle exocytosis /  excitatory synapse / synaptic vesicle endocytosis / detection of calcium ion / positive regulation of synaptic transmission /
excitatory synapse / synaptic vesicle endocytosis / detection of calcium ion / positive regulation of synaptic transmission /  regulation of synaptic transmission, glutamatergic /
regulation of synaptic transmission, glutamatergic /  phosphatidylinositol-4,5-bisphosphate binding / cellular response to calcium ion / hippocampal mossy fiber to CA3 synapse /
phosphatidylinositol-4,5-bisphosphate binding / cellular response to calcium ion / hippocampal mossy fiber to CA3 synapse /  SNARE binding /
SNARE binding /  分泌 /
分泌 /  phospholipid binding /
phospholipid binding /  terminal bouton / synaptic vesicle membrane / response to calcium ion / calcium-dependent protein binding /
terminal bouton / synaptic vesicle membrane / response to calcium ion / calcium-dependent protein binding /  シナプス小胞 /
シナプス小胞 /  presynaptic membrane /
presynaptic membrane /  細胞分化 /
細胞分化 /  calmodulin binding / neuron projection / protein heterodimerization activity /
calmodulin binding / neuron projection / protein heterodimerization activity /  神経繊維 / glutamatergic synapse /
神経繊維 / glutamatergic synapse /  calcium ion binding /
calcium ion binding /  ゴルジ体 / identical protein binding /
ゴルジ体 / identical protein binding /  細胞膜 /
細胞膜 /  細胞質
細胞質
 Rattus norvegicus (ドブネズミ)
Rattus norvegicus (ドブネズミ) 溶液NMR / torsion angle dynamics
溶液NMR / torsion angle dynamics  データ登録者
データ登録者 引用
引用 ジャーナル: Neuron / 年: 2001
ジャーナル: Neuron / 年: 2001 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1k5w.cif.gz
1k5w.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1k5w.ent.gz
pdb1k5w.ent.gz PDB形式
PDB形式 1k5w.json.gz
1k5w.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/k5/1k5w
https://data.pdbj.org/pub/pdb/validation_reports/k5/1k5w ftp://data.pdbj.org/pub/pdb/validation_reports/k5/1k5w
ftp://data.pdbj.org/pub/pdb/validation_reports/k5/1k5w リンク
リンク 集合体
集合体
 要素
要素 Synaptotagmin / SytI / p65
Synaptotagmin / SytI / p65
 Rattus norvegicus (ドブネズミ) / 生物種 (発現宿主): Escherichia coli / 発現宿主:
Rattus norvegicus (ドブネズミ) / 生物種 (発現宿主): Escherichia coli / 発現宿主: 
 Escherichia coli BL21 (大腸菌) / 株 (発現宿主): BL21 / 参照: UniProt: P21707
Escherichia coli BL21 (大腸菌) / 株 (発現宿主): BL21 / 参照: UniProt: P21707 溶液NMR
溶液NMR 試料調製
試料調製
 解析
解析 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj






