+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Brain-derived 42-residue amyloid-beta fibril type A | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of epidermal growth factor-activated receptor activity / signaling receptor activator activity / cytosolic mRNA polyadenylation / collateral sprouting in absence of injury / microglia development / regulation of synapse structure or activity / Formyl peptide receptors bind formyl peptides and many other ligands /  regulation of Wnt signaling pathway / axo-dendritic transport / synaptic assembly at neuromuscular junction ...regulation of epidermal growth factor-activated receptor activity / signaling receptor activator activity / cytosolic mRNA polyadenylation / collateral sprouting in absence of injury / microglia development / regulation of synapse structure or activity / Formyl peptide receptors bind formyl peptides and many other ligands / regulation of Wnt signaling pathway / axo-dendritic transport / synaptic assembly at neuromuscular junction ...regulation of epidermal growth factor-activated receptor activity / signaling receptor activator activity / cytosolic mRNA polyadenylation / collateral sprouting in absence of injury / microglia development / regulation of synapse structure or activity / Formyl peptide receptors bind formyl peptides and many other ligands /  regulation of Wnt signaling pathway / axo-dendritic transport / synaptic assembly at neuromuscular junction / smooth endoplasmic reticulum calcium ion homeostasis / axon midline choice point recognition / astrocyte activation involved in immune response / regulation of spontaneous synaptic transmission / mating behavior / NMDA selective glutamate receptor signaling pathway / regulation of Wnt signaling pathway / axo-dendritic transport / synaptic assembly at neuromuscular junction / smooth endoplasmic reticulum calcium ion homeostasis / axon midline choice point recognition / astrocyte activation involved in immune response / regulation of spontaneous synaptic transmission / mating behavior / NMDA selective glutamate receptor signaling pathway /  繊毛 / Lysosome Vesicle Biogenesis / 繊毛 / Lysosome Vesicle Biogenesis /  PTB domain binding / Golgi-associated vesicle / positive regulation of amyloid fibril formation / neuron remodeling / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / protein serine/threonine kinase binding / Deregulated CDK5 triggers multiple neurodegenerative pathways in Alzheimer's disease models / : / nuclear envelope lumen / suckling behavior / presynaptic active zone / dendrite development / COPII-coated ER to Golgi transport vesicle / modulation of excitatory postsynaptic potential / TRAF6 mediated NF-kB activation / Advanced glycosylation endproduct receptor signaling / neuromuscular process controlling balance / The NLRP3 inflammasome / regulation of presynapse assembly / transition metal ion binding / regulation of multicellular organism growth / intracellular copper ion homeostasis / negative regulation of long-term synaptic potentiation / negative regulation of neuron differentiation / ECM proteoglycans / PTB domain binding / Golgi-associated vesicle / positive regulation of amyloid fibril formation / neuron remodeling / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / protein serine/threonine kinase binding / Deregulated CDK5 triggers multiple neurodegenerative pathways in Alzheimer's disease models / : / nuclear envelope lumen / suckling behavior / presynaptic active zone / dendrite development / COPII-coated ER to Golgi transport vesicle / modulation of excitatory postsynaptic potential / TRAF6 mediated NF-kB activation / Advanced glycosylation endproduct receptor signaling / neuromuscular process controlling balance / The NLRP3 inflammasome / regulation of presynapse assembly / transition metal ion binding / regulation of multicellular organism growth / intracellular copper ion homeostasis / negative regulation of long-term synaptic potentiation / negative regulation of neuron differentiation / ECM proteoglycans /  小胞体 / 小胞体 /  Mitochondrial protein degradation / positive regulation of T cell migration / spindle midzone / Mitochondrial protein degradation / positive regulation of T cell migration / spindle midzone /  Purinergic signaling in leishmaniasis infection / positive regulation of calcium-mediated signaling / Purinergic signaling in leishmaniasis infection / positive regulation of calcium-mediated signaling /  クラスリン / regulation of peptidyl-tyrosine phosphorylation / positive regulation of chemokine production / forebrain development / クラスリン / regulation of peptidyl-tyrosine phosphorylation / positive regulation of chemokine production / forebrain development /  Notchシグナリング / positive regulation of G2/M transition of mitotic cell cycle / neuron projection maintenance / positive regulation of protein metabolic process / ionotropic glutamate receptor signaling pathway / positive regulation of glycolytic process / cholesterol metabolic process / response to interleukin-1 / positive regulation of mitotic cell cycle / extracellular matrix organization / Notchシグナリング / positive regulation of G2/M transition of mitotic cell cycle / neuron projection maintenance / positive regulation of protein metabolic process / ionotropic glutamate receptor signaling pathway / positive regulation of glycolytic process / cholesterol metabolic process / response to interleukin-1 / positive regulation of mitotic cell cycle / extracellular matrix organization /  軸索誘導 / adult locomotory behavior / trans-Golgi network membrane / platelet alpha granule lumen / locomotory behavior / positive regulation of peptidyl-threonine phosphorylation / dendritic shaft / 軸索誘導 / adult locomotory behavior / trans-Golgi network membrane / platelet alpha granule lumen / locomotory behavior / positive regulation of peptidyl-threonine phosphorylation / dendritic shaft /  学習 / positive regulation of interleukin-1 beta production / 学習 / positive regulation of interleukin-1 beta production /  central nervous system development / positive regulation of long-term synaptic potentiation / endosome lumen / astrocyte activation / central nervous system development / positive regulation of long-term synaptic potentiation / endosome lumen / astrocyte activation /  Post-translational protein phosphorylation / positive regulation of JNK cascade / synapse organization / regulation of long-term neuronal synaptic plasticity / microglial cell activation / TAK1-dependent IKK and NF-kappa-B activation / Post-translational protein phosphorylation / positive regulation of JNK cascade / synapse organization / regulation of long-term neuronal synaptic plasticity / microglial cell activation / TAK1-dependent IKK and NF-kappa-B activation /  visual learning / serine-type endopeptidase inhibitor activity / visual learning / serine-type endopeptidase inhibitor activity /  neuromuscular junction / recycling endosome / neuromuscular junction / recycling endosome /  認識 / positive regulation of inflammatory response / Golgi lumen / neuron cellular homeostasis / 認識 / positive regulation of inflammatory response / Golgi lumen / neuron cellular homeostasis /  エンドサイトーシス / positive regulation of non-canonical NF-kappaB signal transduction / cellular response to amyloid-beta / positive regulation of interleukin-6 production / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / neuron projection development / G2/M transition of mitotic cell cycle / positive regulation of tumor necrosis factor production / cell-cell junction / エンドサイトーシス / positive regulation of non-canonical NF-kappaB signal transduction / cellular response to amyloid-beta / positive regulation of interleukin-6 production / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / neuron projection development / G2/M transition of mitotic cell cycle / positive regulation of tumor necrosis factor production / cell-cell junction /  シナプス小胞 シナプス小胞類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | らせん対称体再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.83 Å クライオ電子顕微鏡法 / 解像度: 2.83 Å | |||||||||
 データ登録者 データ登録者 | Tycko R / Lee M / Yau Y-M / Louis JM | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2023 ジャーナル: Proc Natl Acad Sci U S A / 年: 2023タイトル: Structures of brain-derived 42-residue amyloid-β fibril polymorphs with unusual molecular conformations and intermolecular interactions. 著者: Myungwoon Lee / Wai-Ming Yau / John M Louis / Robert Tycko /  要旨: Fibrils formed by the 42-residue amyloid-β peptide (Aβ42), a main component of amyloid deposits in Alzheimer's disease (AD), are known to be polymorphic, i.e., to contain multiple possible ...Fibrils formed by the 42-residue amyloid-β peptide (Aβ42), a main component of amyloid deposits in Alzheimer's disease (AD), are known to be polymorphic, i.e., to contain multiple possible molecular structures. Previous studies of Aβ42 fibrils, including fibrils prepared entirely in vitro or extracted from brain tissue and using solid-state NMR (ssNMR) or cryogenic electron microscopy (cryo-EM) methods, have found polymorphs with differences in amino acid sidechain orientations, lengths of structurally ordered segments, and contacts between cross-β subunit pairs within a single filament. Despite these differences, Aβ42 molecules adopt a common S-shaped conformation in all previously described high-resolution Aβ42 fibril structures. Here we report two cryo-EM-based structures of Aβ42 fibrils that are qualitatively different, in samples derived from AD brain tissue by seeded growth. In type A fibrils, residues 12 to 42 adopt a ν-shaped conformation, with both intra-subunit and intersubunit hydrophobic contacts to form a compact core. In type B fibrils, residues 2 to 42 adopt an υ-shaped conformation, with only intersubunit contacts and internal pores. Type A and type B fibrils have opposite helical handedness. Cryo-EM density maps and molecular dynamics simulations indicate intersubunit K16-A42 salt bridges in type B fibrils and partially occupied K28-A42 salt bridges in type A fibrils. The coexistence of two predominant polymorphs, with differences in N-terminal dynamics, is supported by ssNMR data, as is faithful propagation of structures from first-generation to second-generation brain-seeded Aβ42 fibril samples. These results demonstrate that Aβ42 fibrils can exhibit a greater range of structural variations than seen in previous studies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28740.map.gz emd_28740.map.gz | 437.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28740-v30.xml emd-28740-v30.xml emd-28740.xml emd-28740.xml | 16.4 KB 16.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_28740.png emd_28740.png | 77.4 KB | ||
| その他 |  emd_28740_half_map_1.map.gz emd_28740_half_map_1.map.gz emd_28740_half_map_2.map.gz emd_28740_half_map_2.map.gz | 381.1 MB 381.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28740 http://ftp.pdbj.org/pub/emdb/structures/EMD-28740 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28740 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28740 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8ezdMC  8ezeC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28740.map.gz / 形式: CCP4 / 大きさ: 476.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28740.map.gz / 形式: CCP4 / 大きさ: 476.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.86 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_28740_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
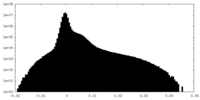
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_28740_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : amyloid-b 42 (Ab42) fibril
| 全体 | 名称: amyloid-b 42 (Ab42) fibril |
|---|---|
| 要素 |
|
-超分子 #1: amyloid-b 42 (Ab42) fibril
| 超分子 | 名称: amyloid-b 42 (Ab42) fibril / タイプ: complex / ID: 1 / キメラ: Yes / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 4514.10 kDa/nm |
-分子 #1: Beta-amyloid protein 42
| 分子 | 名称: Beta-amyloid protein 42 / タイプ: protein_or_peptide / ID: 1 / コピー数: 8 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 4.520087 KDa |
| 組換発現 | 生物種:   Escherichia coli BL21(DE3) (大腸菌) Escherichia coli BL21(DE3) (大腸菌) |
| 配列 | 文字列: DAEFRHDSGY EVHHQKLVFF AEDVGSNKGA IIGLMVGGVV IA |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 0.34 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 構成要素 - 濃度: 10.0 mM / 構成要素 - 名称: Sodium Phosphate / 詳細: 10mM Na-phosphate, 0.1% sodium azide |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 99 % / チャンバー内温度: 93 K / 装置: FEI VITROBOT MARK I 詳細: Preblot for 12-13 seconds and blot for 2.5-3.0 seconds before plunging. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 130000 Bright-field microscopy / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / デジタル化 - サイズ - 横: 11520 pixel / デジタル化 - サイズ - 縦: 8184 pixel / 撮影したグリッド数: 1 / 実像数: 3383 / 平均露光時間: 1.65 sec. / 平均電子線量: 44.65 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| Segment selection | 選択した数: 374821 / ソフトウェア - 名称: RELION (ver. 4.0.0) |
|---|---|
| 初期モデル | モデルのタイプ: NONE / 詳細: featureless cylinder |
| 最終 角度割当 | タイプ: NOT APPLICABLE / ソフトウェア - 名称: RELION (ver. 4.0.0) 詳細: 2.46 Angstrom helical rise and -179.09 degree helical twist |
| 最終 再構成 | 想定した対称性 - らせんパラメータ - Δz: 2.46 Å 想定した対称性 - らせんパラメータ - ΔΦ: -179.09 ° 想定した対称性 - らせんパラメータ - 軸対称性: C1 (非対称) 解像度のタイプ: BY AUTHOR / 解像度: 2.83 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 4.0.0) / 使用した粒子像数: 68481 |
| 詳細 | Gatan Imaging Filter (GIF) Quantum LS |
-原子モデル構築 1
| 詳細 | Manually generated model was fit into the density using PHENIX and UCSF Chimera. Further refinements were performed using Xplor-NIH. |
|---|---|
| 精密化 | プロトコル: OTHER |
| 得られたモデル |  PDB-8ezd: |
 ムービー
ムービー コントローラー
コントローラー



















 Z
Z Y
Y X
X