+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | membrane region of the Trypanosoma brucei mitochondrial ATP synthase dimer | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 キネトプラスト / ATP biosynthetic process / nuclear lumen / ciliary plasm / proton-transporting ATP synthase complex, coupling factor F(o) / mitochondrial proton-transporting ATP synthase complex / proton transmembrane transport / キネトプラスト / ATP biosynthetic process / nuclear lumen / ciliary plasm / proton-transporting ATP synthase complex, coupling factor F(o) / mitochondrial proton-transporting ATP synthase complex / proton transmembrane transport /  ミトコンドリア / ミトコンドリア /  ミトコンドリア内膜 / ミトコンドリア内膜 /  ミトコンドリア ... ミトコンドリア ... キネトプラスト / ATP biosynthetic process / nuclear lumen / ciliary plasm / proton-transporting ATP synthase complex, coupling factor F(o) / mitochondrial proton-transporting ATP synthase complex / proton transmembrane transport / キネトプラスト / ATP biosynthetic process / nuclear lumen / ciliary plasm / proton-transporting ATP synthase complex, coupling factor F(o) / mitochondrial proton-transporting ATP synthase complex / proton transmembrane transport /  ミトコンドリア / ミトコンドリア /  ミトコンドリア内膜 / ミトコンドリア内膜 /  ミトコンドリア / ミトコンドリア /  生体膜 / 生体膜 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Trypanosoma brucei brucei (ブルーストリパノソーマ) Trypanosoma brucei brucei (ブルーストリパノソーマ) | |||||||||
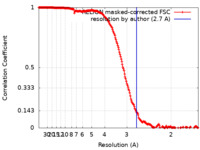
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.7 Å クライオ電子顕微鏡法 / 解像度: 2.7 Å | |||||||||
 データ登録者 データ登録者 | Muehleip A / Gahura O / Zikova A / Amunts A | |||||||||
| 資金援助 | European Union, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: An ancestral interaction module promotes oligomerization in divergent mitochondrial ATP synthases. 著者: Ondřej Gahura / Alexander Mühleip / Carolina Hierro-Yap / Brian Panicucci / Minal Jain / David Hollaus / Martina Slapničková / Alena Zíková / Alexey Amunts /   要旨: Mitochondrial ATP synthase forms stable dimers arranged into oligomeric assemblies that generate the inner-membrane curvature essential for efficient energy conversion. Here, we report cryo-EM ...Mitochondrial ATP synthase forms stable dimers arranged into oligomeric assemblies that generate the inner-membrane curvature essential for efficient energy conversion. Here, we report cryo-EM structures of the intact ATP synthase dimer from Trypanosoma brucei in ten different rotational states. The model consists of 25 subunits, including nine lineage-specific, as well as 36 lipids. The rotary mechanism is influenced by the divergent peripheral stalk, conferring a greater conformational flexibility. Proton transfer in the lumenal half-channel occurs via a chain of five ordered water molecules. The dimerization interface is formed by subunit-g that is critical for interactions but not for the catalytic activity. Although overall dimer architecture varies among eukaryotes, we find that subunit-g together with subunit-e form an ancestral oligomerization motif, which is shared between the trypanosomal and mammalian lineages. Therefore, our data defines the subunit-g/e module as a structural component determining ATP synthase oligomeric assemblies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15560.map.gz emd_15560.map.gz | 339.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15560-v30.xml emd-15560-v30.xml emd-15560.xml emd-15560.xml | 30 KB 30 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_15560_fsc.xml emd_15560_fsc.xml | 19.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_15560.png emd_15560.png | 97.8 KB | ||
| マスクデータ |  emd_15560_msk_1.map emd_15560_msk_1.map | 669.9 MB |  マスクマップ マスクマップ | |
| その他 |  emd_15560_half_map_1.map.gz emd_15560_half_map_1.map.gz emd_15560_half_map_2.map.gz emd_15560_half_map_2.map.gz | 540.6 MB 538.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15560 http://ftp.pdbj.org/pub/emdb/structures/EMD-15560 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15560 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15560 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8ap7MC  8ap6C  8ap8C  8ap9C  8apaC  8apbC  8apcC  8apdC  8apeC  8apfC  8apgC  8aphC  8apjC  8apkC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15560.map.gz / 形式: CCP4 / 大きさ: 669.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15560.map.gz / 形式: CCP4 / 大きさ: 669.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.83 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_15560_msk_1.map emd_15560_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_15560_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_15560_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : mitochondrial ATP synthase dimer from Trypanosoma brucei
+超分子 #1: mitochondrial ATP synthase dimer from Trypanosoma brucei
+分子 #1: ATP synthase subunit a
+分子 #2: subunit-8
+分子 #3: subunit-d
+分子 #4: ATPTB1
+分子 #5: subunit-f
+分子 #6: subunit-i/j
+分子 #7: ATPTB6
+分子 #8: subunit-k
+分子 #9: subunit-e
+分子 #10: subunit-g
+分子 #11: ATPTB11
+分子 #12: ATPTB12
+分子 #13: subunit-b
+分子 #14: ATPEG3
+分子 #15: ATPEG4
+分子 #16: CARDIOLIPIN
+分子 #17: DODECYL-BETA-D-MALTOSIDE
+分子 #18: 2-{[(4-O-alpha-D-glucopyranosyl-alpha-D-glucopyranosyl)oxy]methyl...
+分子 #19: 1,2-dioleoyl-sn-glycero-3-phosphoethanolamine
+分子 #20: 1,2-DIACYL-SN-GLYCERO-3-PHOSPHOCHOLINE
+分子 #21: water
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.2 µm / 最小 デフォーカス(公称値): 1.6 µm Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.2 µm / 最小 デフォーカス(公称値): 1.6 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 温度 | 最低: 70.0 K / 最高: 70.0 K |
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 検出モード: COUNTING / 平均電子線量: 33.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)