+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 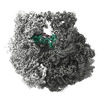 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
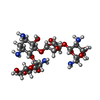
| タイトル | Composite 70S ribosome structure for "Atomistic simulations of the E. coli ribosome provide selection criteria for translationally active substrates | |||||||||
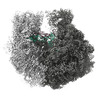
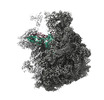
 マップデータ マップデータ | Composite 70S map from 50S- and 30S-focused refinements | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  ribosome (リボソーム) / ribosome (リボソーム) /  tRNA (転移RNA) / tRNA (転移RNA) /  e. coli (大腸菌) e. coli (大腸菌) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of cytoplasmic translational initiation / positive regulation of ribosome biogenesis / DnaA-L2 complex / negative regulation of translational initiation / translational initiation / negative regulation of DNA-templated DNA replication initiation /  ribosome assembly / mRNA regulatory element binding translation repressor activity / assembly of large subunit precursor of preribosome / cytosolic ribosome assembly ...negative regulation of cytoplasmic translational initiation / positive regulation of ribosome biogenesis / DnaA-L2 complex / negative regulation of translational initiation / translational initiation / negative regulation of DNA-templated DNA replication initiation / ribosome assembly / mRNA regulatory element binding translation repressor activity / assembly of large subunit precursor of preribosome / cytosolic ribosome assembly ...negative regulation of cytoplasmic translational initiation / positive regulation of ribosome biogenesis / DnaA-L2 complex / negative regulation of translational initiation / translational initiation / negative regulation of DNA-templated DNA replication initiation /  ribosome assembly / mRNA regulatory element binding translation repressor activity / assembly of large subunit precursor of preribosome / cytosolic ribosome assembly / transcription antitermination / ribosome assembly / mRNA regulatory element binding translation repressor activity / assembly of large subunit precursor of preribosome / cytosolic ribosome assembly / transcription antitermination /  regulation of cell growth / DNA-templated transcription termination / maintenance of translational fidelity / regulation of cell growth / DNA-templated transcription termination / maintenance of translational fidelity /  ribosomal large subunit assembly / mRNA 5'-UTR binding / ribosomal large subunit assembly / mRNA 5'-UTR binding /  ribosomal small subunit biogenesis / ribosomal small subunit biogenesis /  ribosomal small subunit assembly / small ribosomal subunit rRNA binding / large ribosomal subunit / ribosomal small subunit assembly / small ribosomal subunit rRNA binding / large ribosomal subunit /  ribosome binding / ribosome binding /  5S rRNA binding / large ribosomal subunit rRNA binding / small ribosomal subunit / cytosolic small ribosomal subunit / 5S rRNA binding / large ribosomal subunit rRNA binding / small ribosomal subunit / cytosolic small ribosomal subunit /  transferase activity / cytosolic large ribosomal subunit / cytoplasmic translation / transferase activity / cytosolic large ribosomal subunit / cytoplasmic translation /  tRNA binding / negative regulation of translation / tRNA binding / negative regulation of translation /  rRNA binding / rRNA binding /  リボソーム / structural constituent of ribosome / リボソーム / structural constituent of ribosome /  ribonucleoprotein complex / ribonucleoprotein complex /  翻訳 (生物学) / response to antibiotic / 翻訳 (生物学) / response to antibiotic /  mRNA binding / mRNA binding /  RNA binding / zinc ion binding / RNA binding / zinc ion binding /  生体膜 / 生体膜 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.1 Å クライオ電子顕微鏡法 / 解像度: 2.1 Å | |||||||||
 データ登録者 データ登録者 | Watson ZL / Cate JHD | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Chem / 年: 2023 ジャーナル: Nat Chem / 年: 2023タイトル: Atomistic simulations of the Escherichia coli ribosome provide selection criteria for translationally active substrates. 著者: Zoe L Watson / Isaac J Knudson / Fred R Ward / Scott J Miller / Jamie H D Cate / Alanna Schepartz / Ara M Abramyan /  要旨: As genetic code expansion advances beyond L-α-amino acids to backbone modifications and new polymerization chemistries, delineating what substrates the ribosome can accommodate remains a challenge. ...As genetic code expansion advances beyond L-α-amino acids to backbone modifications and new polymerization chemistries, delineating what substrates the ribosome can accommodate remains a challenge. The Escherichia coli ribosome tolerates non-L-α-amino acids in vitro, but few structural insights that explain how are available, and the boundary conditions for efficient bond formation are so far unknown. Here we determine a high-resolution cryogenic electron microscopy structure of the E. coli ribosome containing α-amino acid monomers and use metadynamics simulations to define energy surface minima and understand incorporation efficiencies. Reactive monomers across diverse structural classes favour a conformational space where the aminoacyl-tRNA nucleophile is <4 Å from the peptidyl-tRNA carbonyl with a Bürgi-Dunitz angle of 76-115°. Monomers with free energy minima that fall outside this conformational space do not react efficiently. This insight should accelerate the in vivo and in vitro ribosomal synthesis of sequence-defined, non-peptide heterooligomers. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28254.map.gz emd_28254.map.gz | 35.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28254-v30.xml emd-28254-v30.xml emd-28254.xml emd-28254.xml | 67.1 KB 67.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_28254.png emd_28254.png | 191 KB | ||
| Filedesc metadata |  emd-28254.cif.gz emd-28254.cif.gz | 14.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28254 http://ftp.pdbj.org/pub/emdb/structures/EMD-28254 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28254 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28254 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28254.map.gz / 形式: CCP4 / 大きさ: 361.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28254.map.gz / 形式: CCP4 / 大きさ: 361.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Composite 70S map from 50S- and 30S-focused refinements | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8296 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : 70S ribosome complex with mRNA, A- and P-site Met-NH-tRNAs
+超分子 #1: 70S ribosome complex with mRNA, A- and P-site Met-NH-tRNAs
+分子 #1: 23S rRNA
+分子 #2: 5S rRNA
+分子 #32: Met-NH-tRNA
+分子 #33: 16S rRNA
+分子 #54: mRNA
+分子 #3: 50S ribosomal protein L2
+分子 #4: 50S ribosomal protein L3
+分子 #5: 50S ribosomal protein L4
+分子 #6: 50S ribosomal protein L5
+分子 #7: 50S ribosomal protein L6
+分子 #8: 50S ribosomal protein L9
+分子 #9: 50S ribosomal protein L13
+分子 #10: 50S ribosomal protein L14
+分子 #11: 50S ribosomal protein L15
+分子 #12: 50S ribosomal protein L16
+分子 #13: 50S ribosomal protein L17
+分子 #14: 50S ribosomal protein L18
+分子 #15: 50S ribosomal protein L19
+分子 #16: 50S ribosomal protein L20
+分子 #17: Ribosomal protein L21
+分子 #18: 50S ribosomal protein L22
+分子 #19: 50S ribosomal protein L23
+分子 #20: 50S ribosomal protein L24
+分子 #21: 50S ribosomal protein L25
+分子 #22: 50S ribosomal protein L27
+分子 #23: 50S ribosomal protein L28
+分子 #24: 50S ribosomal protein L29
+分子 #25: 50S ribosomal protein L30
+分子 #26: 50S ribosomal protein L32
+分子 #27: 50S ribosomal protein L33
+分子 #28: 50S ribosomal protein L34
+分子 #29: 50S ribosomal protein L35
+分子 #30: 50S ribosomal protein L36
+分子 #31: 50S ribosomal protein L31
+分子 #34: 30S ribosomal protein S2
+分子 #35: 30S ribosomal protein S3
+分子 #36: 30S ribosomal protein S4
+分子 #37: 30S ribosomal protein S5
+分子 #38: 30S ribosomal protein S6
+分子 #39: 30S ribosomal protein S7
+分子 #40: 30S ribosomal protein S8
+分子 #41: 30S ribosomal protein S9
+分子 #42: 30S ribosomal protein S10
+分子 #43: 30S ribosomal protein S11
+分子 #44: 30S ribosomal protein S12
+分子 #45: 30S ribosomal protein S13
+分子 #46: 30S ribosomal protein S14
+分子 #47: 30S ribosomal protein S15
+分子 #48: 30S ribosomal protein S16
+分子 #49: 30S ribosomal protein S17
+分子 #50: 30S ribosomal protein S18
+分子 #51: 30S ribosomal protein S19
+分子 #52: 30S ribosomal protein S20
+分子 #53: 30S ribosomal protein S21
+分子 #55: MAGNESIUM ION
+分子 #56: SPERMIDINE
+分子 #57: SPERMINE
+分子 #58: POTASSIUM ION
+分子 #59: ZINC ION
+分子 #60: METHIONINE
+分子 #61: PAROMOMYCIN
+分子 #62: water
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 40.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.1 Å / 解像度の算出法: OTHER 詳細: This is a composite map from 50S- and 30S-focused maps 使用した粒子像数: 129455 |
 ムービー
ムービー コントローラー
コントローラー