[English] 日本語
 Yorodumi
Yorodumi- PDB-2xgx: Crystal structure of transcription factor NtcA from Synechococcus... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 2xgx | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of transcription factor NtcA from Synechococcus elongatus (mercury derivative) | ||||||
 Components Components | GLOBAL NITROGEN REGULATOR | ||||||
 Keywords Keywords |  TRANSCRIPTION / TRANSCRIPTION /  NITROGEN ASSIMILATION / CRP/FNR SUPERFAMILY / NITROGEN ASSIMILATION / CRP/FNR SUPERFAMILY /  CYANOBACTERIA / CYANOBACTERIA /  2-OXOGLUTARATE 2-OXOGLUTARATE | ||||||
| Function / homology |  Function and homology information Function and homology information | ||||||
| Biological species |   SYNECHOCOCCUS ELONGATUS (bacteria) SYNECHOCOCCUS ELONGATUS (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 2.85 Å SAD / Resolution: 2.85 Å | ||||||
 Authors Authors | Llacer, J.L. / Castells, M.A. / Rubio, V. | ||||||
 Citation Citation |  Journal: Proc.Natl.Acad.Sci.USA / Year: 2010 Journal: Proc.Natl.Acad.Sci.USA / Year: 2010Title: Structural Basis for the Regulation of Ntca-Dependent Transcription by Proteins Pipx and Pii. Authors: Llacer, J.L. / Espinosa, J. / Castells, M.A. / Contreras, A. / Forchhammer, K. / Rubio, V. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  2xgx.cif.gz 2xgx.cif.gz | 93 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb2xgx.ent.gz pdb2xgx.ent.gz | 75.9 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  2xgx.json.gz 2xgx.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/xg/2xgx https://data.pdbj.org/pub/pdb/validation_reports/xg/2xgx ftp://data.pdbj.org/pub/pdb/validation_reports/xg/2xgx ftp://data.pdbj.org/pub/pdb/validation_reports/xg/2xgx | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Unit cell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Noncrystallographic symmetry (NCS) | NCS domain:
NCS domain segments:
NCS oper: (Code: given Matrix: (-0.4064, -0.9017, -0.1476), Vector  : : |
- Components
Components
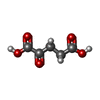
| #1: Protein | Mass: 24862.053 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Details: AN HG ATOM BOUND TO EACH CYS 156 OF THE NTCA DIMER. Source: (gene. exp.)   SYNECHOCOCCUS ELONGATUS (bacteria) / Strain: PCC 7942 / Plasmid: PET15B / Production host: SYNECHOCOCCUS ELONGATUS (bacteria) / Strain: PCC 7942 / Plasmid: PET15B / Production host:   ESCHERICHIA COLI (E. coli) / Strain (production host): ROSETTA / References: UniProt: P29283 ESCHERICHIA COLI (E. coli) / Strain (production host): ROSETTA / References: UniProt: P29283#2: Chemical |  Α-Ketoglutaric acid Α-Ketoglutaric acid#3: Chemical |  Mercury (element) Mercury (element)#4: Chemical | ChemComp-BTB / |  Bis-tris methane Bis-tris methane#5: Water | ChemComp-HOH / |  Water Water |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.25 Å3/Da / Density % sol: 62.2 % / Description: NONE |
|---|---|
Crystal grow | pH: 6.5 Details: NTCA PROTEIN WAS AT 4.7 MG/ML IN 50 MM SODIUM CITRATE PH 6.5, 0.5 M NACL, 5 MM MAGNESIUM CHLORIDE, 50 MM ARGININE HYDROCHLORIDE, 50 MM NA L-GLUTAMATE AND 10 MM 2- OXOGLUTARATE (2OG). ...Details: NTCA PROTEIN WAS AT 4.7 MG/ML IN 50 MM SODIUM CITRATE PH 6.5, 0.5 M NACL, 5 MM MAGNESIUM CHLORIDE, 50 MM ARGININE HYDROCHLORIDE, 50 MM NA L-GLUTAMATE AND 10 MM 2- OXOGLUTARATE (2OG). CRISTALLIZATION SOLUTION: 0.1 M BIS-TRIS PH 6.5, 36 % PEG 400. THEN, SOAKED IN THE SAME SOLUTION CONTAINING ALSO 10MM 2OG AND 2 MM HGCL2. |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  ESRF ESRF  / Beamline: BM16 / Wavelength: 1.007 / Beamline: BM16 / Wavelength: 1.007 |
| Detector | Type: ADSC CCD / Detector: CCD / Date: Feb 26, 2009 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength : 1.007 Å / Relative weight: 1 : 1.007 Å / Relative weight: 1 |
| Reflection | Resolution: 2.85→74.5 Å / Num. obs: 16626 / % possible obs: 97.3 % / Observed criterion σ(I): 1.9 / Redundancy: 6.6 % / Biso Wilson estimate: 74.73 Å2 / Rmerge(I) obs: 0.08 / Net I/σ(I): 8 |
| Reflection shell | Resolution: 2.85→3 Å / Redundancy: 6.6 % / Rmerge(I) obs: 0.46 / Mean I/σ(I) obs: 1.9 / % possible all: 97.3 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  SAD SADStarting model: NONE Resolution: 2.85→50 Å / Cor.coef. Fo:Fc: 0.939 / Cor.coef. Fo:Fc free: 0.909 / SU B: 28.068 / SU ML: 0.251 / Cross valid method: THROUGHOUT / ESU R: 0.745 / ESU R Free: 0.332 / Stereochemistry target values: MAXIMUM LIKELIHOOD Details: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS. ATOM RECORD CONTAINS SUM OF TLS AND RESIDUAL B FACTORS ANISOU RECORD CONTAINS SUM OF TLS AND RESIDUAL U FACTORS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.2 Å / Solvent model: MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 65.129 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.85→50 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
|
 Movie
Movie Controller
Controller
















 PDBj
PDBj