+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6t7c | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
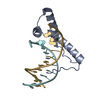
| タイトル | Structure of two copies of human Sox11 transcription factor in complex with a nucleosome | ||||||||||||
 要素 要素 |
| ||||||||||||
 キーワード キーワード |  NUCLEAR PROTEIN / NUCLEAR PROTEIN /  Nucleosome (ヌクレオソーム) / Nucleosome (ヌクレオソーム) /  DNA (デオキシリボ核酸) / DNA (デオキシリボ核酸) /  histones (ヒストン) / histones (ヒストン) /  Sox11 / Sox11 /  transcription factor (転写因子) / transcription factor (転写因子) /  pioneer factor pioneer factor | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報closure of optic fissure / positive regulation of lens epithelial cell proliferation / soft palate development / cornea development in camera-type eye / positive regulation of hippo signaling / noradrenergic neuron differentiation / negative regulation of transcription regulatory region DNA binding / negative regulation of lymphocyte proliferation / hard palate development / lens morphogenesis in camera-type eye ...closure of optic fissure / positive regulation of lens epithelial cell proliferation / soft palate development / cornea development in camera-type eye / positive regulation of hippo signaling / noradrenergic neuron differentiation / negative regulation of transcription regulatory region DNA binding / negative regulation of lymphocyte proliferation / hard palate development / lens morphogenesis in camera-type eye / embryonic skeletal system morphogenesis / regulation of transforming growth factor beta receptor signaling pathway / embryonic digestive tract morphogenesis / neuroepithelial cell differentiation / oligodendrocyte development /  sympathetic nervous system development / positive regulation of hormone secretion / positive regulation of BMP signaling pathway / positive regulation of ossification / positive regulation of neurogenesis / negative regulation of glial cell proliferation / spinal cord development / ventricular septum morphogenesis / lung morphogenesis / positive regulation of stem cell proliferation / eyelid development in camera-type eye / outflow tract morphogenesis / skeletal muscle cell differentiation / anatomical structure morphogenesis / positive regulation of osteoblast differentiation / glial cell proliferation / negative regulation of megakaryocyte differentiation / protein localization to CENP-A containing chromatin / Chromatin modifying enzymes / Replacement of protamines by nucleosomes in the male pronucleus / CENP-A containing nucleosome / Packaging Of Telomere Ends / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine / Deposition of new CENPA-containing nucleosomes at the centromere / Recognition and association of DNA glycosylase with site containing an affected pyrimidine / Cleavage of the damaged pyrimidine / Inhibition of DNA recombination at telomere / Meiotic synapsis / positive regulation of neuron differentiation / telomere organization / RNA Polymerase I Promoter Opening / Interleukin-7 signaling / SUMOylation of chromatin organization proteins / Assembly of the ORC complex at the origin of replication / sympathetic nervous system development / positive regulation of hormone secretion / positive regulation of BMP signaling pathway / positive regulation of ossification / positive regulation of neurogenesis / negative regulation of glial cell proliferation / spinal cord development / ventricular septum morphogenesis / lung morphogenesis / positive regulation of stem cell proliferation / eyelid development in camera-type eye / outflow tract morphogenesis / skeletal muscle cell differentiation / anatomical structure morphogenesis / positive regulation of osteoblast differentiation / glial cell proliferation / negative regulation of megakaryocyte differentiation / protein localization to CENP-A containing chromatin / Chromatin modifying enzymes / Replacement of protamines by nucleosomes in the male pronucleus / CENP-A containing nucleosome / Packaging Of Telomere Ends / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine / Deposition of new CENPA-containing nucleosomes at the centromere / Recognition and association of DNA glycosylase with site containing an affected pyrimidine / Cleavage of the damaged pyrimidine / Inhibition of DNA recombination at telomere / Meiotic synapsis / positive regulation of neuron differentiation / telomere organization / RNA Polymerase I Promoter Opening / Interleukin-7 signaling / SUMOylation of chromatin organization proteins / Assembly of the ORC complex at the origin of replication /  DNAメチル化 / Condensation of Prophase Chromosomes / HCMV Late Events / Chromatin modifications during the maternal to zygotic transition (MZT) / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / SIRT1 negatively regulates rRNA expression / DNAメチル化 / Condensation of Prophase Chromosomes / HCMV Late Events / Chromatin modifications during the maternal to zygotic transition (MZT) / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / SIRT1 negatively regulates rRNA expression /  innate immune response in mucosa / PRC2 methylates histones and DNA / innate immune response in mucosa / PRC2 methylates histones and DNA /  kidney development / Defective pyroptosis / HDACs deacetylate histones / RNA Polymerase I Promoter Escape / Nonhomologous End-Joining (NHEJ) / Transcriptional regulation by small RNAs / Formation of the beta-catenin:TCF transactivating complex / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / NoRC negatively regulates rRNA expression / G2/M DNA damage checkpoint / B-WICH complex positively regulates rRNA expression / HDMs demethylate histones / DNA Damage/Telomere Stress Induced Senescence / Metalloprotease DUBs / neuron differentiation / PKMTs methylate histone lysines / RMTs methylate histone arginines / kidney development / Defective pyroptosis / HDACs deacetylate histones / RNA Polymerase I Promoter Escape / Nonhomologous End-Joining (NHEJ) / Transcriptional regulation by small RNAs / Formation of the beta-catenin:TCF transactivating complex / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / NoRC negatively regulates rRNA expression / G2/M DNA damage checkpoint / B-WICH complex positively regulates rRNA expression / HDMs demethylate histones / DNA Damage/Telomere Stress Induced Senescence / Metalloprotease DUBs / neuron differentiation / PKMTs methylate histone lysines / RMTs methylate histone arginines /  遺伝的組換え / Pre-NOTCH Transcription and Translation / 遺伝的組換え / Pre-NOTCH Transcription and Translation /  nucleosome assembly / Activation of anterior HOX genes in hindbrain development during early embryogenesis / HCMV Early Events / Transcriptional regulation of granulopoiesis / structural constituent of chromatin / UCH proteinases / nucleosome assembly / Activation of anterior HOX genes in hindbrain development during early embryogenesis / HCMV Early Events / Transcriptional regulation of granulopoiesis / structural constituent of chromatin / UCH proteinases /  ヌクレオソーム / antimicrobial humoral immune response mediated by antimicrobial peptide / E3 ubiquitin ligases ubiquitinate target proteins / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / RUNX1 regulates transcription of genes involved in differentiation of HSCs / ヌクレオソーム / antimicrobial humoral immune response mediated by antimicrobial peptide / E3 ubiquitin ligases ubiquitinate target proteins / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / RUNX1 regulates transcription of genes involved in differentiation of HSCs /  nervous system development / chromatin organization / Factors involved in megakaryocyte development and platelet production / Processing of DNA double-strand break ends / HATs acetylate histones / antibacterial humoral response / Senescence-Associated Secretory Phenotype (SASP) / DNA-binding transcription activator activity, RNA polymerase II-specific / Oxidative Stress Induced Senescence / killing of cells of another organism / Estrogen-dependent gene expression nervous system development / chromatin organization / Factors involved in megakaryocyte development and platelet production / Processing of DNA double-strand break ends / HATs acetylate histones / antibacterial humoral response / Senescence-Associated Secretory Phenotype (SASP) / DNA-binding transcription activator activity, RNA polymerase II-specific / Oxidative Stress Induced Senescence / killing of cells of another organism / Estrogen-dependent gene expression類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト)synthetic construct (人工物) | ||||||||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4 Å クライオ電子顕微鏡法 / 解像度: 4 Å | ||||||||||||
 データ登録者 データ登録者 | Dodonova, S.O. / Zhu, F. / Dienemann, C. / Taipale, J. / Cramer, P. | ||||||||||||
| 資金援助 |  ドイツ, 3件 ドイツ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2020 ジャーナル: Nature / 年: 2020タイトル: Nucleosome-bound SOX2 and SOX11 structures elucidate pioneer factor function. 著者: Svetlana O Dodonova / Fangjie Zhu / Christian Dienemann / Jussi Taipale / Patrick Cramer /   要旨: 'Pioneer' transcription factors are required for stem-cell pluripotency, cell differentiation and cell reprogramming. Pioneer factors can bind nucleosomal DNA to enable gene expression from regions ...'Pioneer' transcription factors are required for stem-cell pluripotency, cell differentiation and cell reprogramming. Pioneer factors can bind nucleosomal DNA to enable gene expression from regions of the genome with closed chromatin. SOX2 is a prominent pioneer factor that is essential for pluripotency and self-renewal of embryonic stem cells. Here we report cryo-electron microscopy structures of the DNA-binding domains of SOX2 and its close homologue SOX11 bound to nucleosomes. The structures show that SOX factors can bind and locally distort DNA at superhelical location 2. The factors also facilitate detachment of terminal nucleosomal DNA from the histone octamer, which increases DNA accessibility. SOX-factor binding to the nucleosome can also lead to a repositioning of the N-terminal tail of histone H4 that includes residue lysine 16. We speculate that this repositioning is incompatible with higher-order nucleosome stacking, which involves contacts of the H4 tail with a neighbouring nucleosome. Our results indicate that pioneer transcription factors can use binding energy to initiate chromatin opening, and thereby facilitate nucleosome remodelling and subsequent transcription. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6t7c.cif.gz 6t7c.cif.gz | 256.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6t7c.ent.gz pdb6t7c.ent.gz | 198.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6t7c.json.gz 6t7c.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/t7/6t7c https://data.pdbj.org/pub/pdb/validation_reports/t7/6t7c ftp://data.pdbj.org/pub/pdb/validation_reports/t7/6t7c ftp://data.pdbj.org/pub/pdb/validation_reports/t7/6t7c | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 5種, 10分子 AEBFCGDHKL
| #1: タンパク質 | 分子量: 15389.036 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: HIST2H3A, HIST2H3C, H3F2, H3FM, HIST2H3D / プラスミド: pET22b / 発現宿主: Homo sapiens (ヒト) / 遺伝子: HIST2H3A, HIST2H3C, H3F2, H3FM, HIST2H3D / プラスミド: pET22b / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: Q71DI3 Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: Q71DI3#2: タンパク質 |  ヒストンH4 ヒストンH4分子量: 11394.426 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) Homo sapiens (ヒト)遺伝子: HIST1H4A, H4/A, H4FA, HIST1H4B, H4/I, H4FI, HIST1H4C, H4/G, H4FG, HIST1H4D, H4/B, H4FB, HIST1H4E, H4/J, H4FJ, HIST1H4F, H4/C, H4FC, HIST1H4H, H4/H, H4FH, HIST1H4I, H4/M, H4FM, HIST1H4J, ...遺伝子: HIST1H4A, H4/A, H4FA, HIST1H4B, H4/I, H4FI, HIST1H4C, H4/G, H4FG, HIST1H4D, H4/B, H4FB, HIST1H4E, H4/J, H4FJ, HIST1H4F, H4/C, H4FC, HIST1H4H, H4/H, H4FH, HIST1H4I, H4/M, H4FM, HIST1H4J, H4/E, H4FE, HIST1H4K, H4/D, H4FD, HIST1H4L, H4/K, H4FK, HIST2H4A, H4/N, H4F2, H4FN, HIST2H4, HIST2H4B, H4/O, H4FO, HIST4H4 プラスミド: pET3a / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: P62805 Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: P62805#3: タンパク質 | 分子量: 16707.277 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: HIST1H2AB, H2AFM, HIST1H2AE, H2AFA / プラスミド: LIC-1B (MacroLabs) / 発現宿主: Homo sapiens (ヒト) / 遺伝子: HIST1H2AB, H2AFM, HIST1H2AE, H2AFA / プラスミド: LIC-1B (MacroLabs) / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: P04908 Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: P04908#4: タンパク質 | 分子量: 13921.213 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: HIST1H2BK, H2BFT, HIRIP1 / プラスミド: pET22b / 発現宿主: Homo sapiens (ヒト) / 遺伝子: HIST1H2BK, H2BFT, HIRIP1 / プラスミド: pET22b / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: O60814 Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: O60814#7: タンパク質 | 分子量: 12856.941 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: SOX11 / プラスミド: LIC-1B (MacroLabs) / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SOX11 / プラスミド: LIC-1B (MacroLabs) / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: P35716 Escherichia coli BL21(DE3) (大腸菌) / Variant (発現宿主): CodonPlus-RIL / 参照: UniProt: P35716 |
|---|
-DNA鎖 , 2種, 2分子 IJ
| #5: DNA鎖 | 分子量: 45240.848 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
|---|---|
| #6: DNA鎖 | 分子量: 45484.273 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| |||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 0.229 MDa / 実験値: NO | |||||||||||||||||||||||||
| 由来(天然) |
| |||||||||||||||||||||||||
| 由来(組換発現) |
| |||||||||||||||||||||||||
| 緩衝液 | pH: 7.5 | |||||||||||||||||||||||||
| 緩衝液成分 |
| |||||||||||||||||||||||||
| 試料 | 濃度: 0.15 mg/ml / 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES | |||||||||||||||||||||||||
| 試料支持 | 詳細: 0.39 mB, 25 mA / グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R2/1 | |||||||||||||||||||||||||
急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 289 K 詳細: The sample was applied onto glow-discharged Quantifoil holey carbon grids. The grids were blotted from both sides for 5-10 seconds at 16*C in a chamber at 100% humidity and plunge-frozen into ...詳細: The sample was applied onto glow-discharged Quantifoil holey carbon grids. The grids were blotted from both sides for 5-10 seconds at 16*C in a chamber at 100% humidity and plunge-frozen into liquid ethane using a manual plunger. |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS 詳細: At least 50% of the data were collected at 25* stage tilt in order to partially compensate for preferred orientation of particles on the grid, and to improve angular distribution. |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy / 倍率(公称値): 130000 X / 最大 デフォーカス(公称値): 3500 nm / 最小 デフォーカス(公称値): 1000 nm / Cs Bright-field microscopy / 倍率(公称値): 130000 X / 最大 デフォーカス(公称値): 3500 nm / 最小 デフォーカス(公称値): 1000 nm / Cs : 2.7 mm / C2レンズ絞り径: 100 µm / アライメント法: COMA FREE : 2.7 mm / C2レンズ絞り径: 100 µm / アライメント法: COMA FREE |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 電子線照射量: 1.125 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 撮影したグリッド数: 1 |
| 電子光学装置 | エネルギーフィルター名称 : GIF Bioquantum / エネルギーフィルタースリット幅: 30 eV : GIF Bioquantum / エネルギーフィルタースリット幅: 30 eV |
| 画像スキャン | 動画フレーム数/画像: 40 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 対称性 | 点対称性 : C1 (非対称) : C1 (非対称) | ||||||||||||||||||||||||
3次元再構成 | 解像度: 4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 109666 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| EM volume selection | 詳細: 1733 vesicles and near-complete buds were picked from 61 tomograms. Subtomograms were extracted from the surface of the vesicles. Num. of tomograms: 54 / Num. of volumes extracted: 2547 | ||||||||||||||||||||||||
| 原子モデル構築 | B value: 130 / プロトコル: OTHER / 空間: REAL | ||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6FQ5 |
 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj











































