+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6q0t | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of a MAPK pathway complex | |||||||||
 要素 要素 |
| |||||||||
 キーワード キーワード | TRANSFERASE/PROTEIN BINDING /  TRANSFERASE (転移酵素) / TRANSFERASE-PROTEIN BINDING complex TRANSFERASE (転移酵素) / TRANSFERASE-PROTEIN BINDING complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報epithelial cell proliferation involved in lung morphogenesis / positive regulation of endodermal cell differentiation / trehalose metabolism in response to stress / CD4-positive, alpha-beta T cell differentiation / placenta blood vessel development / CD4-positive or CD8-positive, alpha-beta T cell lineage commitment / regulation of axon regeneration /  MAPキナーゼキナーゼ / negative regulation of synaptic vesicle exocytosis / type B pancreatic cell proliferation ...epithelial cell proliferation involved in lung morphogenesis / positive regulation of endodermal cell differentiation / trehalose metabolism in response to stress / CD4-positive, alpha-beta T cell differentiation / placenta blood vessel development / CD4-positive or CD8-positive, alpha-beta T cell lineage commitment / regulation of axon regeneration / MAPキナーゼキナーゼ / negative regulation of synaptic vesicle exocytosis / type B pancreatic cell proliferation ...epithelial cell proliferation involved in lung morphogenesis / positive regulation of endodermal cell differentiation / trehalose metabolism in response to stress / CD4-positive, alpha-beta T cell differentiation / placenta blood vessel development / CD4-positive or CD8-positive, alpha-beta T cell lineage commitment / regulation of axon regeneration /  MAPキナーゼキナーゼ / negative regulation of synaptic vesicle exocytosis / type B pancreatic cell proliferation / labyrinthine layer development / MAP-kinase scaffold activity / head morphogenesis / Signalling to p38 via RIT and RIN / cerebellar cortex formation / myeloid progenitor cell differentiation / ARMS-mediated activation / SHOC2 M1731 mutant abolishes MRAS complex function / Gain-of-function MRAS complexes activate RAF signaling / endothelial cell apoptotic process / Signaling by MAP2K mutants / negative regulation of fibroblast migration / positive regulation of glucose transmembrane transport / establishment of protein localization to membrane / regulation of Golgi inheritance / trachea formation / mitogen-activated protein kinase kinase binding / regulation of T cell differentiation / regulation of early endosome to late endosome transport / Negative feedback regulation of MAPK pathway / regulation of stress-activated MAPK cascade / positive regulation of axonogenesis / Frs2-mediated activation / protein kinase activator activity / ERBB2-ERBB3 signaling pathway / MAPキナーゼキナーゼ / negative regulation of synaptic vesicle exocytosis / type B pancreatic cell proliferation / labyrinthine layer development / MAP-kinase scaffold activity / head morphogenesis / Signalling to p38 via RIT and RIN / cerebellar cortex formation / myeloid progenitor cell differentiation / ARMS-mediated activation / SHOC2 M1731 mutant abolishes MRAS complex function / Gain-of-function MRAS complexes activate RAF signaling / endothelial cell apoptotic process / Signaling by MAP2K mutants / negative regulation of fibroblast migration / positive regulation of glucose transmembrane transport / establishment of protein localization to membrane / regulation of Golgi inheritance / trachea formation / mitogen-activated protein kinase kinase binding / regulation of T cell differentiation / regulation of early endosome to late endosome transport / Negative feedback regulation of MAPK pathway / regulation of stress-activated MAPK cascade / positive regulation of axonogenesis / Frs2-mediated activation / protein kinase activator activity / ERBB2-ERBB3 signaling pathway /  stress fiber assembly / positive regulation of axon regeneration / face development / endodermal cell differentiation / MAPK3 (ERK1) activation / synaptic vesicle exocytosis / somatic stem cell population maintenance / Bergmann glial cell differentiation / stress fiber assembly / positive regulation of axon regeneration / face development / endodermal cell differentiation / MAPK3 (ERK1) activation / synaptic vesicle exocytosis / somatic stem cell population maintenance / Bergmann glial cell differentiation /  MAP kinase kinase activity / thyroid gland development / Uptake and function of anthrax toxins / MAP kinase kinase activity / thyroid gland development / Uptake and function of anthrax toxins /  MAP kinase kinase kinase activity / Schwann cell development / negative regulation of endothelial cell apoptotic process / positive regulation of substrate adhesion-dependent cell spreading / keratinocyte differentiation / positive regulation of stress fiber assembly / response to cAMP / ERK1 and ERK2 cascade / MAP kinase kinase kinase activity / Schwann cell development / negative regulation of endothelial cell apoptotic process / positive regulation of substrate adhesion-dependent cell spreading / keratinocyte differentiation / positive regulation of stress fiber assembly / response to cAMP / ERK1 and ERK2 cascade /  髄鞘 / cellular response to calcium ion / protein serine/threonine/tyrosine kinase activity / protein serine/threonine kinase activator activity / MAP3K8 (TPL2)-dependent MAPK1/3 activation / substrate adhesion-dependent cell spreading / cellular response to nerve growth factor stimulus / insulin-like growth factor receptor signaling pathway / thymus development / Signal transduction by L1 / long-term synaptic potentiation / 髄鞘 / cellular response to calcium ion / protein serine/threonine/tyrosine kinase activity / protein serine/threonine kinase activator activity / MAP3K8 (TPL2)-dependent MAPK1/3 activation / substrate adhesion-dependent cell spreading / cellular response to nerve growth factor stimulus / insulin-like growth factor receptor signaling pathway / thymus development / Signal transduction by L1 / long-term synaptic potentiation /  運動性 / animal organ morphogenesis / Spry regulation of FGF signaling / RAF activation / Signaling by high-kinase activity BRAF mutants / 運動性 / animal organ morphogenesis / Spry regulation of FGF signaling / RAF activation / Signaling by high-kinase activity BRAF mutants /  visual learning / MAP2K and MAPK activation / epidermal growth factor receptor signaling pathway / positive regulation of protein serine/threonine kinase activity / response to peptide hormone / neuron differentiation / Negative regulation of MAPK pathway / Signaling by RAF1 mutants / Signaling by moderate kinase activity BRAF mutants / Paradoxical activation of RAF signaling by kinase inactive BRAF / Signaling downstream of RAS mutants / visual learning / MAP2K and MAPK activation / epidermal growth factor receptor signaling pathway / positive regulation of protein serine/threonine kinase activity / response to peptide hormone / neuron differentiation / Negative regulation of MAPK pathway / Signaling by RAF1 mutants / Signaling by moderate kinase activity BRAF mutants / Paradoxical activation of RAF signaling by kinase inactive BRAF / Signaling downstream of RAS mutants /  走化性 / 走化性 /  分裂促進因子活性化タンパク質キナーゼ / 分裂促進因子活性化タンパク質キナーゼ /  細胞老化 / Signaling by BRAF and RAF1 fusions / cellular response to xenobiotic stimulus / late endosome / presynapse / 細胞老化 / Signaling by BRAF and RAF1 fusions / cellular response to xenobiotic stimulus / late endosome / presynapse /  cell body / positive regulation of peptidyl-serine phosphorylation / T cell differentiation in thymus / regulation of cell population proliferation / cell body / positive regulation of peptidyl-serine phosphorylation / T cell differentiation in thymus / regulation of cell population proliferation /  heart development / T cell receptor signaling pathway / heart development / T cell receptor signaling pathway /  scaffold protein binding / scaffold protein binding /  protein tyrosine kinase activity / negative regulation of neuron apoptotic process / positive regulation of ERK1 and ERK2 cascade / protein tyrosine kinase activity / negative regulation of neuron apoptotic process / positive regulation of ERK1 and ERK2 cascade /  エンドソーム / エンドソーム /  non-specific serine/threonine protein kinase non-specific serine/threonine protein kinase類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト)  Spodoptera exigua (シロイチモジヨトウ) Spodoptera exigua (シロイチモジヨトウ) | |||||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 5.7 Å クライオ電子顕微鏡法 / 解像度: 5.7 Å | |||||||||
 データ登録者 データ登録者 | Park, E. / Rawson, S. / Jeon, H. / Eck, M.J. | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2019 ジャーナル: Nature / 年: 2019タイトル: Architecture of autoinhibited and active BRAF-MEK1-14-3-3 complexes. 著者: Eunyoung Park / Shaun Rawson / Kunhua Li / Byeong-Won Kim / Scott B Ficarro / Gonzalo Gonzalez-Del Pino / Humayun Sharif / Jarrod A Marto / Hyesung Jeon / Michael J Eck /  要旨: RAF family kinases are RAS-activated switches that initiate signalling through the MAP kinase cascade to control cellular proliferation, differentiation and survival. RAF activity is tightly ...RAF family kinases are RAS-activated switches that initiate signalling through the MAP kinase cascade to control cellular proliferation, differentiation and survival. RAF activity is tightly regulated and inappropriate activation is a frequent cause of cancer; however, the structural basis for RAF regulation is poorly understood at present. Here we use cryo-electron microscopy to determine autoinhibited and active-state structures of full-length BRAF in complexes with MEK1 and a 14-3-3 dimer. The reconstruction reveals an inactive BRAF-MEK1 complex restrained in a cradle formed by the 14-3-3 dimer, which binds the phosphorylated S365 and S729 sites that flank the BRAF kinase domain. The BRAF cysteine-rich domain occupies a central position that stabilizes this assembly, but the adjacent RAS-binding domain is poorly ordered and peripheral. The 14-3-3 cradle maintains autoinhibition by sequestering the membrane-binding cysteine-rich domain and blocking dimerization of the BRAF kinase domain. In the active state, these inhibitory interactions are released and a single 14-3-3 dimer rearranges to bridge the C-terminal pS729 binding sites of two BRAFs, which drives the formation of an active, back-to-back BRAF dimer. Our structural snapshots provide a foundation for understanding normal RAF regulation and its mutational disruption in cancer and developmental syndromes. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6q0t.cif.gz 6q0t.cif.gz | 223.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6q0t.ent.gz pdb6q0t.ent.gz | 150 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6q0t.json.gz 6q0t.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/q0/6q0t https://data.pdbj.org/pub/pdb/validation_reports/q0/6q0t ftp://data.pdbj.org/pub/pdb/validation_reports/q0/6q0t ftp://data.pdbj.org/pub/pdb/validation_reports/q0/6q0t | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 3種, 5分子 ABCXY
| #1: タンパク質 | 分子量: 89306.812 Da / 分子数: 2 / 変異: S365A / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: BRAF, BRAF1, RAFB1 Homo sapiens (ヒト) / 遺伝子: BRAF, BRAF1, RAFB1発現宿主:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ)参照: UniProt: P15056,  non-specific serine/threonine protein kinase non-specific serine/threonine protein kinase#2: タンパク質 | | 分子量: 45835.414 Da / 分子数: 1 / 変異: S218A, S222A / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: MAP2K1, MEK1, PRKMK1 Homo sapiens (ヒト) / 遺伝子: MAP2K1, MEK1, PRKMK1発現宿主:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ)参照: UniProt: Q02750,  MAPキナーゼキナーゼ MAPキナーゼキナーゼ#3: タンパク質 | 分子量: 28108.514 Da / 分子数: 2 / 由来タイプ: 天然 由来: (天然)   Spodoptera exigua (シロイチモジヨトウ) Spodoptera exigua (シロイチモジヨトウ)参照: UniProt: V9P4T4 |
|---|
-非ポリマー , 3種, 3分子 
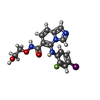



| #4: 化合物 | ChemComp-MG / |
|---|---|
| #5: 化合物 | ChemComp-LCJ / |
| #6: 化合物 | ChemComp-AGS / |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: ERK pathway complex MAPK/ERK pathway / タイプ: COMPLEX / Entity ID: #1-#3 / 由来: MULTIPLE SOURCES MAPK/ERK pathway / タイプ: COMPLEX / Entity ID: #1-#3 / 由来: MULTIPLE SOURCES |
|---|---|
| 分子量 | 値: 280 kDa/nm / 実験値: NO |
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ) |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES |
急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TALOS ARCTICA |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 200 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 200 kV / 照射モード: OTHER |
| 電子レンズ | モード: OTHER |
| 撮影 | 電子線照射量: 53 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) |
- 解析
解析
CTF補正 | タイプ: NONE |
|---|---|
3次元再構成 | 解像度: 5.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 595672 / 対称性のタイプ: POINT |
| 原子モデル構築 | プロトコル: RIGID BODY FIT |
 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj












