+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5u4w | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM Structure of Immature Zika Virus | |||||||||
 要素 要素 |
| |||||||||
 キーワード キーワード |  VIRUS (ウイルス) / immature Zika virus / VIRUS (ウイルス) / immature Zika virus /  viral protein (ウイルスタンパク質) viral protein (ウイルスタンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 : / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity / : / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity /  フラビビリン / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / ribonucleoside triphosphate phosphatase activity / negative regulation of innate immune response / フラビビリン / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / ribonucleoside triphosphate phosphatase activity / negative regulation of innate immune response /  カプシド / nucleoside-triphosphate phosphatase / カプシド / nucleoside-triphosphate phosphatase /  double-stranded RNA binding ... double-stranded RNA binding ... : / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity / : / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity /  フラビビリン / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / ribonucleoside triphosphate phosphatase activity / negative regulation of innate immune response / フラビビリン / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / ribonucleoside triphosphate phosphatase activity / negative regulation of innate immune response /  カプシド / nucleoside-triphosphate phosphatase / カプシド / nucleoside-triphosphate phosphatase /  double-stranded RNA binding / 4 iron, 4 sulfur cluster binding / mRNA (guanine-N7)-methyltransferase / methyltransferase cap1 / clathrin-dependent endocytosis of virus by host cell / double-stranded RNA binding / 4 iron, 4 sulfur cluster binding / mRNA (guanine-N7)-methyltransferase / methyltransferase cap1 / clathrin-dependent endocytosis of virus by host cell /  mRNA (nucleoside-2'-O-)-methyltransferase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / host cell surface / mRNA (nucleoside-2'-O-)-methyltransferase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / host cell surface /  RNA helicase activity / membrane => GO:0016020 / host cell endoplasmic reticulum membrane / host cell perinuclear region of cytoplasm / RNA helicase activity / membrane => GO:0016020 / host cell endoplasmic reticulum membrane / host cell perinuclear region of cytoplasm /  protein dimerization activity / molecular adaptor activity / protein dimerization activity / molecular adaptor activity /  ヘリカーゼ / induction by virus of host autophagy / ヘリカーゼ / induction by virus of host autophagy /  RNA依存性RNAポリメラーゼ / symbiont entry into host cell / viral RNA genome replication / RNA依存性RNAポリメラーゼ / symbiont entry into host cell / viral RNA genome replication /  RNA-dependent RNA polymerase activity / serine-type endopeptidase activity / fusion of virus membrane with host endosome membrane / RNA-dependent RNA polymerase activity / serine-type endopeptidase activity / fusion of virus membrane with host endosome membrane /  中心体 / 中心体 /  エンベロープ (ウイルス) / エンベロープ (ウイルス) /  lipid binding / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / host cell nucleus / structural molecule activity / virion attachment to host cell / GTP binding / virion membrane / lipid binding / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / host cell nucleus / structural molecule activity / virion attachment to host cell / GTP binding / virion membrane /  ATP hydrolysis activity / ATP hydrolysis activity /  タンパク質分解 / extracellular region / タンパク質分解 / extracellular region /  ATP binding / ATP binding /  生体膜 / 生体膜 /  metal ion binding metal ion binding類似検索 - 分子機能 | |||||||||
| 生物種 |    Zika virus (ジカ熱ウイルス) Zika virus (ジカ熱ウイルス) | |||||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 9.1 Å クライオ電子顕微鏡法 / 解像度: 9.1 Å | |||||||||
 データ登録者 データ登録者 | Mangala Prasad, V. / Miller, A.S. / Klose, T. / Sirohi, D. / Buda, G. / Jiang, W. / Kuhn, R.J. / Rossmann, M.G. | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2017 ジャーナル: Nat Struct Mol Biol / 年: 2017タイトル: Structure of the immature Zika virus at 9 Å resolution. 著者: Vidya Mangala Prasad / Andrew S Miller / Thomas Klose / Devika Sirohi / Geeta Buda / Wen Jiang / Richard J Kuhn / Michael G Rossmann /  要旨: The current Zika virus (ZIKV) epidemic is characterized by severe pathogenicity in both children and adults. Sequence changes in ZIKV since its first isolation are apparent when pre-epidemic strains ...The current Zika virus (ZIKV) epidemic is characterized by severe pathogenicity in both children and adults. Sequence changes in ZIKV since its first isolation are apparent when pre-epidemic strains are compared with those causing the current epidemic. However, the residues that are responsible for ZIKV pathogenicity are largely unknown. Here we report the cryo-electron microscopy (cryo-EM) structure of the immature ZIKV at 9-Å resolution. The cryo-EM map was fitted with the crystal structures of the precursor membrane and envelope glycoproteins and was shown to be similar to the structures of other known immature flaviviruses. However, the immature ZIKV contains a partially ordered capsid protein shell that is less prominent in other immature flaviviruses. Furthermore, six amino acids near the interface between pr domains at the top of the spikes were found to be different between the pre-epidemic and epidemic ZIKV, possibly influencing the composition and structure of the resulting viruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5u4w.cif.gz 5u4w.cif.gz | 341.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5u4w.ent.gz pdb5u4w.ent.gz | 277.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5u4w.json.gz 5u4w.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/u4/5u4w https://data.pdbj.org/pub/pdb/validation_reports/u4/5u4w ftp://data.pdbj.org/pub/pdb/validation_reports/u4/5u4w ftp://data.pdbj.org/pub/pdb/validation_reports/u4/5u4w | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
| 2 |
|
| 3 | x 5
|
| 4 | x 6
|
| 5 | 
|
| 対称性 | 点対称性: (シェーンフリース記号 : I (正20面体型対称 : I (正20面体型対称 )) )) |
- 要素
要素
-タンパク質 , 4種, 12分子 ACEBDFGIKHJL
| #1: タンパク質 | 分子量: 44801.410 Da / 分子数: 3 / 由来タイプ: 組換発現 / 由来: (組換発現)    Zika virus (ジカ熱ウイルス) Zika virus (ジカ熱ウイルス)発現宿主:   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ)株 (発現宿主): S2 / 参照: UniProt: O11875*PLUS #2: タンパク質 | 分子量: 9261.531 Da / 分子数: 3 / 由来タイプ: 組換発現 / 由来: (組換発現)    Zika virus (ジカ熱ウイルス) Zika virus (ジカ熱ウイルス)発現宿主:   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ)株 (発現宿主): S2 / 参照: UniProt: A0A0B4L3F2*PLUS #3: タンパク質 | 分子量: 6892.228 Da / 分子数: 3 / Fragment: transmembrane domain (UNP residues 726-791) / 由来タイプ: 天然 / 由来: (天然)    Zika virus (ジカ熱ウイルス) / 参照: UniProt: A0A1B2ZC85, UniProt: A0A024B7W1*PLUS Zika virus (ジカ熱ウイルス) / 参照: UniProt: A0A1B2ZC85, UniProt: A0A024B7W1*PLUS#4: タンパク質 | 分子量: 5984.065 Da / 分子数: 3 / Fragment: transmembrane domain (UNP residues 238-290) / 由来タイプ: 天然 / 由来: (天然)    Zika virus (ジカ熱ウイルス) / 参照: UniProt: A0A142I5B9, UniProt: A0A024B7W1*PLUS Zika virus (ジカ熱ウイルス) / 参照: UniProt: A0A142I5B9, UniProt: A0A024B7W1*PLUS |
|---|
-糖 , 2種, 18分子 
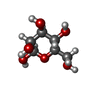

| #5: 糖 | ChemComp-NAG /  N-アセチルグルコサミン N-アセチルグルコサミン#6: 糖 | ChemComp-BMA /  マンノース マンノース |
|---|
-詳細
| 配列の詳細 | The sample was from Zika virus, but the modeled sequences for chains A, B, C, D, E, and F are from ...The sample was from Zika virus, but the modeled sequences for chains A, B, C, D, E, and F are from Dengue virus. |
|---|
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 由来(天然) |
| ||||||||||||||||||||
| ウイルスについての詳細 | 中空か: NO / エンベロープを持つか: YES / 単離: STRAIN / タイプ: VIRION | ||||||||||||||||||||
| 天然宿主 | 生物種: Homo sapiens | ||||||||||||||||||||
| ウイルス殻 | 名称: prM-E glycoprotein / 直径: 600 nm / 三角数 (T数): 1 | ||||||||||||||||||||
| 緩衝液 | pH: 8 | ||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES | ||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 400 divisions/in. / グリッドのタイプ: Ultrathin carbon | ||||||||||||||||||||
急速凍結 | 装置: GATAN CRYOPLUNGE 3 / 凍結剤: ETHANE / 湿度: 80 % |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: SPOT SCAN FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: SPOT SCAN |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | 平均露光時間: 7.6 sec. / 電子線照射量: 4.7 e/Å2 / 検出モード: SUPER-RESOLUTION フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 実像数: 3341 |
- 解析
解析
| EMソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | |||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 14351 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性 : I (正20面体型対称 : I (正20面体型対称 ) ) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||
3次元再構成 | 解像度: 9.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 9315 / アルゴリズム: FOURIER SPACE / 対称性のタイプ: POINT | |||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL / Target criteria: Correlation coefficient |
 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj




