+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5d5b | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | In meso X-ray crystallography structure of the Beta2-adrenergic receptor at 100 K | |||||||||
 要素 要素 | Beta-2 adrenergic receptor,Endolysin,Beta-2 adrenergic receptor | |||||||||
 キーワード キーワード |  Membrane Protein/Hydrolase (生体膜) / Membrane Protein/Hydrolase (生体膜) /  MEMBRANE PROTEIN (膜タンパク質) / MEMBRANE PROTEIN (膜タンパク質) /  HYDROLASE (加水分解酵素) / HYDROLASE (加水分解酵素) /  Membrane Protein-Hydrolase complex (生体膜) Membrane Protein-Hydrolase complex (生体膜) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報desensitization of G protein-coupled receptor signaling pathway by arrestin / beta2-adrenergic receptor activity / norepinephrine-epinephrine-mediated vasodilation involved in regulation of systemic arterial blood pressure / positive regulation of mini excitatory postsynaptic potential / positive regulation of cAMP-dependent protein kinase activity /  norepinephrine binding / norepinephrine binding /  アドレナリン受容体 / アドレナリン受容体 /  熱力学 / positive regulation of autophagosome maturation / positive regulation of AMPA receptor activity ...desensitization of G protein-coupled receptor signaling pathway by arrestin / beta2-adrenergic receptor activity / norepinephrine-epinephrine-mediated vasodilation involved in regulation of systemic arterial blood pressure / positive regulation of mini excitatory postsynaptic potential / positive regulation of cAMP-dependent protein kinase activity / 熱力学 / positive regulation of autophagosome maturation / positive regulation of AMPA receptor activity ...desensitization of G protein-coupled receptor signaling pathway by arrestin / beta2-adrenergic receptor activity / norepinephrine-epinephrine-mediated vasodilation involved in regulation of systemic arterial blood pressure / positive regulation of mini excitatory postsynaptic potential / positive regulation of cAMP-dependent protein kinase activity /  norepinephrine binding / norepinephrine binding /  アドレナリン受容体 / アドレナリン受容体 /  熱力学 / positive regulation of autophagosome maturation / positive regulation of AMPA receptor activity / activation of transmembrane receptor protein tyrosine kinase activity / negative regulation of smooth muscle contraction / positive regulation of lipophagy / response to psychosocial stress / negative regulation of multicellular organism growth / endosome to lysosome transport / adrenergic receptor signaling pathway / diet induced thermogenesis / neuronal dense core vesicle / positive regulation of protein kinase A signaling / 熱力学 / positive regulation of autophagosome maturation / positive regulation of AMPA receptor activity / activation of transmembrane receptor protein tyrosine kinase activity / negative regulation of smooth muscle contraction / positive regulation of lipophagy / response to psychosocial stress / negative regulation of multicellular organism growth / endosome to lysosome transport / adrenergic receptor signaling pathway / diet induced thermogenesis / neuronal dense core vesicle / positive regulation of protein kinase A signaling /  adenylate cyclase binding / smooth muscle contraction / potassium channel regulator activity / positive regulation of bone mineralization / adenylate cyclase-activating adrenergic receptor signaling pathway / brown fat cell differentiation / regulation of sodium ion transport / adenylate cyclase binding / smooth muscle contraction / potassium channel regulator activity / positive regulation of bone mineralization / adenylate cyclase-activating adrenergic receptor signaling pathway / brown fat cell differentiation / regulation of sodium ion transport /  bone resorption / viral release from host cell by cytolysis / activation of adenylate cyclase activity / bone resorption / viral release from host cell by cytolysis / activation of adenylate cyclase activity /  receptor-mediated endocytosis / response to cold / peptidoglycan catabolic process / clathrin-coated endocytic vesicle membrane / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / positive regulation of protein serine/threonine kinase activity / cellular response to amyloid-beta / cell wall macromolecule catabolic process / Cargo recognition for clathrin-mediated endocytosis / receptor-mediated endocytosis / response to cold / peptidoglycan catabolic process / clathrin-coated endocytic vesicle membrane / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / positive regulation of protein serine/threonine kinase activity / cellular response to amyloid-beta / cell wall macromolecule catabolic process / Cargo recognition for clathrin-mediated endocytosis /  リゾチーム / リゾチーム /  Clathrin-mediated endocytosis / Clathrin-mediated endocytosis /  lysozyme activity / lysozyme activity /  amyloid-beta binding / positive regulation of cold-induced thermogenesis / G alpha (s) signalling events / host cell cytoplasm / positive regulation of MAPK cascade / transcription by RNA polymerase II / amyloid-beta binding / positive regulation of cold-induced thermogenesis / G alpha (s) signalling events / host cell cytoplasm / positive regulation of MAPK cascade / transcription by RNA polymerase II /  リソソーム / cell surface receptor signaling pathway / リソソーム / cell surface receptor signaling pathway /  receptor complex / receptor complex /  エンドソーム / endosome membrane / Ub-specific processing proteases / エンドソーム / endosome membrane / Ub-specific processing proteases /  エンドソーム / defense response to bacterium / apical plasma membrane / protein-containing complex binding / エンドソーム / defense response to bacterium / apical plasma membrane / protein-containing complex binding /  ゴルジ体 / protein homodimerization activity / positive regulation of transcription by RNA polymerase II / ゴルジ体 / protein homodimerization activity / positive regulation of transcription by RNA polymerase II /  生体膜 / identical protein binding / 生体膜 / identical protein binding /  細胞核 / 細胞核 /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト)  Enterobacteria phage T4 (ファージ) Enterobacteria phage T4 (ファージ) | |||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.8 Å 分子置換 / 解像度: 3.8 Å | |||||||||
 データ登録者 データ登録者 | Huang, C.-Y. / Olieric, V. / Liu, X. / Kobilka, B. / Wang, M. / Caffrey, M. | |||||||||
| 資金援助 |  アイルランド, 1件 アイルランド, 1件
| |||||||||
 引用 引用 |  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2016 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2016タイトル: In meso in situ serial X-ray crystallography of soluble and membrane proteins at cryogenic temperatures. 著者: Huang, C.Y. / Olieric, V. / Ma, P. / Howe, N. / Vogeley, L. / Liu, X. / Warshamanage, R. / Weinert, T. / Panepucci, E. / Kobilka, B. / Diederichs, K. / Wang, M. / Caffrey, M. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5d5b.cif.gz 5d5b.cif.gz | 110.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5d5b.ent.gz pdb5d5b.ent.gz | 80.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5d5b.json.gz 5d5b.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/d5/5d5b https://data.pdbj.org/pub/pdb/validation_reports/d5/5d5b ftp://data.pdbj.org/pub/pdb/validation_reports/d5/5d5b ftp://data.pdbj.org/pub/pdb/validation_reports/d5/5d5b | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  5d52C  5d53C  5d54C  5d56C  5d57C  5d58C  5d59C  5d5aC  5d5cC  5d5dC  5d5eC  5d5fC  2rh1S S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 / 糖 , 2種, 2分子 A
| #1: タンパク質 | 分子量: 56601.438 Da / 分子数: 1 変異: N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A,N187E, C54T, C97A 由来タイプ: 組換発現 由来: (組換発現)   Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)   Enterobacteria phage T4 (ファージ) Enterobacteria phage T4 (ファージ)遺伝子: ADRB2, ADRB2R, B2AR 発現宿主:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ)参照: UniProt: P07550, UniProt: P00720,  リゾチーム リゾチーム |
|---|---|
| #2: 多糖 | alpha-D-glucopyranose-(1-4)-beta-D-glucopyranose / beta-maltose |
-非ポリマー , 6種, 13分子 
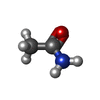








| #3: 化合物 | ChemComp-CAU / ( | ||||
|---|---|---|---|---|---|
| #4: 化合物 | ChemComp-BU1 /  1,4-ブタンジオール 1,4-ブタンジオール | ||||
| #5: 化合物 | ChemComp-ACM /  アセトアミド アセトアミド | ||||
| #6: 化合物 |  コレステロール コレステロール#7: 化合物 | ChemComp-PLM / |  パルミチン酸 パルミチン酸#8: 化合物 | ChemComp-SO4 /  硫酸塩 硫酸塩 |
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 4.02 Å3/Da / 溶媒含有率: 69.42 % |
|---|---|
結晶化 | 温度: 293 K / 手法: 脂質キュービック相法 詳細: 30-35 %(v/v) PEG 400, 0.1-0.2 M Na2SO4, 0.1 M bis-tris propane pH 6.5-7.0 and 5-7 %(v/v) 1,4-butanediol |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X10SA / 波長: 1.03321 Å / ビームライン: X10SA / 波長: 1.03321 Å |
| 検出器 | タイプ: DECTRIS PILATUS 6M-F / 検出器: PIXEL / 日付: 2015年2月18日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長 : 1.03321 Å / 相対比: 1 : 1.03321 Å / 相対比: 1 |
| 反射 | 解像度: 3.8→50 Å / Num. obs: 6835 / % possible obs: 99.6 % / 冗長度: 6.5 % / Net I/σ(I): 3.76 |
| 反射 シェル | 解像度: 3.8→3.9 Å / 冗長度: 4.58 % / Mean I/σ(I) obs: 0.96 / % possible all: 98.8 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 分子置換開始モデル: 2rh1 解像度: 3.8→49.618 Å / SU ML: 0.52 / 交差検証法: THROUGHOUT / σ(F): 1.37 / 位相誤差: 33.87 / 立体化学のターゲット値: ML
| ||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 3.8→49.618 Å
| ||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||
| LS精密化 シェル |
|
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj