+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3epf | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of poliovirus receptor bound to poliovirus type 2 | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード |  VIRUS (ウイルス) / CD155 structure Immunoglobulin Superfamily / poliovirus capsid jelly role / VIRUS (ウイルス) / CD155 structure Immunoglobulin Superfamily / poliovirus capsid jelly role /  Cell adhesion (細胞接着) / Cell adhesion (細胞接着) /  Cell membrane (細胞膜) / Cell membrane (細胞膜) /  Glycoprotein (糖タンパク質) / Host-virus interaction / Glycoprotein (糖タンパク質) / Host-virus interaction /  Immunoglobulin domain (免疫グロブリンフォールド) / Immunoglobulin domain (免疫グロブリンフォールド) /  Membrane (生体膜) / Receptor / Membrane (生体膜) / Receptor /  Secreted (分泌) / Secreted (分泌) /  Transmembrane (膜貫通型タンパク質) / Transmembrane (膜貫通型タンパク質) /  VIRAL PROTEIN (ウイルスタンパク質) VIRAL PROTEIN (ウイルスタンパク質) | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報susceptibility to T cell mediated cytotoxicity / susceptibility to natural killer cell mediated cytotoxicity / Nectin/Necl trans heterodimerization / positive regulation of natural killer cell mediated cytotoxicity directed against tumor cell target / heterophilic cell-cell adhesion via plasma membrane cell adhesion molecules / positive regulation of natural killer cell mediated cytotoxicity / homophilic cell adhesion via plasma membrane adhesion molecules / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity /  ピコルナイン2A ...susceptibility to T cell mediated cytotoxicity / susceptibility to natural killer cell mediated cytotoxicity / Nectin/Necl trans heterodimerization / positive regulation of natural killer cell mediated cytotoxicity directed against tumor cell target / heterophilic cell-cell adhesion via plasma membrane cell adhesion molecules / positive regulation of natural killer cell mediated cytotoxicity / homophilic cell adhesion via plasma membrane adhesion molecules / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / ピコルナイン2A ...susceptibility to T cell mediated cytotoxicity / susceptibility to natural killer cell mediated cytotoxicity / Nectin/Necl trans heterodimerization / positive regulation of natural killer cell mediated cytotoxicity directed against tumor cell target / heterophilic cell-cell adhesion via plasma membrane cell adhesion molecules / positive regulation of natural killer cell mediated cytotoxicity / homophilic cell adhesion via plasma membrane adhesion molecules / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity /  ピコルナイン2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity / symbiont genome entry into host cell via pore formation in plasma membrane / ピコルナイン2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity / symbiont genome entry into host cell via pore formation in plasma membrane /  cell adhesion molecule binding / cell adhesion molecule binding /  picornain 3C / ribonucleoside triphosphate phosphatase activity / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / picornain 3C / ribonucleoside triphosphate phosphatase activity / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane /  接着結合 / 接着結合 /  : / Immunoregulatory interactions between a Lymphoid and a non-Lymphoid cell / nucleoside-triphosphate phosphatase / protein complex oligomerization / virus receptor activity / : / Immunoregulatory interactions between a Lymphoid and a non-Lymphoid cell / nucleoside-triphosphate phosphatase / protein complex oligomerization / virus receptor activity /  signaling receptor activity / monoatomic ion channel activity / signaling receptor activity / monoatomic ion channel activity /  DNA複製 / DNA複製 /  RNA helicase activity / receptor-mediated endocytosis of virus by host cell / induction by virus of host autophagy / RNA helicase activity / receptor-mediated endocytosis of virus by host cell / induction by virus of host autophagy /  RNA依存性RNAポリメラーゼ / symbiont-mediated suppression of host gene expression / viral RNA genome replication / cysteine-type endopeptidase activity / RNA依存性RNAポリメラーゼ / symbiont-mediated suppression of host gene expression / viral RNA genome replication / cysteine-type endopeptidase activity /  RNA-dependent RNA polymerase activity / RNA-dependent RNA polymerase activity /  focal adhesion / DNA-templated transcription / host cell nucleus / structural molecule activity / virion attachment to host cell / focal adhesion / DNA-templated transcription / host cell nucleus / structural molecule activity / virion attachment to host cell /  細胞膜 / 細胞膜 /  タンパク質分解 / タンパク質分解 /  extracellular space / extracellular space /  RNA binding / RNA binding /  ATP binding / ATP binding /  生体膜 / 生体膜 /  metal ion binding / metal ion binding /  細胞膜 / 細胞膜 /  細胞質 細胞質類似検索 - 分子機能 | ||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト)  Poliovirus type 2 (ポリオウイルス) Poliovirus type 2 (ポリオウイルス) | ||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 9 Å クライオ電子顕微鏡法 / 解像度: 9 Å | ||||||
 データ登録者 データ登録者 | Zhang, P. / Mueller, S. / Morais, M.C. / Bator, C.M. / Bowman, V.D. / Hafenstein, S. / Wimmer, E. / Rossmann, M.G. | ||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2008 ジャーナル: Proc Natl Acad Sci U S A / 年: 2008タイトル: Crystal structure of CD155 and electron microscopic studies of its complexes with polioviruses. 著者: Ping Zhang / Steffen Mueller / Marc C Morais / Carol M Bator / Valorie D Bowman / Susan Hafenstein / Eckard Wimmer / Michael G Rossmann /  要旨: When poliovirus (PV) recognizes its receptor, CD155, the virus changes from a 160S to a 135S particle before releasing its genome into the cytoplasm. CD155 is a transmembrane protein with 3 Ig-like ...When poliovirus (PV) recognizes its receptor, CD155, the virus changes from a 160S to a 135S particle before releasing its genome into the cytoplasm. CD155 is a transmembrane protein with 3 Ig-like extracellular domains, D1-D3, where D1 is recognized by the virus. The crystal structure of D1D2 has been determined to 3.5-A resolution and fitted into approximately 8.5-A resolution cryoelectron microscopy reconstructions of the virus-receptor complexes for the 3 PV serotypes. These structures show that, compared with human rhinoviruses, the virus-receptor interactions for PVs have a greater dependence on hydrophobic interactions, as might be required for a virus that can inhabit environments of different pH. The pocket factor was shown to remain in the virus during the first recognition stage. The present structures, when combined with earlier mutational investigations, show that in the subsequent entry stage the receptor moves further into the canyon when at a physiological temperature, thereby expelling the pocket factor and separating the viral subunits to form 135S particles. These results provide a detailed analysis of how a nonenveloped virus can enter its host cell. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3epf.cif.gz 3epf.cif.gz | 226.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3epf.ent.gz pdb3epf.ent.gz | 174.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3epf.json.gz 3epf.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ep/3epf https://data.pdbj.org/pub/pdb/validation_reports/ep/3epf ftp://data.pdbj.org/pub/pdb/validation_reports/ep/3epf ftp://data.pdbj.org/pub/pdb/validation_reports/ep/3epf | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
| 2 |
|
| 3 | x 5
|
| 4 | x 6
|
| 5 | 
|
| 対称性 | 点対称性: (シェーンフリース記号 : I (正20面体型対称 : I (正20面体型対称 )) )) |
- 要素
要素
-タンパク質 , 5種, 5分子 R1243
| #1: タンパク質 |  CD155 / Nectin-like protein 5 / Necl-5 CD155 / Nectin-like protein 5 / Necl-5分子量: 23330.514 Da / 分子数: 1 / 断片: Poliovirus receptor CD155 D1D2 / 変異: N105D, N120S, N188Q, N218Q, N237S / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: PVR, PVS / 発現宿主: Homo sapiens (ヒト) / 遺伝子: PVR, PVS / 発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P15151 Escherichia coli (大腸菌) / 参照: UniProt: P15151 |
|---|---|
| #2: タンパク質 | 分子量: 30734.535 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)   Poliovirus type 2 (ポリオウイルス) Poliovirus type 2 (ポリオウイルス)発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P06210 Escherichia coli (大腸菌) / 参照: UniProt: P06210 |
| #3: タンパク質 | 分子量: 29045.814 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)   Poliovirus type 2 (ポリオウイルス) Poliovirus type 2 (ポリオウイルス)発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P06210 Escherichia coli (大腸菌) / 参照: UniProt: P06210 |
| #4: タンパク質 | 分子量: 7346.957 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)   Poliovirus type 2 (ポリオウイルス) Poliovirus type 2 (ポリオウイルス)発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P06210 Escherichia coli (大腸菌) / 参照: UniProt: P06210 |
| #5: タンパク質 | 分子量: 26115.852 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)   Poliovirus type 2 (ポリオウイルス) Poliovirus type 2 (ポリオウイルス)発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P06210 Escherichia coli (大腸菌) / 参照: UniProt: P06210 |
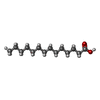
-非ポリマー , 3種, 273分子 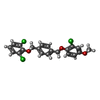



| #6: 化合物 | ChemComp-SC4 / |
|---|---|
| #7: 化合物 | ChemComp-MYR /  ミリスチン酸 ミリスチン酸 |
| #8: 水 | ChemComp-HOH /  水 水 |
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 / 詳細: 10mM Tris-HCl, 20mM NaCl | ||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES | ||||||||||||||||
急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 顕微鏡 | モデル: FEI/PHILIPS CM300FEG/T |
|---|---|
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy / 倍率(公称値): 47000 X / 最大 デフォーカス(公称値): 2745 nm / 最小 デフォーカス(公称値): 1236 nm Bright-field microscopy / 倍率(公称値): 47000 X / 最大 デフォーカス(公称値): 2745 nm / 最小 デフォーカス(公称値): 1236 nm |
| 撮影 | 電子線照射量: 20 e/Å2 / フィルム・検出器のモデル: KODAK SO-163 FILM |
- 解析
解析
| EMソフトウェア | 名称: EMfit / カテゴリ: モデルフィッティング | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 対称性 | 点対称性 : I (正20面体型対称 : I (正20面体型対称 ) ) | ||||||||||||
3次元再構成 | 解像度: 9 Å / ピクセルサイズ(公称値): 2.69 Å / ピクセルサイズ(実測値): 2.66 Å / 対称性のタイプ: POINT | ||||||||||||
| 原子モデル構築 | 空間: REAL | ||||||||||||
| 精密化ステップ | サイクル: LAST
|
 ムービー
ムービー コントローラー
コントローラー



















 PDBj
PDBj










