+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1nah | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | UDP-GALACTOSE 4-EPIMERASE FROM ESCHERICHIA COLI, REDUCED | |||||||||
 要素 要素 | UDP-GALACTOSE 4-EPIMERASE | |||||||||
 キーワード キーワード |  ISOMERASE (異性化酵素) ISOMERASE (異性化酵素) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報colanic acid biosynthetic process /  UDP-ガラクトース-4-エピメラーゼ / racemase and epimerase activity, acting on carbohydrates and derivatives / UDP-ガラクトース-4-エピメラーゼ / racemase and epimerase activity, acting on carbohydrates and derivatives /  UDP-glucose 4-epimerase activity / galactose catabolic process via UDP-galactose / galactose metabolic process / UDP-glucose 4-epimerase activity / galactose catabolic process via UDP-galactose / galactose metabolic process /  NAD+ binding / carbohydrate metabolic process / identical protein binding / NAD+ binding / carbohydrate metabolic process / identical protein binding /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | |||||||||
| 手法 |  X線回折 / 解像度: 1.8 Å X線回折 / 解像度: 1.8 Å | |||||||||
 データ登録者 データ登録者 | Thoden, J.B. / Frey, P.A. / Holden, H.M. | |||||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 1996 ジャーナル: Biochemistry / 年: 1996タイトル: Crystal structures of the oxidized and reduced forms of UDP-galactose 4-epimerase isolated from Escherichia coli. 著者: Thoden, J.B. / Frey, P.A. / Holden, H.M. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1nah.cif.gz 1nah.cif.gz | 95 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1nah.ent.gz pdb1nah.ent.gz | 69.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1nah.json.gz 1nah.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/na/1nah https://data.pdbj.org/pub/pdb/validation_reports/na/1nah ftp://data.pdbj.org/pub/pdb/validation_reports/na/1nah ftp://data.pdbj.org/pub/pdb/validation_reports/na/1nah | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| |||||||||
| 単位格子 |
| |||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 37294.016 Da / 分子数: 1 / 由来タイプ: 組換発現 / 詳細: REDUCED FORM / 由来: (組換発現)   Escherichia coli (大腸菌) / プラスミド: PT7E2 / 発現宿主: Escherichia coli (大腸菌) / プラスミド: PT7E2 / 発現宿主:   Escherichia coli (大腸菌) / 株 (発現宿主): BL21(DE3), PLYSS Escherichia coli (大腸菌) / 株 (発現宿主): BL21(DE3), PLYSS参照: UniProt: P09147,  UDP-ガラクトース-4-エピメラーゼ UDP-ガラクトース-4-エピメラーゼ |
|---|
-非ポリマー , 6種, 498分子 

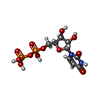








| #2: 化合物 | | #3: 化合物 | ChemComp-NAD / |  ニコチンアミドアデニンジヌクレオチド ニコチンアミドアデニンジヌクレオチド#4: 化合物 | ChemComp-UDP / |  ウリジン二リン酸 ウリジン二リン酸#5: 化合物 | ChemComp-EDO / |  エチレングリコール エチレングリコール#6: 化合物 | ChemComp-PEG / |  ジエチレングリコール ジエチレングリコール#7: 水 | ChemComp-HOH / |  水 水 |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.92 Å3/Da / 溶媒含有率: 57.93 % | ||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
結晶化 | *PLUS 温度: 4 ℃ / pH: 8 / 手法: 蒸気拡散法, ハンギングドロップ法 | ||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 放射 | 散乱光タイプ: x-ray |
|---|---|
| 放射波長 | 相対比: 1 |
| 反射 | Num. obs: 39891 / % possible obs: 97 % |
| 反射 | *PLUS 最高解像度: 1.8 Å / 最低解像度: 30 Å / Num. measured all: 72653 / Rmerge(I) obs: 0.021 |
| 反射 シェル | *PLUS 最高解像度: 1.8 Å / % possible obs: 94 % / Num. unique obs: 7216 / Num. measured obs: 10601 / Rmerge(I) obs: 0.076 |
- 解析
解析
| ソフトウェア | 名称: TNT / 分類: 精密化 | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 1.8→30 Å / 詳細: TNT /
| ||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.8→30 Å
| ||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||
| 精密化 | *PLUS Rfactor obs: 0.165 | ||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS | ||||||||||||||||||||||||||||||
| 拘束条件 | *PLUS
|
 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj







