+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9360 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
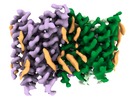
| タイトル | Structure of zebrafish Otop1 in nanodiscs | |||||||||
 マップデータ マップデータ | Structure of zfOtop1 in lipidic nanodiscs | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  Proton channel (プロトンポンプ) / Proton channel (プロトンポンプ) /  Otopetrin / Otopetrin /  MEMBRANE PROTEIN (膜タンパク質) MEMBRANE PROTEIN (膜タンパク質) | |||||||||
| 生物種 |   Danio rerio (ゼブラフィッシュ) Danio rerio (ゼブラフィッシュ) | |||||||||
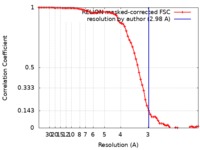
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.98 Å クライオ電子顕微鏡法 / 解像度: 2.98 Å | |||||||||
 データ登録者 データ登録者 | Saotome K / Lee WH | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2019 ジャーナル: Nat Struct Mol Biol / 年: 2019タイトル: Structures of the otopetrin proton channels Otop1 and Otop3. 著者: Kei Saotome / Bochuan Teng / Che Chun Alex Tsui / Wen-Hsin Lee / Yu-Hsiang Tu / Joshua P Kaplan / Mark S P Sansom / Emily R Liman / Andrew B Ward /   要旨: Otopetrins (Otop1-Otop3) comprise one of two known eukaryotic proton-selective channel families. Otop1 is required for otoconia formation and a candidate mammalian sour taste receptor. Here we report ...Otopetrins (Otop1-Otop3) comprise one of two known eukaryotic proton-selective channel families. Otop1 is required for otoconia formation and a candidate mammalian sour taste receptor. Here we report cryo-EM structures of zebrafish Otop1 and chicken Otop3 in lipid nanodiscs. The structures reveal a dimeric architecture, with each subunit forming 12 transmembrane helices divided into structurally similar amino (N) and carboxy (C) domains. Cholesterol-like molecules occupy various sites in Otop1 and Otop3 and occlude a central tunnel. In molecular dynamics simulations, hydrophilic vestibules formed by the N and C domains and in the intrasubunit interface between N and C domains form conduits for water entry into the membrane core, suggesting three potential proton conduction pathways. By mutagenesis, we tested the roles of charged residues in each putative permeation pathway. Our results provide a structural basis for understanding selective proton permeation and gating of this conserved family of proton channels. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9360.map.gz emd_9360.map.gz | 28.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9360-v30.xml emd-9360-v30.xml emd-9360.xml emd-9360.xml | 11.6 KB 11.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_9360_fsc.xml emd_9360_fsc.xml | 7.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_9360.png emd_9360.png | 197.6 KB | ||
| Filedesc metadata |  emd-9360.cif.gz emd-9360.cif.gz | 5.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9360 http://ftp.pdbj.org/pub/emdb/structures/EMD-9360 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9360 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9360 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9360.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9360.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Structure of zfOtop1 in lipidic nanodiscs | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.03 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Zebrafish Otopetrin1 in lipidic nanodiscs
| 全体 | 名称: Zebrafish Otopetrin1 in lipidic nanodiscs |
|---|---|
| 要素 |
|
-超分子 #1: Zebrafish Otopetrin1 in lipidic nanodiscs
| 超分子 | 名称: Zebrafish Otopetrin1 in lipidic nanodiscs / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Danio rerio (ゼブラフィッシュ) Danio rerio (ゼブラフィッシュ) |
| 分子量 | 理論値: 65853 kDa/nm |
-分子 #1: Otopetrin1
| 分子 | 名称: Otopetrin1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Danio rerio (ゼブラフィッシュ) Danio rerio (ゼブラフィッシュ) |
| 分子量 | 理論値: 65.817 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GPVEHGGTDS MWLNKYNPAA ASSASSSSSS DAENKLFSRL KVSLTKKYPQ KNAELLSAQY GTNLLLLGVS VMLALAAQSG PVKEEHLLS FITVLMLVQL VWMLCYMIRR ERERSPVPER DAHAGASWIR GGLTMLALLS LIMDAFRIGY FVGYHSCISA A LGVYPIVH ...文字列: GPVEHGGTDS MWLNKYNPAA ASSASSSSSS DAENKLFSRL KVSLTKKYPQ KNAELLSAQY GTNLLLLGVS VMLALAAQSG PVKEEHLLS FITVLMLVQL VWMLCYMIRR ERERSPVPER DAHAGASWIR GGLTMLALLS LIMDAFRIGY FVGYHSCISA A LGVYPIVH ALHTISQVHF LWFHIKDVIK KYETFERFGV IHAVFTNLLL WCNGVMSETE HFMHNHRRRL IEMGYANLST VD VQPHCNC TTSVCSMFST SLYYLYPFNI EYHIFVSAML FVMWKNIGRT LDRHSNRKRR STGSTGLLLG PLGGLVALAS SVS VLVVYL IHLEKTEEMH EAAVSMFYYY GVAMMACMCV GSGTGLLVYR MENRPMDTGS NPARTLDTEL LLASSLGSWL MSWC SVVAS VAEAGQKSPS FSWTSLTYSL LLVLEKCIQN LFIVESLYRR HSEEEEDAAA PQVFSVAVPP YDGILNHGYE AHDKH REAE PAAGSHALSR KQPDAPLPAG QRLDVTPGRK RQILKNICMF LFMCNISLWI LPAFGCRPQY DNPLENETFG TSVWTT VLN VAIPLNLFYR MHSVASLFEV FRKV |
-分子 #2: CHOLESTEROL HEMISUCCINATE
| 分子 | 名称: CHOLESTEROL HEMISUCCINATE / タイプ: ligand / ID: 2 / コピー数: 6 / 式: Y01 |
|---|---|
| 分子量 | 理論値: 486.726 Da |
| Chemical component information |  ChemComp-Y01: |
-分子 #3: CHOLESTEROL
| 分子 | 名称: CHOLESTEROL / タイプ: ligand / ID: 3 / コピー数: 2 / 式: CLR |
|---|---|
| 分子量 | 理論値: 386.654 Da |
| Chemical component information |  ChemComp-CLR: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.1 mg/mL |
|---|---|
| 緩衝液 | pH: 8 |
| グリッド | モデル: Quantifoil, UltrAuFoil, R1.2/1.3 / 材質: GOLD |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 283 K |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー