+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-8981 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM reconstruction of domain-swapped, glycan-reactive, neutralizing antibody 2G12 bound to HIV-1 Env BG505 DS-SOSIP, which was also bound to CD4-binding site antibody VRC03 | |||||||||
 マップデータ マップデータ | Refined map from cryoSparc postprocessed in Relion using map fro cryoSparc | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HIV-1 Env /  complex / complex /  neutralizing (中和抗体) / neutralizing (中和抗体) /  VIRAL PROTEIN (ウイルスタンパク質) / domain-swapped antibody VIRAL PROTEIN (ウイルスタンパク質) / domain-swapped antibody | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / virus-mediated perturbation of host defense response / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell /  viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane /  エンベロープ (ウイルス) ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / virus-mediated perturbation of host defense response / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / エンベロープ (ウイルス) ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / virus-mediated perturbation of host defense response / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell /  viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane /  エンベロープ (ウイルス) / structural molecule activity / virion attachment to host cell / host cell plasma membrane / virion membrane / identical protein binding / エンベロープ (ウイルス) / structural molecule activity / virion attachment to host cell / host cell plasma membrane / virion membrane / identical protein binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
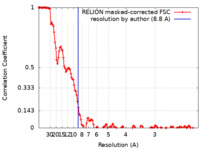
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 8.8 Å クライオ電子顕微鏡法 / 解像度: 8.8 Å | |||||||||
 データ登録者 データ登録者 | Acharya P / Kwong PD | |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2019 ジャーナル: Structure / 年: 2019タイトル: Structural Survey of Broadly Neutralizing Antibodies Targeting the HIV-1 Env Trimer Delineates Epitope Categories and Characteristics of Recognition. 著者: Gwo-Yu Chuang / Jing Zhou / Priyamvada Acharya / Reda Rawi / Chen-Hsiang Shen / Zizhang Sheng / Baoshan Zhang / Tongqing Zhou / Robert T Bailer / Venkata P Dandey / Nicole A Doria-Rose / Mark ...著者: Gwo-Yu Chuang / Jing Zhou / Priyamvada Acharya / Reda Rawi / Chen-Hsiang Shen / Zizhang Sheng / Baoshan Zhang / Tongqing Zhou / Robert T Bailer / Venkata P Dandey / Nicole A Doria-Rose / Mark K Louder / Krisha McKee / John R Mascola / Lawrence Shapiro / Peter D Kwong /  要旨: Over the past decade, structures have been determined for broadly neutralizing antibodies that recognize all major exposed surfaces of the prefusion-closed HIV-1-envelope (Env) trimer. To understand ...Over the past decade, structures have been determined for broadly neutralizing antibodies that recognize all major exposed surfaces of the prefusion-closed HIV-1-envelope (Env) trimer. To understand this recognition and its implications, we analyzed 206 antibody-HIV-1 Env structures from the Protein Data Bank with resolution suitable to define interaction chemistries and measured antibody neutralization on a 208-strain panel. Those with >25% breadth segregated into almost two dozen classes based on ontogeny and recognition and into six epitope categories based on recognized Env residues. For paratope, the number of protruding loops and level of somatic hypermutation were significantly higher for broad HIV-1 neutralizing antibodies than for a comparison set of non-HIV-1 antibodies (p < 0.0001). For epitope, the number of independent sequence segments was higher (p < 0.0001), as well as the glycan component surface area (p = 0.0005). The unusual characteristics of epitope and paratope delineated here are likely to reflect respectively virus-immune evasion and antibody-recognition solutions that allow effective neutralization of HIV-1. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_8981.map.gz emd_8981.map.gz | 11.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-8981-v30.xml emd-8981-v30.xml emd-8981.xml emd-8981.xml | 20.6 KB 20.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_8981_fsc.xml emd_8981_fsc.xml | 13.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_8981.png emd_8981.png | 94.7 KB | ||
| Filedesc metadata |  emd-8981.cif.gz emd-8981.cif.gz | 7.2 KB | ||
| その他 |  emd_8981_additional.map.gz emd_8981_additional.map.gz emd_8981_additional_1.map.gz emd_8981_additional_1.map.gz | 105.2 MB 105.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-8981 http://ftp.pdbj.org/pub/emdb/structures/EMD-8981 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-8981 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-8981 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_8981.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_8981.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Refined map from cryoSparc postprocessed in Relion using map fro cryoSparc | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.0961 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Unsharpened map from cryoSparc
| ファイル | emd_8981_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map from cryoSparc | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Unsharpened map from cryoSparc
| ファイル | emd_8981_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map from cryoSparc | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Ternary complex HIV-1 Env BG505 DS-SOSIP with Fab fragments of an...
| 全体 | 名称: Ternary complex HIV-1 Env BG505 DS-SOSIP with Fab fragments of antibodies 2G12 and VRC03. |
|---|---|
| 要素 |
|
-超分子 #1: Ternary complex HIV-1 Env BG505 DS-SOSIP with Fab fragments of an...
| 超分子 | 名称: Ternary complex HIV-1 Env BG505 DS-SOSIP with Fab fragments of antibodies 2G12 and VRC03. タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
-分子 #1: 2G12 Light chain
| 分子 | 名称: 2G12 Light chain / タイプ: protein_or_peptide / ID: 1 / コピー数: 6 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.130762 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: VVMTQSPSTL SASVGDTITI TCRASQSIET WLAWYQQKPG KAPKLLIYKA STLKTGVPSR FSGSGSGTEF TLTISGLQFD DFATYHCQH YAGYSATFGQ GTRVEIKRTV AAPSVFIFPP SDEQLKSGTA SVVCLLNNFY PREAKVQWKV DNALQSGNSQ E SVTEQDSK ...文字列: VVMTQSPSTL SASVGDTITI TCRASQSIET WLAWYQQKPG KAPKLLIYKA STLKTGVPSR FSGSGSGTEF TLTISGLQFD DFATYHCQH YAGYSATFGQ GTRVEIKRTV AAPSVFIFPP SDEQLKSGTA SVVCLLNNFY PREAKVQWKV DNALQSGNSQ E SVTEQDSK DSTYSLSSTL TLSKADYEKH KVYACEVTHQ GLSSPVTKSF NRGE |
-分子 #2: 2G12 heavy chain
| 分子 | 名称: 2G12 heavy chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 6 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.932869 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVESGGG LVKAGGSLIL SCGVSNFRIS AHTMNWVRRV PGGGLEWVAS ISTSSTYRDY ADAVKGRFTV SRDDLEDFVY LQMHKMRVE DTAIYYCARK GSDRLSDNDP FDAWGPGTVV TVSPASTKGP SVFPLAPSSK STSGGTAALG CLVKDYFPEP V TVSWNSGA ...文字列: EVQLVESGGG LVKAGGSLIL SCGVSNFRIS AHTMNWVRRV PGGGLEWVAS ISTSSTYRDY ADAVKGRFTV SRDDLEDFVY LQMHKMRVE DTAIYYCARK GSDRLSDNDP FDAWGPGTVV TVSPASTKGP SVFPLAPSSK STSGGTAALG CLVKDYFPEP V TVSWNSGA LTSGVHTFPA VLQSSGLYSL SSVVTVPSSS LGTQTYICNV NHKPSNTKVD KKVEPKS |
-分子 #3: Envelope glycoprotein gp120
| 分子 | 名称: Envelope glycoprotein gp120 / タイプ: protein_or_peptide / ID: 3 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 53.086102 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: AENLWVTVYY GVPVWKDAET TLFCASDAKA YETEKHNVWA THACVPTDPN PQEIHLENVT EEFNMWKNNM VEQMHTDIIS LWDQSLKPC VKLTPLCVTL QCTNVTNNIT DDMRGELKNC SFNMTTELRD KKQKVYSLFY RLDVVQINEN QGNRSNNSNK E YRLINCNT ...文字列: AENLWVTVYY GVPVWKDAET TLFCASDAKA YETEKHNVWA THACVPTDPN PQEIHLENVT EEFNMWKNNM VEQMHTDIIS LWDQSLKPC VKLTPLCVTL QCTNVTNNIT DDMRGELKNC SFNMTTELRD KKQKVYSLFY RLDVVQINEN QGNRSNNSNK E YRLINCNT SACTQACPKV SFEPIPIHYC APAGFAILKC KDKKFNGTGP CPSVSTVQCT HGIKPVVSTQ LLLNGSLAEE EV MIRSENI TNNAKNILVQ FNTPVQINCT RPNNNTRKSI RIGPGQAFYA TGDIIGDIRQ AHCNVSKATW NETLGKVVKQ LRK HFGNNT IIRFANSSGG DLEVTTHSFN CGGEFFYCNT SGLFNSTWIS NTSVQGSNST GSNDSITLPC RIKQIINMWQ RIGQ CMYAP PIQGVIRCVS NITGLILTRD GGSTNSTTET FRPGGGDMRD NWRSELYKYK VVKIEPLGVA PTRCKRRVV UniProtKB: Envelope glycoprotein gp160 |
-分子 #4: Envelope glycoprotein gp160
| 分子 | 名称: Envelope glycoprotein gp160 / タイプ: protein_or_peptide / ID: 4 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 19.102811 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: AVGIGAVFLG FLGAAGSTMG AASMTLTVQA RNLLSGIVQQ QSNLLRAPEA QQHLLKLTVW GIKQLQARVL AVERYLRDQQ LLGIWGCSG KLICCTNVPW NSSWSNRNLS EIWDNMTWLQ WDKEISNYTQ IIYGLLEESQ NQQEKNEQDL LALDGSAPTK A KRRVVQRE KR UniProtKB: Envelope glycoprotein gp160 |
-分子 #5: VRC03 heavy chain
| 分子 | 名称: VRC03 heavy chain / タイプ: protein_or_peptide / ID: 5 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.699861 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QVQLVQSGAV IKTPGSSVKI SCRASGYNFR DYSIHWVRLI PDKGFEWIGW IKPLWGAVSY ARQLQGRVSM TRQLSQDPDD PDWGVAYME FSGLTPADTA EYFCVRRGSC DYCGDFPWQY WCQGTVVVVS SASTKGPSVF PLAPSSGGTA ALGCLVKDYF P EPVTVSWN ...文字列: QVQLVQSGAV IKTPGSSVKI SCRASGYNFR DYSIHWVRLI PDKGFEWIGW IKPLWGAVSY ARQLQGRVSM TRQLSQDPDD PDWGVAYME FSGLTPADTA EYFCVRRGSC DYCGDFPWQY WCQGTVVVVS SASTKGPSVF PLAPSSGGTA ALGCLVKDYF P EPVTVSWN SGALTSGVHT FPAVLQSSGL YSLSSVVTVP SSSLGTQTYI CNVNHKPSNT KVDKKVEPK |
-分子 #6: VRC03 Light chain
| 分子 | 名称: VRC03 Light chain / タイプ: protein_or_peptide / ID: 6 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.043652 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EIVLTQSPGI LSLSPGETAT LFCKASQGGN AMTWYQKRRG QVPRLLIYDT SRRASGVPDR FVGSGSGTDF FLTINKLDRE DFAVYYCQQ FEFFGLGSEL EVHRTVAAPS VFIFPPSDEQ LKSGTASVVC LLNNFYPREA KVQWKVDNAL QSGNSQESVT E QDSKDSTY ...文字列: EIVLTQSPGI LSLSPGETAT LFCKASQGGN AMTWYQKRRG QVPRLLIYDT SRRASGVPDR FVGSGSGTDF FLTINKLDRE DFAVYYCQQ FEFFGLGSEL EVHRTVAAPS VFIFPPSDEQ LKSGTASVVC LLNNFYPREA KVQWKVDNAL QSGNSQESVT E QDSKDSTY SLSSTLTLSK ADYEKHKVYA CEVTHQGLSS PVTKSFNRGE |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.01 / 構成要素 - 濃度: 150.0 mM / 構成要素 - 名称: HEPES |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 298 K / 装置: SPOTITON 詳細: 0.005% dodecyl maltoside was added to sample before vitification. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 105000 Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 撮影したグリッド数: 1 / 実像数: 2206 / 平均露光時間: 10.0 sec. / 平均電子線量: 63.84 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
|---|---|
| 得られたモデル |  PDB-6e5p: |
 ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)