+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7860 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151 Fab | |||||||||
 マップデータ マップデータ | HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151 Fab, full map | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.9 Å クライオ電子顕微鏡法 / 解像度: 4.9 Å | |||||||||
 データ登録者 データ登録者 | Berndsens ZB / Rantalainen KR / Ward AB | |||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2018 ジャーナル: Cell Rep / 年: 2018タイトル: Co-evolution of HIV Envelope and Apex-Targeting Neutralizing Antibody Lineage Provides Benchmarks for Vaccine Design. 著者: Kimmo Rantalainen / Zachary T Berndsen / Sasha Murrell / Liwei Cao / Oluwarotimi Omorodion / Jonathan L Torres / Mengyu Wu / Jeffrey Umotoy / Jeffrey Copps / Pascal Poignard / Elise Landais / ...著者: Kimmo Rantalainen / Zachary T Berndsen / Sasha Murrell / Liwei Cao / Oluwarotimi Omorodion / Jonathan L Torres / Mengyu Wu / Jeffrey Umotoy / Jeffrey Copps / Pascal Poignard / Elise Landais / James C Paulson / Ian A Wilson / Andrew B Ward /  要旨: Broadly neutralizing antibodies (bnAbs) targeting the HIV envelope glycoprotein (Env) typically take years to develop. Longitudinal analyses of both neutralizing antibody lineages and viruses at ...Broadly neutralizing antibodies (bnAbs) targeting the HIV envelope glycoprotein (Env) typically take years to develop. Longitudinal analyses of both neutralizing antibody lineages and viruses at serial time points during infection provide a basis for understanding the co-evolutionary contest between HIV and the humoral immune system. Here, we describe the structural characterization of an apex-targeting antibody lineage and autologous clade A viral Env from a donor in the Protocol C cohort. Comparison of Ab-Env complexes at early and late time points reveals that, within the antibody lineage, the CDRH3 loop rigidifies, the bnAb angle of approach steepens, and surface charges are mutated to accommodate glycan changes. Additionally, we observed differences in site-specific glycosylation between soluble and full-length Env constructs, which may be important for tuning optimal immunogenicity in soluble Env trimers. These studies therefore provide important guideposts for design of immunogens that prime and mature nAb responses to the Env V2-apex. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7860.map.gz emd_7860.map.gz | 116.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7860-v30.xml emd-7860-v30.xml emd-7860.xml emd-7860.xml | 18.2 KB 18.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_7860_fsc.xml emd_7860_fsc.xml | 11.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_7860.png emd_7860.png | 98 KB | ||
| マスクデータ |  emd_7860_msk_1.map emd_7860_msk_1.map | 125 MB |  マスクマップ マスクマップ | |
| その他 |  emd_7860_half_map_1.map.gz emd_7860_half_map_1.map.gz emd_7860_half_map_2.map.gz emd_7860_half_map_2.map.gz | 98.3 MB 98.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7860 http://ftp.pdbj.org/pub/emdb/structures/EMD-7860 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7860 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7860 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7860.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7860.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151 Fab, full map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.03 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_7860_msk_1.map emd_7860_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
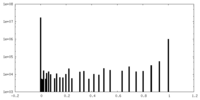
| 密度ヒストグラム |
-ハーフマップ: HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151...
| ファイル | emd_7860_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151 Fab, half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
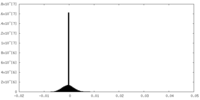
| 密度ヒストグラム |
-ハーフマップ: HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151...
| ファイル | emd_7860_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 complex with PGT151 Fab, half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : HIV-1 Envelope glycoprotein clone PC64M18C043.SOSIP.664 in comple...
| 全体 | 名称: HIV-1 Envelope glycoprotein clone PC64M18C043.SOSIP.664 in complex with PGT151 Fab |
|---|---|
| 要素 |
|
-超分子 #1: HIV-1 Envelope glycoprotein clone PC64M18C043.SOSIP.664 in comple...
| 超分子 | 名称: HIV-1 Envelope glycoprotein clone PC64M18C043.SOSIP.664 in complex with PGT151 Fab タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
-分子 #1: HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664
| 分子 | 名称: HIV-1 Envelope Glycoprotein clone PC64M18C043.SOSIP.664 タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MDAMKRGLCC VLLLCGAVFV SPSQEIHARF RRGARAANNL WVTVYYGVPV WRDAETTLFC ASDAKAYDTE VHNVWATHAC VPTDPSPQEI HLANVTEKFD MWKNSMVEQM HTDIISLWDE SLKPCVKLTP LCITLNCTNI TRNVTGGNLT EEGKEELKNC SFNATTELRD ...文字列: MDAMKRGLCC VLLLCGAVFV SPSQEIHARF RRGARAANNL WVTVYYGVPV WRDAETTLFC ASDAKAYDTE VHNVWATHAC VPTDPSPQEI HLANVTEKFD MWKNSMVEQM HTDIISLWDE SLKPCVKLTP LCITLNCTNI TRNVTGGNLT EEGKEELKNC SFNATTELRD KIQKVHSLFY RLDLVELNEG NSSDSNTSMY RLINCNTSAI TQACPKVSFE PIPIHYCAPA GFAILKCREK EFNGTGPCKK VSTVQCTHGI KPVVSTQLLL NGSLAEGKVK IRCENISNNA KTILVQLTTP VRINCTRPSN NTRTSIRIGP GQSFYATGDI IGDIRKAYCN VSESEWKEAL GKVVEQLRNH FNKTITFASS SGGDLEITTH SFNCGGEFFY CNTSSLFNST WDGNSATNST QVPNGTITLP CRIKQIINMW QRTGQAMYAP PIPGKIRCDS NITGLILIRD GGNNNNESET FRPGGGDMRN NWRSELYKYK VVKIDPLGVA PTGCKRRVVE RRRRRRAVGI GAVLFGFLGA AGSTMGAASL TLTVQARQLL SGIVQQQSNL LRAPEAQQHL LRLTVWGIKQ LQARVLAVER YLSDQQLLGI WGCSGKLICC TNVPWNSSWS NKSQDEIWNN MTWLQWDKEI SNYTDTIYYL IEKSQNQQEV NEKDLLALD |
-分子 #2: Immunoglobulin G PGT151 Fab, Heavy chain
| 分子 | 名称: Immunoglobulin G PGT151 Fab, Heavy chain / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: RVQLVESGGG VVQPGKSVRL SCVVSDFPFS KYPMYWVRQA PGKGLEWVAA ISGDAWHVVY SNSVQGRFLV SRDNVKNTLY LEMNSLKIE DTAVYRCARM FQESGPPRLD RWSGRNYYYY SGMDVWGQGT TVTVSSASTK GPSVFPLAPS SKSTSGGTAA L GCLVKDYF ...文字列: RVQLVESGGG VVQPGKSVRL SCVVSDFPFS KYPMYWVRQA PGKGLEWVAA ISGDAWHVVY SNSVQGRFLV SRDNVKNTLY LEMNSLKIE DTAVYRCARM FQESGPPRLD RWSGRNYYYY SGMDVWGQGT TVTVSSASTK GPSVFPLAPS SKSTSGGTAA L GCLVKDYF PEPVTVSWNS GALTSGVHTF PAVLQSSGLY SLSSVVTVPS SSLGTQTYIC NVNHKPSNTK VDKRVEPKSC DK |
-分子 #3: Immunoglobulin G PGT151, Light chain
| 分子 | 名称: Immunoglobulin G PGT151, Light chain / タイプ: protein_or_peptide / ID: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: DIVMTQTPLS LSVTPGQPAS ISCKSSESLR QSNGKTSLYW YRQKPGQSPQ LLVFEVSNRF SGVSDRFVGS GSGTDFTLRI SRVEAEDVG FYYCMQSKDF PLTFGGGTKV DLKRTVAAPS VFIFPPSDEQ LKSGTASVVC LLNNFYPREA KVQWKVDNAL Q SGNSQESV ...文字列: DIVMTQTPLS LSVTPGQPAS ISCKSSESLR QSNGKTSLYW YRQKPGQSPQ LLVFEVSNRF SGVSDRFVGS GSGTDFTLRI SRVEAEDVG FYYCMQSKDF PLTFGGGTKV DLKRTVAAPS VFIFPPSDEQ LKSGTASVVC LLNNFYPREA KVQWKVDNAL Q SGNSQESV TEQDSKDSTY SLSSTLTLSK ADYEKHKVYA CEVTHQGLSS PVTKSFNRGE C |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 7 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 詳細: Detergent removed with Biobeads prior to grid freezing |
| グリッド | モデル: C-flat-2/2 / 材質: COPPER / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm Bright-field microscopy / Cs: 2.7 mm |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 実像数: 1555 / 平均電子線量: 81.1 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




















 Z
Z Y
Y X
X