+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7601 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SARS spike glycoprotein, stabilized variant, S1 CTD configuration: ACE2-bound, downwards, upwards | |||||||||
 マップデータ マップデータ | SARS Spike Glycoprotein, Stabilized variant, single upwards S1 CTD conformation | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / positive regulation of amino acid transport /  アンジオテンシン変換酵素2 / positive regulation of L-proline import across plasma membrane / アンジオテンシン変換酵素2 / positive regulation of L-proline import across plasma membrane /  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; 金属プロテアーゼ / angiotensin-mediated drinking behavior / tryptophan transport / positive regulation of gap junction assembly ...Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / positive regulation of amino acid transport / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; 金属プロテアーゼ / angiotensin-mediated drinking behavior / tryptophan transport / positive regulation of gap junction assembly ...Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / positive regulation of amino acid transport /  アンジオテンシン変換酵素2 / positive regulation of L-proline import across plasma membrane / アンジオテンシン変換酵素2 / positive regulation of L-proline import across plasma membrane /  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; 金属プロテアーゼ / angiotensin-mediated drinking behavior / tryptophan transport / positive regulation of gap junction assembly / regulation of systemic arterial blood pressure by renin-angiotensin / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; 金属プロテアーゼ / angiotensin-mediated drinking behavior / tryptophan transport / positive regulation of gap junction assembly / regulation of systemic arterial blood pressure by renin-angiotensin /  regulation of vasoconstriction / regulation of cardiac conduction / peptidyl-dipeptidase activity / angiotensin maturation / maternal process involved in female pregnancy / Metabolism of Angiotensinogen to Angiotensins / regulation of vasoconstriction / regulation of cardiac conduction / peptidyl-dipeptidase activity / angiotensin maturation / maternal process involved in female pregnancy / Metabolism of Angiotensinogen to Angiotensins /  metallocarboxypeptidase activity / Attachment and Entry / negative regulation of signaling receptor activity / metallocarboxypeptidase activity / Attachment and Entry / negative regulation of signaling receptor activity /  carboxypeptidase activity / regulation of cytokine production / positive regulation of cardiac muscle contraction / carboxypeptidase activity / regulation of cytokine production / positive regulation of cardiac muscle contraction /  ウイルスのライフサイクル / blood vessel diameter maintenance / negative regulation of smooth muscle cell proliferation / regulation of transmembrane transporter activity / brush border membrane / ウイルスのライフサイクル / blood vessel diameter maintenance / negative regulation of smooth muscle cell proliferation / regulation of transmembrane transporter activity / brush border membrane /  繊毛 / endocytosis involved in viral entry into host cell / negative regulation of ERK1 and ERK2 cascade / endocytic vesicle membrane / SARS-CoV-1 activates/modulates innate immune responses / 繊毛 / endocytosis involved in viral entry into host cell / negative regulation of ERK1 and ERK2 cascade / endocytic vesicle membrane / SARS-CoV-1 activates/modulates innate immune responses /  metallopeptidase activity / positive regulation of reactive oxygen species metabolic process / virus receptor activity / regulation of cell population proliferation / metallopeptidase activity / positive regulation of reactive oxygen species metabolic process / virus receptor activity / regulation of cell population proliferation /  regulation of inflammatory response / regulation of inflammatory response /  endopeptidase activity / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / Potential therapeutics for SARS / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / entry receptor-mediated virion attachment to host cell / receptor-mediated endocytosis of virus by host cell / Attachment and Entry / endopeptidase activity / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / Potential therapeutics for SARS / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / entry receptor-mediated virion attachment to host cell / receptor-mediated endocytosis of virus by host cell / Attachment and Entry /  membrane fusion / positive regulation of viral entry into host cell / receptor-mediated virion attachment to host cell / host cell surface receptor binding / symbiont entry into host cell / membrane fusion / positive regulation of viral entry into host cell / receptor-mediated virion attachment to host cell / host cell surface receptor binding / symbiont entry into host cell /  脂質ラフト / apical plasma membrane / fusion of virus membrane with host plasma membrane / 脂質ラフト / apical plasma membrane / fusion of virus membrane with host plasma membrane /  小胞体 / fusion of virus membrane with host endosome membrane / 小胞体 / fusion of virus membrane with host endosome membrane /  エンベロープ (ウイルス) / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / host cell plasma membrane / virion membrane / エンベロープ (ウイルス) / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / host cell plasma membrane / virion membrane /  細胞膜 / 細胞膜 /  extracellular space / extracellular exosome / zinc ion binding / extracellular region / extracellular space / extracellular exosome / zinc ion binding / extracellular region /  生体膜 / identical protein binding / 生体膜 / identical protein binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   SARS coronavirus (SARS コロナウイルス) / SARS coronavirus (SARS コロナウイルス) /   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 7.6 Å クライオ電子顕微鏡法 / 解像度: 7.6 Å | |||||||||
 データ登録者 データ登録者 | Kirchdoerfer RN / Wang N / Pallesen J / Turner HL / Cottrell CA / McLellan JS / Ward AB | |||||||||
 引用 引用 |  ジャーナル: Sci Rep / 年: 2018 ジャーナル: Sci Rep / 年: 2018タイトル: Stabilized coronavirus spikes are resistant to conformational changes induced by receptor recognition or proteolysis. 著者: Robert N Kirchdoerfer / Nianshuang Wang / Jesper Pallesen / Daniel Wrapp / Hannah L Turner / Christopher A Cottrell / Kizzmekia S Corbett / Barney S Graham / Jason S McLellan / Andrew B Ward /  要旨: Severe acute respiratory syndrome coronavirus (SARS-CoV) emerged in 2002 as a highly transmissible pathogenic human betacoronavirus. The viral spike glycoprotein (S) utilizes angiotensin-converting ...Severe acute respiratory syndrome coronavirus (SARS-CoV) emerged in 2002 as a highly transmissible pathogenic human betacoronavirus. The viral spike glycoprotein (S) utilizes angiotensin-converting enzyme 2 (ACE2) as a host protein receptor and mediates fusion of the viral and host membranes, making S essential to viral entry into host cells and host species tropism. As SARS-CoV enters host cells, the viral S is believed to undergo a number of conformational transitions as it is cleaved by host proteases and binds to host receptors. We recently developed stabilizing mutations for coronavirus spikes that prevent the transition from the pre-fusion to post-fusion states. Here, we present cryo-EM analyses of a stabilized trimeric SARS-CoV S, as well as the trypsin-cleaved, stabilized S, and its interactions with ACE2. Neither binding to ACE2 nor cleavage by trypsin at the S1/S2 cleavage site impart large conformational changes within stabilized SARS-CoV S or expose the secondary cleavage site, S2'. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
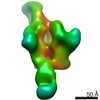
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7601.map.gz emd_7601.map.gz | 162.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7601-v30.xml emd-7601-v30.xml emd-7601.xml emd-7601.xml | 19.7 KB 19.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_7601_fsc.xml emd_7601_fsc.xml | 12.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_7601.png emd_7601.png | 84.9 KB | ||
| マスクデータ |  emd_7601_msk_1.map emd_7601_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| その他 |  emd_7601_half_map_1.map.gz emd_7601_half_map_1.map.gz emd_7601_half_map_2.map.gz emd_7601_half_map_2.map.gz | 140.3 MB 140.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7601 http://ftp.pdbj.org/pub/emdb/structures/EMD-7601 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7601 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7601 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7573C  7574C  7575C  7576C  7577C  7578C  7579C  7580C  7581C  7582C  7584C  7585C  7586C  7602C  7603C  7604C  7605C  7606C  7607C  7608C  6crvC  6crwC  6crxC  6crzC  6cs0C  6cs1C  6cs2C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7601.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7601.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | SARS Spike Glycoprotein, Stabilized variant, single upwards S1 CTD conformation | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.03 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_7601_msk_1.map emd_7601_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
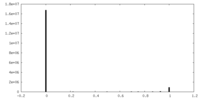
| 投影像・断面図 |
| ||||||||||||
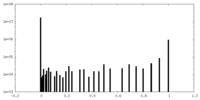
| 密度ヒストグラム |
-ハーフマップ: SARS Spike Glycoprotein, Stabilized variant, single upwards S1...
| ファイル | emd_7601_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | SARS Spike Glycoprotein, Stabilized variant, single upwards S1 CTD conformation | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: SARS Spike Glycoprotein, Stabilized variant, single upwards S1...
| ファイル | emd_7601_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | SARS Spike Glycoprotein, Stabilized variant, single upwards S1 CTD conformation | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SARS Spike Glycoprotein complexed to ACE2 receptor
| 全体 | 名称: SARS Spike Glycoprotein complexed to ACE2 receptor |
|---|---|
| 要素 |
|
-超分子 #1: SARS Spike Glycoprotein complexed to ACE2 receptor
| 超分子 | 名称: SARS Spike Glycoprotein complexed to ACE2 receptor / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   SARS coronavirus (SARS コロナウイルス) / 株: Tor2 SARS coronavirus (SARS コロナウイルス) / 株: Tor2 |
| 組換発現 | 生物種:   Homo sapiens (ヒト) / 組換細胞: HEK293F Homo sapiens (ヒト) / 組換細胞: HEK293F |
| 分子量 | 理論値: 620 KDa |
-分子 #1: SARS spike glycoprotein
| 分子 | 名称: SARS spike glycoprotein / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   SARS coronavirus (SARS コロナウイルス) / 株: Tor2 SARS coronavirus (SARS コロナウイルス) / 株: Tor2 |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: SDLDRCTTFD DVQAPNYTQH TSSMRGVYYP DEIFRSDTLY LTQDLFLPFY SNVTGFHTIN HTFGNPVIPF KDGIYFAATE KSNVVRGWVF GSTMNNKSQS VIIINNSTNV VIRACNFELC DNPFFAVSKP MGTQTHTMIF DNAFNCTFEY ISDAFSLDVS EKSGNFKHLR ...文字列: SDLDRCTTFD DVQAPNYTQH TSSMRGVYYP DEIFRSDTLY LTQDLFLPFY SNVTGFHTIN HTFGNPVIPF KDGIYFAATE KSNVVRGWVF GSTMNNKSQS VIIINNSTNV VIRACNFELC DNPFFAVSKP MGTQTHTMIF DNAFNCTFEY ISDAFSLDVS EKSGNFKHLR EFVFKNKDGF LYVYKGYQPI DVVRDLPSGF NTLKPIFKLP LGINITNFRA ILTAFSPAQD IWGTSAAAYF VGYLKPTTFM LKYDENGTIT DAVDCSQNPL AELKCSVKSF EIDKGIYQTS NFRVVPSGDV VRFPNITNLC PFGEVFNATK FPSVYAWERK KISNCVADYS VLYNSTFFST FKCYGVSATK LNDLCFSNVY ADSFVVKGDD VRQIAPGQTG VIADYNYKLP DDFMGCVLAW NTRNIDATST GNYNYKYRYL RHGKLRPFER DISNVPFSPD GKPCTPPALN CYWPLNDYGF YTTTGIGYQP YRVVVLSFEL LNAPATVCGP KLSTDLIKNQ CVNFNFNGLT GTGVLTPSSK RFQPFQQFGR DVSDFTDSVR DPKTSEILDI SPCAFGGVSV ITPGTNASSE VAVLYQDVNC TDVSTAIHAD QLTPAWRIYS TGNNVFQTQA GCLIGAEHVD TSYECDIPIG AGICASYHTV SLLRSTSQKS IVAYTMSLGA DSSIAYSNNT IAIPTNFSIS ITTEVMPVSM AKTSVDCNMY ICGDSTECAN LLLQYGSFCT QLNRALSGIA AEQDRNTREV FAQVKQMYKT PTLKYFGGFN FSQILPDPLK PTKRSFIEDL LFNKVTLADA GFMKQYGECL GDINARDLIC AQKFNGLTVL PPLLTDDMIA AYTAALVSGT ATAGWTFGAG AALQIPFAMQ MAYRFNGIGV TQNVLYENQK QIANQFNKAI SQIQESLTTT STALGKLQDV VNQNAQALNT LVKQLSSNFG AISSVLNDIL SRLDPPEAEV QIDRLITGRL QSLQTYVTQQ LIRAAEIRAS ANLAATKMSE CVLGQSKRVD FCGKGYHLMS FPQAAPHGVV FLHVTYVPSQ ERNFTTAPAI CHEGKAYFPR EGVFVFNGTS WFITQRNFFS PQIITTDNTF VSGNCDVVIG IINNTVYDPL QPELDSFKEE LDKYFKNHTS PDVDLGDISG INASVVNIQK EIDRLNEVAK NLNESLIDLQ ELGKYEQGSG YIPEAPRDGQ AYVRKDGEWV LLSTFLGRSL EVLFQ |
-分子 #2: Angiotensin converting enzyme 2
| 分子 | 名称: Angiotensin converting enzyme 2 / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: STIEEQAKTF LDKFNHEAED LFYQSSLASW NYNTNITEEN VQNMNNAGDK WSAFLKEQST LAQMYPLQEI QNLTVKLQLQ ALQQNGSSVL SEDKSKRLNT ILNTMSTIYS TGKVCNPDNP QECLLLEPGL NEIMANSLDY NERLWAWESW RSEVGKQLRP LYEEYVVLKN ...文字列: STIEEQAKTF LDKFNHEAED LFYQSSLASW NYNTNITEEN VQNMNNAGDK WSAFLKEQST LAQMYPLQEI QNLTVKLQLQ ALQQNGSSVL SEDKSKRLNT ILNTMSTIYS TGKVCNPDNP QECLLLEPGL NEIMANSLDY NERLWAWESW RSEVGKQLRP LYEEYVVLKN EMARANHYED YGDYWRGDYE VNGVDGYDYS RGQLIEDVEH TFEEIKPLYE HLHAYVRAKL MNAYPSYISP IGCLPAHLLG DMWGRFWTNL YSLTVPFGQK PNIDVTDAMV DQAWDAQRIF KEAEKFFVSV GLPNMTQGFW ENSMLTDPGN VQKAVCHPTA WDLGKGDFRI LMCTKVTMDD FLTAHHEMGH IQYDMAYAAQ PFLLRNGANE GFHEAVGEIM SLSAATPKHL KSIGLLSPDF QEDNETEINF LLKQALTIVG TLPFTYMLEK WRWMVFKGEI PKDQWMKKWW EMKREIVGVV EPVPHDETYC DPASLFHVSN DYSFIRYYTR TLYQFQFQEA LCQAAKHEGP LHKCDISNST EAGQKLFNML RLGKSEPWTL ALENVVGAKN MNVRPLLNYF EPLFTWLKDQ NKNSFVGWST DWSPYADGSL EVLFQ |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.35 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: C-flat-2/2 4C / 材質: COPPER / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: PLASMA CLEANING / 前処理 - 雰囲気: OTHER | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 29000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 29000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 撮影したグリッド数: 1 / 平均露光時間: 0.25 sec. / 平均電子線量: 65.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー













 Z
Z Y
Y X
X