[日本語] English
 万見
万見- EMDB-7343: Ebola nucleoprotein nucleocapsid-like assembly and the asymmetric unit -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7343 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Ebola nucleoprotein nucleocapsid-like assembly and the asymmetric unit | ||||||||||||||||||||||||
 マップデータ マップデータ | Ebola nucleoprotein nucleocapsid-like assembly | ||||||||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||||||||
 キーワード キーワード |  Ebola (エボラ出血熱) / Ebola (エボラ出血熱) /  nucleoprotein (核タンパク質) / nucleoprotein (核タンパク質) /  nucleocapsid (カプシド) / helical reconstruction / nucleocapsid (カプシド) / helical reconstruction /  RNA BINDING PROTEIN (RNA結合タンパク質) RNA BINDING PROTEIN (RNA結合タンパク質) | ||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報viral RNA genome packaging / helical viral capsid / viral nucleocapsid / host cell cytoplasm /  ribonucleoprotein complex / ribonucleoprotein complex /  RNA binding RNA binding類似検索 - 分子機能 | ||||||||||||||||||||||||
| 生物種 |   Zaire ebolavirus (エボラウイルス) Zaire ebolavirus (エボラウイルス) | ||||||||||||||||||||||||
| 手法 | らせん対称体再構成法 /  クライオ電子顕微鏡法 / 解像度: 5.8 Å クライオ電子顕微鏡法 / 解像度: 5.8 Å | ||||||||||||||||||||||||
 データ登録者 データ登録者 | Su Z / Wu C / Pintilie GD / Chiu W / Amarasinghe GK / Leung DW | ||||||||||||||||||||||||
| 資金援助 |  米国, 7件 米国, 7件
| ||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2015 ジャーナル: Cell Rep / 年: 2015タイトル: An Intrinsically Disordered Peptide from Ebola Virus VP35 Controls Viral RNA Synthesis by Modulating Nucleoprotein-RNA Interactions. 著者: Daisy W Leung / Dominika Borek / Priya Luthra / Jennifer M Binning / Manu Anantpadma / Gai Liu / Ian B Harvey / Zhaoming Su / Ariel Endlich-Frazier / Juanli Pan / Reed S Shabman / Wah Chiu / ...著者: Daisy W Leung / Dominika Borek / Priya Luthra / Jennifer M Binning / Manu Anantpadma / Gai Liu / Ian B Harvey / Zhaoming Su / Ariel Endlich-Frazier / Juanli Pan / Reed S Shabman / Wah Chiu / Robert A Davey / Zbyszek Otwinowski / Christopher F Basler / Gaya K Amarasinghe /  要旨: During viral RNA synthesis, Ebola virus (EBOV) nucleoprotein (NP) alternates between an RNA-template-bound form and a template-free form to provide the viral polymerase access to the RNA template. In ...During viral RNA synthesis, Ebola virus (EBOV) nucleoprotein (NP) alternates between an RNA-template-bound form and a template-free form to provide the viral polymerase access to the RNA template. In addition, newly synthesized NP must be prevented from indiscriminately binding to noncognate RNAs. Here, we investigate the molecular bases for these critical processes. We identify an intrinsically disordered peptide derived from EBOV VP35 (NPBP, residues 20-48) that binds NP with high affinity and specificity, inhibits NP oligomerization, and releases RNA from NP-RNA complexes in vitro. The structure of the NPBP/ΔNPNTD complex, solved to 3.7 Å resolution, reveals how NPBP peptide occludes a large surface area that is important for NP-NP and NP-RNA interactions and for viral RNA synthesis. Together, our results identify a highly conserved viral interface that is important for EBOV replication and can be targeted for therapeutic development. | ||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7343.map.gz emd_7343.map.gz | 11.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7343-v30.xml emd-7343-v30.xml emd-7343.xml emd-7343.xml | 19.5 KB 19.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_7343.png emd_7343.png | 204.8 KB | ||
| Filedesc metadata |  emd-7343.cif.gz emd-7343.cif.gz | 6.5 KB | ||
| その他 |  emd_7343_additional.map.gz emd_7343_additional.map.gz emd_7343_additional_1.map.gz emd_7343_additional_1.map.gz | 117.5 KB 117.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7343 http://ftp.pdbj.org/pub/emdb/structures/EMD-7343 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7343 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7343 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7343.map.gz / 形式: CCP4 / 大きさ: 70.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7343.map.gz / 形式: CCP4 / 大きさ: 70.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ebola nucleoprotein nucleocapsid-like assembly | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.4 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Ebola nucleoprotein asymmetric unit
| ファイル | emd_7343_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ebola nucleoprotein asymmetric unit | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
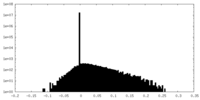
| 密度ヒストグラム |
-追加マップ: Ebola nucleoprotein asymmetric unit
| ファイル | emd_7343_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ebola nucleoprotein asymmetric unit | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : eNP nucleocapsid-like assembly
| 全体 | 名称: eNP nucleocapsid-like assembly |
|---|---|
| 要素 |
|
-超分子 #1: eNP nucleocapsid-like assembly
| 超分子 | 名称: eNP nucleocapsid-like assembly / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Zaire ebolavirus (エボラウイルス) Zaire ebolavirus (エボラウイルス) |
-分子 #1: Nucleoprotein
| 分子 | 名称: Nucleoprotein / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Zaire ebolavirus (エボラウイルス) Zaire ebolavirus (エボラウイルス) |
| 分子量 | 理論値: 48.14259 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: LTAGLSVQQG IVRQRVIPVY QVNNLEEICQ LIIQAFEAGV DFQESADSFL LMLCLHHAYQ GDYKLFLESG AVKYLEGHGF RFEVKKRDG VKRLEELLPA VSSGKNIKRT LAAMPEEETT EANAGQFLSF ASLFLPKLVV GEKACLEKVQ RQIQVHAEQG L IQYPTAWQ ...文字列: LTAGLSVQQG IVRQRVIPVY QVNNLEEICQ LIIQAFEAGV DFQESADSFL LMLCLHHAYQ GDYKLFLESG AVKYLEGHGF RFEVKKRDG VKRLEELLPA VSSGKNIKRT LAAMPEEETT EANAGQFLSF ASLFLPKLVV GEKACLEKVQ RQIQVHAEQG L IQYPTAWQ SVGHMMVIFR LMRTNFLIKF LLIHQGMHMV AGHDANDAVI SNSVAQARFS GLLIVKTVLD HILQKTERGV RL HPLARTA KVKNEVNSFK AALSSLAKHG EYAPFARLLN LSGVNNLEHG LFPQLSAIAL GVATAHGSTL AGVNVGEQYQ QLR EAATEA EKQLQQYAES RELDHLGLDD QEKKILMNFH QKKNEISFQQ TNAMVTLRKE RLAKLTEAIT AASLPKTSGH YDDD DDIPF PGPINDDDNP GHQDDDPTDS QDTTIPDV UniProtKB:  核タンパク質 核タンパク質 |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 構成要素 - 濃度: 12.0 mM / 構成要素 - 式: PBS / 構成要素 - 名称: Phosphate-buffered saline / 詳細: 150 mM NaCl, 3 mM KCl, 10 mM Na2HPO4, 2 mM KH2PO4 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 40 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 283 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 3200FSC |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 4.7 mm / 倍率(公称値): 30000 Bright-field microscopy / Cs: 4.7 mm / 倍率(公称値): 30000 |
| 特殊光学系 | エネルギーフィルター - 名称: In-column Omega Filter エネルギーフィルター - エネルギー下限: 30 eV エネルギーフィルター - エネルギー上限: 30 eV |
| 試料ステージ | 試料ホルダーモデル: JEOL 3200FSC CRYOHOLDER / ホルダー冷却材: NITROGEN |
| 温度 | 最低: 86.0 K / 最高: 86.0 K |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3838 pixel / デジタル化 - サイズ - 縦: 3710 pixel / デジタル化 - 画像ごとのフレーム数: 2-32 / 撮影したグリッド数: 2 / 実像数: 1266 / 平均露光時間: 8.0 sec. / 平均電子線量: 24.0 e/Å2 |
- 画像解析
画像解析
| Segment selection | 選択した数: 200685 |
|---|---|
| 初期モデル | モデルのタイプ: NONE |
| 最終 角度割当 | タイプ: NOT APPLICABLE / ソフトウェア - 名称: RELION (ver. 2-beta) |
| 最終 再構成 | 想定した対称性 - らせんパラメータ - Δz: 2.65 Å 想定した対称性 - らせんパラメータ - ΔΦ: -8.53 ° 想定した対称性 - らせんパラメータ - 軸対称性: C1 (非対称) 解像度のタイプ: BY AUTHOR / 解像度: 5.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 2-beta) / 使用した粒子像数: 169526 |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 温度因子: 276 / 当てはまり具合の基準: Correlation coefficient |
|---|---|
| 得られたモデル |  PDB-6c54: |
 ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X