+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-6999 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of T=1 Penaeus vannamei nodavirus | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  Nodaviridae / shrimp nodavirus / Nodaviridae / shrimp nodavirus /  VIRUS LIKE PARTICLE (ウイルス様粒子) VIRUS LIKE PARTICLE (ウイルス様粒子) | |||||||||
| 機能・相同性 | Icosahedral viral capsid protein, S domain /  Viral coat protein (S domain) / T=3 icosahedral viral capsid / Viral coat protein (S domain) / T=3 icosahedral viral capsid /  Viral coat protein subunit / structural molecule activity / Viral coat protein subunit / structural molecule activity /  カプシド カプシド 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Penaeus vannamei nodavirus (ウイルス) Penaeus vannamei nodavirus (ウイルス) | |||||||||
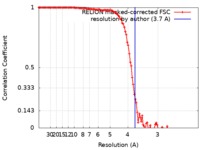
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.7 Å クライオ電子顕微鏡法 / 解像度: 3.7 Å | |||||||||
 データ登録者 データ登録者 | Chen NC / Miyazaki N | |||||||||
| 資金援助 |  台湾, 1件 台湾, 1件
| |||||||||
 引用 引用 |  ジャーナル: Commun Biol / 年: 2019 ジャーナル: Commun Biol / 年: 2019タイトル: The atomic structures of shrimp nodaviruses reveal new dimeric spike structures and particle polymorphism. 著者: Nai-Chi Chen / Masato Yoshimura / Naoyuki Miyazaki / Hong-Hsiang Guan / Phimonphan Chuankhayan / Chien-Chih Lin / Shao-Kang Chen / Pei-Ju Lin / Yen-Chieh Huang / Kenji Iwasaki / Atsushi ...著者: Nai-Chi Chen / Masato Yoshimura / Naoyuki Miyazaki / Hong-Hsiang Guan / Phimonphan Chuankhayan / Chien-Chih Lin / Shao-Kang Chen / Pei-Ju Lin / Yen-Chieh Huang / Kenji Iwasaki / Atsushi Nakagawa / Sunney I Chan / Chun-Jung Chen /    要旨: Shrimp nodaviruses, including (PvNV) and nodaviruses (MrNV), cause white-tail disease in shrimps, with high mortality. The viral capsid structure determines viral assembly and host specificity ...Shrimp nodaviruses, including (PvNV) and nodaviruses (MrNV), cause white-tail disease in shrimps, with high mortality. The viral capsid structure determines viral assembly and host specificity during infections. Here, we show cryo-EM structures of = 3 and = 1 PvNV-like particles (PvNV-LPs), crystal structures of the protrusion-domains (P-domains) of PvNV and MrNV, and the crystal structure of the ∆N-ARM-PvNV shell-domain (S-domain) in = 1 subviral particles. The capsid protein of PvNV reveals five domains: the P-domain with a new jelly-roll structure forming cuboid-like spikes; the jelly-roll S-domain with two calcium ions; the linker between the S- and P-domains exhibiting new cross and parallel conformations; the N-arm interacting with nucleotides organized along icosahedral two-fold axes; and a disordered region comprising the basic -terminal arginine-rich motif (N-ARM) interacting with RNA. The N-ARM controls = 3 and = 1 assemblies. Increasing the /-termini flexibility leads to particle polymorphism. Linker flexibility may influence the dimeric-spike arrangement. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_6999.map.gz emd_6999.map.gz | 21.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-6999-v30.xml emd-6999-v30.xml emd-6999.xml emd-6999.xml | 13.4 KB 13.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_6999_fsc.xml emd_6999_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_6999.png emd_6999.png | 88.7 KB | ||
| Filedesc metadata |  emd-6999.cif.gz emd-6999.cif.gz | 5.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-6999 http://ftp.pdbj.org/pub/emdb/structures/EMD-6999 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6999 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6999 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_6999.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_6999.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.12 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Penaeus vannamei nodavirus
| 全体 | 名称:  Penaeus vannamei nodavirus (ウイルス) Penaeus vannamei nodavirus (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Penaeus vannamei nodavirus
| 超分子 | 名称: Penaeus vannamei nodavirus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / NCBI-ID: 430911 / 生物種: Penaeus vannamei nodavirus / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:   Litopenaeus vannamei (バナメイエビ) Litopenaeus vannamei (バナメイエビ) |
-分子 #1: Capsid protein
| 分子 | 名称: Capsid protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Penaeus vannamei nodavirus (ウイルス) Penaeus vannamei nodavirus (ウイルス) |
| 分子量 | 理論値: 40.262168 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MKRKPNSNQN NNNNRGNGNG LRRVRGGRVS RRRVVINQSN QSMPVTSNGA PLQALTSYSR PNVNKISRLG PDSDFLTSVV AKASTSIVT PADRILVKQP LSASSFPGTR ITGLSSYWER YKWLSAVARY VPAVPNTVAC QFVMYIDTDP LDDPSNISDD N QIVRQAVS ...文字列: MKRKPNSNQN NNNNRGNGNG LRRVRGGRVS RRRVVINQSN QSMPVTSNGA PLQALTSYSR PNVNKISRLG PDSDFLTSVV AKASTSIVT PADRILVKQP LSASSFPGTR ITGLSSYWER YKWLSAVARY VPAVPNTVAC QFVMYIDTDP LDDPSNISDD N QIVRQAVS QAGSNQFNFN TSKTVPLIVR ADNQYYYTGV DKQNLRFSLQ GILYIIQVTD LINFNGELIT QDLTCGSLFL DW LVNFSIP QINPTSLTDV RVDKAVNFIK PEVSGVAEIQ TVTGLSPSTS YLLTPAFLEQ NFQSEAGIYI LSATPVEGEG TIS INMDPT VTTVSGFIKV KTDTFGTFDL SVVLTTASKK QTTGFNIIAA TS UniProtKB:  カプシド カプシド |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 6 mg/mL | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
| |||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: MOLYBDENUM / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE | |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 0.01 mm / 最大 デフォーカス(公称値): 2.75 µm / 最小 デフォーカス(公称値): 1.25 µm / 倍率(公称値): 59000 Bright-field microscopy / Cs: 0.01 mm / 最大 デフォーカス(公称値): 2.75 µm / 最小 デフォーカス(公称値): 1.25 µm / 倍率(公称値): 59000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 2806 / 平均露光時間: 2.0 sec. / 平均電子線量: 40.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー