+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4746 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of calcium-bound human TMEM16K / Anoctamin 10 in detergent (2mM Ca2+, closed form) | |||||||||
 マップデータ マップデータ | RELION3 post processed map sharpened with a bfactor of -112A**2 | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報intracellularly calcium-gated chloride channel activity / calcium-activated cation channel activity / chloride transport /  chloride channel activity / monoatomic cation transport / chloride transmembrane transport / monoatomic ion transmembrane transport / Stimuli-sensing channels / Induction of Cell-Cell Fusion / intracellular membrane-bounded organelle ...intracellularly calcium-gated chloride channel activity / calcium-activated cation channel activity / chloride transport / chloride channel activity / monoatomic cation transport / chloride transmembrane transport / monoatomic ion transmembrane transport / Stimuli-sensing channels / Induction of Cell-Cell Fusion / intracellular membrane-bounded organelle ...intracellularly calcium-gated chloride channel activity / calcium-activated cation channel activity / chloride transport /  chloride channel activity / monoatomic cation transport / chloride transmembrane transport / monoatomic ion transmembrane transport / Stimuli-sensing channels / Induction of Cell-Cell Fusion / intracellular membrane-bounded organelle / chloride channel activity / monoatomic cation transport / chloride transmembrane transport / monoatomic ion transmembrane transport / Stimuli-sensing channels / Induction of Cell-Cell Fusion / intracellular membrane-bounded organelle /  生体膜 / 生体膜 /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
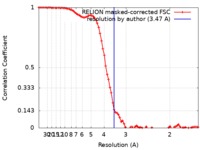
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.47 Å クライオ電子顕微鏡法 / 解像度: 3.47 Å | |||||||||
 データ登録者 データ登録者 | Pike ACW / Bushell SR / Shintre CA / Tessitore A / Baronina A / Chu A / Mukhopadhyay S / Shrestha L / Chalk R / Burgess-Brown NA ...Pike ACW / Bushell SR / Shintre CA / Tessitore A / Baronina A / Chu A / Mukhopadhyay S / Shrestha L / Chalk R / Burgess-Brown NA / Love J / Huiskonen JT / Edwards AM / Arrowsmith CH / Bountra C / Carpenter EP / Structural Genomics Consortium (SGC) | |||||||||
| 資金援助 |  英国, 2件 英国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019タイトル: The structural basis of lipid scrambling and inactivation in the endoplasmic reticulum scramblase TMEM16K. 著者: Simon R Bushell / Ashley C W Pike / Maria E Falzone / Nils J G Rorsman / Chau M Ta / Robin A Corey / Thomas D Newport / John C Christianson / Lara F Scofano / Chitra A Shintre / Annamaria ...著者: Simon R Bushell / Ashley C W Pike / Maria E Falzone / Nils J G Rorsman / Chau M Ta / Robin A Corey / Thomas D Newport / John C Christianson / Lara F Scofano / Chitra A Shintre / Annamaria Tessitore / Amy Chu / Qinrui Wang / Leela Shrestha / Shubhashish M M Mukhopadhyay / James D Love / Nicola A Burgess-Brown / Rebecca Sitsapesan / Phillip J Stansfeld / Juha T Huiskonen / Paolo Tammaro / Alessio Accardi / Elisabeth P Carpenter /    要旨: Membranes in cells have defined distributions of lipids in each leaflet, controlled by lipid scramblases and flip/floppases. However, for some intracellular membranes such as the endoplasmic ...Membranes in cells have defined distributions of lipids in each leaflet, controlled by lipid scramblases and flip/floppases. However, for some intracellular membranes such as the endoplasmic reticulum (ER) the scramblases have not been identified. Members of the TMEM16 family have either lipid scramblase or chloride channel activity. Although TMEM16K is widely distributed and associated with the neurological disorder autosomal recessive spinocerebellar ataxia type 10 (SCAR10), its location in cells, function and structure are largely uncharacterised. Here we show that TMEM16K is an ER-resident lipid scramblase with a requirement for short chain lipids and calcium for robust activity. Crystal structures of TMEM16K show a scramblase fold, with an open lipid transporting groove. Additional cryo-EM structures reveal extensive conformational changes from the cytoplasmic to the ER side of the membrane, giving a state with a closed lipid permeation pathway. Molecular dynamics simulations showed that the open-groove conformation is necessary for scramblase activity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4746.map.gz emd_4746.map.gz | 41.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4746-v30.xml emd-4746-v30.xml emd-4746.xml emd-4746.xml | 23.4 KB 23.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4746_fsc.xml emd_4746_fsc.xml | 8.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4746.png emd_4746.png | 171.9 KB | ||
| マスクデータ |  emd_4746_msk_1.map emd_4746_msk_1.map | 45.2 MB |  マスクマップ マスクマップ | |
| その他 |  emd_4746_half_map_1.map.gz emd_4746_half_map_1.map.gz emd_4746_half_map_2.map.gz emd_4746_half_map_2.map.gz | 33.9 MB 33.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4746 http://ftp.pdbj.org/pub/emdb/structures/EMD-4746 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4746 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4746 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4746.map.gz / 形式: CCP4 / 大きさ: 45.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4746.map.gz / 形式: CCP4 / 大きさ: 45.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION3 post processed map sharpened with a bfactor of -112A**2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.822 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_4746_msk_1.map emd_4746_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: RELION3 unfiltered halfmap1
| ファイル | emd_4746_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION3 unfiltered halfmap1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: RELION3 unfiltered halfmap2
| ファイル | emd_4746_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION3 unfiltered halfmap2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Anoctamin 10
| 全体 | 名称: Anoctamin 10 Calcium-dependent chloride channel Calcium-dependent chloride channel |
|---|---|
| 要素 |
|
-超分子 #1: Anoctamin 10
| 超分子 | 名称: Anoctamin 10 / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 153 KDa |
| 組換発現 | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ)組換プラスミド: PFB-CT10HF-LIC |
-分子 #1: Anoctamin-10
| 分子 | 名称: Anoctamin-10 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 77.276016 KDa |
| 組換発現 | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ) |
| 配列 | 文字列: MKVTLSALDT SESSFTPLVV IELAQDVKEE TKEWLKNRII AKKKDGGAQL LFRPLLNKYE QETLENQNLY LVGASKIRML LGAEAVGLV KECNDNTMRA FTYRTRQNFK GFDDNNDDFL TMAECQFIIK HELENLRAKD EKMIPGYPQA KLYPGKSLLR R LLTSGIVI ...文字列: MKVTLSALDT SESSFTPLVV IELAQDVKEE TKEWLKNRII AKKKDGGAQL LFRPLLNKYE QETLENQNLY LVGASKIRML LGAEAVGLV KECNDNTMRA FTYRTRQNFK GFDDNNDDFL TMAECQFIIK HELENLRAKD EKMIPGYPQA KLYPGKSLLR R LLTSGIVI QVFPLHDSEA LKKLEDTWYT RFALKYQPID SIRGYFGETI ALYFGFLEYF TFALIPMAVI GLPYYLFVWE DY DKYVIFA SFNLIWSTVI LELWKRGCAN MTYRWGTLLM KRKFEEPRPG FHGVLGINSI TGKEEPLYPS YKRQLRIYLV SLP FVCLCL YFSLYVMMIY FDMEVWALGL HENSGSEWTS VLLYVPSIIY AIVIEIMNRL YRYAAEFLTS WENHRLESAY QNHL ILKVL VFNFLNCFAS LFYIAFVLKD MKLLRQSLAT LLITSQILNQ IMESFLPYWL QRKHGVRVKR KVQALKADID ATLYE QVIL EKEMGTYLGT FDDYLELFLQ FGYVSLFSCV YPLAAAFAVL NNFTEVNSDA LKMCRVFKRP FSEPSANIGV WQLAFE TMS VISVVTNCAL IGMSPQVNAV FPESKADLIL IVVAVEHALL ALKFILAFAI PDKPRHIQMK LARLEFESLE ALKQQQM KL VTENLKEEPM ESGKEKATAE NLYFQ |
-分子 #2: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 2 / コピー数: 6 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-分子 #3: 1,2-DIACYL-SN-GLYCERO-3-PHOSPHOCHOLINE
| 分子 | 名称: 1,2-DIACYL-SN-GLYCERO-3-PHOSPHOCHOLINE / タイプ: ligand / ID: 3 / コピー数: 2 / 式: PC1 |
|---|---|
| 分子量 | 理論値: 790.145 Da |
| Chemical component information |  ChemComp-PC1: |
-分子 #4: UNDECYL-MALTOSIDE
| 分子 | 名称: UNDECYL-MALTOSIDE / タイプ: ligand / ID: 4 / コピー数: 20 / 式: UMQ |
|---|---|
| 分子量 | 理論値: 496.589 Da |
| Chemical component information | 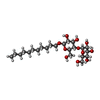 ChemComp-UMQ: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3 mg/mL | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR | ||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 278 K / 装置: FEI VITROBOT MARK IV / 詳細: blot for 3.5sec prior to plunging. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.25 µm Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.25 µm |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - 画像ごとのフレーム数: 1-20 / 撮影したグリッド数: 1 / 実像数: 3421 / 平均露光時間: 8.0 sec. / 平均電子線量: 50.9 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| 詳細 | phenix.real_space_refine with NCS contraints, rotamer, cbeta and ramachandran restraints using postprocessed RELION3 map |
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 176 / 当てはまり具合の基準: Correlation coef |
| 得られたモデル |  PDB-6r7x: |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X