+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-3771 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Three-dimensional reconstruction of FLiP virion | |||||||||
 マップデータ マップデータ | Reconstruction of Flavobacterium infecting lipid-containing phage FLiP | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 | Major capsid protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   unidentified phage (ファージ) unidentified phage (ファージ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.0 Å クライオ電子顕微鏡法 / 解像度: 4.0 Å | |||||||||
 データ登録者 データ登録者 | De Colibus L / Gillum A / Stuart DI / Huiskonen JT | |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2017 ジャーナル: Proc Natl Acad Sci U S A / 年: 2017タイトル: Virus found in a boreal lake links ssDNA and dsDNA viruses. 著者: Elina Laanto / Sari Mäntynen / Luigi De Colibus / Jenni Marjakangas / Ashley Gillum / David I Stuart / Janne J Ravantti / Juha T Huiskonen / Lotta-Riina Sundberg /   要旨: Viruses have impacted the biosphere in numerous ways since the dawn of life. However, the evolution, genetic, structural, and taxonomic diversity of viruses remain poorly understood, in part because ...Viruses have impacted the biosphere in numerous ways since the dawn of life. However, the evolution, genetic, structural, and taxonomic diversity of viruses remain poorly understood, in part because sparse sampling of the virosphere has concentrated mostly on exploring the abundance and diversity of dsDNA viruses. Furthermore, viral genomes are highly diverse, and using only the current sequence-based methods for classifying viruses and studying their phylogeny is complicated. Here we describe a virus, FLiP (-infecting, lipid-containing phage), with a circular ssDNA genome and an internal lipid membrane enclosed in the icosahedral capsid. The 9,174-nt-long genome showed limited sequence similarity to other known viruses. The genetic data imply that this virus might use replication mechanisms similar to those found in other ssDNA replicons. However, the structure of the viral major capsid protein, elucidated at near-atomic resolution using cryo-electron microscopy, is strikingly similar to that observed in dsDNA viruses of the PRD1-adenovirus lineage, characterized by a major capsid protein bearing two β-barrels. The strong similarity between FLiP and another member of the structural lineage, bacteriophage PM2, extends to the capsid organization (pseudo = 21 ) despite the difference in the genetic material packaged and the lack of significant sequence similarity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_3771.map.gz emd_3771.map.gz | 1.2 GB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-3771-v30.xml emd-3771-v30.xml emd-3771.xml emd-3771.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_3771_fsc.xml emd_3771_fsc.xml | 24.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_3771.png emd_3771.png | 199.4 KB | ||
| マスクデータ |  emd_3771_msk_1.map emd_3771_msk_1.map | 1.3 GB |  マスクマップ マスクマップ | |
| その他 |  emd_3771_half_map_1.map.gz emd_3771_half_map_1.map.gz emd_3771_half_map_2.map.gz emd_3771_half_map_2.map.gz | 1 GB 1 GB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-3771 http://ftp.pdbj.org/pub/emdb/structures/EMD-3771 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3771 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3771 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_3771.map.gz / 形式: CCP4 / 大きさ: 1.3 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_3771.map.gz / 形式: CCP4 / 大きさ: 1.3 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of Flavobacterium infecting lipid-containing phage FLiP | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.35 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_3771_msk_1.map emd_3771_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
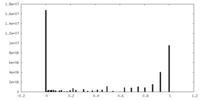
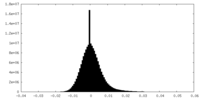
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_3771_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
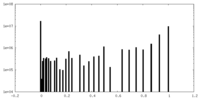
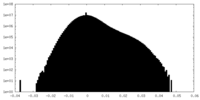
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_3771_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
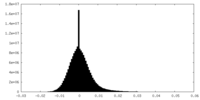
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : unidentified phage
| 全体 | 名称:   unidentified phage (ファージ) unidentified phage (ファージ) |
|---|---|
| 要素 |
|
-超分子 #1: unidentified phage
| 超分子 | 名称: unidentified phage / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Flavobacterium infecting lipid-containing phage FLiP NCBI-ID: 38018 / 生物種: unidentified phage / ウイルスタイプ: VIRION / ウイルス・単離状態: SPECIES / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:   Flavobacterium (フラボバクテリウム属) / 株: sp B330 Flavobacterium (フラボバクテリウム属) / 株: sp B330 |
| ウイルス殻 | Shell ID: 1 / 名称: Capsid / 直径: 550.0 Å / T番号(三角分割数): 25 |
-分子 #1: Major capsid protein
| 分子 | 名称: Major capsid protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 10 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   unidentified phage (ファージ) unidentified phage (ファージ) |
| 分子量 | 理論値: 34.533934 KDa |
| 配列 | 文字列: MTIKYLSSET EKLMNQTVSG IDVCFTLIGV DDDSFASGSK NDYISDTPKF LDPSNVHIKA TLKRGGKDYV LFSENLALLA KYSTITQGR DQWEEGVKLA AKEMVHLVYI PFSGNTNWPA HINLKDNDVL EVYVNVVRGA YGAELDANAC ICDVRTSPSI G VEKFIPFM ...文字列: MTIKYLSSET EKLMNQTVSG IDVCFTLIGV DDDSFASGSK NDYISDTPKF LDPSNVHIKA TLKRGGKDYV LFSENLALLA KYSTITQGR DQWEEGVKLA AKEMVHLVYI PFSGNTNWPA HINLKDNDVL EVYVNVVRGA YGAELDANAC ICDVRTSPSI G VEKFIPFM TSYSIRANQA TDLVNLGNDV TRIALLSMTN DVSNIPNAFT DVTLSSDRLD KNFNSNQLIL EHSKCIEDSV RS HANEVDS YLIHEDIEID SAKVHLKMNP AKIRENTIYL VRSHFQTSLE ILQKAVAMEE KHQSADIAKV PAT |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.2 / 詳細: 20 mM PBS |
|---|---|
| グリッド | モデル: C-flat-2/2 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK III |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 最大 デフォーカス(補正後): 2.5 µm / 最小 デフォーカス(補正後): 0.7 µm / 倍率(補正後): 37037 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.0 mm / 倍率(公称値): 160000 Bright-field microscopy / Cs: 2.0 mm / 倍率(公称値): 160000 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS エネルギーフィルター - エネルギー下限: 0 eV エネルギーフィルター - エネルギー上限: 20 eV |
| 試料ステージ | 試料ホルダーモデル: OTHER / ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サンプリング間隔: 5.0 µm / デジタル化 - 画像ごとのフレーム数: 1-22 / 平均電子線量: 22.0 e/Å2 |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 84.31 当てはまり具合の基準: Cross-correlation coefficient |
|---|---|
| 得られたモデル |  PDB-5oac: |
 ムービー
ムービー コントローラー
コントローラー












 Z
Z Y
Y X
X