+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22598 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human serine palmitoyltransferase complex SPTLC1/SPLTC2/ssSPTa | |||||||||
 マップデータ マップデータ | Sharpened_map | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報sphinganine biosynthetic process / regulation of fat cell apoptotic process /  serine C-palmitoyltransferase complex / sphingomyelin biosynthetic process / SPOTS complex / serine C-palmitoyltransferase complex / sphingomyelin biosynthetic process / SPOTS complex /  serine C-palmitoyltransferase activity / serine C-palmitoyltransferase activity /  serine C-palmitoyltransferase / sphingolipid biosynthetic process / Sphingolipid de novo biosynthesis / sphingosine biosynthetic process ...sphinganine biosynthetic process / regulation of fat cell apoptotic process / serine C-palmitoyltransferase / sphingolipid biosynthetic process / Sphingolipid de novo biosynthesis / sphingosine biosynthetic process ...sphinganine biosynthetic process / regulation of fat cell apoptotic process /  serine C-palmitoyltransferase complex / sphingomyelin biosynthetic process / SPOTS complex / serine C-palmitoyltransferase complex / sphingomyelin biosynthetic process / SPOTS complex /  serine C-palmitoyltransferase activity / serine C-palmitoyltransferase activity /  serine C-palmitoyltransferase / sphingolipid biosynthetic process / Sphingolipid de novo biosynthesis / sphingosine biosynthetic process / ceramide biosynthetic process / sphingolipid metabolic process / positive regulation of lipophagy / adipose tissue development / serine C-palmitoyltransferase / sphingolipid biosynthetic process / Sphingolipid de novo biosynthesis / sphingosine biosynthetic process / ceramide biosynthetic process / sphingolipid metabolic process / positive regulation of lipophagy / adipose tissue development /  protein localization / protein localization /  pyridoxal phosphate binding / endoplasmic reticulum membrane / pyridoxal phosphate binding / endoplasmic reticulum membrane /  小胞体 小胞体類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.3 Å クライオ電子顕微鏡法 / 解像度: 3.3 Å | |||||||||
 データ登録者 データ登録者 | Wang Y / Niu Y / Zhang Z / Zhao H / Myasnikov A / Kalathur R / Lee CH | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2021 ジャーナル: Nat Struct Mol Biol / 年: 2021タイトル: Structural insights into the regulation of human serine palmitoyltransferase complexes. 著者: Yingdi Wang / Yiming Niu / Zhe Zhang / Kenneth Gable / Sita D Gupta / Niranjanakumari Somashekarappa / Gongshe Han / Hongtu Zhao / Alexander G Myasnikov / Ravi C Kalathur / Teresa M Dunn / Chia-Hsueh Lee /   要旨: Sphingolipids are essential lipids in eukaryotic membranes. In humans, the first and rate-limiting step of sphingolipid synthesis is catalyzed by the serine palmitoyltransferase holocomplex, which ...Sphingolipids are essential lipids in eukaryotic membranes. In humans, the first and rate-limiting step of sphingolipid synthesis is catalyzed by the serine palmitoyltransferase holocomplex, which consists of catalytic components (SPTLC1 and SPTLC2) and regulatory components (ssSPTa and ORMDL3). However, the assembly, substrate processing and regulation of the complex are unclear. Here, we present 8 cryo-electron microscopy structures of the human serine palmitoyltransferase holocomplex in various functional states at resolutions of 2.6-3.4 Å. The structures reveal not only how catalytic components recognize the substrate, but also how regulatory components modulate the substrate-binding tunnel to control enzyme activity: ssSPTa engages SPTLC2 and shapes the tunnel to determine substrate specificity. ORMDL3 blocks the tunnel and competes with substrate binding through its amino terminus. These findings provide mechanistic insights into sphingolipid biogenesis governed by the serine palmitoyltransferase complex. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22598.map.gz emd_22598.map.gz | 203.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22598-v30.xml emd-22598-v30.xml emd-22598.xml emd-22598.xml | 12.6 KB 12.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_22598.png emd_22598.png | 52.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22598 http://ftp.pdbj.org/pub/emdb/structures/EMD-22598 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22598 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22598 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22598.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22598.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened_map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.0005 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : human serine palmitoyltransferase complexes
| 全体 | 名称: human serine palmitoyltransferase complexes |
|---|---|
| 要素 |
|
-超分子 #1: human serine palmitoyltransferase complexes
| 超分子 | 名称: human serine palmitoyltransferase complexes / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Serine palmitoyltransferase 1
| 分子 | 名称: Serine palmitoyltransferase 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO / EC番号:  serine C-palmitoyltransferase serine C-palmitoyltransferase |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 52.80677 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MATATEQWVL VEMVQALYEA PAYHLILEGI LILWIIRLLF SKTYKLQERS DLTVKEKEEL IEEWQPEPLV PPVPKDHPAL NYNIVSGPP SHKTVVNGKE CINFASFNFL GLLDNPRVKA AALASLKKYG VGTCGPRGFY GTFDVHLDLE DRLAKFMKTE E AIIYSYGF ...文字列: MATATEQWVL VEMVQALYEA PAYHLILEGI LILWIIRLLF SKTYKLQERS DLTVKEKEEL IEEWQPEPLV PPVPKDHPAL NYNIVSGPP SHKTVVNGKE CINFASFNFL GLLDNPRVKA AALASLKKYG VGTCGPRGFY GTFDVHLDLE DRLAKFMKTE E AIIYSYGF ATIASAIPAY SKRGDIVFVD RAACFAIQKG LQASRSDIKL FKHNDMADLE RLLKEQEIED QKNPRKARVT RR FIVVEGL YMNTGTICPL PELVKLKYKY KARIFLEESL SFGVLGEHGR GVTEHYGINI DDIDLISANM ENALASIGGF CCG RSFVID HQRLSGQGYC FSASLPPLLA AAAIEALNIM EENPGIFAVL KEKCGQIHKA LQGISGLKVV GESLSPAFHL QLEE STGSR EQDVRLLQEI VDQCMNRSIA LTQARYLEKE EKCLPPPSIR VVVTVEQTEE ELERAASTIK EVAQAVLL |
-分子 #2: Serine palmitoyltransferase 2
| 分子 | 名称: Serine palmitoyltransferase 2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO / EC番号:  serine C-palmitoyltransferase serine C-palmitoyltransferase |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 60.851902 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MRPEPGGCCC RRTVRANGCV ANGEVRNGYV RSSAAAAAAA AAGQIHHVTQ NGGLYKRPFN EAFEETPMLV AVLTYVGYGV LTLFGYLRD FLRYWRIEKC HHATEREEQK DFVSLYQDFE NFYTRNLYMR IRDNWNRPIC SVPGARVDIM ERQSHDYNWS F KYTGNIIK ...文字列: MRPEPGGCCC RRTVRANGCV ANGEVRNGYV RSSAAAAAAA AAGQIHHVTQ NGGLYKRPFN EAFEETPMLV AVLTYVGYGV LTLFGYLRD FLRYWRIEKC HHATEREEQK DFVSLYQDFE NFYTRNLYMR IRDNWNRPIC SVPGARVDIM ERQSHDYNWS F KYTGNIIK GVINMGSYNY LGFARNTGSC QEAAAKVLEE YGAGVCSTRQ EIGNLDKHEE LEELVARFLG VEAAMAYGMG FA TNSMNIP ALVGKGCLIL SDELNHASLV LGARLSGATI RIFKHNNMQS LEKLLKDAIV YGQPRTRRPW KKILILVEGI YSM EGSIVR LPEVIALKKK YKAYLYLDEA HSIGALGPTG RGVVEYFGLD PEDVDVMMGT FTKSFGASGG YIGGKKELID YLRT HSHSA VYATSLSPPV VEQIITSMKC IMGQDGTSLG KECVQQLAEN TRYFRRRLKE MGFIIYGNED SPVVPLMLYM PAKIG AFGR EMLKRNIGVV VVGFPATPII ESRARFCLSA AHTKEILDTA LKEIDEVGDL LQLKYSRHRL |
-分子 #3: Serine palmitoyltransferase small subunit A
| 分子 | 名称: Serine palmitoyltransferase small subunit A / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 8.471095 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MAGMALARAW KQMSWFYYQY LLVTALYMLE PWERTVFNSM LVSIVGMALY TGYVFMPQHI MAILHYFEIV Q |
-分子 #4: PYRIDOXAL-5'-PHOSPHATE
| 分子 | 名称: PYRIDOXAL-5'-PHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 2 / 式: PLP |
|---|---|
| 分子量 | 理論値: 247.142 Da |
| Chemical component information |  ChemComp-PLP: |
-分子 #5: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(tri...
| 分子 | 名称: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(trimethylammonio)ethyl phosphate タイプ: ligand / ID: 5 / コピー数: 4 / 式: POV |
|---|---|
| 分子量 | 理論値: 760.076 Da |
| Chemical component information | 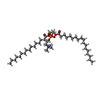 ChemComp-POV: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 60.35 e/Å2 |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期 角度割当 | タイプ: ANGULAR RECONSTITUTION |
|---|---|
| 最終 角度割当 | タイプ: ANGULAR RECONSTITUTION |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 238610 |
 ムービー
ムービー コントローラー
コントローラー



























