+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-20517 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
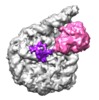
| タイトル | Set2 bound to nucleosome | |||||||||
 マップデータ マップデータ | Set2 bound to nucleosome, Class Ub | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報: / [histone H3]-lysine36 N-trimethyltransferase / histone H3K36 methyltransferase activity /  ribosomal large subunit export from nucleus / modification-dependent protein catabolic process / ribosomal large subunit export from nucleus / modification-dependent protein catabolic process /  protein tag activity / protein tag activity /  ribosomal large subunit assembly / structural constituent of chromatin / ribosomal large subunit assembly / structural constituent of chromatin /  ヌクレオソーム / ヌクレオソーム /  リボソーム生合成 ...: / [histone H3]-lysine36 N-trimethyltransferase / histone H3K36 methyltransferase activity / リボソーム生合成 ...: / [histone H3]-lysine36 N-trimethyltransferase / histone H3K36 methyltransferase activity /  ribosomal large subunit export from nucleus / modification-dependent protein catabolic process / ribosomal large subunit export from nucleus / modification-dependent protein catabolic process /  protein tag activity / protein tag activity /  ribosomal large subunit assembly / structural constituent of chromatin / ribosomal large subunit assembly / structural constituent of chromatin /  ヌクレオソーム / ヌクレオソーム /  リボソーム生合成 / リボソーム生合成 /  染色体 / cytoplasmic translation / cytosolic large ribosomal subunit / protein ubiquitination / structural constituent of ribosome / protein heterodimerization activity / 染色体 / cytoplasmic translation / cytosolic large ribosomal subunit / protein ubiquitination / structural constituent of ribosome / protein heterodimerization activity /  ubiquitin protein ligase binding / regulation of DNA-templated transcription / ubiquitin protein ligase binding / regulation of DNA-templated transcription /  ミトコンドリア / ミトコンドリア /  DNA binding / DNA binding /  細胞核 / 細胞核 /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Chaetomium thermophilum (菌類) / synthetic construct (人工物) / Chaetomium thermophilum (菌類) / synthetic construct (人工物) /  Xenopus laevis (アフリカツメガエル) / Xenopus laevis (アフリカツメガエル) /  Chaetomium thermophilum (strain DSM 1495 / CBS 144.50 / IMI 039719) (菌類) Chaetomium thermophilum (strain DSM 1495 / CBS 144.50 / IMI 039719) (菌類) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.1 Å クライオ電子顕微鏡法 / 解像度: 4.1 Å | |||||||||
 データ登録者 データ登録者 | Halic M / Bilokapic S | |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019タイトル: Nucleosome and ubiquitin position Set2 to methylate H3K36. 著者: Silvija Bilokapic / Mario Halic /  要旨: Histone H3 lysine 36 methylation (H3K36me) is a conserved histone modification deposited by the Set2 methyltransferases. Recent findings show that over-expression or mutation of Set2 enzymes promotes ...Histone H3 lysine 36 methylation (H3K36me) is a conserved histone modification deposited by the Set2 methyltransferases. Recent findings show that over-expression or mutation of Set2 enzymes promotes cancer progression, however, mechanisms of H3K36me are poorly understood. Set2 enzymes show spurious activity on histones and histone tails, and it is unknown how they obtain specificity to methylate H3K36 on the nucleosome. In this study, we present 3.8 Å cryo-EM structure of Set2 bound to the mimic of H2B ubiquitinated nucleosome. Our structure shows that Set2 makes extensive interactions with the H3 αN, the H3 tail, the H2A C-terminal tail and stabilizes DNA in the unwrapped conformation, which positions Set2 to specifically methylate H3K36. Moreover, we show that ubiquitin contributes to Set2 positioning on the nucleosome and stimulates the methyltransferase activity. Notably, our structure uncovers interfaces that can be targeted by small molecules for development of future cancer therapies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_20517.map.gz emd_20517.map.gz | 47.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-20517-v30.xml emd-20517-v30.xml emd-20517.xml emd-20517.xml | 20.4 KB 20.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_20517.png emd_20517.png | 424 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-20517 http://ftp.pdbj.org/pub/emdb/structures/EMD-20517 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20517 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20517 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_20517.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_20517.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Set2 bound to nucleosome, Class Ub | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.04 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Set2 bound to ubiquitinated nucleosome
+超分子 #1: Set2 bound to ubiquitinated nucleosome
+超分子 #2: Histone-lysine N-methyltransferase
+超分子 #3: DNA
+超分子 #4: Histone H3, Histone H4, Ubiquitin-60S ribosomal protein L40,Histo...
+分子 #1: Histone H3
+分子 #2: Histone H4
+分子 #3: Ubiquitin-60S ribosomal protein L40,Histone H2A
+分子 #4: Histone H2B 1.1
+分子 #7: Histone-lysine N-methyltransferase
+分子 #5: DNA (145-MER)
+分子 #6: DNA (145-MER)
+分子 #8: ZINC ION
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) #0 - 検出モード: COUNTING / #0 - 平均電子線量: 75.0 e/Å2 / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: GATAN K2 BASE (4k x 4k) #1 - 平均電子線量: 75.0 e/Å2 / #2 - Image recording ID: 3 #2 - フィルム・検出器のモデル: GATAN K2 BASE (4k x 4k) #2 - 平均電子線量: 75.0 e/Å2 / #3 - Image recording ID: 4 #3 - フィルム・検出器のモデル: GATAN K2 BASE (4k x 4k) #3 - 平均電子線量: 75.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
|---|---|
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 67000 |
| Image recording ID | 1 |
 ムービー
ムービー コントローラー
コントローラー