+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1849 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cognate 70S-TC complex | ||||||||||||
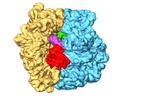
 マップデータ マップデータ | Surface rendered view of Cognate 70S-TC complex | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード |  ribosome (リボソーム) / ribosome (リボソーム) /  ternary complex / cognate ternary complex / cognate | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報guanyl-nucleotide exchange factor complex / negative regulation of cytoplasmic translational initiation /  guanosine tetraphosphate binding / translational elongation / guanosine tetraphosphate binding / translational elongation /  stringent response / ornithine decarboxylase inhibitor activity / misfolded RNA binding / transcription antitermination factor activity, RNA binding / Group I intron splicing / RNA folding ...guanyl-nucleotide exchange factor complex / negative regulation of cytoplasmic translational initiation / stringent response / ornithine decarboxylase inhibitor activity / misfolded RNA binding / transcription antitermination factor activity, RNA binding / Group I intron splicing / RNA folding ...guanyl-nucleotide exchange factor complex / negative regulation of cytoplasmic translational initiation /  guanosine tetraphosphate binding / translational elongation / guanosine tetraphosphate binding / translational elongation /  stringent response / ornithine decarboxylase inhibitor activity / misfolded RNA binding / transcription antitermination factor activity, RNA binding / Group I intron splicing / RNA folding / stringent response / ornithine decarboxylase inhibitor activity / misfolded RNA binding / transcription antitermination factor activity, RNA binding / Group I intron splicing / RNA folding /  transcriptional attenuation / endoribonuclease inhibitor activity / RNA-binding transcription regulator activity / positive regulation of ribosome biogenesis / negative regulation of cytoplasmic translation / transcriptional attenuation / endoribonuclease inhibitor activity / RNA-binding transcription regulator activity / positive regulation of ribosome biogenesis / negative regulation of cytoplasmic translation /  translation elongation factor activity / translational termination / DnaA-L2 complex / : / four-way junction DNA binding / negative regulation of translational initiation / translation repressor activity / translational initiation / negative regulation of DNA-templated DNA replication initiation / regulation of mRNA stability / translation elongation factor activity / translational termination / DnaA-L2 complex / : / four-way junction DNA binding / negative regulation of translational initiation / translation repressor activity / translational initiation / negative regulation of DNA-templated DNA replication initiation / regulation of mRNA stability /  ribosome assembly / mRNA regulatory element binding translation repressor activity / response to reactive oxygen species / assembly of large subunit precursor of preribosome / positive regulation of RNA splicing / DNA endonuclease activity / transcription elongation factor complex / cytosolic ribosome assembly / regulation of DNA-templated transcription elongation / transcription antitermination / ribosome assembly / mRNA regulatory element binding translation repressor activity / response to reactive oxygen species / assembly of large subunit precursor of preribosome / positive regulation of RNA splicing / DNA endonuclease activity / transcription elongation factor complex / cytosolic ribosome assembly / regulation of DNA-templated transcription elongation / transcription antitermination /  regulation of cell growth / maintenance of translational fidelity / DNA-templated transcription termination / response to radiation / mRNA 5'-UTR binding / regulation of cell growth / maintenance of translational fidelity / DNA-templated transcription termination / response to radiation / mRNA 5'-UTR binding /  ribosomal small subunit biogenesis / small ribosomal subunit rRNA binding / ribosomal small subunit biogenesis / small ribosomal subunit rRNA binding /  ribosomal large subunit assembly / ribosomal large subunit assembly /  ribosomal small subunit assembly / cytosolic small ribosomal subunit / large ribosomal subunit rRNA binding / ribosomal small subunit assembly / cytosolic small ribosomal subunit / large ribosomal subunit rRNA binding /  ribosome binding / large ribosomal subunit / ribosome binding / large ribosomal subunit /  リボソーム生合成 / リボソーム生合成 /  regulation of translation / cytoplasmic translation / small ribosomal subunit / regulation of translation / cytoplasmic translation / small ribosomal subunit /  5S rRNA binding / cytosolic large ribosomal subunit / 5S rRNA binding / cytosolic large ribosomal subunit /  transferase activity / transferase activity /  tRNA binding / negative regulation of translation / tRNA binding / negative regulation of translation /  rRNA binding / molecular adaptor activity / rRNA binding / molecular adaptor activity /  リボソーム / structural constituent of ribosome / リボソーム / structural constituent of ribosome /  ribonucleoprotein complex / ribonucleoprotein complex /  翻訳 (生物学) / response to antibiotic / 翻訳 (生物学) / response to antibiotic /  mRNA binding / mRNA binding /  GTPase activity / negative regulation of DNA-templated transcription / GTP binding / GTPase activity / negative regulation of DNA-templated transcription / GTP binding /  DNA binding / DNA binding /  RNA binding / zinc ion binding / RNA binding / zinc ion binding /  生体膜 / 生体膜 /  細胞膜 / 細胞膜 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | ||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 8.25 Å クライオ電子顕微鏡法 / 解像度: 8.25 Å | ||||||||||||
 データ登録者 データ登録者 | Agirrezabala X / Schreiner E / Trabuco LG / Lei J / Ortiz-Meoz RF / Schulten K / Green R / Frank J | ||||||||||||
 引用 引用 |  ジャーナル: EMBO J / 年: 2011 ジャーナル: EMBO J / 年: 2011タイトル: Structural insights into cognate versus near-cognate discrimination during decoding. 著者: Xabier Agirrezabala / Eduard Schreiner / Leonardo G Trabuco / Jianlin Lei / Rodrigo F Ortiz-Meoz / Klaus Schulten / Rachel Green / Joachim Frank /  要旨: The structural basis of the tRNA selection process is investigated by cryo-electron microscopy of ribosomes programmed with UGA codons and incubated with ternary complex (TC) containing the near- ...The structural basis of the tRNA selection process is investigated by cryo-electron microscopy of ribosomes programmed with UGA codons and incubated with ternary complex (TC) containing the near-cognate Trp-tRNA(Trp) in the presence of kirromycin. Going through more than 350 000 images and employing image classification procedures, we find ∼8% in which the TC is bound to the ribosome. The reconstructed 3D map provides a means to characterize the arrangement of the near-cognate aa-tRNA with respect to elongation factor Tu (EF-Tu) and the ribosome, as well as the domain movements of the ribosome. One of the interesting findings is that near-cognate tRNA's acceptor stem region is flexible and CCA end becomes disordered. The data bring direct structural insights into the induced-fit mechanism of decoding by the ribosome, as the analysis of the interactions between small and large ribosomal subunit, aa-tRNA and EF-Tu and comparison with the cognate case (UGG codon) offers clues on how the conformational signals conveyed to the GTPase differ in the two cases. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1849.map.gz emd_1849.map.gz | 54.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1849-v30.xml emd-1849-v30.xml emd-1849.xml emd-1849.xml | 11.8 KB 11.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1849.tif 1849.tif | 1.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1849 http://ftp.pdbj.org/pub/emdb/structures/EMD-1849 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1849 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1849 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1849.map.gz / 形式: CCP4 / 大きさ: 58.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1849.map.gz / 形式: CCP4 / 大きさ: 58.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Surface rendered view of Cognate 70S-TC complex | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.5 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Cognate 70S-TC complex
| 全体 | 名称: Cognate 70S-TC complex |
|---|---|
| 要素 |
|
-超分子 #1000: Cognate 70S-TC complex
| 超分子 | 名称: Cognate 70S-TC complex / タイプ: sample / ID: 1000 詳細: 70S.fMet-tRNAfMet.EF-Tu.Trp-tRNATrp on cognate codon 集合状態: Monomeric / Number unique components: 4 |
|---|---|
| 分子量 | 理論値: 2.8 MDa / 手法: Sedimentation |
-超分子 #1: 70S Ribosome
| 超分子 | 名称: 70S Ribosome / タイプ: complex / ID: 1 / 組換発現: No / Ribosome-details: ribosome-prokaryote: ALL |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
-分子 #1: fMet-tRNAfMet
| 分子 | 名称: fMet-tRNAfMet / タイプ: rna / ID: 1 / Name.synonym: fMet-tRNAfMet / 分類: TRANSFER / Structure: SINGLE STRANDED / Synthetic?: No |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: CGCGGGGTGG AGCAGCCTGG TAGCTCGTCG GGCTCATAAC CCGAAGATCG TCGGTTCAAA TCCGGCCCCC GCAACCA |
-分子 #3: Trp-tRNATrp
| 分子 | 名称: Trp-tRNATrp / タイプ: rna / ID: 3 / 分類: TRANSFER / Structure: SINGLE STRANDED / Synthetic?: No |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: AGGGGCGTAG TTCAATTGGT AGAGCACCGG TCTCCAAAAC CGGGTGTTGG GAGTTCGAGT CTCTCCGCCC CTGCCA |
-分子 #2: EF-Tu
| 分子 | 名称: EF-Tu / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 集合状態: Monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.04 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 詳細: HiFi (50 mM Tris-HCl pH 7.5, 70mM NH4Cl, 30 mM KCl, 3.5 mM MgCl2, 0.5 mM spermidine, 8mM putrescine, 2 mM DTT) |
| 凍結 | 凍結剤: NITROGEN / チャンバー内湿度: 90 % / チャンバー内温度: 80 K / 装置: OTHER / 詳細: Vitrification instrument: Vitrobot / 手法: Blot for 6 seconds |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F30 |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 58269 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 59000 Bright-field microscopy / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 59000 |
| 試料ステージ | 試料ホルダー: Eucentric / 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| アライメント法 | Legacy - 非点収差: Objective corrected at 100,000 times magnification |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: TVIPS TEMCAM-F415 (4k x 4k) 平均電子線量: 20 e/Å2 詳細: Automated data collection system AutoEMation (CCD mag. 100000x) TVIPS TemCam-F415 |
| 実験機器 |  モデル: Tecnai F30 / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: Defocus groups, Wiener filter |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 8.25 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: Spider / 使用した粒子像数: 359223 |
-原子モデル構築 1
| 初期モデル | PDB ID:  2i2v |
|---|---|
| ソフトウェア | 名称: MDFF |
| 詳細 | Protocol: MD-based flexible fitting |
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: RMSD, cross correlation |
| 得られたモデル |  PDB-4v6k: |
 ムービー
ムービー コントローラー
コントローラー