+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12563 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Supramolecular assembly module of yeast Chelator-GID SR4 E3 ubiquitin ligase | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報GID complex / traversing start control point of mitotic cell cycle / regulation of nitrogen utilization / negative regulation of gluconeogenesis / proteasome-mediated ubiquitin-dependent protein catabolic process /  細胞周期 / 細胞周期 /  細胞核 / 細胞核 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Saccharomyces cerevisiae (パン酵母) / Saccharomyces cerevisiae (パン酵母) /   Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母) Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母) | |||||||||
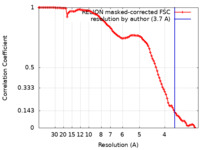
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.7 Å クライオ電子顕微鏡法 / 解像度: 3.7 Å | |||||||||
 データ登録者 データ登録者 | Chrustowicz J / Sherpa D / Prabu JR / Schulman BA | |||||||||
| 資金援助 |  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2021 ジャーナル: Mol Cell / 年: 2021タイトル: GID E3 ligase supramolecular chelate assembly configures multipronged ubiquitin targeting of an oligomeric metabolic enzyme. 著者: Dawafuti Sherpa / Jakub Chrustowicz / Shuai Qiao / Christine R Langlois / Laura A Hehl / Karthik Varma Gottemukkala / Fynn M Hansen / Ozge Karayel / Susanne von Gronau / J Rajan Prabu / ...著者: Dawafuti Sherpa / Jakub Chrustowicz / Shuai Qiao / Christine R Langlois / Laura A Hehl / Karthik Varma Gottemukkala / Fynn M Hansen / Ozge Karayel / Susanne von Gronau / J Rajan Prabu / Matthias Mann / Arno F Alpi / Brenda A Schulman /  要旨: How are E3 ubiquitin ligases configured to match substrate quaternary structures? Here, by studying the yeast GID complex (mutation of which causes deficiency in glucose-induced degradation of ...How are E3 ubiquitin ligases configured to match substrate quaternary structures? Here, by studying the yeast GID complex (mutation of which causes deficiency in glucose-induced degradation of gluconeogenic enzymes), we discover supramolecular chelate assembly as an E3 ligase strategy for targeting an oligomeric substrate. Cryoelectron microscopy (cryo-EM) structures show that, to bind the tetrameric substrate fructose-1,6-bisphosphatase (Fbp1), two minimally functional GID E3s assemble into the 20-protein Chelator-GID, which resembles an organometallic supramolecular chelate. The Chelator-GID assembly avidly binds multiple Fbp1 degrons so that multiple Fbp1 protomers are simultaneously ubiquitylated at lysines near the allosteric and substrate binding sites. Importantly, key structural and biochemical features, including capacity for supramolecular assembly, are preserved in the human ortholog, the CTLH E3. Based on our integrative structural, biochemical, and cell biological data, we propose that higher-order E3 ligase assembly generally enables multipronged targeting, capable of simultaneously incapacitating multiple protomers and functionalities of oligomeric substrates. #1:  ジャーナル: Biorxiv / 年: 2021 ジャーナル: Biorxiv / 年: 2021タイトル: GID E3 ligase supramolecular chelate assembly configures multipronged ubiquitin targeting of an oligomeric metabolic enzyme 著者: Sherpa D / Chrustowicz J / Qiao S / Langlois CR / Hehl LA / Gottemukkala KV / Hansen FM / Karayel O / Prabu JR / Mann M / Alpi AF / Schulman BA | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12563.map.gz emd_12563.map.gz | 5.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12563-v30.xml emd-12563-v30.xml emd-12563.xml emd-12563.xml | 23.3 KB 23.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_12563_fsc.xml emd_12563_fsc.xml | 10.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_12563.png emd_12563.png | 130.6 KB | ||
| マスクデータ |  emd_12563_msk_1.map emd_12563_msk_1.map | 91.1 MB |  マスクマップ マスクマップ | |
| その他 |  emd_12563_additional_1.map.gz emd_12563_additional_1.map.gz emd_12563_half_map_1.map.gz emd_12563_half_map_1.map.gz emd_12563_half_map_2.map.gz emd_12563_half_map_2.map.gz | 81 MB 71.3 MB 71.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12563 http://ftp.pdbj.org/pub/emdb/structures/EMD-12563 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12563 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12563 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12563.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12563.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.58 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_12563_msk_1.map emd_12563_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #1
| ファイル | emd_12563_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_12563_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_12563_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Supramolecular assembly module of yeast Chelator-GID SR4 comprisi...
| 全体 | 名称: Supramolecular assembly module of yeast Chelator-GID SR4 comprising Gid1, Gid8 and a homodimer of Gid7 |
|---|---|
| 要素 |
|
-超分子 #1: Supramolecular assembly module of yeast Chelator-GID SR4 comprisi...
| 超分子 | 名称: Supramolecular assembly module of yeast Chelator-GID SR4 comprising Gid1, Gid8 and a homodimer of Gid7 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Generated by focused refinement of Chelator-GID SR4 + Fbp1 map |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 分子量 | 理論値: 330 KDa |
-分子 #1: Vacuolar import and degradation protein 30
| 分子 | 名称: Vacuolar import and degradation protein 30 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母) Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母)株: ATCC 204508 / S288c |
| 分子量 | 理論値: 108.28768 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MSEYMDDVDR EFINCLFPSY LLQQPVAYDL WILYLQHRKL FHKLKNTNLI NADENPTGVG MGRTKLTALT RKEIWSKLMN LGVLGTISF EAVNDDYLIQ VYKYFYPDVN DFTLRFGVKD SNKNSVRVMK ASSDMRKNAQ ELLEPVLSER EMALNSNTSL E NDRNDDDD ...文字列: MSEYMDDVDR EFINCLFPSY LLQQPVAYDL WILYLQHRKL FHKLKNTNLI NADENPTGVG MGRTKLTALT RKEIWSKLMN LGVLGTISF EAVNDDYLIQ VYKYFYPDVN DFTLRFGVKD SNKNSVRVMK ASSDMRKNAQ ELLEPVLSER EMALNSNTSL E NDRNDDDD DDDDDDDDDD DDDDDDDESD LESLEGEVDT DTDDNNEGDG SDNHEEGGEE GSRGADADVS SAQQRAERVA DP WIYQRSR SAINIETESR NLWDTSDKNS GLQYYPPDQS PSSSFSSPRV SSGNDKNDNE ATNVLSNSGS KKKNSMIPDI YKI LGYFLP SRWQAQPNNS LQLSQDGITH LQPNPDYHSY MTYERSSASS ASTRNRLRTS FENSGKVDFA VTWANKSLPD NKLT IFYYE IKVLSVTSTE SAENSNIVIG YKLVENELME ATTKKSVSRS SVAGSSSSLG GSNNMSSNRV PSTSFTMEGT QRRDY IYEG GVSAMSLNVD GSINKCQKYG FDLNVFGYCG FDGLITNSTE QSKEYAKPFG RDDVIGCGIN FIDGSIFFTK NGIHLG NAF TDLNDLEFVP YVALRPGNSI KTNFGLNEDF VFDIIGYQDK WKSLAYEHIC RGRQMDVSIE EFDSDESEED ETENGPE EN KSTNVNEDLM DIDQEDGAAG NKDTKKLNDE KDNNLKFLLG EDNRFIDGKL VRPDVNNINN LSVDDGSLPN TLNVMIND Y LIHEGLVDVA KGFLKDLQKD AVNVNGQHSE SKDVIRHNER QIMKEERMVK IRQELRYLIN KGQISKCINY IDNEIPDLL KNNLELVFEL KLANYLVMIK KSSSKDDDEI ENLILKGQEL SNEFIYDTKI PQSLRDRFSG QLSNVSALLA YSNPLVEAPK EISGYLSDE YLQERLFQVS NNTILTFLHK DSECALENVI SNTRAMLSTL LEYNAFGSTN SSDPRYYKAI NFDEDVLNL |
-分子 #2: Glucose-induced degradation protein 7
| 分子 | 名称: Glucose-induced degradation protein 7 / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母) Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母)株: ATCC 204508 / S288c |
| 分子量 | 理論値: 84.607297 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSHTNKIAYV LNNDTEETAS PSSVGCFDKK QLTKLLIHTL KELGYDSAAN QLLLESGGYQ NESNHIQTFF KLIKTGQFHL INWQIVCSL PLAHSSPLRS EWLQRLLIPT PTPATTSLFD HMLLQLQYLQ QLMSSVNSST CSDAEIATLR NYVEIMILVN R QIFLEFFH ...文字列: MSHTNKIAYV LNNDTEETAS PSSVGCFDKK QLTKLLIHTL KELGYDSAAN QLLLESGGYQ NESNHIQTFF KLIKTGQFHL INWQIVCSL PLAHSSPLRS EWLQRLLIPT PTPATTSLFD HMLLQLQYLQ QLMSSVNSST CSDAEIATLR NYVEIMILVN R QIFLEFFH PVTNSASHKG PHTALPVLYL RKILKNFIEI WDSLLVSNDQ FLNEENIFNP ETTLRELSTY LTNPKLTAQL NL ERDHLID AISKYIDPNE LVPKGRLLHL LKQAIKYQQS QDIFNIIDPD DDASFSSPPH RINLLQDNFS HDLTVTFQEW KTI QDTTDE IWFLTFSPNG KYLASATSES SRGYFITVYD VEQDFKIYKT CVSLSQSVLY LMFSPDSRYL VACPFSEDVT IYDM NATSL PDASATDSFL LYPSTRLSPM DSFKLDTTTY PDDTESSASS SSRPANANSN QSRVWCCDAF HTAERAGWMV VGSPD REAI VHSLTTKESL FSLKGRTCIA LGHDENISGR KSIDPAKVLY KPTSSNGNWQ YVEDDETFPR VHDVKISYDD KYVLLM THQ GVIDVYDFSG FPSKEELSKQ TVDPKNFLIP RIARLDVGKN MTCISLPLNT THQGFHRQQI SESQHLVLVS LQDNELQ MW DYKENILIQK YFGQKQQHFI IRSCFAYGNK LVMSGSEDGK IYIWDRIRGN LVSVLSGHST VMSNSTKPMG KNCNVVAS N PADKEMFASG GDDGKIKIWK ISRN |
-分子 #3: Glucose-induced degradation protein 8
| 分子 | 名称: Glucose-induced degradation protein 8 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母) Saccharomyces cerevisiae (strain ATCC 204508 / S288c) (パン酵母)株: ATCC 204508 / S288c |
| 分子量 | 理論値: 55.803309 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MTISTLSNET TKSGSCSGQG KNGGKDFTYG KKCFTKEEWK EQVAKYSAMG ELYANKTIHY PLKIQPNSSG GSQDEGFATI QTTPIEPTL PRLLLNYFVS MAYEDSSIRM AKELGFIRNN KDIAVFNDLY KIKERFHIKH LIKLGRINEA MEEINSIFGL E VLEETFNA ...文字列: MTISTLSNET TKSGSCSGQG KNGGKDFTYG KKCFTKEEWK EQVAKYSAMG ELYANKTIHY PLKIQPNSSG GSQDEGFATI QTTPIEPTL PRLLLNYFVS MAYEDSSIRM AKELGFIRNN KDIAVFNDLY KIKERFHIKH LIKLGRINEA MEEINSIFGL E VLEETFNA TGSYTGRTDR QQQQQQQQFD IDGDLHFKLL LLNLIEMIRS HHQQENITKD SNDFILNLIQ YSQNKLAIKA SS SVKKMQE LELAMTLLLF PLSDSADSGS IKLPKSLQNL YSISLRSKIA DLVNEKLLKF IHPRIQFEIS NNNSKFPDLL NSD KKIITQ NFTVYNNNLV NGSNGTKITH ISSDQPINEK MSSNEVTAAA NSVWLNQRDG NVGTGSAATT FHNLENKNYW NQTS ELLSS SNGKEKGLEF NNYYSSEFPY EPRLTQIMKL WCWCENQLHH NQIGVPRVEN SDENLYFQSG WSHPQFEKGG GSGGG SGGS AWSHPQFEK |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 79.2 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー































 Z
Z Y
Y X
X