+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0212 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | PAN-proteasome in state 1 | |||||||||
 マップデータ マップデータ | Pseudo-single capped PAN-proteasome in state 1 | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報proteasome-activating nucleotidase complex / protein unfolding /  proteasome endopeptidase complex / proteasome core complex, beta-subunit complex / proteasome core complex, alpha-subunit complex / threonine-type endopeptidase activity / proteasomal protein catabolic process / ubiquitin-dependent protein catabolic process / proteasome endopeptidase complex / proteasome core complex, beta-subunit complex / proteasome core complex, alpha-subunit complex / threonine-type endopeptidase activity / proteasomal protein catabolic process / ubiquitin-dependent protein catabolic process /  ATP hydrolysis activity / ATP hydrolysis activity /  ATP binding / ATP binding /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |    Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) / Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) /    Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属) Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 6.86 Å クライオ電子顕微鏡法 / 解像度: 6.86 Å | |||||||||
 データ登録者 データ登録者 | Majumder P / Rudack T / Beck F / Baumeister W | |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2019 ジャーナル: Proc Natl Acad Sci U S A / 年: 2019タイトル: Cryo-EM structures of the archaeal PAN-proteasome reveal an around-the-ring ATPase cycle. 著者: Parijat Majumder / Till Rudack / Florian Beck / Radostin Danev / Günter Pfeifer / István Nagy / Wolfgang Baumeister /  要旨: Proteasomes occur in all three domains of life, and are the principal molecular machines for the regulated degradation of intracellular proteins. They play key roles in the maintenance of protein ...Proteasomes occur in all three domains of life, and are the principal molecular machines for the regulated degradation of intracellular proteins. They play key roles in the maintenance of protein homeostasis, and control vital cellular processes. While the eukaryotic 26S proteasome is extensively characterized, its putative evolutionary precursor, the archaeal proteasome, remains poorly understood. The primordial archaeal proteasome consists of a 20S proteolytic core particle (CP), and an AAA-ATPase module. This minimal complex degrades protein unassisted by non-ATPase subunits that are present in a 26S proteasome regulatory particle (RP). Using cryo-EM single-particle analysis, we determined structures of the archaeal CP in complex with the AAA-ATPase PAN (proteasome-activating nucleotidase). Five conformational states were identified, elucidating the functional cycle of PAN, and its interaction with the CP. Coexisting nucleotide states, and correlated intersubunit signaling features, coordinate rotation of the PAN-ATPase staircase, and allosterically regulate N-domain motions and CP gate opening. These findings reveal the structural basis for a sequential around-the-ring ATPase cycle, which is likely conserved in AAA-ATPases. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0212.map.gz emd_0212.map.gz | 7.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0212-v30.xml emd-0212-v30.xml emd-0212.xml emd-0212.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_0212.png emd_0212.png | 78.1 KB | ||
| その他 |  emd_0212_additional.map.gz emd_0212_additional.map.gz | 1.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0212 http://ftp.pdbj.org/pub/emdb/structures/EMD-0212 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0212 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0212 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6he8MC  0209C  0210C  0211C  0213C  0214C  0215C  0216C  6he4C  6he5C  6he7C  6he9C  6heaC  6hecC  6hedC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0212.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0212.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Pseudo-single capped PAN-proteasome in state 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.34 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: AAAob of PAN-proteasome in state 1
| ファイル | emd_0212_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | AAAob of PAN-proteasome in state 1 | ||||||||||||
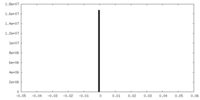
| 投影像・断面図 |
| ||||||||||||
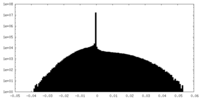
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : PAN-proteasome
| 全体 | 名称: PAN-proteasome |
|---|---|
| 要素 |
|
-超分子 #1: PAN-proteasome
| 超分子 | 名称: PAN-proteasome / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:    Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 分子量 | 理論値: 1.25 MDa |
-超分子 #2: 20S-proteasome
| 超分子 | 名称: 20S-proteasome / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:    Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
-超分子 #3: Proteasome-activating nucleotidase (PAN)
| 超分子 | 名称: Proteasome-activating nucleotidase (PAN) / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #3 |
|---|---|
| 由来(天然) | 生物種:    Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) Archaeoglobus fulgidus DSM 4304 (アルカエオグロブス属) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
-分子 #1: Proteasome subunit alpha
| 分子 | 名称: Proteasome subunit alpha / タイプ: protein_or_peptide / ID: 1 / コピー数: 14 / 光学異性体: LEVO / EC番号:  proteasome endopeptidase complex proteasome endopeptidase complex |
|---|---|
| 由来(天然) | 生物種:    Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属) Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属)株: ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126 |
| 分子量 | 理論値: 27.15616 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: QMGYDRAITV FSPDGRLFQV EYAREAVKRG ATAIGIKCKE GVILIADKRV GSKLLEADTI EKIYKIDEHI CAATSGLVAD ARVLIDRAR IEAQINRLTY DEPITVKELA KKICDFKQQY TQYGGVRPFG VSLLIAGVDE VPKLYETDPS GALLEYKATA I GMGRNAVT ...文字列: QMGYDRAITV FSPDGRLFQV EYAREAVKRG ATAIGIKCKE GVILIADKRV GSKLLEADTI EKIYKIDEHI CAATSGLVAD ARVLIDRAR IEAQINRLTY DEPITVKELA KKICDFKQQY TQYGGVRPFG VSLLIAGVDE VPKLYETDPS GALLEYKATA I GMGRNAVT EFFEKEYRDD LSFDDAMVLG LVAMGLSIES ELVPENIEVG YVKVDDRTFK EVSPEELKPY VERANERIRE LL KK |
-分子 #2: Proteasome subunit beta
| 分子 | 名称: Proteasome subunit beta / タイプ: protein_or_peptide / ID: 2 / コピー数: 14 / 光学異性体: LEVO / EC番号:  proteasome endopeptidase complex proteasome endopeptidase complex |
|---|---|
| 由来(天然) | 生物種:    Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属) Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属)株: ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126 |
| 分子量 | 理論値: 22.132283 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: TTTVGLVCKD GVVMATEKRA TMGNFIASKA AKKIYQIADR MAMTTAGSVG DAQFLARIIK IEANLYEIRR ERKPTVRAIA TLTSNLLNS YRYFPYLVQL LIGGIDSEGK SIYSIDPIGG AIEEKDIVAT GSGSLTAYGV LEDRFTPEIG VDEAVELAVR A IYSAMKRD ...文字列: TTTVGLVCKD GVVMATEKRA TMGNFIASKA AKKIYQIADR MAMTTAGSVG DAQFLARIIK IEANLYEIRR ERKPTVRAIA TLTSNLLNS YRYFPYLVQL LIGGIDSEGK SIYSIDPIGG AIEEKDIVAT GSGSLTAYGV LEDRFTPEIG VDEAVELAVR A IYSAMKRD SASGDGIDVV KITEDEFYQY SPEEVEQILA KFRK |
-分子 #3: Proteasome-activating nucleotidase
| 分子 | 名称: Proteasome-activating nucleotidase / タイプ: protein_or_peptide / ID: 3 / コピー数: 6 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属) Archaeoglobus fulgidus (strain ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126) (アルカエオグロブス属)株: ATCC 49558 / VC-16 / DSM 4304 / JCM 9628 / NBRC 100126 |
| 分子量 | 理論値: 44.102977 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: LLEKLKKLEE DYYKLRELYR RLEDEKKFIE SERIRYEREV RRLRSEVERL RSPPLLVGVV SDILEDGRVV VKSSTGPKFV VNTSQYINE EELKPGARVA LNQQTLAIVN VLPTSKDPMV YGFEVEEKPE VSYEDIGGLD VQIEEIREAV ELPLLKPELF A EVGIEPPK ...文字列: LLEKLKKLEE DYYKLRELYR RLEDEKKFIE SERIRYEREV RRLRSEVERL RSPPLLVGVV SDILEDGRVV VKSSTGPKFV VNTSQYINE EELKPGARVA LNQQTLAIVN VLPTSKDPMV YGFEVEEKPE VSYEDIGGLD VQIEEIREAV ELPLLKPELF A EVGIEPPK GVLLYGPPGT GKTLLAKAVA NQTRATFIRV VGSEFVQKYI GEGARLVREV FQLAKEKAPS IIFIDELDAI AA RRTNSDT SGDREVQRTM MQLLAELDGF DPRGDVKVIG ATNRIDILDP AILRPGRFDR IIEVPLPTFE GRIQIFKIHT RKM KLAEDV DFKELARITE GASGADIKAI CTEAGMFAIR EERAKVTMLD FTKAIEKVLK KTTPIPDLKG VMFV |
-分子 #4: ADENOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 4 / 式: ATP |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information |  ChemComp-ATP: |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 5 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #6: ADENOSINE-5'-DIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-DIPHOSPHATE / タイプ: ligand / ID: 6 / コピー数: 1 / 式: ADP |
|---|---|
| 分子量 | 理論値: 427.201 Da |
| Chemical component information |  ChemComp-ADP: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.1 |
|---|---|
| 凍結 | 凍結剤: ETHANE-PROPANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 30.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | ソフトウェア - 名称: MotionCorr2 |
|---|---|
| 初期 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 6.86 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 2.1) / 使用した粒子像数: 38230 |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-6he8: |
 ムービー
ムービー コントローラー
コントローラー













 Z
Z Y
Y X
X