+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0051 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Core Centromere Binding Factor 3 (CBF3) with monomeric Ndc10 | |||||||||
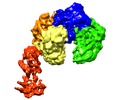
 マップデータ マップデータ | Reconstruction of the CBF3CCdeltaN (Core complex of CBF3 comprising the homodimer of Cep3deltaN and the heterodimer of Skp1-Ctf13) in complex with domains 1-2 of Ndc10 | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RAVE complex / Iron uptake and transport / CBF3 complex / regulation of transcription by galactose / regulation of sulfur amino acid metabolic process / cellular response to methylmercury / vacuolar proton-transporting V-type ATPase complex assembly / FBXL7 down-regulates AURKA during mitotic entry and in early mitosis /  septin ring assembly / mitotic spindle elongation ...RAVE complex / Iron uptake and transport / CBF3 complex / regulation of transcription by galactose / regulation of sulfur amino acid metabolic process / cellular response to methylmercury / vacuolar proton-transporting V-type ATPase complex assembly / FBXL7 down-regulates AURKA during mitotic entry and in early mitosis / septin ring assembly / mitotic spindle elongation ...RAVE complex / Iron uptake and transport / CBF3 complex / regulation of transcription by galactose / regulation of sulfur amino acid metabolic process / cellular response to methylmercury / vacuolar proton-transporting V-type ATPase complex assembly / FBXL7 down-regulates AURKA during mitotic entry and in early mitosis /  septin ring assembly / mitotic spindle elongation / centromeric DNA binding / regulation of exit from mitosis / Antigen processing: Ubiquitination & Proteasome degradation / vacuolar acidification / septin ring assembly / mitotic spindle elongation / centromeric DNA binding / regulation of exit from mitosis / Antigen processing: Ubiquitination & Proteasome degradation / vacuolar acidification /  kinetochore assembly / condensed chromosome, centromeric region / kinetochore assembly / condensed chromosome, centromeric region /  regulation of metabolic process / exit from mitosis / regulation of metabolic process / exit from mitosis /  spindle pole body / positive regulation of glucose transmembrane transport / protein neddylation / mitotic intra-S DNA damage checkpoint signaling / silent mating-type cassette heterochromatin formation / spindle pole body / positive regulation of glucose transmembrane transport / protein neddylation / mitotic intra-S DNA damage checkpoint signaling / silent mating-type cassette heterochromatin formation /  mitochondrial fusion / DNA binding, bending / SCF-dependent proteasomal ubiquitin-dependent protein catabolic process / mitochondrial fusion / DNA binding, bending / SCF-dependent proteasomal ubiquitin-dependent protein catabolic process /  SCF複合体 / mitotic spindle assembly checkpoint signaling / SCF複合体 / mitotic spindle assembly checkpoint signaling /  DNA replication origin binding / regulation of mitotic cell cycle / cullin family protein binding / subtelomeric heterochromatin formation / regulation of protein-containing complex assembly / spindle midzone / DNA replication origin binding / regulation of mitotic cell cycle / cullin family protein binding / subtelomeric heterochromatin formation / regulation of protein-containing complex assembly / spindle midzone /  細胞内膜系 / negative regulation of cytoplasmic translation / 細胞内膜系 / negative regulation of cytoplasmic translation /  chromosome segregation / G1/S transition of mitotic cell cycle / spindle / chromosome segregation / G1/S transition of mitotic cell cycle / spindle /  動原体 / G2/M transition of mitotic cell cycle / mitotic cell cycle / ubiquitin-dependent protein catabolic process / protein-containing complex assembly / 動原体 / G2/M transition of mitotic cell cycle / mitotic cell cycle / ubiquitin-dependent protein catabolic process / protein-containing complex assembly /  chromosome, telomeric region / protein ubiquitination / DNA-binding transcription factor activity, RNA polymerase II-specific / chromosome, telomeric region / protein ubiquitination / DNA-binding transcription factor activity, RNA polymerase II-specific /  DNA binding / zinc ion binding / identical protein binding / DNA binding / zinc ion binding / identical protein binding /  細胞核 / 細胞核 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.2 Å クライオ電子顕微鏡法 / 解像度: 4.2 Å | |||||||||
 データ登録者 データ登録者 | Zhang WJ / Lukoynova N / Vaughan CK | |||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2018 ジャーナル: Cell Rep / 年: 2018タイトル: Insights into Centromere DNA Bending Revealed by the Cryo-EM Structure of the Core Centromere Binding Factor 3 with Ndc10. 著者: Wenjuan Zhang / Natalya Lukoyanova / Shomon Miah / Jonathan Lucas / Cara K Vaughan /  要旨: The centromere binding factor 3 (CBF3) complex binds the third centromere DNA element in organisms with point centromeres, such as S. cerevisiae. It is an essential complex for assembly of the ...The centromere binding factor 3 (CBF3) complex binds the third centromere DNA element in organisms with point centromeres, such as S. cerevisiae. It is an essential complex for assembly of the kinetochore in these organisms, as it facilitates genetic centromere specification and allows association of all other kinetochore components. We determined high-resolution structures of the core complex of CBF3 alone and in association with a monomeric construct of Ndc10, using cryoelectron microscopy (cryo-EM). We identify the DNA-binding site of the complex and present a model in which CBF3 induces a tight bend in centromeric DNA, thus facilitating assembly of the centromeric nucleosome. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0051.map.gz emd_0051.map.gz | 59.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0051-v30.xml emd-0051-v30.xml emd-0051.xml emd-0051.xml | 19.3 KB 19.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_0051_fsc.xml emd_0051_fsc.xml | 9.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_0051.png emd_0051.png | 129.6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0051 http://ftp.pdbj.org/pub/emdb/structures/EMD-0051 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0051 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0051 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0051.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0051.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of the CBF3CCdeltaN (Core complex of CBF3 comprising the homodimer of Cep3deltaN and the heterodimer of Skp1-Ctf13) in complex with domains 1-2 of Ndc10 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Core CBF3 in complex with Ndc10 D1-2
| 全体 | 名称: Core CBF3 in complex with Ndc10 D1-2 |
|---|---|
| 要素 |
|
-超分子 #1: Core CBF3 in complex with Ndc10 D1-2
| 超分子 | 名称: Core CBF3 in complex with Ndc10 D1-2 / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: The truncated CBF3 complex, recombinantly expressed in Saccharomyces cerevisiae. It comprises a Cep3 homodimer, in which the binuclear zinc cluster domains are truncated, full length ...詳細: The truncated CBF3 complex, recombinantly expressed in Saccharomyces cerevisiae. It comprises a Cep3 homodimer, in which the binuclear zinc cluster domains are truncated, full length heterodimer of Skp1 and Ctf13, and a monomeric construct Ndc10 comprising domains 1-2. |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 組換発現 | 生物種:   Saccharomyces cerevisiae (パン酵母) / 組換プラスミド: modified pRS424 and pRS426 Saccharomyces cerevisiae (パン酵母) / 組換プラスミド: modified pRS424 and pRS426 |
| 分子量 | 理論値: 286 KDa |
-分子 #1: Centromere DNA-binding protein complex CBF3 subunit B
| 分子 | 名称: Centromere DNA-binding protein complex CBF3 subunit B タイプ: protein_or_peptide / ID: 1 詳細: N-terminal polyhistidine purification tagTruncation of the binuclear zinc cluster domain コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 68.454125 KDa |
| 組換発現 | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 配列 | 文字列: MGGSSHHHHH HSSGLVPRGS HMKLITASSS KEYLPDLLLF WQNYEYWITN IGLYKTKQRD LTRTPANLDT DTEECMFWMN YLQKDQSFQ LMNFAMENLG ALYFGSIGDI SELYLRVEQY WDRRADKNHS VDGKYWDALI WSVFTMCIYY MPVEKLAEIF S VYPLHEYL ...文字列: MGGSSHHHHH HSSGLVPRGS HMKLITASSS KEYLPDLLLF WQNYEYWITN IGLYKTKQRD LTRTPANLDT DTEECMFWMN YLQKDQSFQ LMNFAMENLG ALYFGSIGDI SELYLRVEQY WDRRADKNHS VDGKYWDALI WSVFTMCIYY MPVEKLAEIF S VYPLHEYL GSNKRLNWED GMQLVMCQNF ARCSLFQLKQ CDFMAHPDIR LVQAYLILAT TTFPYDEPLL ANSLLTQCIH TF KNFHVDD FRPLLNDDPV ESIAKVTLGR IFYRLCGCDY LQSGPRKPIA LHTEVSSLLQ HAAYLQDLPN VDVYREENST EVL YWKIIS LDRDLDQYLN KSSKPPLKTL DAIRRELDIF QYKVDSLEED FRSNNSRFQK FIALFQISTV SWKLFKMYLI YYDT ADSLL KVIHYSKVII SLIVNNFHAK SEFFNRHPMV MQTITRVVSF ISFYQIFVES AAVKQLLVDL TELTANLPTI FGSKL DKLV YLTERLSKLK LLWDKVQLLD SGDSFYHPVF KILQNDIKII ELKNDEMFSL IKGLGSLVPL NKLRQESLLE EEDENN TEP SDFRTIVEEF QSEYNISDIL S |
-分子 #2: Suppressor of kinetochore protein 1
| 分子 | 名称: Suppressor of kinetochore protein 1 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 22.558451 KDa |
| 組換発現 | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 配列 | 文字列: MGVTSNVVLV SGEGERFTVD KKIAERSLLL KNYLNDMHDS NLQNNSDSES DSDSETNHKS KDNNNGDDDD EDDDEIVMPV PNVRSSVLQ KVIEWAEHHR DSNFPDEDDD DSRKSAPVDS WDREFLKVDQ EMLYEIILAA NYLNIKPLLD AGCKVVAEMI R GRSPEEIR ...文字列: MGVTSNVVLV SGEGERFTVD KKIAERSLLL KNYLNDMHDS NLQNNSDSES DSDSETNHKS KDNNNGDDDD EDDDEIVMPV PNVRSSVLQ KVIEWAEHHR DSNFPDEDDD DSRKSAPVDS WDREFLKVDQ EMLYEIILAA NYLNIKPLLD AGCKVVAEMI R GRSPEEIR RTFNIVNDFT PEEEAAIRRE NEWAEDRGS |
-分子 #3: Centromere DNA-binding protein complex CBF3 subunit C
| 分子 | 名称: Centromere DNA-binding protein complex CBF3 subunit C タイプ: protein_or_peptide / ID: 3 / 詳細: C-terminal CBP purification tag / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 60.899961 KDa |
| 組換発現 | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 配列 | 文字列: MGPSFNPVRF LELPIDIRKE VYFHLDGNFC GAHPYPIDIL YKSNDVELPG KPSYKRSKRS KKLLRYMYPV FATYLNIFEY SPQLIEKWL EYAFWLRYDC LVLDCFKVNH LYDGTLIDAL EWTYLDNELR LAYFNKASML EVWYTFKEYK KWVIDSVAFD E LDLLNVSN ...文字列: MGPSFNPVRF LELPIDIRKE VYFHLDGNFC GAHPYPIDIL YKSNDVELPG KPSYKRSKRS KKLLRYMYPV FATYLNIFEY SPQLIEKWL EYAFWLRYDC LVLDCFKVNH LYDGTLIDAL EWTYLDNELR LAYFNKASML EVWYTFKEYK KWVIDSVAFD E LDLLNVSN IQFNIDNLTP QLVDKCLSIL EQKDLFATIG EVQFGQDEEV GEEKDVDVSG ANSDENSSPS STIKNKKRSA SK RSHSDNG NVGATHNQLT SISVIRTIRS MESMKSLRKI TVRGEKLYEL LINFHGFRDN PGKTISYIVK RRINEIRLSR MNQ ISRTGL ADFTRWDNLQ KLVLSRVAYI DLNSIVFPKN FKSLTMKRVS KIKWWNIEEN ILKELKVDKR TFKSLYIKED DSKF TKFFN LRHTRIKELD KSEINQITYL RCQAIVWLSF RTLNHIKLQN VSEVFNNIIV PRALFDSKRV EIYRCEKISQ VLVIG SRSG SENLYFQGSK RRWKKNFIAV SAANRFKKIS SSGAL |
-分子 #4: Centromere DNA-binding protein complex CBF3 subunit A
| 分子 | 名称: Centromere DNA-binding protein complex CBF3 subunit A タイプ: protein_or_peptide / ID: 4 詳細: Domains 1-2 of Ndc10 with a non-cleavable C-terminal StrepII tag コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 66.159578 KDa |
| 組換発現 | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 配列 | 文字列: MGRSSILFLL KLMKIMDVQQ QQEAMSSEDR FQELVDSLKP RTAHQYKTYY TKYIQWCQLN QIIPTPEDNS VNSVPYKDLP ISAELIHWF LLDTLITDDK PGEKREETED LDEEEENSFK IATLKKIIGS LNFLSKLCKV HENPNANIDT KYLESVTKLH T HWIDSQKA ...文字列: MGRSSILFLL KLMKIMDVQQ QQEAMSSEDR FQELVDSLKP RTAHQYKTYY TKYIQWCQLN QIIPTPEDNS VNSVPYKDLP ISAELIHWF LLDTLITDDK PGEKREETED LDEEEENSFK IATLKKIIGS LNFLSKLCKV HENPNANIDT KYLESVTKLH T HWIDSQKA ITTNETNNTN TQVLCPPLLK VSLNLWNPET NHLSEKFFKT CSEKLRFLVD FQLRSYLNLS FEERSKIRFG SL KLGKRDR DAIIYHKVTH SAEKKDTPGH HQLLALLPQD CPFICPQTTL AAYLYLRFYG IPSVSKGDGF PNLNADENGS LLQ DIPILR GKSLTTYPRE ETFSNYYTTV FRYCHLPYKR REYFNKCNLV YPTWDEDTFR TFFNEENHGN WLEQPEAFAF PDKI PFDFK KIMNFKSPYT SYSTNAKKDP FPPPKDLLVQ IFPEIDEYKR HDYEGLSQNS RDFLDLMEVL RERFLSNLPW IYKFF PNHD IFQDPIFGNS DFQSYFNDKT IHSKGSPILS FDILPGFNKI YKNKTNFYSL LIERPSQLTF ASSHNPDTHP WSHPQF EK |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.15 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil, UltrAuFoil, R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK I | ||||||||||||
| 詳細 | The sample is homogeneous and well-dispersed on grids. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 47170 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm Bright-field microscopy / Cs: 2.7 mm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - 画像ごとのフレーム数: 1-40 / 撮影したグリッド数: 1 / 実像数: 2003 / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 詳細 | "Fit in map" function used to place 6FE8 and 4ACO with out further refinement or model building |
|---|---|
| 得られたモデル |  PDB-6gsa: |
 ムービー
ムービー コントローラー
コントローラー