+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0039 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of paused transcription complex Pol II-DSIF-NELF | |||||||||
 マップデータ マップデータ | Globally refined PEC map selected for NELF-AC containing particles (Map 2). | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |   Sus scrofa (ブタ) / Sus scrofa (ブタ) /   Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
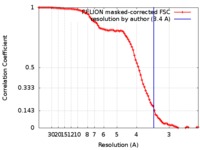
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.4 Å クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Vos SM / Farnung L / Urlaub H / Cramer P | |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2018 ジャーナル: Nature / 年: 2018タイトル: Structure of paused transcription complex Pol II-DSIF-NELF. 著者: Seychelle M Vos / Lucas Farnung / Henning Urlaub / Patrick Cramer /  要旨: Metazoan gene regulation often involves the pausing of RNA polymerase II (Pol II) in the promoter-proximal region. Paused Pol II is stabilized by the protein complexes DRB sensitivity-inducing factor ...Metazoan gene regulation often involves the pausing of RNA polymerase II (Pol II) in the promoter-proximal region. Paused Pol II is stabilized by the protein complexes DRB sensitivity-inducing factor (DSIF) and negative elongation factor (NELF). Here we report the cryo-electron microscopy structure of a paused transcription elongation complex containing Sus scrofa Pol II and Homo sapiens DSIF and NELF at 3.2 Å resolution. The structure reveals a tilted DNA-RNA hybrid that impairs binding of the nucleoside triphosphate substrate. NELF binds the polymerase funnel, bridges two mobile polymerase modules, and contacts the trigger loop, thereby restraining Pol II mobility that is required for pause release. NELF prevents binding of the anti-pausing transcription elongation factor IIS (TFIIS). Additionally, NELF possesses two flexible 'tentacles' that can contact DSIF and exiting RNA. These results define the paused state of Pol II and provide the molecular basis for understanding the function of NELF during promoter-proximal gene regulation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0039.map.gz emd_0039.map.gz | 49.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0039-v30.xml emd-0039-v30.xml emd-0039.xml emd-0039.xml | 23.5 KB 23.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_0039_fsc.xml emd_0039_fsc.xml | 9.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_0039.png emd_0039.png | 204.2 KB | ||
| マスクデータ |  emd_0039_msk_1.map emd_0039_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| その他 |  emd_0039_additional.map.gz emd_0039_additional.map.gz emd_0039_half_map_1.map.gz emd_0039_half_map_1.map.gz emd_0039_half_map_2.map.gz emd_0039_half_map_2.map.gz | 7.7 MB 49.6 MB 49.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0039 http://ftp.pdbj.org/pub/emdb/structures/EMD-0039 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0039 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0039 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0039.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0039.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Globally refined PEC map selected for NELF-AC containing particles (Map 2). | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.2277 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_0039_msk_1.map emd_0039_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Postprocessed/B-factor sharpened NELF-AC selected particles PEC map (Map...
| ファイル | emd_0039_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Postprocessed/B-factor sharpened NELF-AC selected particles PEC map (Map 2). Applied B-factor of -65. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1 for globally refined NELF-AC containing particles (Map 2).
| ファイル | emd_0039_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 for globally refined NELF-AC containing particles (Map 2). | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 2 for globally refined NELF-AC containing particles (Map 2).
| ファイル | emd_0039_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 for globally refined NELF-AC containing particles (Map 2). | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : RNA Polymerase II-DSIF-PAF-SPT6 elongation complex (EC*)
| 全体 | 名称: RNA Polymerase II-DSIF-PAF-SPT6 elongation complex (EC*) |
|---|---|
| 要素 |
|
-超分子 #1: RNA Polymerase II-DSIF-PAF-SPT6 elongation complex (EC*)
| 超分子 | 名称: RNA Polymerase II-DSIF-PAF-SPT6 elongation complex (EC*) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#21, #23 |
|---|---|
| 分子量 | 理論値: 927.1 KDa |
-超分子 #2: RNA Polymerase II
| 超分子 | 名称: RNA Polymerase II / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#9, #11, #10, #12 |
|---|---|
| 由来(天然) | 生物種:   Sus scrofa (ブタ) Sus scrofa (ブタ) |
-超分子 #3: associated proteins
| 超分子 | 名称: associated proteins / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #13, #16, #18, #23, #19-#22 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
-超分子 #4: Nucleic acids
| 超分子 | 名称: Nucleic acids / タイプ: complex / ID: 4 / 親要素: 1 / 含まれる分子: #14-#15, #17 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 組換発現 | 生物種: synthetic construct (人工物) |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD Bright-field microscopy / 倍率(公称値): 165000 Bright-field microscopy / 倍率(公称値): 165000 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS / エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 検出モード: COUNTING / 実像数: 11740 / 平均露光時間: 9.0 sec. / 平均電子線量: 46.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X