+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of BCL10 R58Q filament | |||||||||
 マップデータ マップデータ | CryoEM structure of BCL10 R58Q | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | filament / CBM complex / IMMUNE SYSTEM | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of lymphotoxin A production / polkadots / CBM complex / antifungal innate immune response / protein kinase B binding / T cell apoptotic process / positive regulation of mast cell cytokine production / CARD domain binding / programmed cell death / negative regulation of mature B cell apoptotic process ...positive regulation of lymphotoxin A production / polkadots / CBM complex / antifungal innate immune response / protein kinase B binding / T cell apoptotic process / positive regulation of mast cell cytokine production / CARD domain binding / programmed cell death / negative regulation of mature B cell apoptotic process / B cell apoptotic process / positive regulation of extrinsic apoptotic signaling pathway / response to food / non-canonical NF-kappaB signal transduction / toll-like receptor signaling pathway / positive regulation of T cell receptor signaling pathway / cytoplasmic microtubule / positive regulation of cysteine-type endopeptidase activity involved in apoptotic process / positive regulation of phosphorylation / general transcription initiation factor binding / immunological synapse / NF-kappaB binding / immunoglobulin mediated immune response / cellular defense response / lipopolysaccharide-mediated signaling pathway / positive regulation of protein ubiquitination / neural tube closure / positive regulation of interleukin-8 production / Activation of NF-kappaB in B cells / cellular response to mechanical stimulus / protein homooligomerization / CLEC7A (Dectin-1) signaling / FCERI mediated NF-kB activation / positive regulation of interleukin-6 production / positive regulation of T cell activation / Downstream TCR signaling / E3 ubiquitin ligases ubiquitinate target proteins / positive regulation of NF-kappaB transcription factor activity / protein-macromolecule adaptor activity / T cell receptor signaling pathway / positive regulation of canonical NF-kappaB signal transduction / protease binding / cellular response to lipopolysaccharide / transcription coactivator activity / adaptive immune response / lysosome / membrane raft / positive regulation of apoptotic process / innate immune response / ubiquitin protein ligase binding / positive regulation of DNA-templated transcription / protein-containing complex binding / perinuclear region of cytoplasm / protein-containing complex / identical protein binding / nucleus / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 4.6 Å | |||||||||
 データ登録者 データ登録者 | David L / Wu H | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Cancer Discov / 年: 2022 ジャーナル: Cancer Discov / 年: 2022タイトル: BCL10 Mutations Define Distinct Dependencies Guiding Precision Therapy for DLBCL. 著者: Min Xia / Liron David / Matt Teater / Johana Gutierrez / Xiang Wang / Cem Meydan / Andrew Lytle / Graham W Slack / David W Scott / Ryan D Morin / Ozlem Onder / Kojo S J Elenitoba-Johnson / ...著者: Min Xia / Liron David / Matt Teater / Johana Gutierrez / Xiang Wang / Cem Meydan / Andrew Lytle / Graham W Slack / David W Scott / Ryan D Morin / Ozlem Onder / Kojo S J Elenitoba-Johnson / Nahuel Zamponi / Leandro Cerchietti / Tianbao Lu / Ulrike Philippar / Lorena Fontan / Hao Wu / Ari M Melnick /    要旨: Activated B cell-like diffuse large B-cell lymphomas (ABC-DLBCL) have unfavorable outcomes and chronic activation of CARD11-BCL10-MALT1 (CBM) signal amplification complexes that form due to ...Activated B cell-like diffuse large B-cell lymphomas (ABC-DLBCL) have unfavorable outcomes and chronic activation of CARD11-BCL10-MALT1 (CBM) signal amplification complexes that form due to polymerization of BCL10 subunits, which is affected by recurrent somatic mutations in ABC-DLBCLs. Herein, we show that BCL10 mutants fall into at least two functionally distinct classes: missense mutations of the BCL10 CARD domain and truncation of its C-terminal tail. Truncating mutations abrogated a motif through which MALT1 inhibits BCL10 polymerization, trapping MALT1 in its activated filament-bound state. CARD missense mutations enhanced BCL10 filament formation, forming glutamine network structures that stabilize BCL10 filaments. Mutant forms of BCL10 were less dependent on upstream CARD11 activation and thus manifested resistance to BTK inhibitors, whereas BCL10 truncating but not CARD mutants were hypersensitive to MALT1 inhibitors. Therefore, BCL10 mutations are potential biomarkers for BTK inhibitor resistance in ABC-DLBCL, and further precision can be achieved by selecting therapy based on specific biochemical effects of distinct mutation classes. SIGNIFICANCE: ABC-DLBCLs feature frequent mutations of signaling mediators that converge on the CBM complex. We use structure-function approaches to reveal that BCL10 mutations fall into two distinct ...SIGNIFICANCE: ABC-DLBCLs feature frequent mutations of signaling mediators that converge on the CBM complex. We use structure-function approaches to reveal that BCL10 mutations fall into two distinct biochemical classes. Both classes confer resistance to BTK inhibitors, whereas BCL10 truncations confer hyperresponsiveness to MALT1 inhibitors, providing a road map for precision therapies in ABC-DLBCLs. See related commentary by Phelan and Oellerich, p. 1844. This article is highlighted in the In This Issue feature, p. 1825. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_27095.map.gz emd_27095.map.gz | 71.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-27095-v30.xml emd-27095-v30.xml emd-27095.xml emd-27095.xml | 15.1 KB 15.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_27095.png emd_27095.png | 173 KB | ||
| Filedesc metadata |  emd-27095.cif.gz emd-27095.cif.gz | 5.2 KB | ||
| その他 |  emd_27095_half_map_1.map.gz emd_27095_half_map_1.map.gz emd_27095_half_map_2.map.gz emd_27095_half_map_2.map.gz | 59.7 MB 59.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-27095 http://ftp.pdbj.org/pub/emdb/structures/EMD-27095 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27095 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27095 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8czdMC  8czoC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_27095.map.gz / 形式: CCP4 / 大きさ: 76.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_27095.map.gz / 形式: CCP4 / 大きさ: 76.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoEM structure of BCL10 R58Q | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.87 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: half map1
| ファイル | emd_27095_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map1 | ||||||||||||
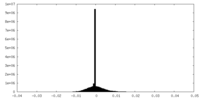
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map 2
| ファイル | emd_27095_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 2 | ||||||||||||
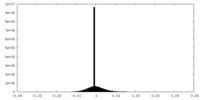
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : filament
| 全体 | 名称: filament |
|---|---|
| 要素 |
|
-超分子 #1: filament
| 超分子 | 名称: filament / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: B-cell lymphoma/leukemia 10
| 分子 | 名称: B-cell lymphoma/leukemia 10 / タイプ: protein_or_peptide / ID: 1 / コピー数: 20 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 12.585502 KDa |
| 組換発現 | 生物種:  Escherichia phage EcSzw-2 (ファージ) Escherichia phage EcSzw-2 (ファージ) |
| 配列 | 文字列: EEDLTEVKKD ALENLRVYLC EKIIAERHFD HLRAKKILSR EDTEEISCQT SSRKRAGKLL DYLQENPKGL DTLVESIRRE KTQNFLIQK ITDEVLKLRN IKLEHLK UniProtKB: B-cell lymphoma/leukemia 10 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 300 | |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK III |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 撮影したグリッド数: 1 / 実像数: 3439 / 平均電子線量: 38.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 2.7 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 36000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 想定した対称性 - らせんパラメータ - Δz: 5.0 Å 想定した対称性 - らせんパラメータ - ΔΦ: -100.8 ° 想定した対称性 - らせんパラメータ - 軸対称性: C1 (非対称) 解像度のタイプ: BY AUTHOR / 解像度: 4.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1) / 使用した粒子像数: 30000 |
|---|---|
| 初期モデル | モデルのタイプ: EMDB MAP EMDB ID: |
| 最終 角度割当 | タイプ: NOT APPLICABLE |
 ムービー
ムービー コントローラー
コントローラー










 Z
Z Y
Y X
X