+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Chaetoceros socialis forma radians RNA virus 1 full capsid | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | pseudo-T=3 / icosahedral / VIRUS | |||||||||
| 機能・相同性 | Capsid protein VP4, dicistrovirus / Cricket paralysis virus, VP4 / Dicistrovirus, capsid-polyprotein, C-terminal / CRPV capsid protein like / Picornavirus/Calicivirus coat protein / Viral coat protein subunit / Structural polyprotein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Chaetoceros socialis forma radians RNA virus 1 (ウイルス) Chaetoceros socialis forma radians RNA virus 1 (ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.0 Å | |||||||||
 データ登録者 データ登録者 | Wang H / Okamoto K / Munke A | |||||||||
| 資金援助 |  スウェーデン, 1件 スウェーデン, 1件
| |||||||||
 引用 引用 |  ジャーナル: Viruses / 年: 2022 ジャーナル: Viruses / 年: 2022タイトル: Structural Insights into Common and Host-Specific Receptor-Binding Mechanisms in Algal Picorna-like Viruses. 著者: Han Wang / Anna Munke / Siqi Li / Yuji Tomaru / Kenta Okamoto /    要旨: viruses are abundant algal viruses that regulate the dynamics of algal blooms in aquatic environments. They employ a narrow host range because they merely lyse their algal host species. This host- ... viruses are abundant algal viruses that regulate the dynamics of algal blooms in aquatic environments. They employ a narrow host range because they merely lyse their algal host species. This host-specific lysis is thought to correspond to the unique receptor-binding mechanism of the viruses. Here, we present the atomic structures of the full and empty capsids of Chaetoceros socialis forma radians RNA virus 1 built-in 3.0 Å and 3.1 Å cryo-electron microscopy maps. The empty capsid structure and the structural variability provide insights into its assembly and uncoating intermediates. In conjunction with the previously reported atomic model of the Chaetoceros tenuissimus RNA virus type II capsid, we have identified the common and diverse structural features of the VP1 surface between the viruses. We have also tested the potential usage of AlphaFold2 for structural prediction of the VP1s and a subsequent structural phylogeny for classifying viruses by their hosts. These findings will be crucial for inferring the host-specific receptor-binding mechanism in viruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15823.map.gz emd_15823.map.gz | 154.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15823-v30.xml emd-15823-v30.xml emd-15823.xml emd-15823.xml | 15 KB 15 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_15823.png emd_15823.png | 224.3 KB | ||
| Filedesc metadata |  emd-15823.cif.gz emd-15823.cif.gz | 5.4 KB | ||
| その他 |  emd_15823_half_map_1.map.gz emd_15823_half_map_1.map.gz emd_15823_half_map_2.map.gz emd_15823_half_map_2.map.gz | 151.3 MB 151.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15823 http://ftp.pdbj.org/pub/emdb/structures/EMD-15823 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15823 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15823 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8b38MC  8b3jC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15823.map.gz / 形式: CCP4 / 大きさ: 163.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15823.map.gz / 形式: CCP4 / 大きさ: 163.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||
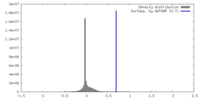
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_15823_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
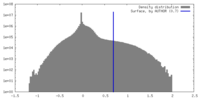
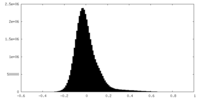
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_15823_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
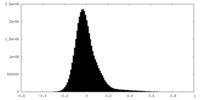
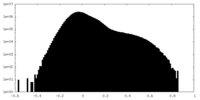
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Chaetoceros socialis forma radians RNA virus 1
| 全体 | 名称:  Chaetoceros socialis forma radians RNA virus 1 (ウイルス) Chaetoceros socialis forma radians RNA virus 1 (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Chaetoceros socialis forma radians RNA virus 1
| 超分子 | 名称: Chaetoceros socialis forma radians RNA virus 1 / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / NCBI-ID: 2169725 / 生物種: Chaetoceros socialis forma radians RNA virus 1 / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|
-分子 #1: Structural polyprotein
| 分子 | 名称: Structural polyprotein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Chaetoceros socialis forma radians RNA virus 1 (ウイルス) Chaetoceros socialis forma radians RNA virus 1 (ウイルス) |
| 分子量 | 理論値: 29.930619 KDa |
| 配列 | 文字列: SPLAIAGNRA GGSGAITLEP FGSDNTSPEL SKLHFGETYD HMRVLVKGYN FYKAVLDNTT ITDPDNPSGT VVIRSTVPDF PAPRGHIPN GPDKPFLPHP ENAALCTHLT WFSPCYVARR GGIRWKYLHF GARFGATDAP KGLGFVNRVP QVPYGRRPLG N ERLPLTDV ...文字列: SPLAIAGNRA GGSGAITLEP FGSDNTSPEL SKLHFGETYD HMRVLVKGYN FYKAVLDNTT ITDPDNPSGT VVIRSTVPDF PAPRGHIPN GPDKPFLPHP ENAALCTHLT WFSPCYVARR GGIRWKYLHF GARFGATDAP KGLGFVNRVP QVPYGRRPLG N ERLPLTDV NGFNPTELSQ AFSNENGGVY ATDLDVQPAI EVELPFYSSL RFVNPRWDDY EKIGIHRHSI DLLSYRTNGA KC EDAWMAY VAAGDDFNLS WMLSCPPFRL VNL UniProtKB: Structural polyprotein |
-分子 #2: Structural polyprotein
| 分子 | 名称: Structural polyprotein / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Chaetoceros socialis forma radians RNA virus 1 (ウイルス) Chaetoceros socialis forma radians RNA virus 1 (ウイルス) |
| 分子量 | 理論値: 26.871293 KDa |
| 配列 | 文字列: AVKDTIEGNS ETLSGTHQNE TLALYSNVDQ TAVKIMSSID PTRADCVSND HELGNFLSRP VRIMRESISL DERTSTTIAP WDVYLRHPM INKKIANYEY LRANLVLEVV VNGGPFFYGK MLLGYTPFGY EDSLKNFNRI PIGHQNTMLS QQPHVKIDFC E STGGVLHL ...文字列: AVKDTIEGNS ETLSGTHQNE TLALYSNVDQ TAVKIMSSID PTRADCVSND HELGNFLSRP VRIMRESISL DERTSTTIAP WDVYLRHPM INKKIANYEY LRANLVLEVV VNGGPFFYGK MLLGYTPFGY EDSLKNFNRI PIGHQNTMLS QQPHVKIDFC E STGGVLHL PFVYNRNYMR ISEGSGEPAS MGELRLNTLN ALKNISFTGP ASSVATITVF AYLDNVELVA PSANDPITAQ QP EL UniProtKB: Structural polyprotein |
-分子 #3: Structural polyprotein
| 分子 | 名称: Structural polyprotein / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Chaetoceros socialis forma radians RNA virus 1 (ウイルス) Chaetoceros socialis forma radians RNA virus 1 (ウイルス) |
| 分子量 | 理論値: 31.098668 KDa |
| 配列 | 文字列: CRPVVIDPPH KYRPTYVGNM ANADIAEAVD KLSLTSKQEL TINHDVIGKK SDGDDMHLST FFGREAYMDR FEWKTTDSYD TLLFYTHVH PILFKRFEAT SGDYDVGMLL PPVGYATIPF SFWRGGMTFR FSIVASAFHR GRLRIVYQPQ GGLGTVPGFS A AFNRVIDL ...文字列: CRPVVIDPPH KYRPTYVGNM ANADIAEAVD KLSLTSKQEL TINHDVIGKK SDGDDMHLST FFGREAYMDR FEWKTTDSYD TLLFYTHVH PILFKRFEAT SGDYDVGMLL PPVGYATIPF SFWRGGMTFR FSIVASAFHR GRLRIVYQPQ GGLGTVPGFS A AFNRVIDL GDARDFEVTV EWNQNIAFRE VHTTGSNVPS AQYTPGLDVG RTSQLPLGDQ TSVSNGVLAV YVVNDLVSPD GG TDESVEV NWFVKGAPSF EVASRDTKFA RWSTHWSQEE F UniProtKB: Structural polyprotein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 30.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 3984 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー





 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)