+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8ox7 | |||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
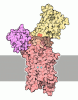
| タイトル | Cryo-EM structure of ATP8B1-CDC50A in E2P autoinhibited "closed" conformation | |||||||||||||||||||||||||||
 要素 要素 |
| |||||||||||||||||||||||||||
 キーワード キーワード |  MEMBRANE PROTEIN (膜タンパク質) / lipid transporter autoinhibition P-type ATPase P4-ATPase CDC50A MEMBRANE PROTEIN (膜タンパク質) / lipid transporter autoinhibition P-type ATPase P4-ATPase CDC50A | |||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報vestibulocochlear nerve formation / regulation of plasma membrane organization /  regulation of microvillus assembly / positive regulation of phospholipid translocation / phosphatidylcholine flippase activity / aminophospholipid flippase activity / aminophospholipid transport / phosphatidylserine flippase activity / protein localization to endosome / inner ear receptor cell development ...vestibulocochlear nerve formation / regulation of plasma membrane organization / regulation of microvillus assembly / positive regulation of phospholipid translocation / phosphatidylcholine flippase activity / aminophospholipid flippase activity / aminophospholipid transport / phosphatidylserine flippase activity / protein localization to endosome / inner ear receptor cell development ...vestibulocochlear nerve formation / regulation of plasma membrane organization /  regulation of microvillus assembly / positive regulation of phospholipid translocation / phosphatidylcholine flippase activity / aminophospholipid flippase activity / aminophospholipid transport / phosphatidylserine flippase activity / protein localization to endosome / inner ear receptor cell development / phosphatidylserine floppase activity / regulation of microvillus assembly / positive regulation of phospholipid translocation / phosphatidylcholine flippase activity / aminophospholipid flippase activity / aminophospholipid transport / phosphatidylserine flippase activity / protein localization to endosome / inner ear receptor cell development / phosphatidylserine floppase activity /  phospholipid-translocating ATPase complex / ATPase-coupled intramembrane lipid transporter activity / positive regulation of protein exit from endoplasmic reticulum / xenobiotic transmembrane transport / phospholipid-translocating ATPase complex / ATPase-coupled intramembrane lipid transporter activity / positive regulation of protein exit from endoplasmic reticulum / xenobiotic transmembrane transport /  cardiolipin binding / phosphatidylcholine floppase activity / stereocilium / apical protein localization / bile acid metabolic process / bile acid and bile salt transport / P-type phospholipid transporter / phospholipid translocation / transport vesicle membrane / azurophil granule membrane / Golgi organization / Ion transport by P-type ATPases / specific granule membrane / monoatomic ion transmembrane transport / regulation of chloride transport / sensory perception of sound / cardiolipin binding / phosphatidylcholine floppase activity / stereocilium / apical protein localization / bile acid metabolic process / bile acid and bile salt transport / P-type phospholipid transporter / phospholipid translocation / transport vesicle membrane / azurophil granule membrane / Golgi organization / Ion transport by P-type ATPases / specific granule membrane / monoatomic ion transmembrane transport / regulation of chloride transport / sensory perception of sound /  ゴルジ体 / positive regulation of neuron projection development / late endosome membrane / early endosome membrane / ゴルジ体 / positive regulation of neuron projection development / late endosome membrane / early endosome membrane /  nuclear body / apical plasma membrane / negative regulation of DNA-templated transcription / Neutrophil degranulation / structural molecule activity / nuclear body / apical plasma membrane / negative regulation of DNA-templated transcription / Neutrophil degranulation / structural molecule activity /  ゴルジ体 / magnesium ion binding / ゴルジ体 / magnesium ion binding /  小胞体 / 小胞体 /  ATP hydrolysis activity / ATP hydrolysis activity /  核質 / 核質 /  ATP binding / ATP binding /  生体膜 / 生体膜 /  細胞膜 / 細胞膜 /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||||||||||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||||||||||||||||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.56 Å クライオ電子顕微鏡法 / 解像度: 2.56 Å | |||||||||||||||||||||||||||
 データ登録者 データ登録者 | Dieudonne, T. / Kummerer, F. / Juknaviciute Laursen, M. / Stock, C. / Kock Flygaard, R. / Khalid, S. / Lenoir, G. / Lyons, J.A. / Lindorff-Larsen, K. / Nissen, P. | |||||||||||||||||||||||||||
| 資金援助 | European Union,  デンマーク, デンマーク,  フランス, フランス,  英国, 8件 英国, 8件
| |||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: Activation and substrate specificity of the human P4-ATPase ATP8B1. 著者: Thibaud Dieudonné / Felix Kümmerer / Michelle Juknaviciute Laursen / Charlott Stock / Rasmus Kock Flygaard / Syma Khalid / Guillaume Lenoir / Joseph A Lyons / Kresten Lindorff-Larsen / Poul Nissen /    要旨: Asymmetric distribution of phospholipids in eukaryotic membranes is essential for cell integrity, signaling pathways, and vesicular trafficking. P4-ATPases, also known as flippases, participate in ...Asymmetric distribution of phospholipids in eukaryotic membranes is essential for cell integrity, signaling pathways, and vesicular trafficking. P4-ATPases, also known as flippases, participate in creating and maintaining this asymmetry through active transport of phospholipids from the exoplasmic to the cytosolic leaflet. Here, we present a total of nine cryo-electron microscopy structures of the human flippase ATP8B1-CDC50A complex at 2.4 to 3.1 Å overall resolution, along with functional and computational studies, addressing the autophosphorylation steps from ATP, substrate recognition and occlusion, as well as a phosphoinositide binding site. We find that the P4-ATPase transport site is occupied by water upon phosphorylation from ATP. Additionally, we identify two different autoinhibited states, a closed and an outward-open conformation. Furthermore, we identify and characterize the PI(3,4,5)P binding site of ATP8B1 in an electropositive pocket between transmembrane segments 5, 7, 8, and 10. Our study also highlights the structural basis of a broad lipid specificity of ATP8B1 and adds phosphatidylinositol as a transport substrate for ATP8B1. We report a critical role of the sn-2 ester bond of glycerophospholipids in substrate recognition by ATP8B1 through conserved S403. These findings provide fundamental insights into ATP8B1 catalytic cycle and regulation, and substrate recognition in P4-ATPases. | |||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8ox7.cif.gz 8ox7.cif.gz | 277.9 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8ox7.ent.gz pdb8ox7.ent.gz | 216.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8ox7.json.gz 8ox7.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ox/8ox7 https://data.pdbj.org/pub/pdb/validation_reports/ox/8ox7 ftp://data.pdbj.org/pub/pdb/validation_reports/ox/8ox7 ftp://data.pdbj.org/pub/pdb/validation_reports/ox/8ox7 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  17259MC  8ox4C  8ox5C  8ox6C  8ox8C  8ox9C  8oxaC  8oxbC  8oxcC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 2種, 2分子 BA
| #1: タンパク質 | 分子量: 41085.984 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: TMEM30A, C6orf67, CDC50A / 発現宿主: Homo sapiens (ヒト) / 遺伝子: TMEM30A, C6orf67, CDC50A / 発現宿主:   Saccharomyces cerevisiae (パン酵母) / 参照: UniProt: Q9NV96 Saccharomyces cerevisiae (パン酵母) / 参照: UniProt: Q9NV96 |
|---|---|
| #2: タンパク質 |  / ATPase class I type 8B member 1 / Familial intrahepatic cholestasis type 1 / P4-ATPase flippase ...ATPase class I type 8B member 1 / Familial intrahepatic cholestasis type 1 / P4-ATPase flippase complex alpha subunit ATP8B1 / ATPase class I type 8B member 1 / Familial intrahepatic cholestasis type 1 / P4-ATPase flippase ...ATPase class I type 8B member 1 / Familial intrahepatic cholestasis type 1 / P4-ATPase flippase complex alpha subunit ATP8B1分子量: 143976.781 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: ATP8B1, ATPIC, FIC1, PFIC / 発現宿主: Homo sapiens (ヒト) / 遺伝子: ATP8B1, ATPIC, FIC1, PFIC / 発現宿主:   Saccharomyces cerevisiae (パン酵母) / 参照: UniProt: O43520, P-type phospholipid transporter Saccharomyces cerevisiae (パン酵母) / 参照: UniProt: O43520, P-type phospholipid transporter |
-糖 , 2種, 3分子 
| #3: 多糖 | beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta- ...beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose オリゴ糖 / 分子量: 586.542 Da / 分子数: 1 / 由来タイプ: 組換発現 オリゴ糖 / 分子量: 586.542 Da / 分子数: 1 / 由来タイプ: 組換発現 |
|---|---|
| #4: 糖 |  N-アセチルグルコサミン N-アセチルグルコサミン |
-非ポリマー , 3種, 3分子 
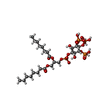



| #5: 化合物 | ChemComp-MG / |
|---|---|
| #6: 化合物 | ChemComp-IP9 / ( |
| #7: 水 | ChemComp-HOH /  水 水 |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: ATP8B1-CDC50A complex / タイプ: COMPLEX / Entity ID: #1-#2 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 値: 0.185 MDa / 実験値: NO |
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 緩衝液 | pH: 7 |
| 試料 | 濃度: 3 mg/ml / 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES詳細: 50 mM MOPS-Tris pH 7, 100 mM KCl, 1 mM DTT, 5 mM MgCl2 supplemented with 0.03 mg.mL-1 LMNG, 0.0015 mg.mL-1 PI(3,4,5)P3 and 2 mM ATP |
急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 1900 nm / 最小 デフォーカス(公称値): 700 nm / Cs Bright-field microscopy / 最大 デフォーカス(公称値): 1900 nm / 最小 デフォーカス(公称値): 700 nm / Cs : 2.7 mm : 2.7 mm |
| 撮影 | 電子線照射量: 60 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) |
| 電子光学装置 | エネルギーフィルター名称 : GIF Bioquantum / エネルギーフィルタースリット幅: 20 eV : GIF Bioquantum / エネルギーフィルタースリット幅: 20 eV |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||
3次元再構成 | 解像度: 2.56 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 573549 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: FLEXIBLE FIT / 空間: REAL | ||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 7PY4 Accession code: 7PY4 / Source name: PDB / タイプ: experimental model | ||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj