+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4205 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
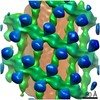
| タイトル | Subtomogram average of Rift Valley fever virus hexamer at pH 7.5 in absence of target membrane | |||||||||
 マップデータ マップデータ | Subtomogram average of Rift Valley fever virus hexamer without a target membrane at pH 7.5 | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |    Rift Valley fever virus (リフトバレー熱ウイルス) Rift Valley fever virus (リフトバレー熱ウイルス) | |||||||||
| 手法 | サブトモグラム平均法 /  クライオ電子顕微鏡法 / 解像度: 14.0 Å クライオ電子顕微鏡法 / 解像度: 14.0 Å | |||||||||
 データ登録者 データ登録者 | Sai L / Huiskonen JT | |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2018 ジャーナル: Nat Commun / 年: 2018タイトル: Shielding and activation of a viral membrane fusion protein. 著者: Steinar Halldorsson / Sai Li / Mengqiu Li / Karl Harlos / Thomas A Bowden / Juha T Huiskonen /   要旨: Entry of enveloped viruses relies on insertion of hydrophobic residues of the viral fusion protein into the host cell membrane. However, the intermediate conformations during fusion remain unknown. ...Entry of enveloped viruses relies on insertion of hydrophobic residues of the viral fusion protein into the host cell membrane. However, the intermediate conformations during fusion remain unknown. Here, we address the fusion mechanism of Rift Valley fever virus. We determine the crystal structure of the Gn glycoprotein and fit it with the Gc fusion protein into cryo-electron microscopy reconstructions of the virion. Our analysis reveals how the Gn shields the hydrophobic fusion loops of the Gc, preventing premature fusion. Electron cryotomography of virions interacting with membranes under acidic conditions reveals how the fusogenic Gc is activated upon removal of the Gn shield. Repositioning of the Gn allows extension of Gc and insertion of fusion loops in the outer leaflet of the target membrane. These data show early structural transitions that enveloped viruses undergo during host cell entry and indicate that analogous shielding mechanisms are utilized across diverse virus families. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4205.map.gz emd_4205.map.gz | 7.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4205-v30.xml emd-4205-v30.xml emd-4205.xml emd-4205.xml | 9.9 KB 9.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_4205.png emd_4205.png | 42.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4205 http://ftp.pdbj.org/pub/emdb/structures/EMD-4205 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4205 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4205 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4197C  4198C  4199C  4200C  4201C  4202C  4203C  4204C  4206C  4207C  4208C  4209C  4210C  4211C  6f8pC  6f9bC  6f9cC  6f9dC  6f9eC  6f9fC C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4205.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4205.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Subtomogram average of Rift Valley fever virus hexamer without a target membrane at pH 7.5 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.7 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Rift Valley fever virus
| 全体 | 名称:    Rift Valley fever virus (リフトバレー熱ウイルス) Rift Valley fever virus (リフトバレー熱ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Rift Valley fever virus
| 超分子 | 名称: Rift Valley fever virus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 / 詳細: Cultured in Vero cells / NCBI-ID: 11588 / 生物種: Rift Valley fever virus / ウイルスタイプ: VIRION / ウイルス・単離状態: OTHER / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| ウイルス殻 | Shell ID: 1 / 名称: Glycoprotein shell / 直径: 1100.0 Å / T番号(三角分割数): 12 |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 / 詳細: PBS |
|---|---|
| 凍結 | 凍結剤: ETHANE-PROPANE |
| 詳細 | Unfixed sample with added liposomes |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F30 |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS エネルギーフィルター - エネルギー下限: 0 eV エネルギーフィルター - エネルギー上限: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - 画像ごとのフレーム数: 1-8 / 平均露光時間: 3.2 sec. / 平均電子線量: 150.0 e/Å2 |
| 実験機器 |  モデル: Tecnai F30 / 画像提供: FEI Company |
- 画像解析
画像解析
| 抽出 | トモグラム数: 17 / 使用した粒子像数: 9502 | ||||||
|---|---|---|---|---|---|---|---|
| CTF補正 | ソフトウェア:
| ||||||
| 最終 角度割当 | タイプ: NOT APPLICABLE / ソフトウェア - 名称: Dynamo | ||||||
| 最終 再構成 | 想定した対称性 - 点群: C6 (6回回転対称 ) / 解像度のタイプ: BY AUTHOR / 解像度: 14.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: Dynamo / 使用したサブトモグラム数: 9502 ) / 解像度のタイプ: BY AUTHOR / 解像度: 14.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: Dynamo / 使用したサブトモグラム数: 9502 |
 ムービー
ムービー コントローラー
コントローラー